Практикум 8. Сигналы и мотивы часть 3
PSI-blast
Для последовательности с ID=P0AD49 проведены итерации PSI-Blast с порогом E-value 0.005. Это Рибосома-ассоциированный ингибитор А (Ribosome-associated inhibitor A) из Кишечной палочки (Escherichia coli (strain K12)).
Во время стационарной фазы (когда размер бактериальной популяции остается неизменным - количество умерших клеток равно количеству появившихся) предотвращает формирование димера 70S (что инактивирует рибосому - трансляция не начинается). Вероятно, это нужно для регуляции эффективности трансляции при перехое от экспоненциальной фазы роста популяции к стационарной.
Эндонуклеазы рестрикции
В данном практикуме нужно было попробовать предсказать специфичность некоторых из эндонуклеаз рестрикции.
В начале из базы данных NCBI genomes был скачан геном Chromobacterium violaceum ATCC 12472. Из директории
/P/y18/term4/pr8/TypeII_REs.tsvбыл скопирован файл с отобранными из рестриктазной базы данных рестриктазами.
Из этого файла конвеером
cut -f 5 TypeII_REs.tsv | sort -u | grep -Ev "Recognition" > sites.txtбыл получен файл sites.txt, содержащий сайты рестрикции разных рестриктаз. Внутри файла были два странных сайта C и -. Их было решено удалить, так как рестриктаза по сайту - видимо просто является неспецифичной эндонуклеазой, а по C фатально порежет любой геном. Осталось 207 сайтов. По этим сайтам и был осуществлено измерение представленности в геноме. Для этого использовалась программа CBcalc.
cbcalc -s sites.txt --burge -o out.tsv ChromViol.fasta
Из полученного файла выбираем сайты с O/E ratio < 0,8. Таких оказалось 8 штук:
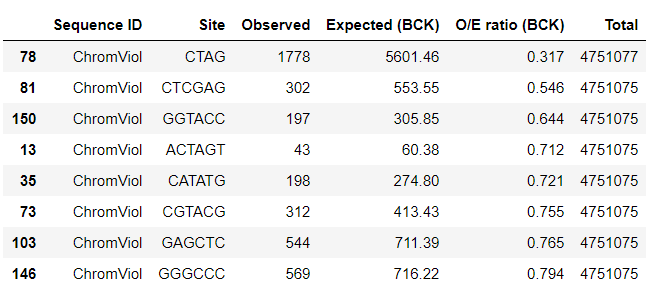
AbrI, Acc65I, ApaI, BfaIA, BfaIB, BstVI, BsuMIA, BsuMIB, BsuMIC, CchI, KpnI, MjaI, MthZI, PaeR7I, R1.BsuMI, R2.BsuMI, R3.BsuMI, SacI, Sgr13350I, SpeI, TliI, XhoIОбработка вывода программы и поиск рестриктаз были проведены при помощи библиотеки pandas. Посмотреть скрипты.
