Мини-обзор бактерии Clostridioides difficile 630
Гаврилова Яна Анатольевна
Московский государственный университет имени М.В.Ломоносова, факультет биоинженерии и
биоинформатики
1 ВВЕДЕНИЕ
1 ВВЕДЕНИЕ
Clostridioides difficile 630 — это грамположительная бактерия, вызывающая поражения кишечника человека, проявляющиеся в виде антибиотикоассоциированной диареи и колита[1].
Патогенность микроорганизма определяется способностью вырабатывать токсины TсdA и TсdB[2]. Тяжесть заболевания и возможность развития осложнений связывают с дополнительными факторами:
адгезивными функциями;
спорообразованием;
формированием биоплёнок;
модификацией клеточной стенки;
транскрипцией[2].
Важную роль в патогенезе играют белки системы quorum-sensing, регулирующие уровень продукции токсинов, а также гены резистентности к антибиотикам[2].
| Superkingdom | Bacteria |
| Phylum | Bacillota |
| Class | Clostridia |
| Order | Peptostreptococcales |
| Family | Peptostreptococcaceae |
| Genus | Clostridioides |
| Species | Clostridioides difficile |
2 МЕТОДЫ
Данные по геному исследуемой бактерии были взяты с сайта Национального Центра Биотехнологической информации (NCBI).
Для анализа данных использовались электронные таблицы Google Sheets (методы СЧЁТЕСЛИ, COUNTA, создания фильтров для столбцов, построения столбчатых диаграмм).
3 РЕЗУЛЬТАТЫ
3.1 Длины белков, закодированных в геноме бактерии Clostridioides dif icile 630
Результат анализа длин белков, встречающихся в бактерии Clostridioides difficile 630 можно представить в виде гистограммы:
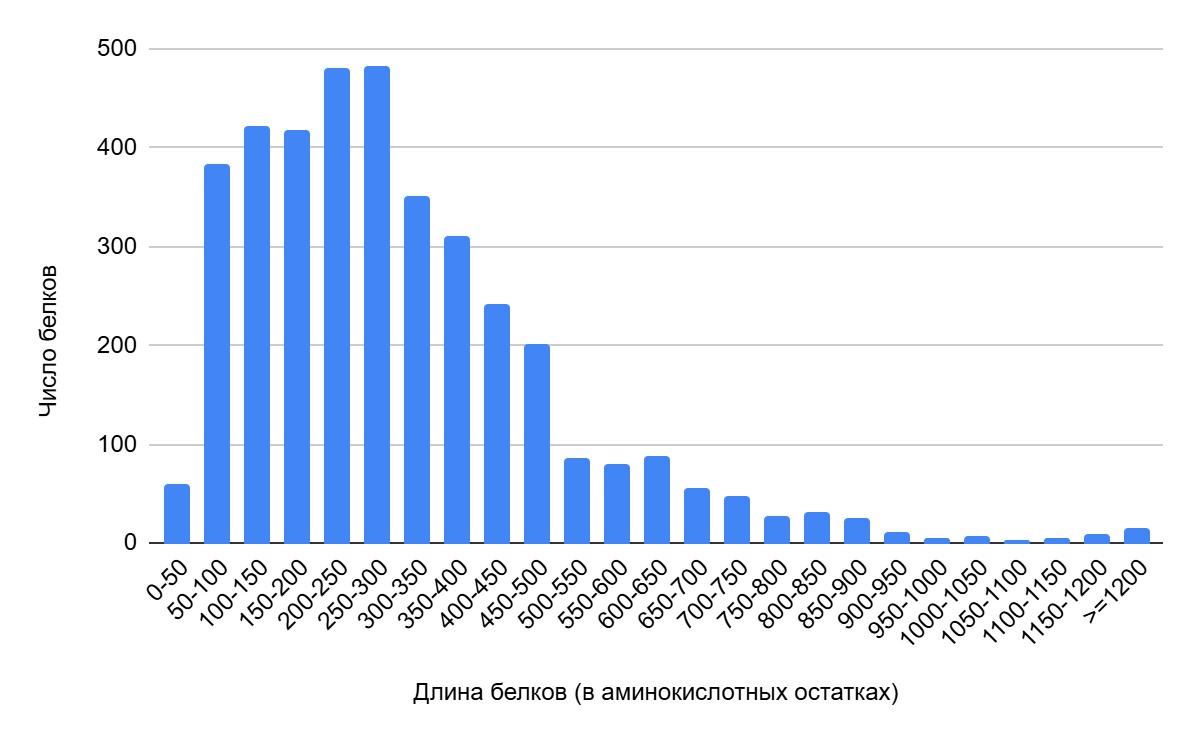
Как видно из Рисунка 1, наиболее распространённая длина белка находится в диапазоне от 150 до 350 аминокислотных остатков (а.о.), с выраженным пиком в районе 200–300 а.о.
Преобладание белков средней длины характерно для бактерий[4].
3.2 Встречаемость альтернативных стоп-кодонов в кодирующих последовательностях
Кодирующие белки последовательности у бактерий преимущественно используют в качестве старт-кодона ATG, что при трансляции приводит к включению формил-метионина в участок синтезируемого полипептида. Тем не менее, анализ геномных данных показывает, что на долю рамок считывания, начинающихся с ATG, приходится в среднем лишь около 80,1% от общего числа таких последовательностей. Оставшаяся часть распределяется между альтернативными инициирующими кодонами: GTG инициирует примерно 11,6% открытых рамок, а TTG — 7,8%. Интересно, что это соотношение демонстрирует высокую степень сохранности среди различных групп бактерий [5].
При анализе белок-кодирующих последовательностей было выявлено, что стандартный старт-кодон ATG используется в 85,4% случаев. На долю альтернативных кодонов GTG приходится 5,96%, а TTG — 7,44% от общего числа. Кроме того, в единичных случаях были зарегистрированы и другие стартовые кодоны (подробнее см. Таблицу 2).
| Старт-кодон | Количество CDS | Процент |
|---|---|---|
| ATG | 3294 | 85,40% |
| TTG | 287 | 7,44% |
| GTG | 230 | 5,96% |
| ATA | 12 | 0,31% |
| ATT | 8 | 0,21% |
| CAT | 3 | 0,08% |
| CTG | 3 | 0,08% |
| ACA | 2 | 0,05% |
| ATC | 2 | 0,05% |
| CTT | 2 | 0,05% |
| AAA | 1 | 0,03% |
| AAC | 1 | 0,03% |
| AAG | 1 | 0,03% |
| AGA | 1 | 0,03% |
| CAA | 1 | 0,03% |
| CCC | 1 | 0,03% |
| CTA | 1 | 0,03% |
| GAA | 1 | 0,03% |
| GAC | 1 | 0,03% |
| GTC | 1 | 0,03% |
| GTT | 1 | 0,03% |
| TCA | 1 | 0,03% |
| TCT | 1 | 0,03% |
| TTT | 1 | 0,03% |
| Сумма | 3857 | 100,00% |
| Сумма без ATG | 563 | 14,60% |
Геном Clostridioides difficile 630 представлен псевдогенами и нормальными генами.
Псевдогены — это нефункциональные сегменты ДНК, которые напоминают функциональные гены[6].
В ходе исследования были посчитаны встречаемости альтернативных стоп-кодонов по отдельности в псевдогенах и в нормальных генах (см. таблицу (1) Сопроводительных материалов).
Было выявлено, что в псевдогенах стандартный старт-кодон ATG используется в 43,4% случаев. На долю альтернативных кодонов GTG и CAT приходится 5,88% от общего числа. TTG в качестве старт-кодона не выступал, а на остальные альтернативные старт-кодоны приходится 0-3,92%.
В нормальных генах стандартный старт-кодон ATG используется в 85,97% случаев. На долю альтернативных кодонов GTG приходится 5,96%, а TTG — 7,54% от общего числа. Другие стартовые кодоны были зарегистрированы в единичных случаях.
Таким образом, представленность альтернативных инициирующих кодонов оказалась меньше ожидаемой, в псевдогенах же она отличается ещё больше.
3.3 Длины известных белков
Была поставлена задача проанализировать, как кодирующие белки последовательности с известным названием распределяются по различным диапазонам длины белка
В Таблице 3 подтверждаются результаты, полученным в п. 3.1: белков “средней длины” в геноме бактерии больше всего.
Стоит заметить, что не все кодирующие последовательности, имеющие схожие названия, относятся к одной категории длины (см. таблицу (2) Сопроводительных материалов). Так, например, кодирующую область dnaK условно можно отнести к “очень длинным”, dnaG - к “длинным”, а dnaN - к “средним”. Это может говорить о том, что общие названия кодирующим областям даются не на основе их длины.
Сопроводительные материалы
- (1) - Ссылка на таблицу Start codons в Google Sheets
- (2) - Ссылка на таблицу Feature_table в Google Sheets
- (3) - Ссылка на таблицу СDS from genome of Clostridioides difficile 630 в Google Sheets
Список литературы
- [1] Sorokina, J. V., & Belyi, Y. F. (2023). Type IV secretion system in Clostridioides difficile: Structural features and its role as a pathogenicity factor. Journal of Microbiology, Epidemiology and Immunobiology, (4), 345–353.
- [2] Burke, K. E., & Lamont, J. T. (2014). Clostridium difficile infection: A worldwide disease. Gut and Liver, *8*(1), 1–6.
- [3] Taxonomy Browser [NCBI]: Clostridioides difficile 630 Taxonomy. (2020). In Schoch, C. L., et al. (Eds.), NCBI Taxonomy Database. National Center for Biotechnology Information.
- [4] Brocchieri, L., & Karlin, S. (2005). Protein length in eukaryotic and prokaryotic proteomes. Nucleic Acids Research, *33*(10), 3390–3400.
- [5] Villegas, A., & Kropinski, A. M. (2008). An analysis of initiation codon utilization in the Domain Bacteria – concerns about the quality of bacterial genome annotation. Microbiology, *154*(9), 2559–2561.
- [6] Gerstein, M., & Zheng, D. (2006). The real life of pseudogenes. Scientific American, *295*(2), 48–55.