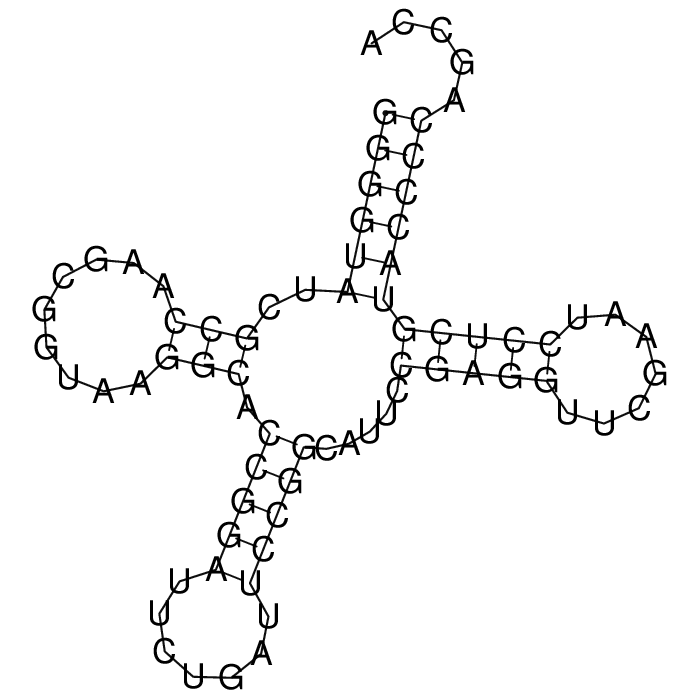
Предсказать пространственную структуру РНК используя различные алгоритмы. Последовательность взята из объекта 1GTS.

| Участок структуры | Реальная структура(find_pair) | Предсказанная структура(einverted) | Предсказанная алгоритмом Зукера |
|---|---|---|---|
| Акцепторный стебель | [2-7;66-71] | [2-7;66-71] | [2-7;66-71 |
| D-стебель | [10-12;23-25] | [9-10;63-64] | [10-12;23-25] |
| Антикодонныйстебель | [26-33;37-44] | - | [27-31;39-43] |
| Т-стебель | [49-53;61-65] | - | [49-53;61-65] |
| Число пар нуклеотидов | 22 | 8 | 19 |
Был проведён анализ объекта 1pp8
Было написано два сценария:
Данные в таблице получены при помощи сценария в pymol: script
| Контакты атомов белка с | Полярные | Неполярные | Всего |
|---|---|---|---|
| остатками 2'-дезоксирибозы | 9 | 53 | 62 |
| остатками фосфорной кислоты | 38 | 45 | 83 |
| остатками азотистых оснований со стороны большой бороздки | 5 | 20 | 25 |
| остатками азотистых оснований со стороны малой бороздки | 6 | 7 | 13 |
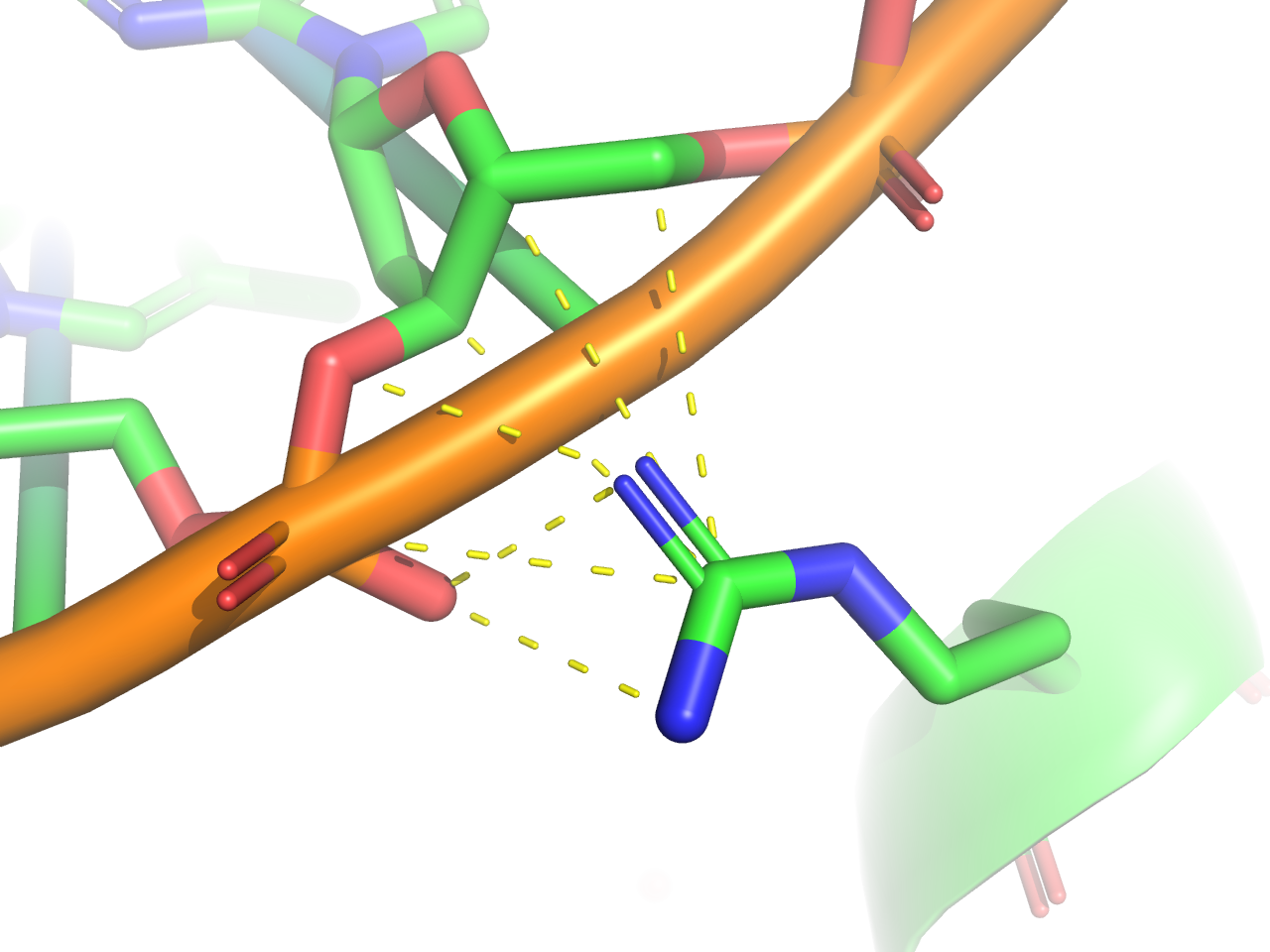
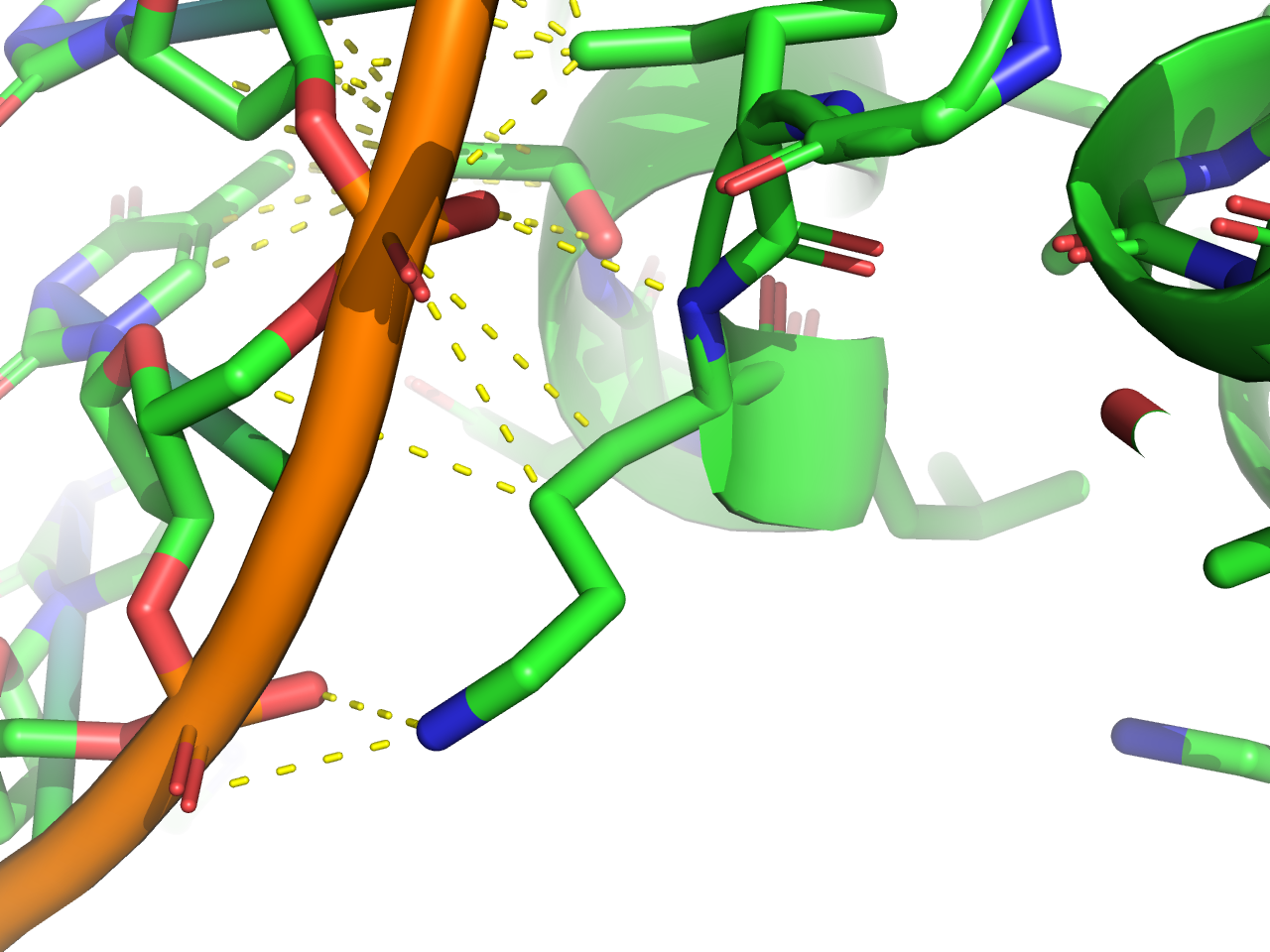
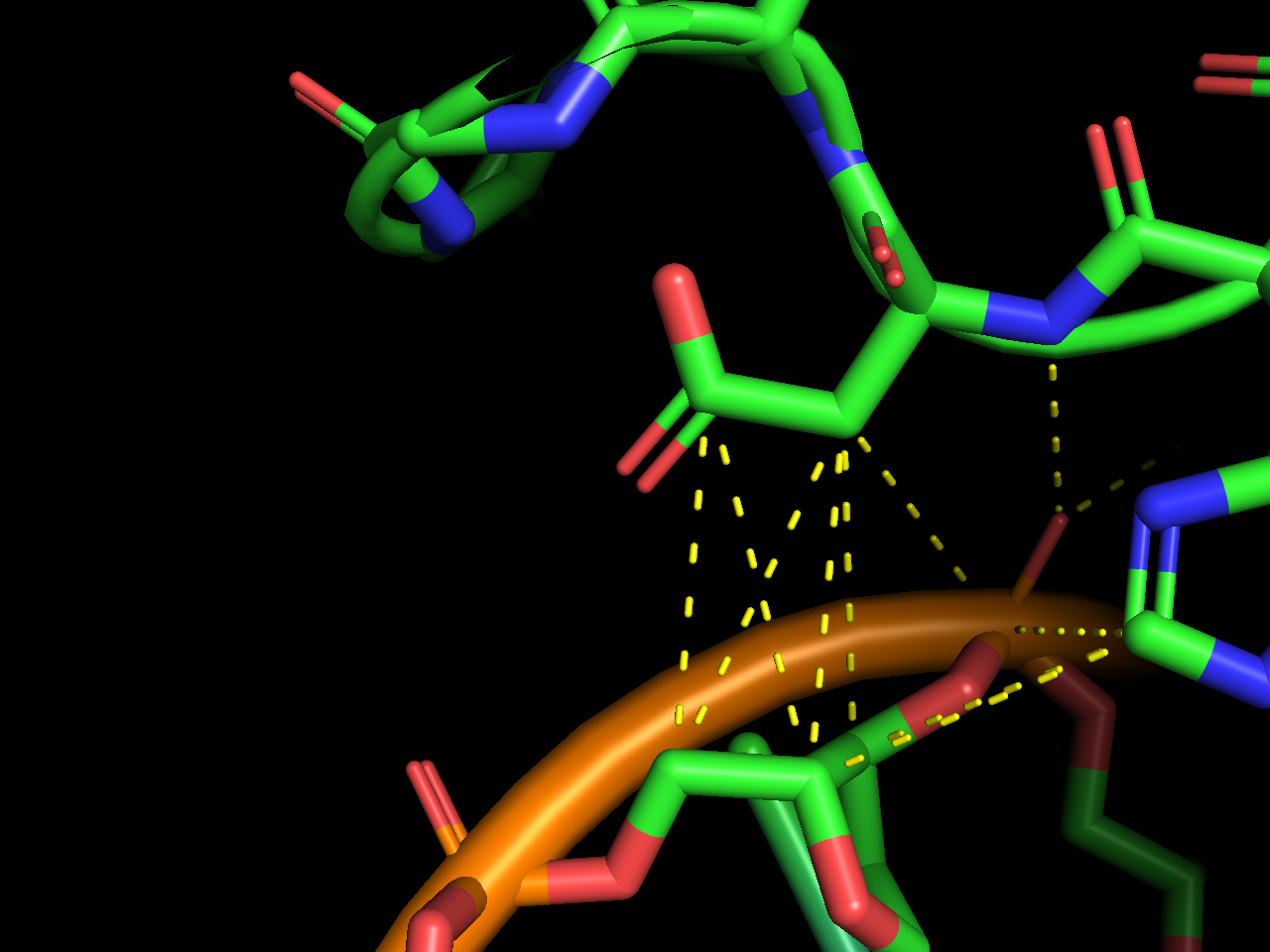
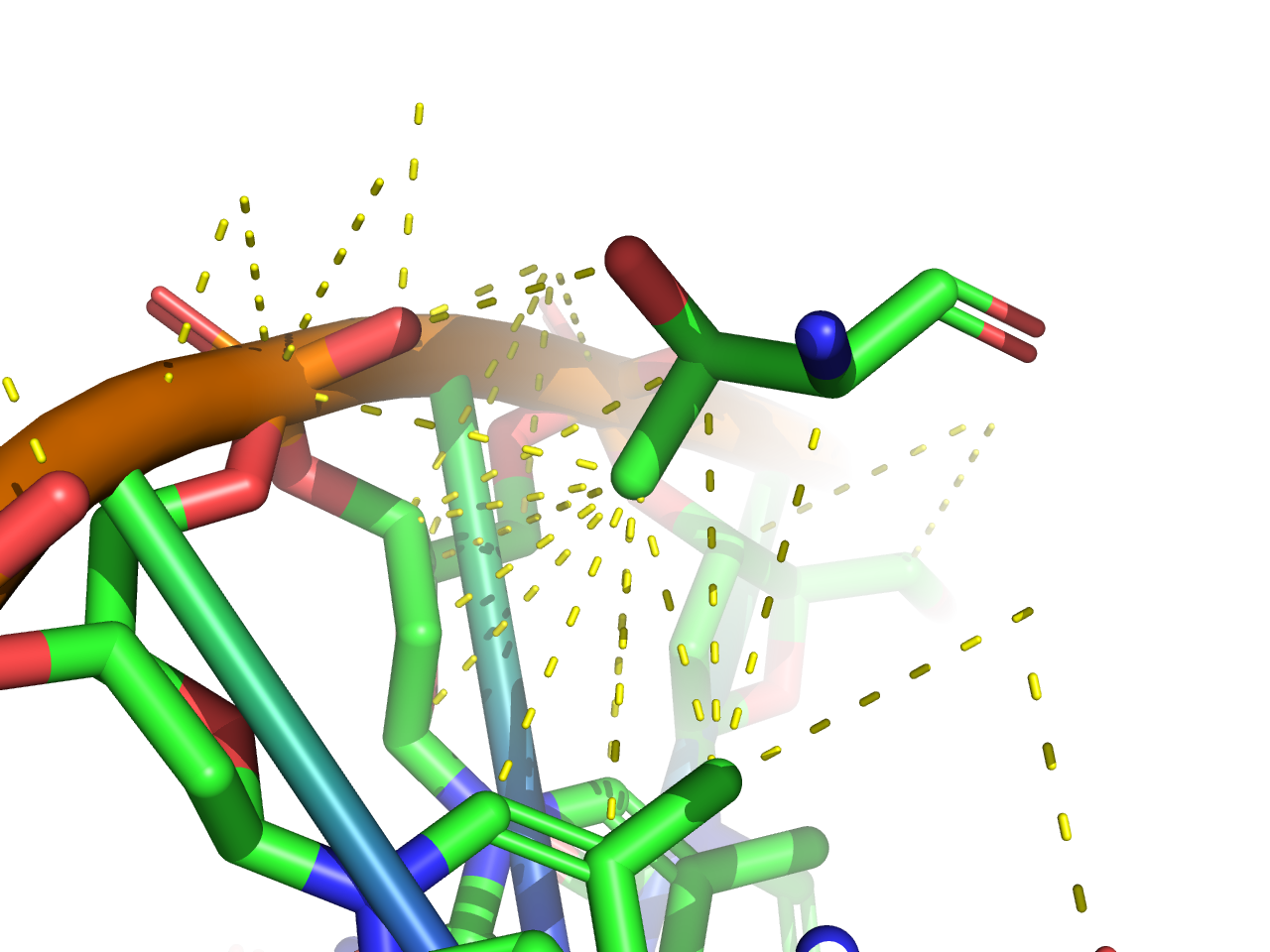
Требуется получить популярную схему ДНК-белковых контактов при помощи nucplot. Так как мой объект 1pp8 состоит из нескольких сборок, nucplot не смог создатьать ps-файл command output error. Поэтому для анализа я взял Assembly1 из соответствующей 1pp8 записи PDB.
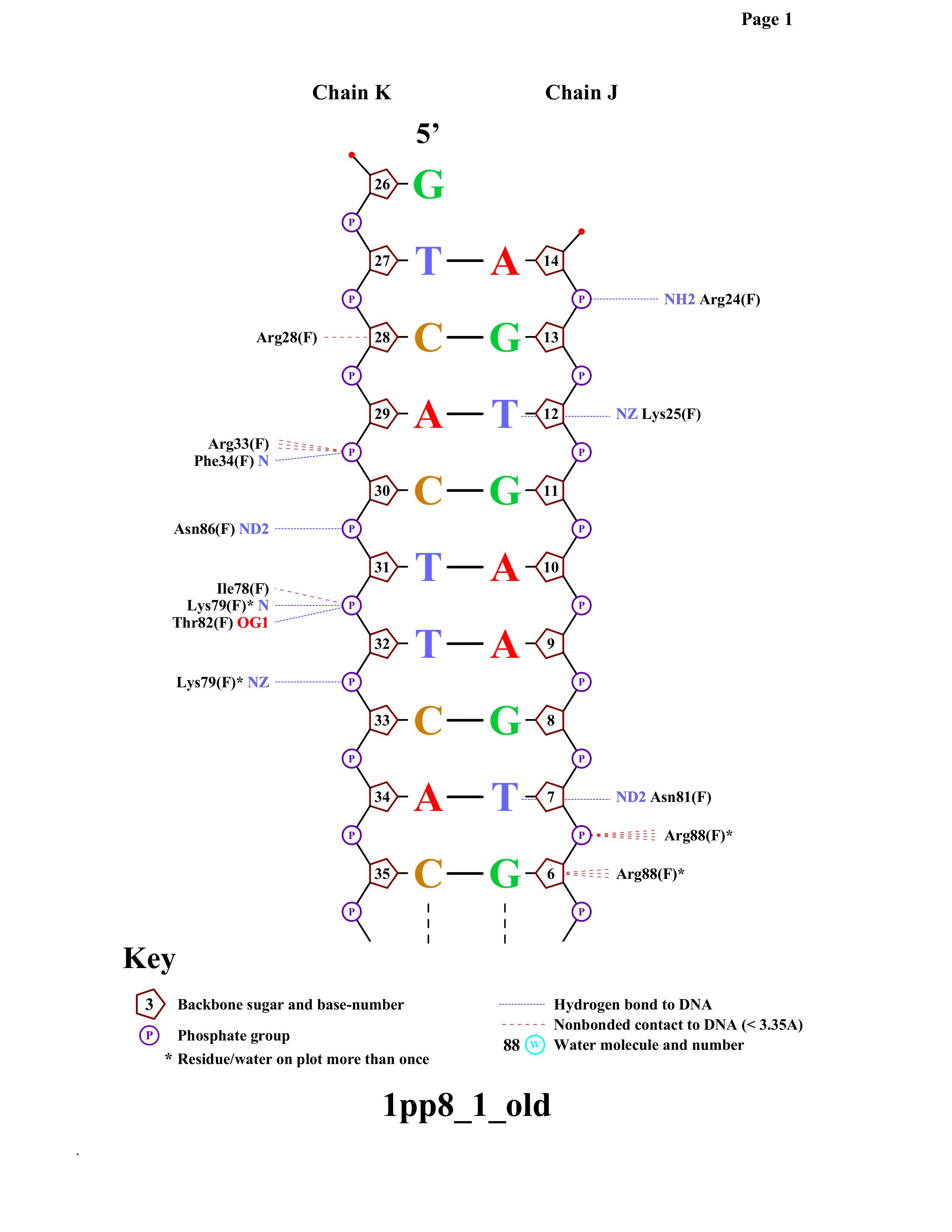
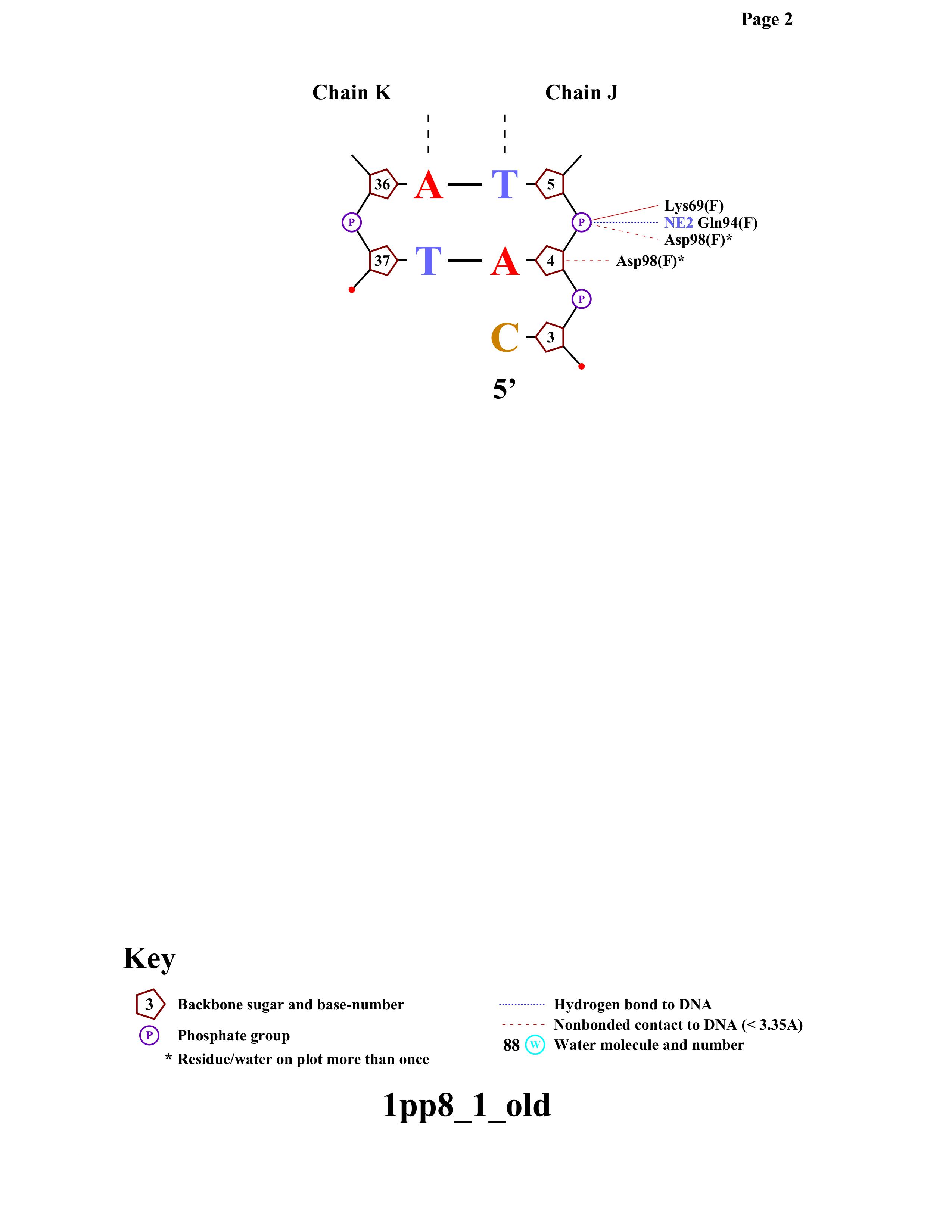
Как видно из схемы, наибольшей по числу контактов является Arg88. Второе место занимают Lys79 и Asp98.
Рассмотрим их контакты подробнее.