Мотивы в белках. PSSM и паттерны. PSI-BLAST. Банк Prosite
1. PSI-BLAST
Для работы был выбран AC P74518, который соответствует белку
Ribosome hibernation promotion factor.
Он во время стационарной фазы стимулирует и стабилизирует димеризацию рибосом 70S
с помощью фактора модуляции рибосом (RMF),
что приводит к образованию инактивированных рибосом 100S.
Далее был проведен поиск с помощью Protein BLAST (PSI-BLAST (Position-Specific Iterative Basic
Local Alignment Search Tool) в банке Swiss-Prot.
Результаты итераций приведены в Таблице 1.
Таблица 1. Итерации
| Номер итерации | Число находок выше порога (0,005) |
Идентификатор худшей находки выше порога | E-value этой находки |
Идентификатор лучшей находки ниже порога | E-value этой находки |
| 1 | 24 |
P33987.1 | 3e-05 |
P74518.1 | 5e-141 |
| 2 | 28 |
P9WMA8.1 | 3e-06 |
P74518.1 | 1e-85 |
| 3 | 28 |
P24694.1 | 2e-20 |
P74518.1 | 1e-80 |
В результате поиска уже четвертая итерация не показала изменения результатов,
при этом разрыв E-value между худшей находкой над порогом и лучшей под порогом достаточно большой.
Так что можно сделать вывод, что находки составляют семейство гомологичных белков.
2. Prosite
В банке Prosite был найден мотив PS01127
для поиска паттернов в семействе белков EFTS.
Мы получили два паттерна:
1. EF_TS_2, PS01127; Elongation factor Ts signature 2:
[ELAS]-[LIVMF]-[NVCKGST]-[SCVA]-[QE]-T-D-[FS]-[VLA]-[SAT]- [KRNLAQS]
2. EF_TS_1, PS01126; Elongation factor Ts signature 1:
L-R-x(2)-[ST]-[GSDNQ]-x-[GSA]-[LIVMF]-x(0,1)-[DENKAC]-x-K- [KRNEQS]-[AV]-L
Далее выравнивания были открыты в Jalview и было найдено место, которому соответствует паттерн 1.
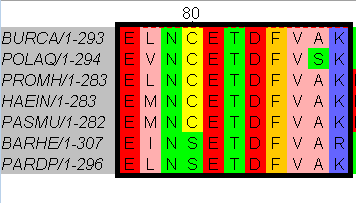
Затем паттерн был сделан более строгим: E-[LIVM]-N-[SC]-E-T-D-F-V-[SA]-[KR]
По более строгому паттерну в Prosite был найден список белков, содержащих данный паттерн:
Matchlist.txt.
Далее на сайте Uniprot были найдены белки протеобактерий из семейства EFTS:
true.list.
С помощью Excel мы сравнили данные списки (Таблица 2).
Таблица 2. Результаты поиска
| True positives | 253 |
| False positives | 228 |
| False negatives | 163 |
Вернуться на главную страницу
© Наумова Юлия, 2019
