Скачаем с ebi.ac.uk короткие чтения,
полученные по технологии Illumina из бактерии Buchnera aphidicola и разархивируем (gunzip -d SRR4240358.fastq.gz).
Удалим возможные остатки адаптеров и чтения с длиной менее 30 и качеством менее 20.
Размер исходного файла составил 1125 МБ, где было 10543839 чтений.
После применения программы Trimmomatic размер файла уменьшился до 876 МБ, а число чтений сократилось до 8580909.
Граф состоит из 702 вершин, N50 = 15362.
Самые длинные контиги:
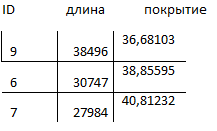
Контиги с аномально большим или аномально малым покрытием:


Таблица с информацией о контигах: pr14_vlv.xlsx
4. Анализ
Сравним при помощи megablast с параметрами по умолчанию три самых длинных контига с хромосомой Buchnera aphidicola (GenBank/EMBL AC — CP009253).
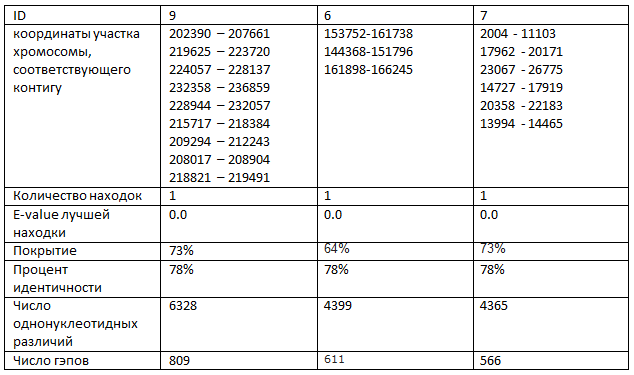
Разрывы на картах локального сходства означают не полную целостность соответствия.
Карта локального сходства для контига с ID=9
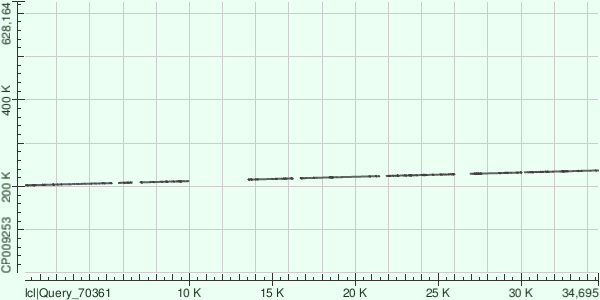
Данный контиг лёг на прямую цепь хромосомы c 8 разрывами.
Карта локального сходства для контига с ID=6
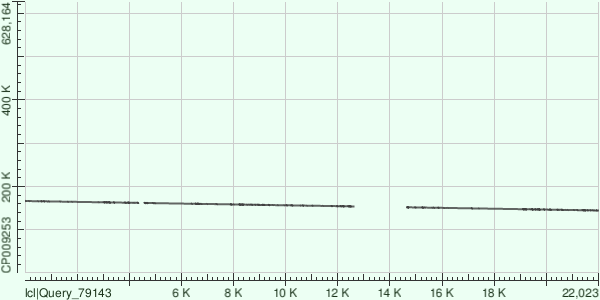
Контиг инвертирован относительно последовательности хромосомы бактерии, присутствует 2 разрыва.
Карта локального сходства для контига с ID=7
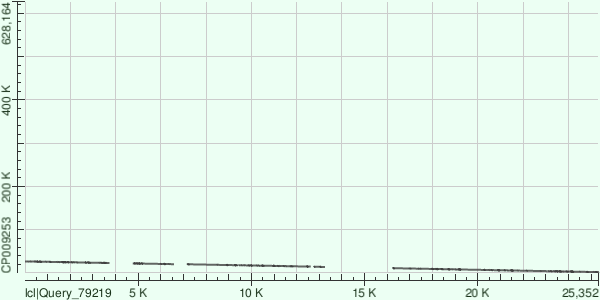
Контиг инвертирован относительно последовательности хромосомы бактерии, присутствует 5 разрывов.