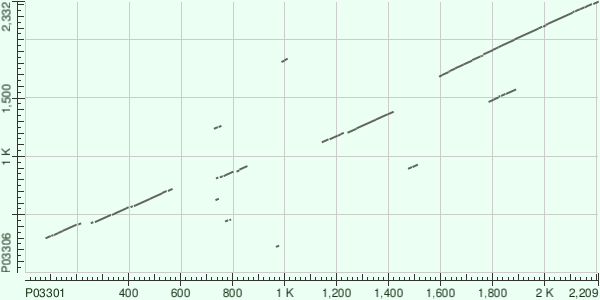
Рисунок 1. Карта локального сходства белков P03301 и P03306.
| % Identities | % Positives | Length | Gaps | Score | Score (bits) | |
| I. | 29 | 49 | P03301: 614 (27,8 %) P03306: 643 (27,6 %) | 59 (8 %) | 644 | 252 |
| II. | 37 | 51 | P03301: 276 (12,5 %) P03306: 262 (11,2 %) | 26 (9 %) | 398 | 157 |
Рисунок 1. Карта локального сходства белков P03301 и P03306.

| Номер выравнивания | Координаты участка белка | Названия зрелых белков |
| I. | P03301: 1594 - 2208 | Protein 3CD |
| I. | P03306: 1684 - 2327 | Picornain 3C (1650 - 1862) RNA-directed RNApolymerase 3D-POL (1863 - 2332) |
| II. | P03301: 1143 - 1419 | Protein 2C |
| II. | P03306: 1121 - 1383 | Protein 2C |
| ID белков | Вес, который выдает программа water | Медиана весов случайных выравниваний | Верхний квартиль | Вес в битах | p-значение |
| DACB_ECOLI и DACB_BACSU | 53.0 | 47.0 | 52.5 | 2.091 | 0.24 |
| PURK_ECOLI и FADH_BACSU | 34.5 | 39.75 | 45.25 | 0.046 | 0.97 |
В практикуме 9 характеристики оптимальных локальных выравниваний этих двух пар белков мне казались очень похожими, но p-значение показало, что эти выравнивания принципиально различаются. Конечно, DACB_ECOLI и DACB_BACSU – не самые хорошо выравнивающиеся гомологи, но 0,24 – приемлемая для гомологов величина, относительно числа 0.97.
| ID белков | Вес, который выдает программа water | Медиана весов случайных выравниваний | Верхний квартиль | Вес в битах | p-значение |
| DACB_ECOLI и DACB_BACSU | 53.0 | 33.0 | 35.0 | 11 | 4.88e-4 |
| PURK_ECOLI и FADH_BACSU | 34.5 | 31.0 | 34.0 | 2.17 | 0.22 |
Данные результаты получены при “Gap extension penalty" = 4 и с использованием матрицы аминокислотных замен EBLOSUM90. При таком изменении параметров p-значение для пар гомологичных и негомологичных белков сильно изменилось. Вероятность того, что выравнивание перемешанных последовательностей той же длины для негомологов будет иметь такой же вес и выше оказалась всего 0.22, то есть при данных параметрах совпадения в выравнивании признаются не случайными. Это кажется неправдоподобным.
| ID белков | Вес, который выдает программа water | Медиана весов случайных выравниваний | Верхний квартиль | 1/8 | Вес в битах | p-значение |
| DACB_ECOLI и DACB_BACSU | 53.0 | 45.5 | 51.5 | 55.75 | 2.71 | 0.15 |
| PURK_ECOLI и FADH_BACSU | 34.5 | 39.5 | 44.75 | 50.0 | 3 | 0.125 |
Действительно работает
| Находка | ID | AC | Organism | % Identities | % Positives | Gaps | Score | Score (bits) | Expect | Coverage |
| I. | SUBT_BACAM | P00782.1 | Bacillus amyloliquefaciens | 98 | 99 | 0 | 1930 | 748 | 0.0 | ALV04273.1: 100% P00782.1: 100% |
| II. | SUBN_BACNA | P35835.1 | Bacillus subtilis subsp. natto | 86 | 92 | 1 (0 %) | 1713 | 664 | 0.0 | ALV04273.1: 100% P35835.1: 100% |
© Belousova Evgenia, 2017