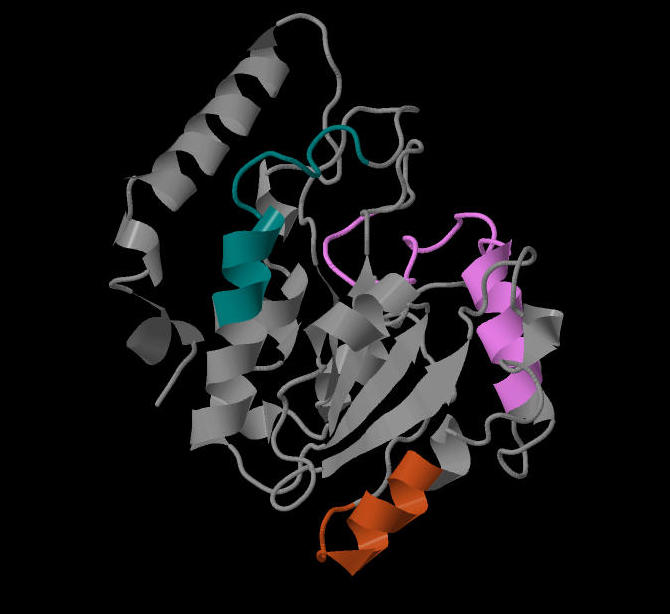
Рисунок 1. Высококонсервативные в выравнивании области белка UNG_ECOLI.
| Protein name | ID 1 | ID 2 | Score | % Identity | % Similarity | Gaps | Indels |
| D-alanyl-D-alanine carboxypeptidase DacB | DACB_ECOLI | DACB_BACSU | 26.5 | 13.1% | 23.7% | 313 | 25 |
| Isocitrate dehydrogenase [NADP] | IDH_ECOLI | IDH_BACSU | 1451.5 | 65.6% | 77.1% | 27 | 6 |
| Uracil-DNA glycosylase | UNG_ECOLI | UNG_BACSU | 606.5 | 50.9% | 66.4% | 10 | 5 |
| Protein name | ID 1 | ID 2 | Score | % Identity | % Similarity | Gaps | Indels | Coverage 1 | Coverage 2 |
| D-alanyl-D-alanine carboxypeptidase DacB | DACB_ECOLI | DACB_BACSU | 53.0 | 23.7% | 35.6% | 55 | 11 | 38.8% | 51.3% |
| Isocitrate dehydrogenase [NADP] | IDH_ECOLI | IDH_BACSU | 1453.5 | 67.0% | 78.8% | 19 | 4 | 97.8% | 99.3% |
| Uracil-DNA glycosylase | UNG_ECOLI | UNG_BACSU | 621.0 | 53.5% | 69.8% | 2 | 2 | 93.5% | 94.2% |
Глобальное выравнивание:
| Proteins' names | ID 1 | ID 2 | Score | % Identity | % Similarity | Gaps | % Gaps | Indels |
| N5-carboxyaminoimidazole ribonucleotide synthase ( E. coli), 2,4-dienoyl-CoA reductase ( B. subtilis) | PURK_ECOLI | FADH_BACSU | 28.5 | 10,5% | 17,6% | 301 | 66,2% | 17 |
Локальное выравнивание:
| Proteins' names | ID 1 | ID 2 | Score | % Identity | % Similarity | Gaps | % Gaps | Indels | 1 Coverage | 2 Coverage |
| N5-carboxyaminoimidazole ribonucleotide synthase ( E. coli), 2,4-dienoyl-CoA reductase ( B. subtilis) | PURK_ECOLI | FADH_BACSU | 34,5 | 21,5% | 38,0% | 21 | 26,6% | 4 | 17,5% | 28,7% |
|
Белки PURK_ECOLI и FADH_BACSU совершенно разные по функциям: синтаза модифицированных рибонуклеотидов (лигаза) и 2,4-диеноил редуктаза (оксидоредуктаза); и относятся к разным видам бактерий, но удивительно, что их выравнивания оказались сопоставимыми, например, с выравниваниями DACB_ECOLI и DACB_BACSU, которые казались мне в предыдущем задании гомологами. Выравнивание белков DACB_ECOLI и DACB_BACSU. Возможно, дело в том, что в DACB_BACSU произошла большая делеция, которая сильно испортила показатели выравнивания, хотя в целом видно, что у белков DACB гомологичная область больше, чем у PURK_ECOLI и FADH_BACSU. Выравнивание белков PURK_ECOLI и FADH_BACSU. Хотя, конечно, нечто подобное есть и во втором вырвнивании. Возможно, стоит обратить внимание на то, что у глобальных выравниваний обоих пар Score почти одинаковый (26,5 и 28,5), а при переходе к локальному выравниванию, у пары DACB он возрастает гораздо сильнее (53,0 против 34,5). Показатели % Identity и % Similarity у пары DACB и PURK_ECOLI и FADH_BACSU очень похожи в локальном выравнивании (23.7% и 35.6% против 21,5% и 38,0%), но это нормально, потому что процент покрытия у DACB гораздо больше (38.8% и 51.3% против 17,5% и 28,7%). |
| В Swiss-Prot нашлось 407 белков, чьи ID начинаются с UNG_. Я выбрала белки, принадлежащие Mycobacterium bovis (strain BCG / Pasteur 1173P2), Bordetella pertussis (strain Tohama I / ATCC BAA-589 / NCTC 13251), Chlamydia muridarum (strain MoPn / Nigg), Escherichia coli O9:H4 (strain HS), Yersinia pseudotuberculosis serotype I (strain IP32953), Escherichia coli, Bacillus subtilis (strain 168). В целом белки выровнялись хорошо, наблюдаемые довольно широкие консервативные полосы не могут быть случайностью, то есть данные белки гомологичны. Сильнее всего от других отличается, скорее всего, белок UNG_BORPE, потому что у него наблюдаются два "хвоста" (в начале и в конце последовательности), которых нет у остальных белков. Следующий по непохожести - UNG_MYCBP, далее - UNG_CHLMU, хотя белки UNG_CHLMU, UNG_ECOHS, UNG_YERPS, UNG_ECOLI и UNG_BACSU уже значительно сильнее похожи друг на друга. Еще более похожи белки UNG_ECOHS, UNG_YERPS, UNG_ECOLI, что понятно, потому что, например, UNG_ECOHS и UNG_ECOLI - просто штаммы одного вида. В структуре белков наблюдаются три высококонсервативные области, которые показаны на рисунке 1 (изображен белок UNG_ECOLI): 72-95 нуклеотиды (фиолетовая), 134-146 (зеленая), 205-215 (оранжевая), третья область очень нечеткая. Вероятно, данные области играют важную роль в связывании с лигандами или содержат в себе активный центр фермента. |
Рисунок 1. Высококонсервативные в выравнивании области белка UNG_ECOLI.

© Belousova Evgenia, 2017