Blast-поиск белков, гомологичных CLPX_ECOLI(АТФ-связывающий домен Clp протеазы)
BACSU

CLOTE

ENTFA

LACAC

LISMO
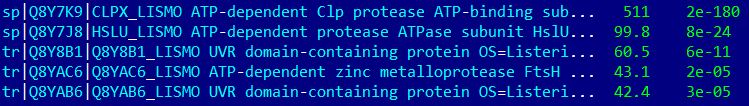
STAAR
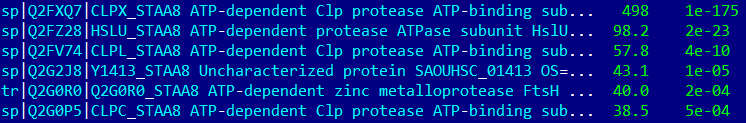
STAES
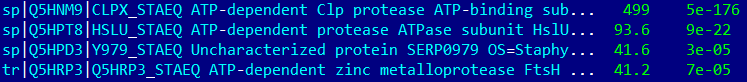
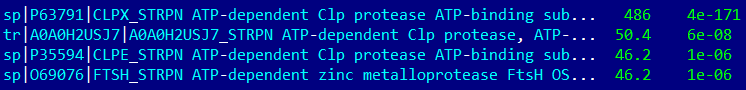
STRPN
Реконструкция филогении
Была выполнена методом Neighbour-joining с применением бутстреп-анализа.
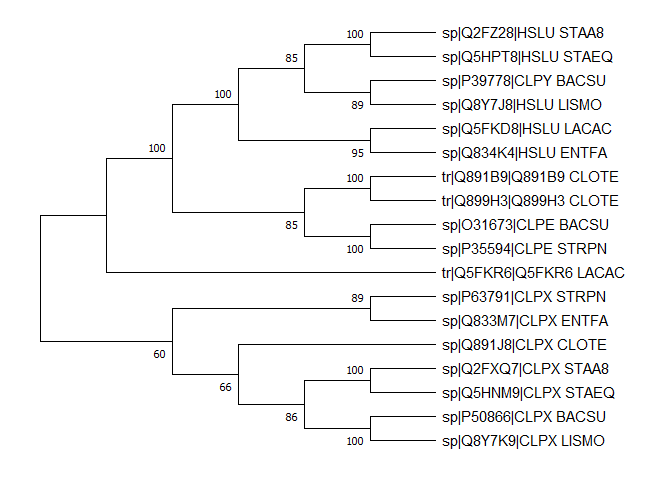
Парологи — HSLU STAA8 & CLPX STAA8, CLPE BACSU & CLPX BACSU & CLPY BACSU, CLPX LISMO & HSLU LISMO.
Ортологи — CLPX BACSU & CLPX LISMO, HSLU LACAC & HSLU ENTFA, HSLU STAA8 & HSLU STAEQ.
Группы ортологов

Два белка для CLOTE считаю паралогами и по отдельности ортологичным к группе.
Схлопнутое дерево
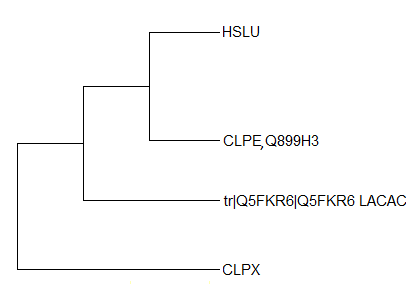
В группу CLPX вошли 7 организмов из 8 (не вошел LACAC, потому что его последовательность не аннотирована и отражается как Q5FKR6). Дерево по другим видам реконструировано верно.
В группу CLPE, Q899H3 вошли два белка-паролога из CLOTE и CLPE BACSU и CLPE STRPN. Для этих организмов дерево тоже реконструировано верно.
В группу HSLU вошли 6 организмов (кроме STRPN, CLOTE). Все белки, кроме бациллярного (несет CLPY) — HSLU. Дерево было реконструировано верно.