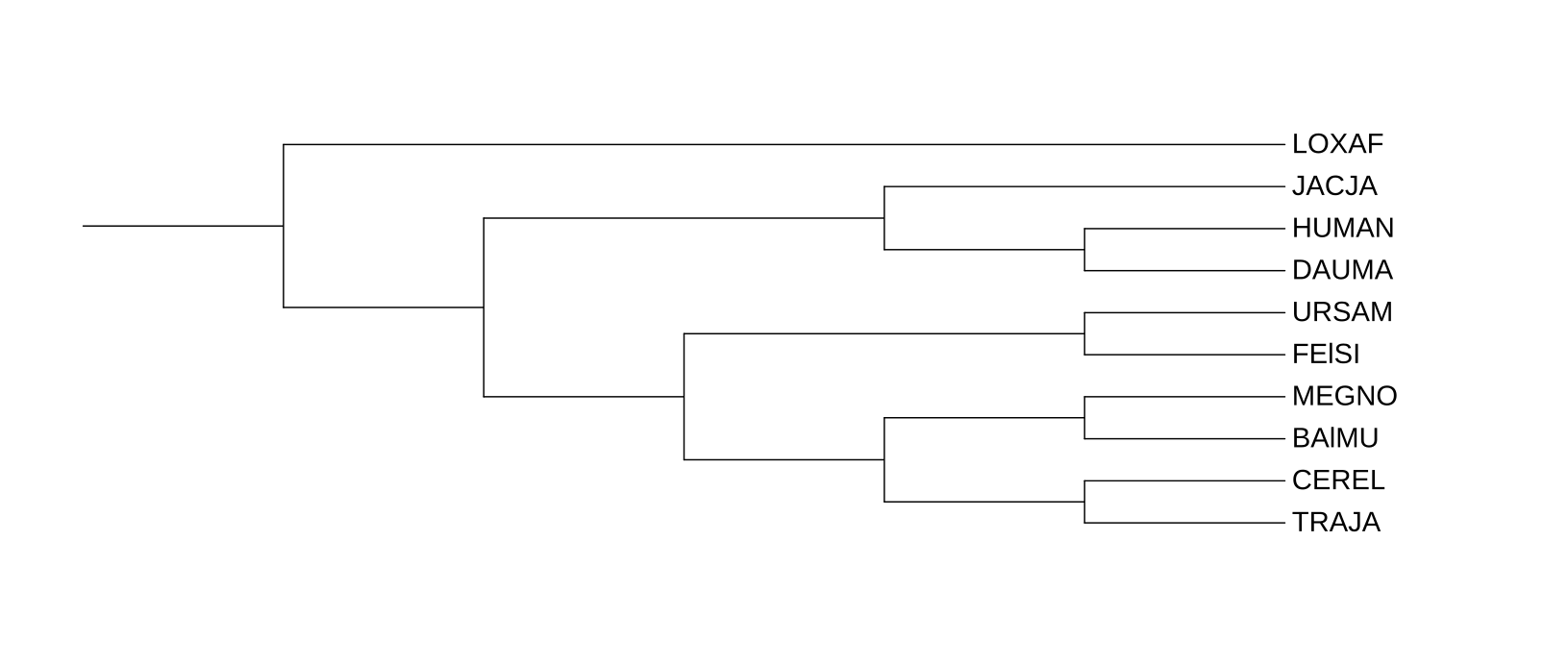
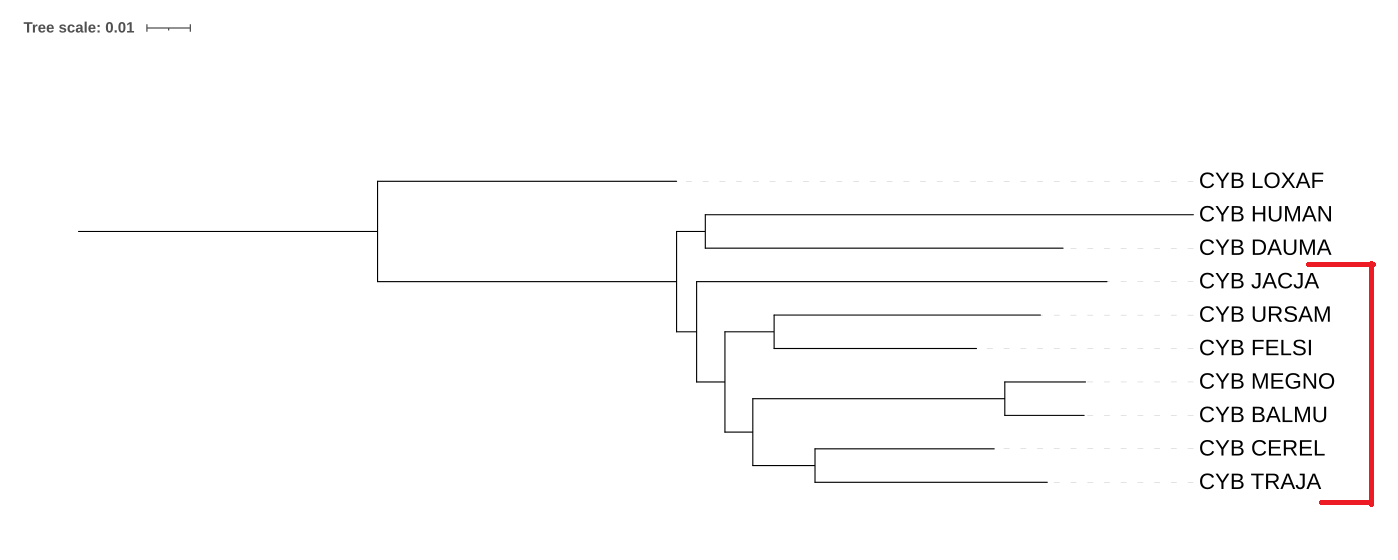
В этом практикуме были построены три филогенетических дерева на основе последовательностей цитохромов B.
Список с последовательностями белков:
seqret @cyb.list cyb.fasta
Получение выравнивания последовательностей:
muscle -align cyb.fasta -output cyb-alignment.fasta
Команда для реконструкции дерева с помощью FastMe c моделью p-distance:
fastme -i cyb.phy -o fastme_pdist_tree -pp
FastMe с моделью MtREV:
fastme -i cyb.phy -o fastme_mtrev_tree -pm
Реконструкция дерева программой IQ-Tree:
iqtree -s cyb.phy


В отличии от дерева на основе таксономии, в реконструированном дереве JACJA не образует кладу с HUMAN и DAUMA, а вместо этого имеется ошибочная клада, отмеченная красной скобкой.

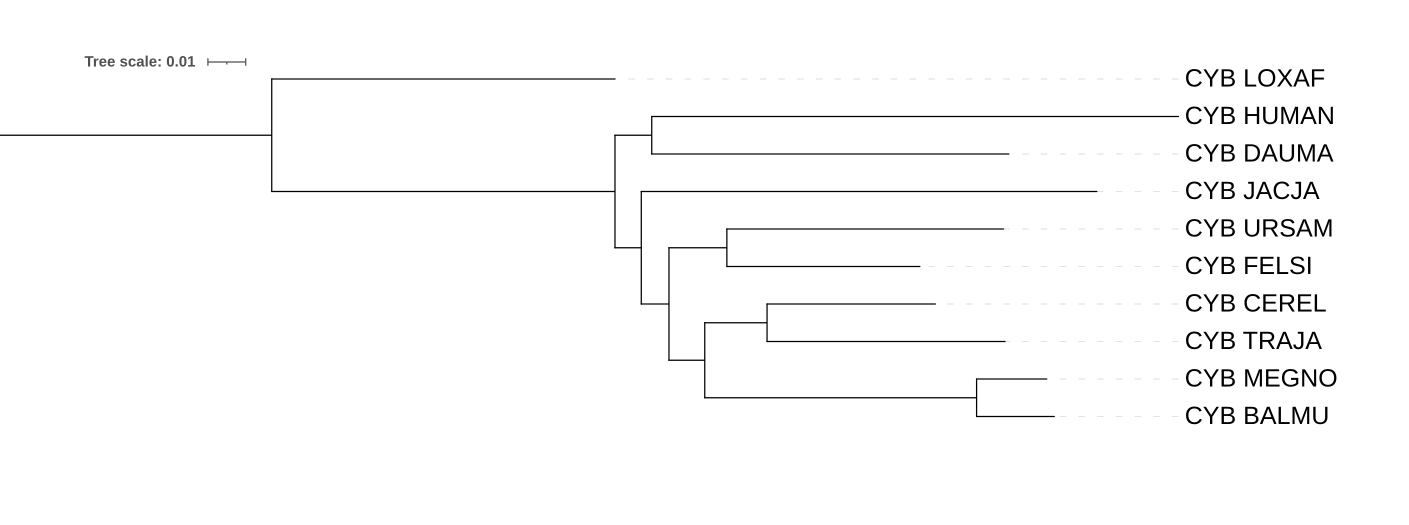
Дерево, реконструированное с помощью метода MtREV имеет такие же клады, как и при использованнии p-distance, отличие состоит в длинне ветвей.

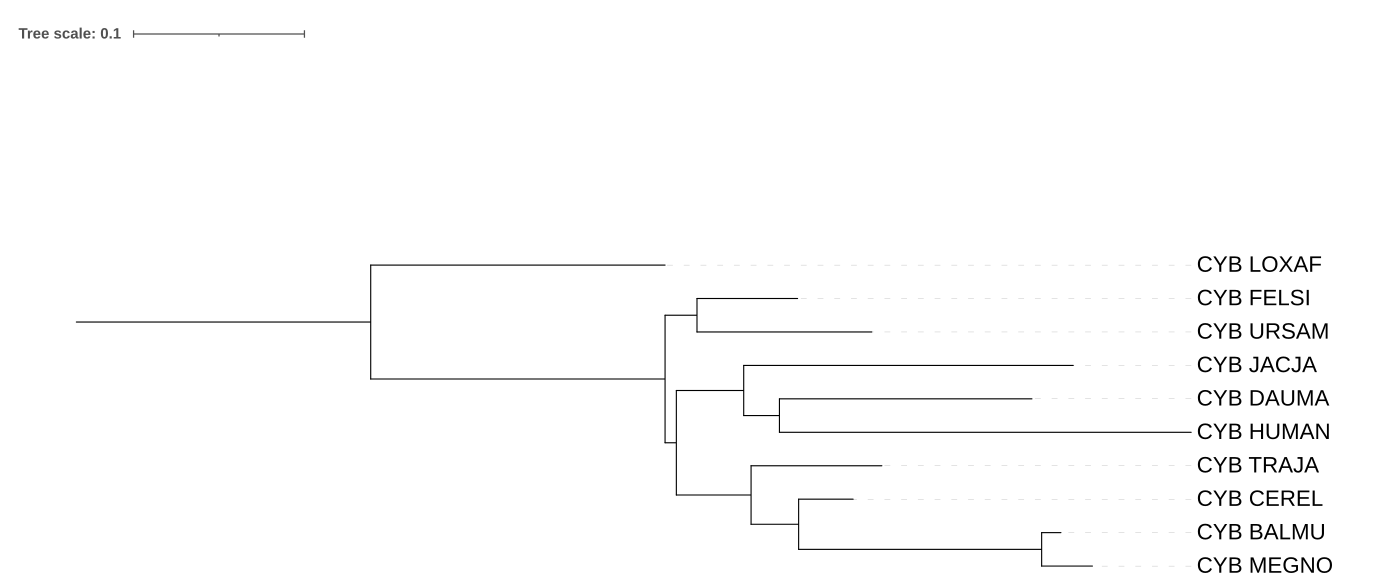
Полученное дерево имеет куда больше ошибочных клад, чем предыдущие. FELSI и URSAM оказались сестрински ко всем (кроме LOXAF). CEREL образует кладу с BALMU и MEGNO, хотя должна с TRAJA.