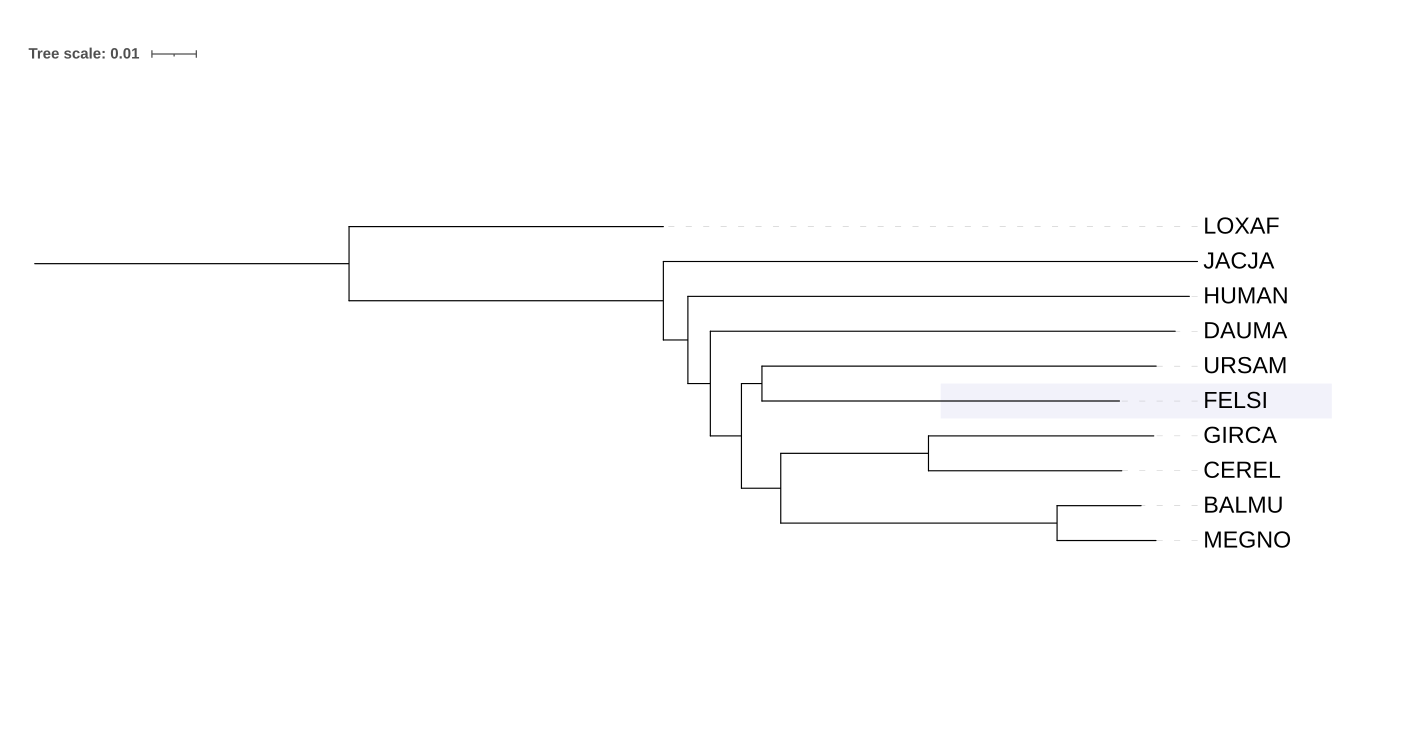
Для раннее выбраных животных были получены деревья на основе последовательности их малой РНК митохондриальных рибосом (12S rRNA). Для вида Tragulus не имелось размеченного митохондриального генома, поэтому вместо него взял Giraffa camelopardalis (GIRCA). Он не самый близкий к Tragulus, но топология относительно CEREL аналогичная.
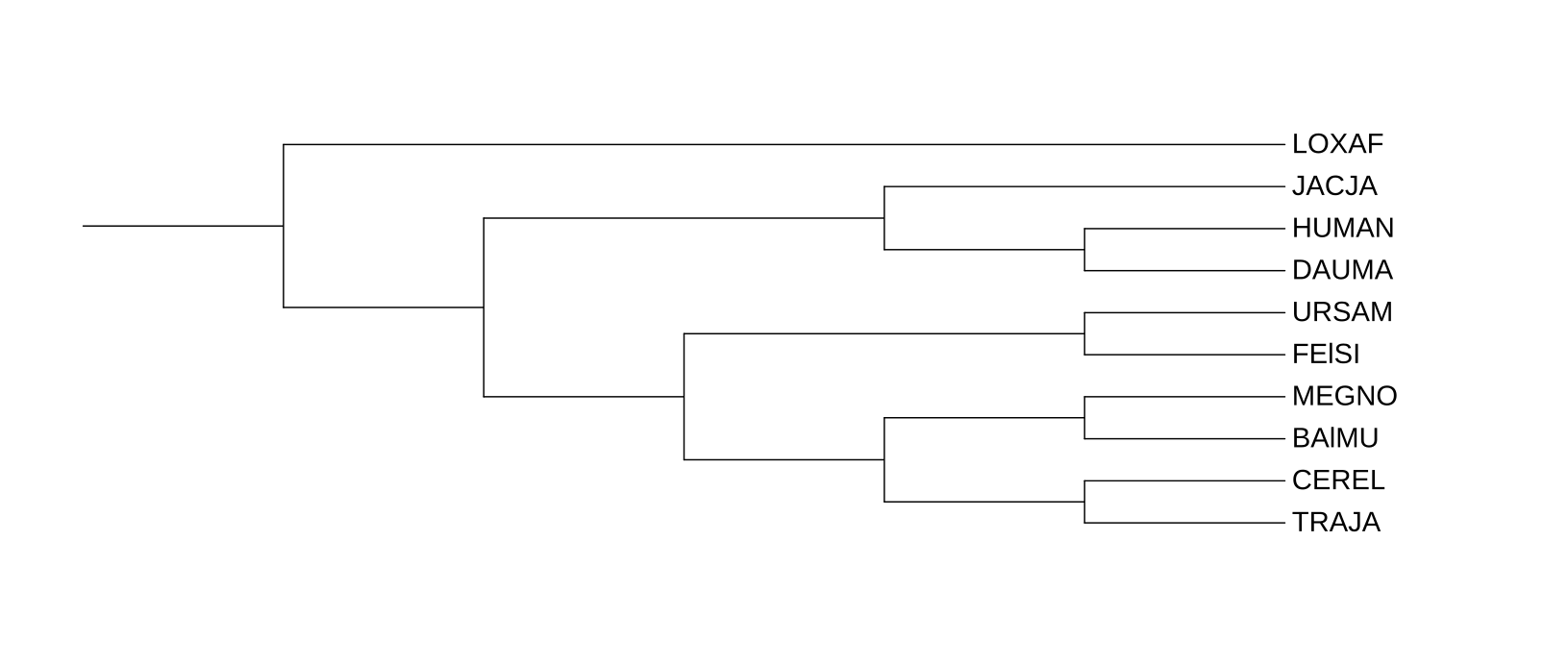
Все деревья в практикуме строились с помощью FastME методом p-distance


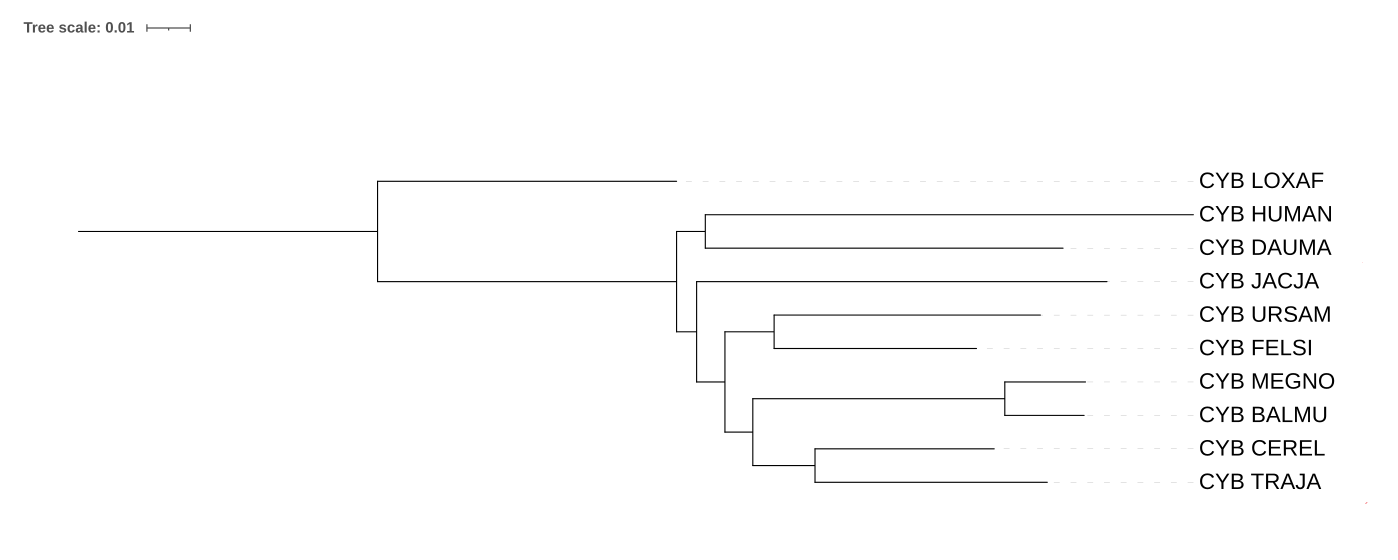

У всех реконструкций проблемы с кладой (JACJA,(HUMAN,DAUMA));. В случае реконструкции по цитохрому b из клады выпадает JACJA, а для 12S rRNA все три вида не объединены. Таким образом реконструкция по цитохрому b ближе к дереву на основе таксономии.
Для укоренения использовался Гигантский кенгуру (Macropus giganteus — MACGI).

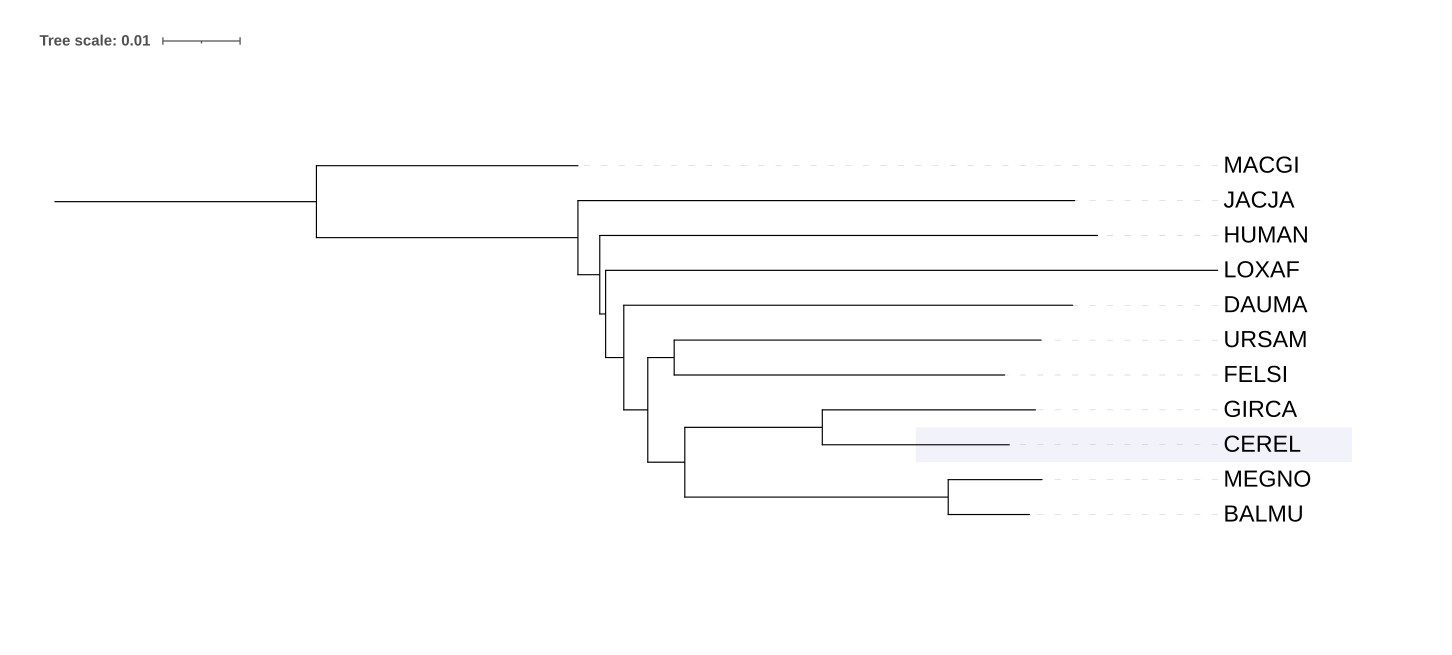
Главная странность — LOXAF, находящийся в середине дерева. Также JACJA,HUMAN и DAUMA опять не объединены.
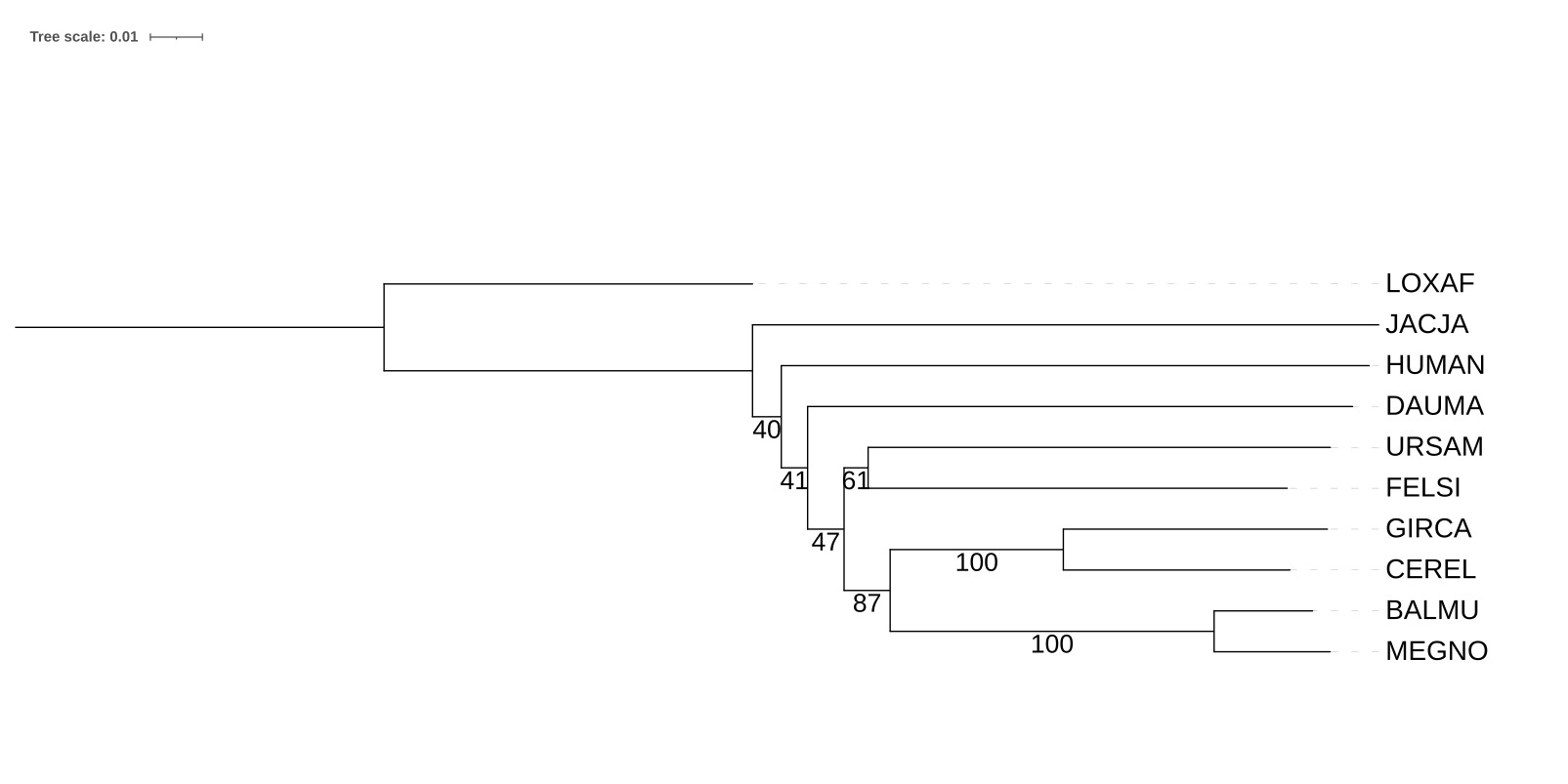
Полученный вес ветвей согласуется с правильностью их реконструкции. Например (GIRCA,CEREL) и (BALMU, MEGNO) имеет вес по 100, а между собой 87. Неправильно реконструированные ветви имеют меньший вес.