Ортологи и паралоги
Нахождение гомологов
Я провела поиск гомологов белка CLPX_ECOLI в протеомах выбранных организмов с помощью команд, представленных ниже:
cat AROAE.fasta BORPE.fasta BURMA.fasta PARDP.fasta PSEAE.fasta ROSDO.fasta SHEDO.fasta > ~/term4/pr4/prot.fasta
makeblastdb -dbtype prot -in prot.fasta -out col
blastp -query CLPX.fasta -db col -evalue 0.0001 -out result.txt
Файлс выдачей бласта.
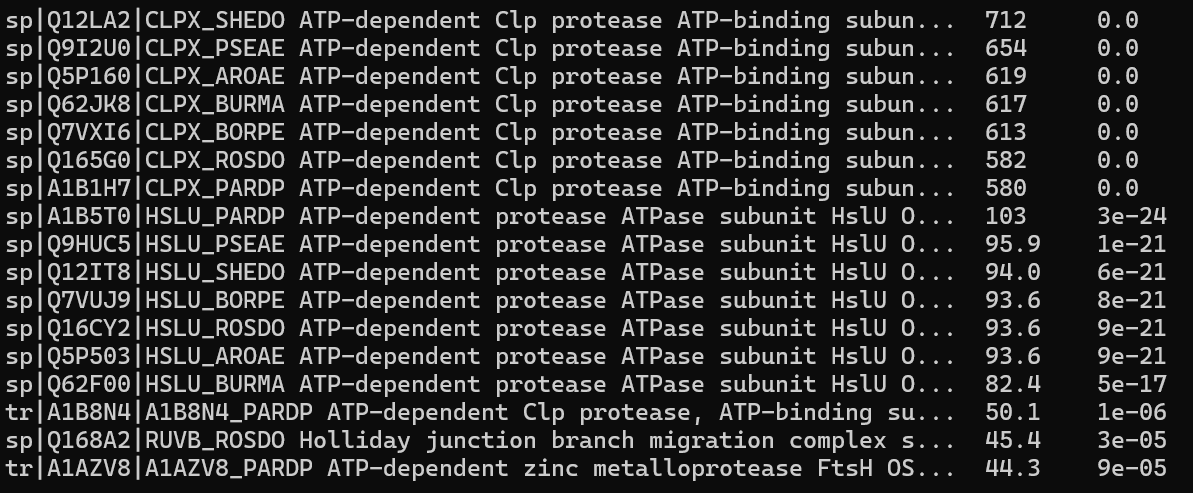
Рис1. Находки бласта
Реконструкция и визуализация
Я изменила название находок на их мнемоники, выровняла методом muscle и построила дерево программой fastme с бутстрепом 100.
Провела визуализацию дерева программой iTOL. Укоренила в среднюю точку и включила отображение бутстрепа кружочками с подписанной легендой.
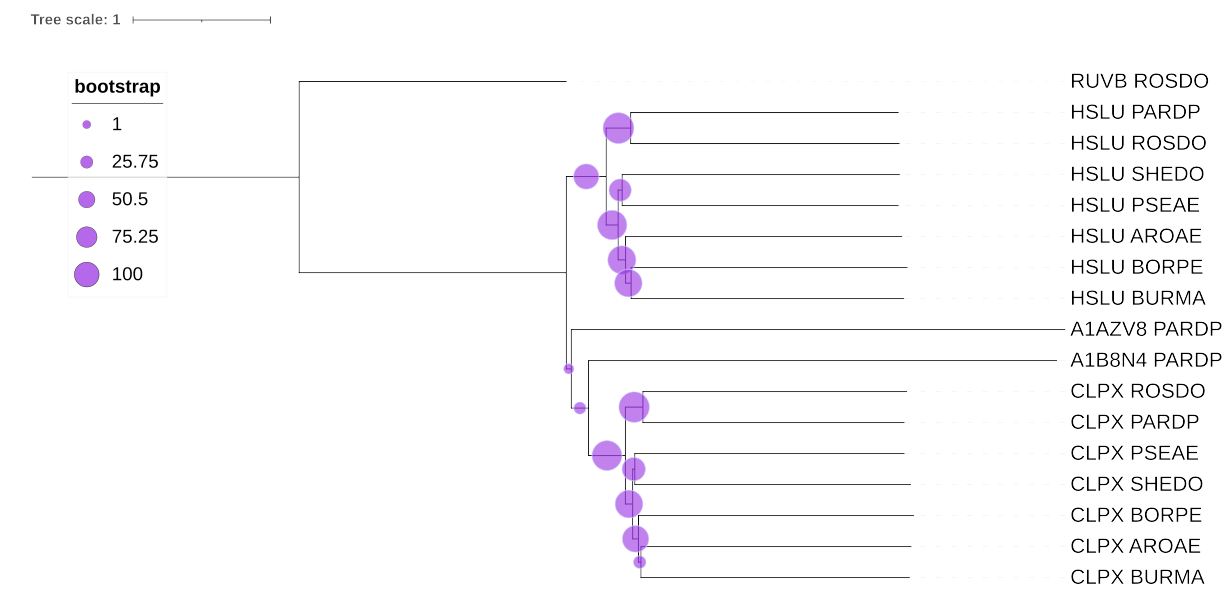
Рис2. Дерево гомологов (без выделение)
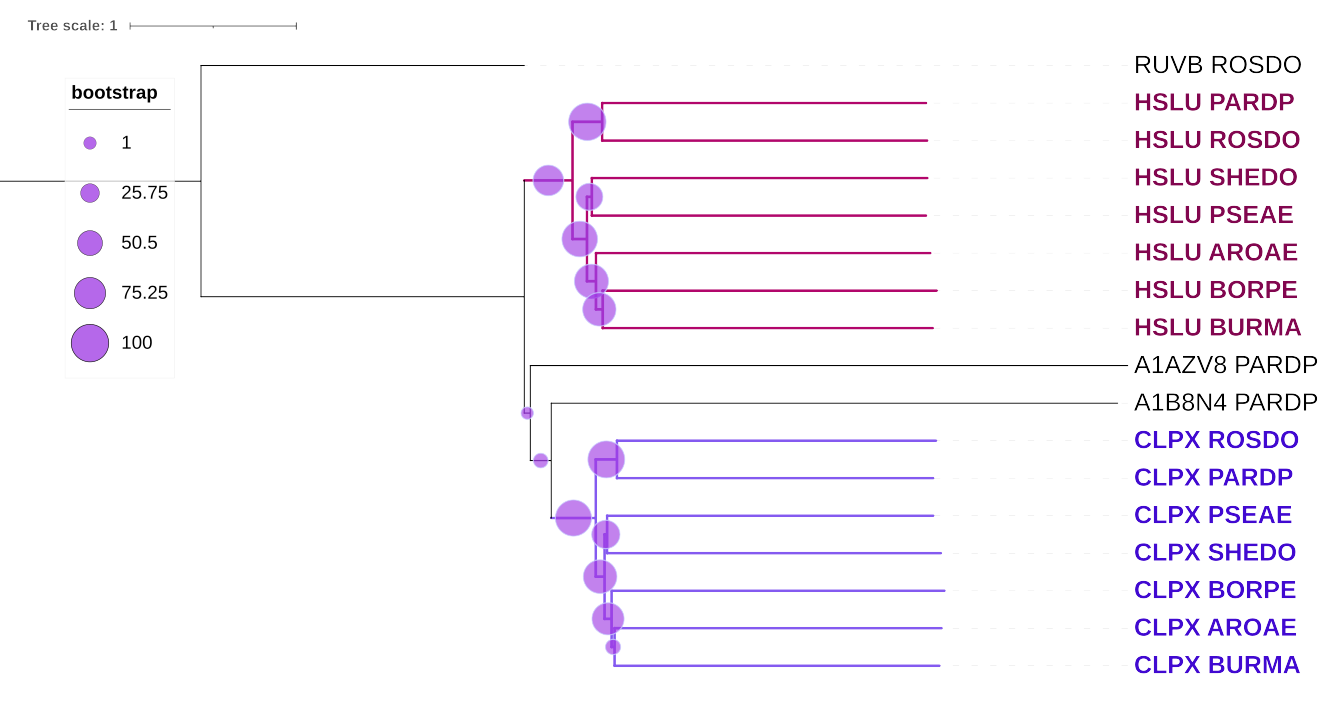
Рис3. Дерево гомологов с выделенными группами
Примеры ортологов: CLPX_ROSDO и CLPX_AROAE, CLPX_BORPE и CLPX_BURMA, HSLU_SHEDO и HSLU_PSEAE.
Примеры паралогов: CLPX_ROSDO и HSLU_ROSDO, CLPX_BORPE и HSLU_BORPE, CLPX_SHEDO и HSLU_SHEDO.
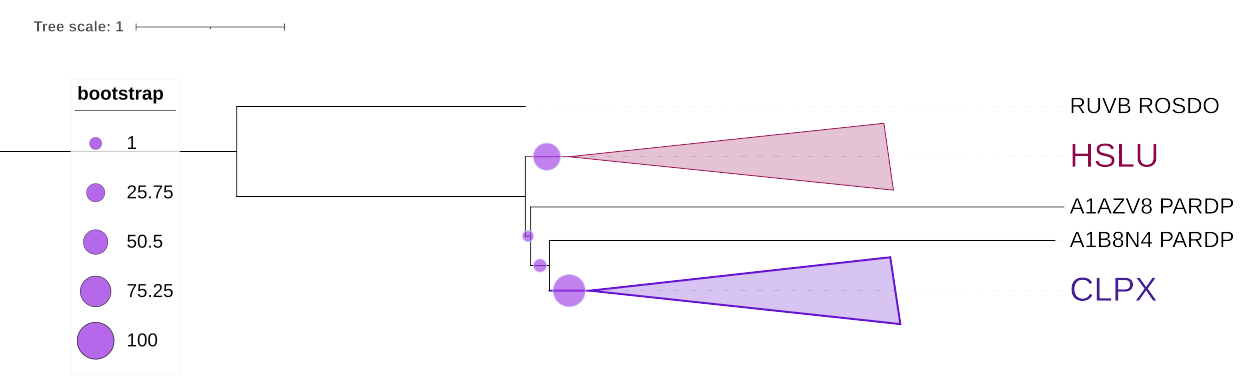
Рис4. Дерево гомологов со схлопнутыми группами. Состав CLPX: CLPX_PARDP, CLPX_ROSDO, CLPX_PSEAE, CLPX_SHEDO, CLPX_AROAE, CLPX_BORPE, CLPX_BURMA; состав HSLU: HSLU_PARDP, HSLU_SHEDO, HSLU_ROSDO, HSLU_PSEAE, HSLU_AROAE, HSLU_BORPE, HSLU_BURMA.
Получились две большие ортологические группы, содержащие все 7 выбранных орагнизмов:
CLPX: ATP-dependent Clp protease ATP-binding subunit ClpX, АТФ связывающая субъединица АТФ зависимой Clp протеазы.
Состав CLPX: CLPX_PARDP, CLPX_ROSDO, CLPX_PSEAE, CLPX_SHEDO, CLPX_AROAE, CLPX_BORPE, CLPX_BURMA;
HSLU: ATP-dependent protease ATPase subunit HslU, АТФ зависящая субъединица АТФ зависимой протеазы HslU.
Состав HSLU: HSLU_PARDP, HSLU_SHEDO, HSLU_ROSDO, HSLU_PSEAE, HSLU_AROAE, HSLU_BORPE, HSLU_BURMA.
По моему скромному мнению, реконструированная филогения по белкам не совсем отвечает истинной филогении. Пример: если рассмотреть группу CLPX, то в ней AROAE и BURMA стоят вместе против BORPE, хотя в истином дереве BORPE и BURMA роднее можду собой, чем с AROAE.