Сигналы и мотивы II
IC & LOGO
Для выполнения задания было использовано четвертое выравнивание. Итоговая таблица была создана с помощью незатейливого, но несложного скрипта на питоне, значение IC = 10.46.

Проверка мотива
В предыдущем практикуме был найден предполагаемый TRS для SARS-CoV.

Далее результаты выдачи MEME были использованы для запуска FIMO.
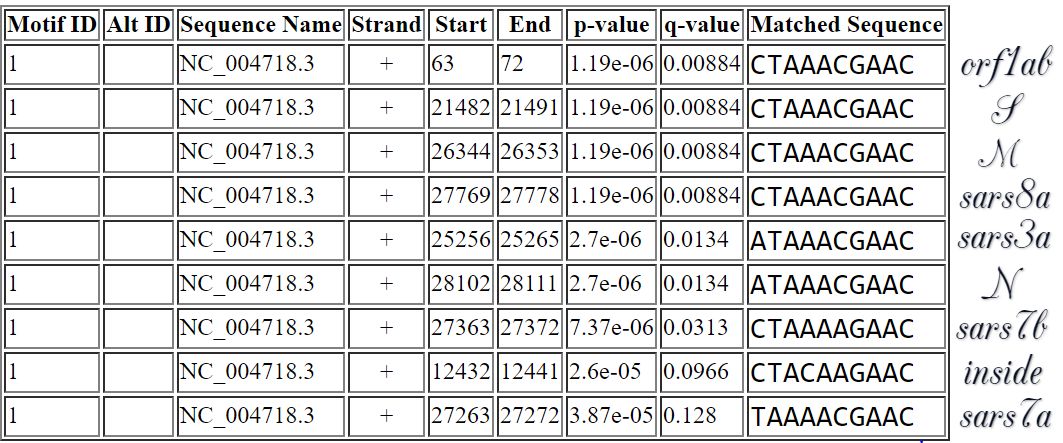
Анализ:
- длина мотива - десять, однако его начало соответствует core sequence из статьи
- есть ровно один сигнал в лидерной последовательности до начала гена полипротеина
- есть сигналы перед старт-кодонами семи поздних генов из двенадцати
- между сигналами и старт-кодонами поздних генов нет ATG
- есть один сигнал внутри полипротеина (альтернативная транскрипция?)
- вообще говоря, вероятность найти такой длинный мотив в больше, чем половине генов, мала
Мотив далек от идеала, но все-таки выглядит довольно неслучайно, так что можно предположить, что он все-таки играет какую-то регуляторную роль.
Последовательность козак
Выполнение этого задания сопровождалось страданиями. Старт-кодон присутствовал во всех генах, но MEME никак не мог его найти.
Поэтому было просто взято окружение ATG и построено LOGO. Возможно, все так и задумывалось, а я потеряла час времени из-за отсутствия нейронов в голове.
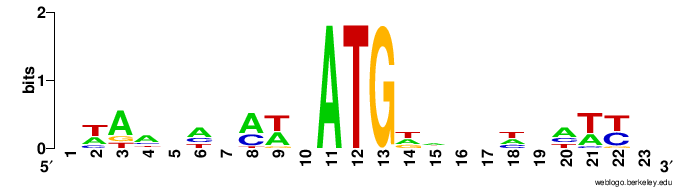
Хочется сравнить ее с настоящей, человеческой, взятой из англовики.
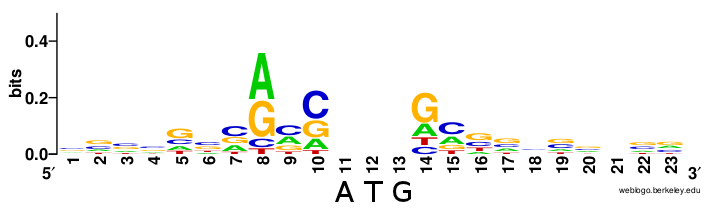
Честно говоря, могло бы быть и лучше. В конце концов, этот вирус вызвал эпидемию в 2002-2003 годах, а значит кроме прочего должен нормально транскрибироваться в человеческих клетках. Какие-то совпадения отчетливо видны только на -3 и +1 позициях; разочаровывающе.
Самое время прерваться на любование толстым енотом, который выглядит прямо как очень-сильно-удивленная-от-количества-работы я на карантине:

Сравнение мотивов
Для начала был взят геном SARS-CoV-2 (потому что почему бы и да).

Что-то слишком длинно. Ну да ладно.
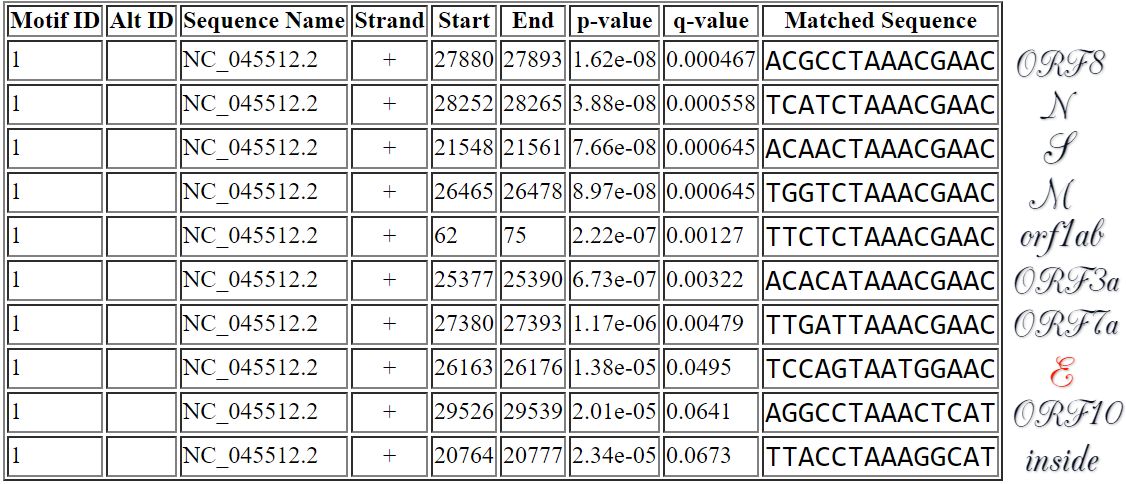
Анализ:
- длина мотива - четырнадцать, однако его середина соответствует core sequence из статьи
- есть ровно один сигнал в лидерной последовательности до начала гена полипротеина
- есть сигналы перед старт-кодонами восьми поздних генов из десяти...
- ...однако через шесть нуклеотидов после сигнала перед геном E выплывает старт-кодон :(
- есть один сигнал внутри полипротеина (альтернативная транскрипция?)
- вообще говоря, вероятность найти такой длинный мотив почти во всех генах мала
Что самое клевое - оно правда похоже на мотив обычного SARS-CoV! Если отрезать первые четыре нуклеотида, получится то же самое с чуть меньшей консервативностью (если можно так сказать). Все-таки это штаммы одного вида.
Для второго эксперимента был взят MERS-CoV, вызвавший несколько вспышек с довольно высокой смертностью и не искорененный до сих пор.

Выглядит многообещающе!
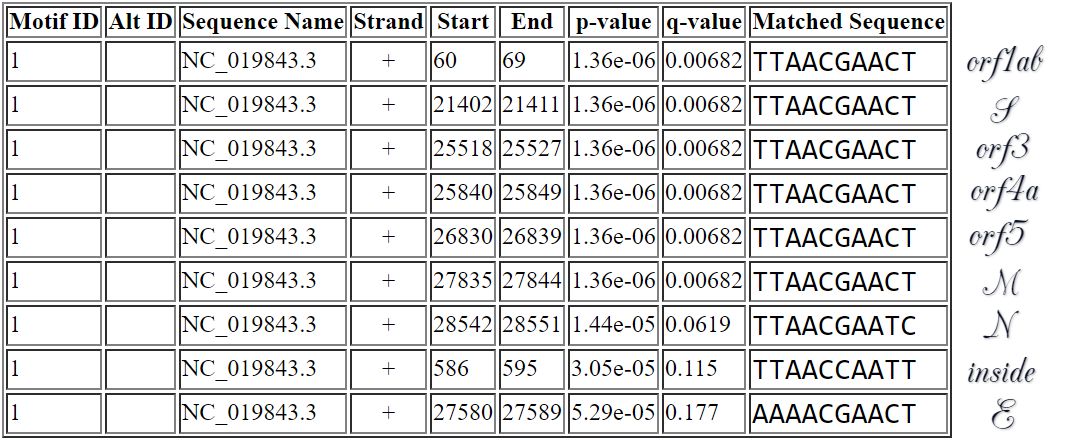
Анализ:
- длина мотива - десять, однако его начало похоже core sequence из статьи
- есть ровно один сигнал в лидерной последовательности до начала гена полипротеина
- есть сигналы перед старт-кодонами семи поздних генов из девяти
- между сигналами и старт-кодонами поздних генов нет ATG
- есть один сигнал внутри полипротеина (альтернативная транскрипция?)
- вообще говоря, вероятность найти такой длинный мотив почти во всех генах мала
И... оно прямо как предыдущие два! Первые девять нуклеотидов (за исключением второго) повторяют мотивы SARS-CoV с немного другими вероятностями. Можно сделать вывод, что в пределах рода (в данном случае Betacoronavirus) мотивы довольно схожи, и почти повторяются для разных штаммов одного вида.