Задание 1
- Для того, чтобы найти гомологов белка CLPX_ECOLI сначала были скачаны и сложены в один fasta файл протеомы выбраных мной бактерий в Практикум 1 с помощью команды cat
- После этого были сделаны индексные файлы для blast
makeblastdb -dbtype prot -in blastdb.fasta
- Далее запущен blastp
blastp -evalue 0.001 -query CLPX_ECOLI.fasta -db blastdb.fasta -out blastp.txt
- Выдача blast - гомологичные белки
sp|Q891J8|CLPX_CLOTE ATP-dependent Clp protease ATP-binding sub... 538 0.0 sp|Q2RL30|CLPX_MOOTA ATP-dependent Clp protease ATP-binding sub... 533 0.0 sp|A5I6W0|CLPX_CLOBH ATP-dependent Clp protease ATP-binding sub... 530 0.0 sp|Q5KWJ9|CLPX_GEOKA ATP-dependent Clp protease ATP-binding sub... 520 0.0 sp|P50866|CLPX_BACSU ATP-dependent Clp protease ATP-binding sub... 516 0.0 sp|Q8Y7K9|CLPX_LISMO ATP-dependent Clp protease ATP-binding sub... 511 1e-179 sp|Q2FXQ7|CLPX_STAA8 ATP-dependent Clp protease ATP-binding sub... 498 1e-174 tr|Q1GAP8|Q1GAP8_LACDA ATP-dependent Clp protease ATP-binding s... 475 2e-165 sp|P39778|CLPY_BACSU ATP-dependent protease ATPase subunit ClpY... 106 2e-25 sp|Q5L0N1|HSLU_GEOKA ATP-dependent protease ATPase subunit HslU... 105 6e-25 sp|Q1G9V4|HSLU_LACDA ATP-dependent protease ATPase subunit HslU... 101 2e-23 tr|Q2RJP5|Q2RJP5_MOOTA ATP-dependent protease ATPase subunit Hs... 100 4e-23 sp|Q8Y7J8|HSLU_LISMO ATP-dependent protease ATPase subunit HslU... 99.8 6e-23 sp|Q2FZ28|HSLU_STAA8 ATP-dependent protease ATPase subunit HslU... 98.2 2e-22 tr|Q8Y8B1|Q8Y8B1_LISMO UVR domain-containing protein OS=Listeri... 60.5 5e-10 sp|Q2FV74|CLPL_STAA8 ATP-dependent Clp protease ATP-binding sub... 57.8 4e-09 sp|O31673|CLPE_BACSU ATP-dependent Clp protease ATP-binding sub... 56.2 1e-08 tr|Q1GB74|Q1GB74_LACDA UVR domain-containing protein OS=Lactoba... 52.4 2e-07 tr|A5I766|A5I766_CLOBH ATP-dependent zinc metalloprotease FtsH ... 52.0 3e-07 tr|Q2RLR4|Q2RLR4_MOOTA AAA domain-containing protein OS=Moorell... 50.1 6e-07 tr|Q2RLP6|Q2RLP6_MOOTA AAA domain-containing protein OS=Moorell... 48.5 2e-06 tr|Q891B9|Q891B9_CLOTE ATP-dependent zinc metalloprotease FtsH ... 47.8 5e-06 tr|Q899H3|Q899H3_CLOTE ATP-dependent zinc metalloprotease FtsH ... 46.6 1e-05 tr|Q1GBN8|Q1GBN8_LACDA ATP-dependent zinc metalloprotease FtsH ... 46.6 1e-05 tr|A5I7Q0|A5I7Q0_CLOBH ATP-dependent zinc metalloprotease FtsH ... 46.2 1e-05 tr|Q1G869|Q1G869_LACDA ATP-dependent Clp protease, ATP-binding ... 45.8 2e-05 tr|Q5L436|Q5L436_GEOKA UVR domain-containing protein OS=Geobaci... 44.7 5e-05 tr|Q5KUR3|Q5KUR3_GEOKA AAA domain-containing protein OS=Geobaci... 44.3 5e-05 sp|Q2G2J8|Y1413_STAA8 Uncharacterized protein SAOUHSC_01413 OS=... 43.1 9e-05 tr|Q895L6|Q895L6_CLOTE AAA domain-containing protein OS=Clostri... 43.5 1e-04 tr|Q2RM95|Q2RM95_MOOTA ATP-dependent zinc metalloprotease FtsH ... 43.1 2e-04 tr|Q8YAC6|Q8YAC6_LISMO ATP-dependent zinc metalloprotease FtsH ... 43.1 2e-04 tr|Q898D1|Q898D1_CLOTE AAA domain-containing protein OS=Clostri... 42.7 2e-04 tr|Q5L3T1|Q5L3T1_GEOKA ATP-dependent zinc metalloprotease FtsH ... 42.4 2e-04 tr|A5I501|A5I501_CLOBH AAA domain-containing protein OS=Clostri... 41.6 3e-04 tr|A5HYU4|A5HYU4_CLOBH ATP-dependent zinc metalloprotease FtsH ... 41.2 5e-04 tr|Q5KZ67|Q5KZ67_GEOKA AAA domain-containing protein OS=Geobaci... 40.8 5e-04 sp|P37476|FTSH_BACSU ATP-dependent zinc metalloprotease FtsH OS... 40.8 7e-04 tr|Q2RJJ8|Q2RJJ8_MOOTA AAA domain-containing protein OS=Moorell... 40.4 0.001
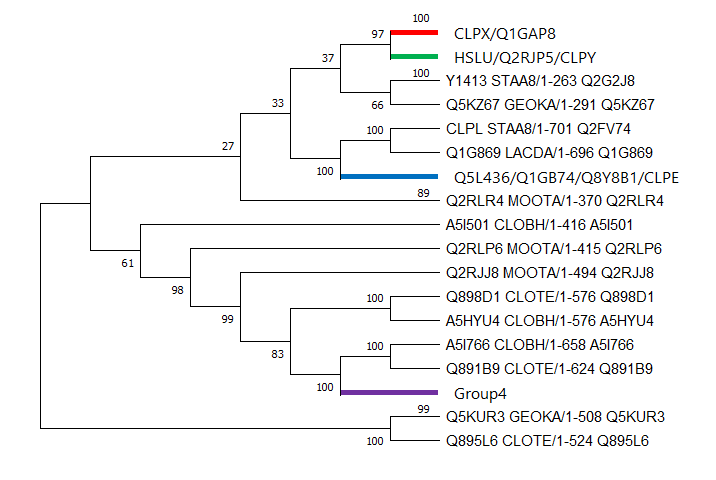
- После этого было построено дерево в программе MEGAX Neighbor-Joining методом с бутстреп анализом
- Из полученного дерева выделяем тройку ортологов и паралогов:
- Ортологи: Q898D1 CLOTE и A5HYU4 CLOBH; Q5L3T1 GEOKA и P37476 BACSU; P39778 BACSU и Q5L0N1 GEOKA
- Паралоги: Q2RJJ8 и Q2RLP6 MOOTA; Q5L436 и Q5KZ67 GEOKA; Q1GAP8 и Q1G9V4 LACDA
- Дерево в Newick-формате: (((((((CLPX_GEOKA/1-421_Q5KWJ9,CLPX_BACSU/1-420_P50866),CLPX_LISMO/1-419_Q8Y7K9),CLPX_STAA8/1-420_Q2FXQ7),(CLPX_MOOTA/1-419_Q2RL30,(CLPX_CLOTE/1-431_Q891J8,CLPX_CLOBH/1-429_A5I6W0))),Q1GAP8_LACDA/1-417_Q1GAP8),(HSLU_LACDA/1-464_Q1G9V4,(Q2RJP5_MOOTA/1-461_Q2RJP5,(HSLU_STAA8/1-467_Q2FZ28,(HSLU_LISMO/1-469_Q8Y7J8,(CLPY_BACSU/1-467_P39778,HSLU_GEOKA/1-465_Q5L0N1)))))),(Y1413_STAA8/1-263_Q2G2J8,Q5KZ67_GEOKA/1-291_Q5KZ67),((CLPL_STAA8/1-701_Q2FV74,Q1G869_LACDA/1-696_Q1G869),(Q5L436_GEOKA/1-810_Q5L436,(Q1GB74_LACDA/1-731_Q1GB74,(Q8Y8B1_LISMO/1-724_Q8Y8B1,CLPE_BACSU/1-699_O31673)))),Q2RLR4_MOOTA/1-370_Q2RLR4,(A5I501_CLOBH/1-416_A5I501,(Q2RLP6_MOOTA/1-415_Q2RLP6,(Q2RJJ8_MOOTA/1-494_Q2RJJ8,((Q898D1_CLOTE/1-576_Q898D1,A5HYU4_CLOBH/1-576_A5HYU4),((A5I766_CLOBH/1-658_A5I766,Q891B9_CLOTE/1-624_Q891B9),(((Q899H3_CLOTE/1-603_Q899H3,A5I7Q0_CLOBH/1-601_A5I7Q0),Q2RM95_MOOTA/1-645_Q2RM95),(Q1GBN8_LACDA/1-737_Q1GBN8,(Q8YAC6_LISMO/1-691_Q8YAC6,(Q5L3T1_GEOKA/1-632_Q5L3T1,FTSH_BACSU/1-637_P37476))))))))),(Q5KUR3_GEOKA/1-508_Q5KUR3,Q895L6_CLOTE/1-524_Q895L6));
- Далее была сделана визуализация с покрашенными ортологичными группами (Рис.1) и со схлопнутыми ортологичными группами (Рис.2)