Практикум №2
Создание выравниваний
В этом практикуме необходимо создать выравнивание последовательностей цитохромов В из выбранных организмов практикума №1, реконструировать дерево тремя способами, визуализировать их с помощью iTOL и сравнить деревья с деревом видов.
Для справки: Цитохром B — это белок, являющийся ключевым компонентом дыхательной цепи митохондрий. Этот ген есть в митохондриальной ДНК у всех животных и поскольку он очень важен для жизни, он является одним из самых популярных молекулярных маркеров в филогенетике.Для построения выравнивания цитохромов В был создан список cyb_list формата sw:cyb_*, далее выполнили команду:
seqret @cyb.list cyb.fastaПосле выполнения этой команды, появился файл с названием cyb.fasta c аминокислотными последовательностями для каждого из выбранных организмов. Далее необходимо выровнять эти последовательностями, воспользуемся следующей командой:
muscle -align
cyb.fasta -output cyb-alignment.fastaРеконструирование филогенетических деревьев
Перед выполнением этой части задания необходимо перевести выравнивания в единственный формат, который воспринимается программой FastME ("phylip-relaxed").
Была написана программа, берующая на вход выравнивание в формате fasta и выдающая выравнивание в формате phylip-relaxed.
Выдача1. Программа FastME
Для построения дерева FastME использует эволюционные расстояния, в этом практикуме рассмотрим две модели: p-distance и MtREV.
Это самая простая модель, которая считает расстояние как долю различающихся позиций в выравнивании. Команда:
fastme -i cyb.phy -pp -o cyb_fastme_p.treЭто уже специализированная модель для митохондриальных белков, учитывающая множество факторов, которые упускает модель p-distance. Команда:
fastme -i cyb.phy -pM -o cyb_fastme_mtrev.tre
2. Программа IQ-Tree
Эта программа использует метод максимального правдоподобия, то есть сама ищет наиболее вероятную модель эволюции, которая больше подходит под наши последовательности. Команда:
iqtree -s cyb.phyПрограмма создает несколько файлов, нужный нам - cyb.phy.treefile (файл со скобочной формулой дерева)
Визуализация и сравнение деревьев
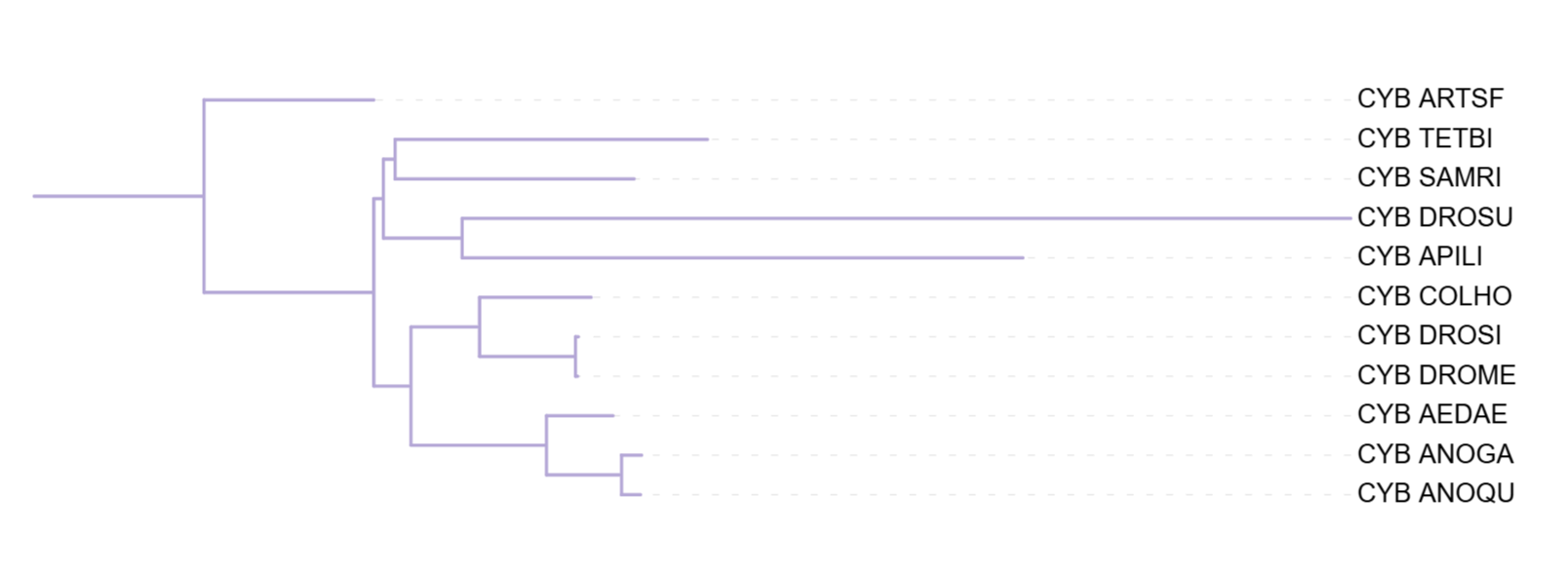
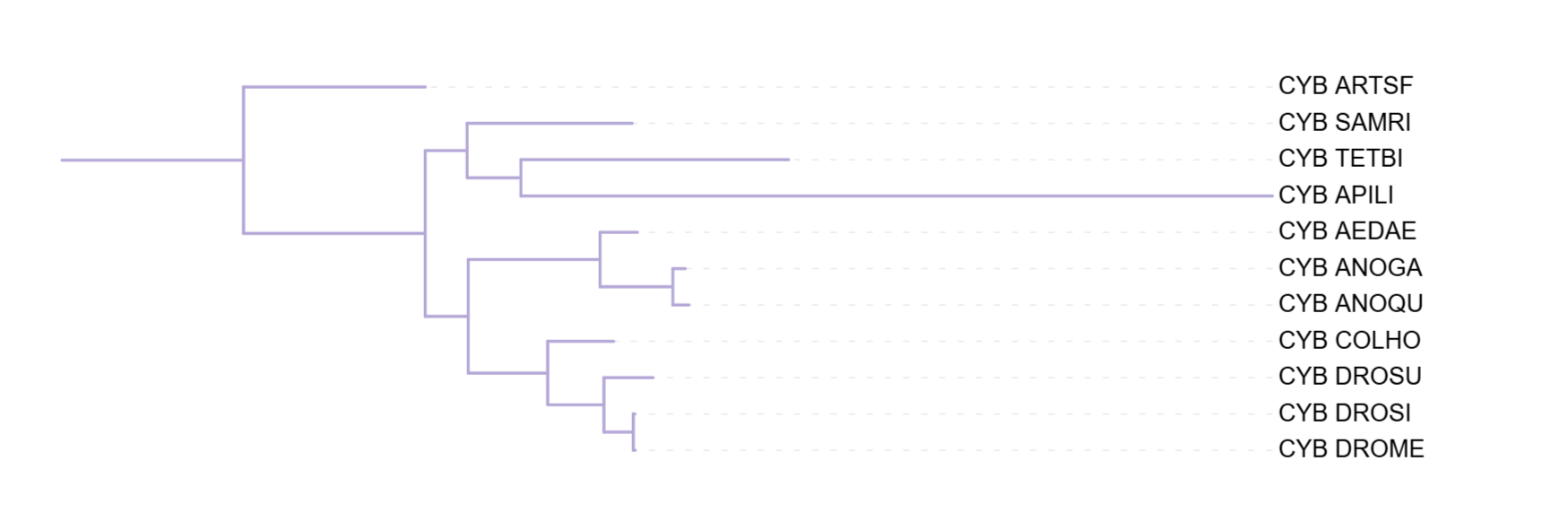

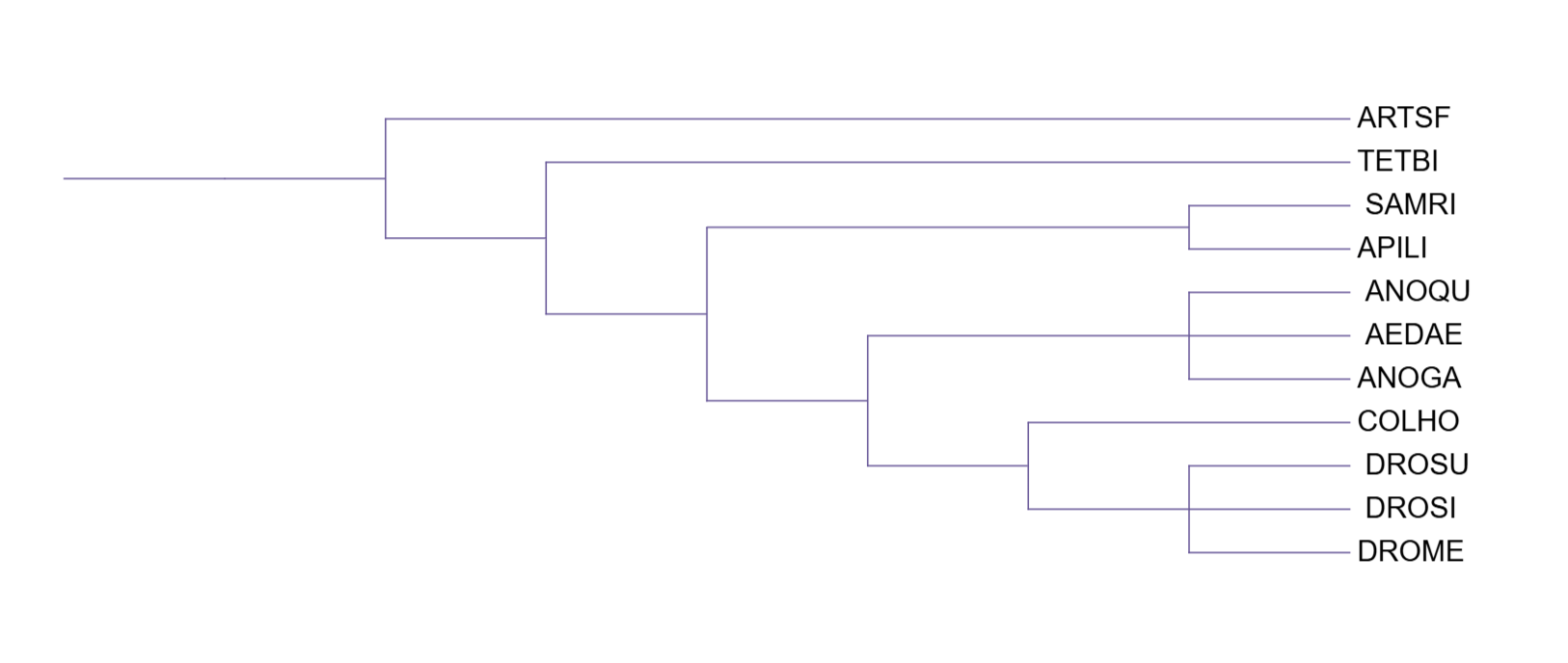
Все три реконструированные дерева верно отделяют ракообразных (ARTSF) от остальных организмов. Наибольшие расхождения с таксономией затрагивают TETBI - гигантскую коллемболу (ногохвостка, паукообразные), которую никакой метод не отнес к отдельной группе. Группа комаров (ANOGA, AEDAE, ANOQU) формировала кладу во всех трёх деревьях. Дрозофилы в основном тоже обособлялись одной группой, однако при использовании p-distance DROSU обособляется и сближается с пчелой APILI. Наименьшее количество противоречий с таксономией наблюдается в деревьях, построенных с использованием моделей MtREV и IQ-TREE.