A- и В- формы ДНК. Структура РНК
Задание 1.
|
Целью данного задания было создание A-, B- и Z-формы дуплекса ДНК с помощью программы fiber пакета 3DNA.
Последовательностью одной из нитей дуплекса является 5 раз повторенная последовательность "gatc".
Полученные структуры сохраняем в файлах gatc-a.pdb, gatc-b.pdb и gatc-z.pdb.
|
Задание 2.
Упражнение 1.
|
В данном задании нужно было изучить B-структуру в JMol-е и определить, какие атомы заданного основания обращены в сторону той или иной бороздки.
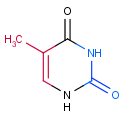
Тимин был моим основанием. С помощью MarvinSketch получаем изображение выбранного тимина.
Выделяем красным атомы, смотрящие в сторону большой бороздки, синим - в сторону малой.
Я выбрала тимин № 31. Тимин отсутствует в z-форме, поэтому в таблице поставлены прочерки.
|
Таблица 1. Ориентация атомов заданного основания
| Параметр |
A-форма |
В-форма |
Z-форма |
| Атомы, обращенные в сторону большой бороздки |
O2, C2, N1 |
C5, C6, C7 |
- |
| Атомы, обращенные в сторону малой бороздки |
O4, C4, C5, C7 |
O2, C2, N3 |
- |
| Остальные атомы |
C6, N3 |
O4, C4, N1 |
- |
Рис.1 - Тимин с соответственно покрашенными атомами
Упражнение 2.
Таблица 2. Сравнение спиральных параметров форм ДНК
| Параметр |
A-форма |
В-форма |
Z-форма |
| Тип спирали (правая или левая) |
Правая |
Правая |
Левая |
| Шаг спирали (A) |
28.03 (4:A-15:A) |
33.75 (8:A-18:A) |
43.50 (24:B-36:B) |
| Число оснований на виток |
11 |
10 |
12 |
| Ширина малой бороздки |
7.28 A (9:A-25:B) |
11.69 A (15:A-30:B) |
11.57 A (11:A-32:B) |
| Ширина большой бороздки |
16.97 A (12:A-32:B) |
17.21 A (8:A-30:B) |
14.37 A (10:A-37:B) |
С помощью JMol получаем данные по ширине/шагу, которые заносим в таблицу.
Упражнение 3.
Таблица 3. Сравнение торсионных углов в структурах A- и B-форм.
| Торсионный угол |
A-форма (заданное) |
A-форма (измеренное) |
B-форма (заданное) |
B-форма (измеренное) |
| α |
62 |
-51.7 |
63 |
-29.9 |
| β |
173 |
174.8 |
171 |
136.3 |
| γ |
52 |
41.7 |
54 |
31.2 |
| δ |
88/3 |
79.1 |
123/131 |
143.3 |
| ε |
178 |
-65.3 |
155 |
-39.4 |
| ζ |
-50 |
-85.4 |
-90 |
-69.1 |
| χ |
-160 |
-157.2 |
-117 |
-98.0 |
|
|
|
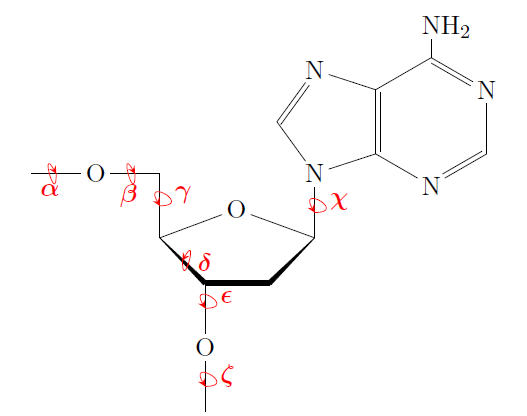
На представленном ниже рисунке (рис. 2) можно увидеть, где находится тот или иной торсионный угол.
Цель задания: сравнить торсионные углы в структурах А- и В-форм. А также сравнить их с установленными значениями.
Результаты можно получить с помощью программы JMol, команды "Измерение торсионных (диэдральных) углов".
"Заданные" значения A-формы и B- практически совпадают для первых 3 углов, в то время на другие различны, в среднем, на 20-40 градусов.
Заметим, что значения теоретическое и практическое для углов χ и β формы A- довольно близки по значению.
Но, преимущественно, значения теоретические/практические углов мало схожи, особенно для B-формы.
|
Рис.2 - Торсионные углы
Задание 3.
Упражнение 1.
|
В данном задании необходимо было определить торсионные углы в структуре ДНК и тРНК и определить среднее их значение с помощью Excel.
Также нужно было определить номер "деформированного" нуклеотида (с наиболее отклоняющимся значением какого-либо из торсионных углов, а лучше сразу и нескольких углов).
Для определения торсионных углов использовался пакет 3DNA (команда: find_pair -t XXXX_old.pdb stdout | analyze).
Причем краевые нуклеотиды не следовало рассматривать.
|
|
Самые "деформированные" нуклеотиды (тРНК): 4, 6, 22 (по 2 углам); 9, 18, 21, 25 (по 1 углу).
|
|
Самые "деформированные" нуклеотиды (ДНК): 15, 16, 20, 28, 33, 40, 42, 46 (по 1 углу).
|
Таблица 4. Средние значения торсионных углов в тРНК и ДНК
| Структура |
α |
β |
γ |
δ |
ε |
ζ |
χ |
| тРНК |
-24.45 |
95.23 |
51.39 |
82.71 |
-120.85 |
-59.88 |
-151.38 |
| ДНК |
-54.88 |
49.35 |
33.35 |
132.09 |
-142.33 |
-89.47 |
-126.66 |
Ссылка на файл Excel с данными по торсионным углам
Упражнение 2.
|
У этого задания несколько подпунктов:
|
|
1) Определить номера нуклеотидов, образующих стебли(stems) во вторичной структуре заданной тРНК;
|
|
2) Определить неканонические пары оснований в структуре тРНК;
|
|
3) Определить, есть дополнительные водородные связи в тРНК, стабилизирующие ее третичную структуру (для этого следует рассмотреть комплементарные пары, не имеющие отношения к стеблям).
|
|
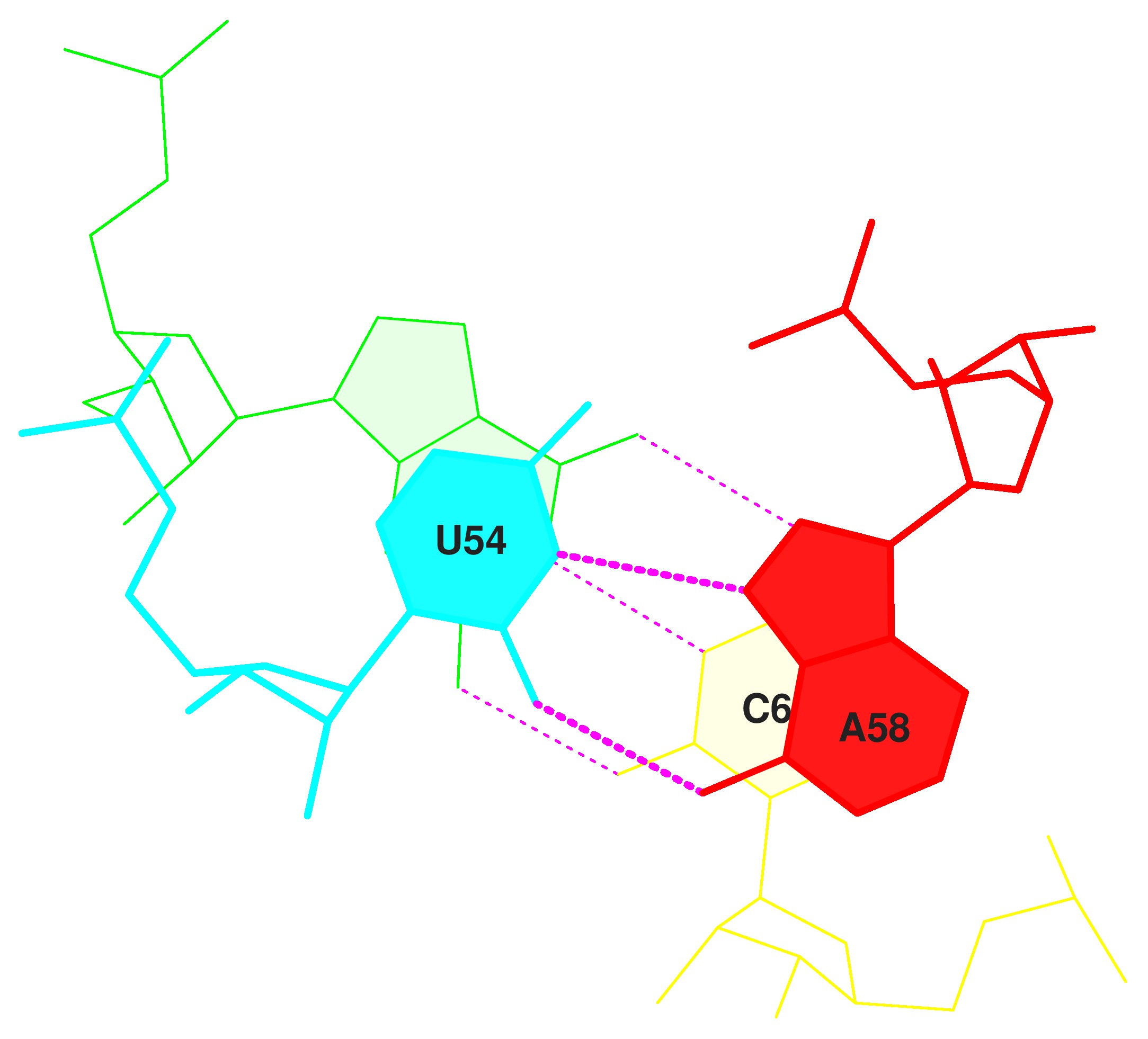
Неканонические пары оснований в структуре тРНК: 55U--18G, 38U--32U, 44C--26A, 13A--45A.
|
|
Также были найдены стебли в данной вторичной структуре тРНК:
1st stem: с 2:B--71:B по 7:B--66:B; 2nd stem: с 49:B--65:B по 53:B--61:B;
3rd stem: с 37:B--33:B по 44:B--26:B; 4th stem: с 10:B--25:B по 12:B--23:B.
|
|
Дополнительные водородные связи в тРНК (комплементарные пары, не имеющие отношения к стеблям):
54U--58A, 55U--18G, 13A--45A, 14A--8U, 15G--48C, 19G--56C.
|
Упражнение 3.
|
Цель задания: найти возможные стекинг-взаимодействия.
|
|
Для этого необходимо найти данные о величине площади "перекрывании" 2-х последовательных пар азотистых оснований, используя файл формата out.
Для пар с наибольшими значениями получить стандартное изображение стекинг-взаимодействия.
|
|
В файле была найдены необходимые пары - Section#0011 (GU/AC), с наибольшой площадью перекрытия - 11.38( 5.63).
Для получения изображения были использованы команды: ex_str -11 stacking.pdb step11.pdb и stack2img -cdolt step11.pdb step11.ps.
|
Рис.3 - Стандартное изображение стекинг-взаимодействия для описанных выше пар
© Kalashnikova Anastasia, 2016