
Для животных из практикума 1 были получены последовательности 12S рРНК из EMBLB с помощью программы seqret.
Однако, для Herpestes edwardsi (HERED) найти митохондриальный геном не удалось, поэтому для выполнения дальнейшего анализа вместо этого мангуста, я взяла другого, для которого митохондриальный геном есть: Herpestes brachyurus hosei. Мнемоника этого создания: 9CARN.
Последовательности были выровнены программой muscle и выравнивание было переведено в phylip-relaxed формат (подробно про это написано в практикуме 2).
Далее программой iqtree было построено дерево (рис 1).

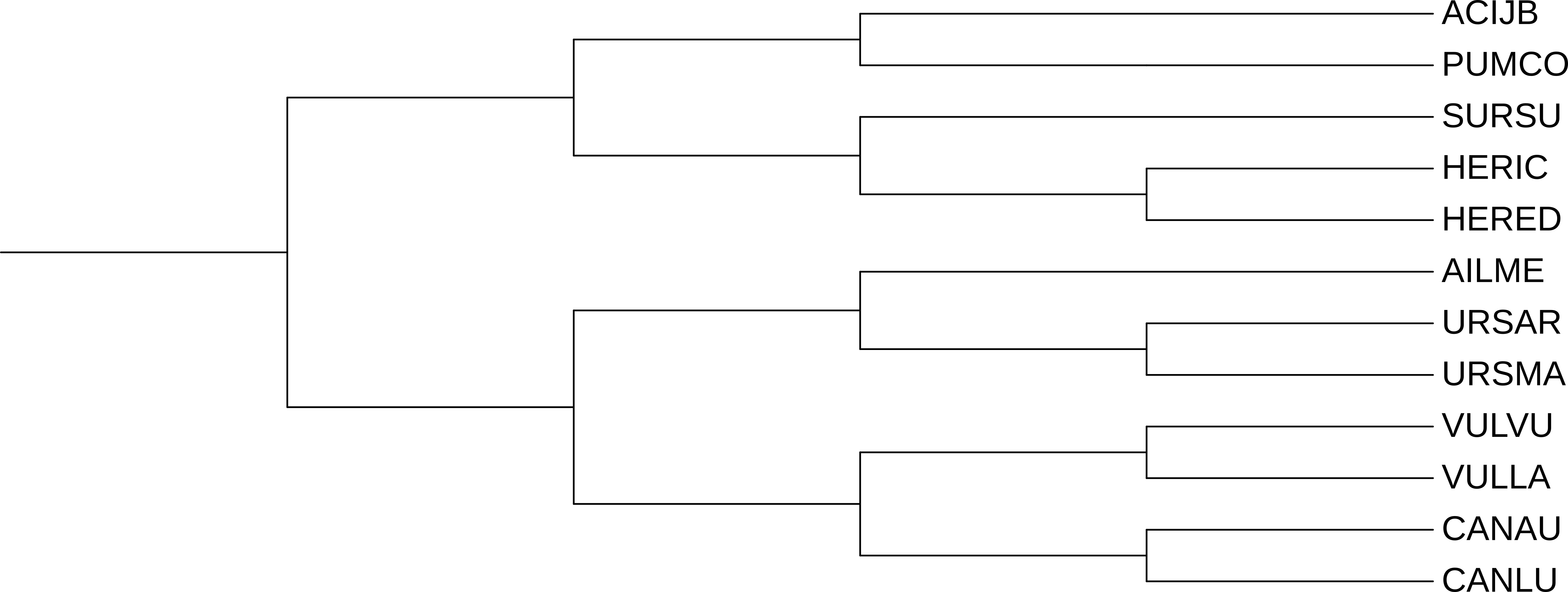
В сравнении с таксономическим деревом (рис 2) неправильно реконструировалась клада из мангустов и суриката.
В полученном дереве SURSU объединен в одну кладу с 9CARN, а опираясь на таксономию SURSU должен быть сестринской группой к кладе 9CARN и HERIC.
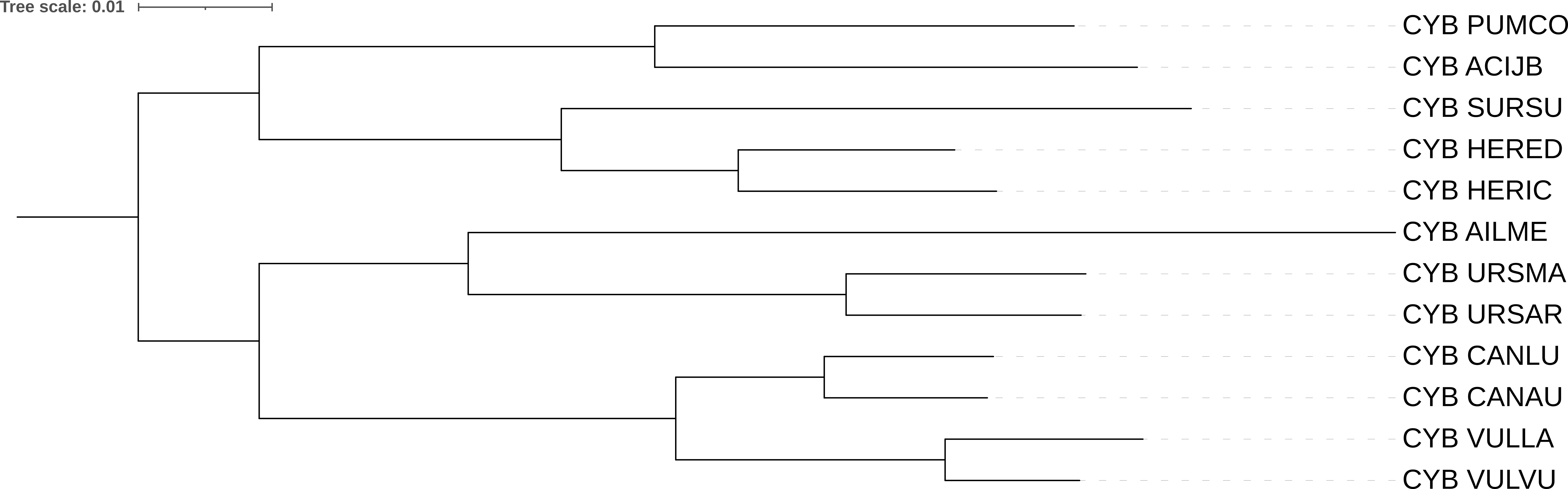
Дерево, построенное программой FastME по последовательности цитохромов (рис 3) топологически совпадает с таксономическим (рис 2), так что там отличия от дерева по 12S (рис 1), такие же, как были описаны выше.
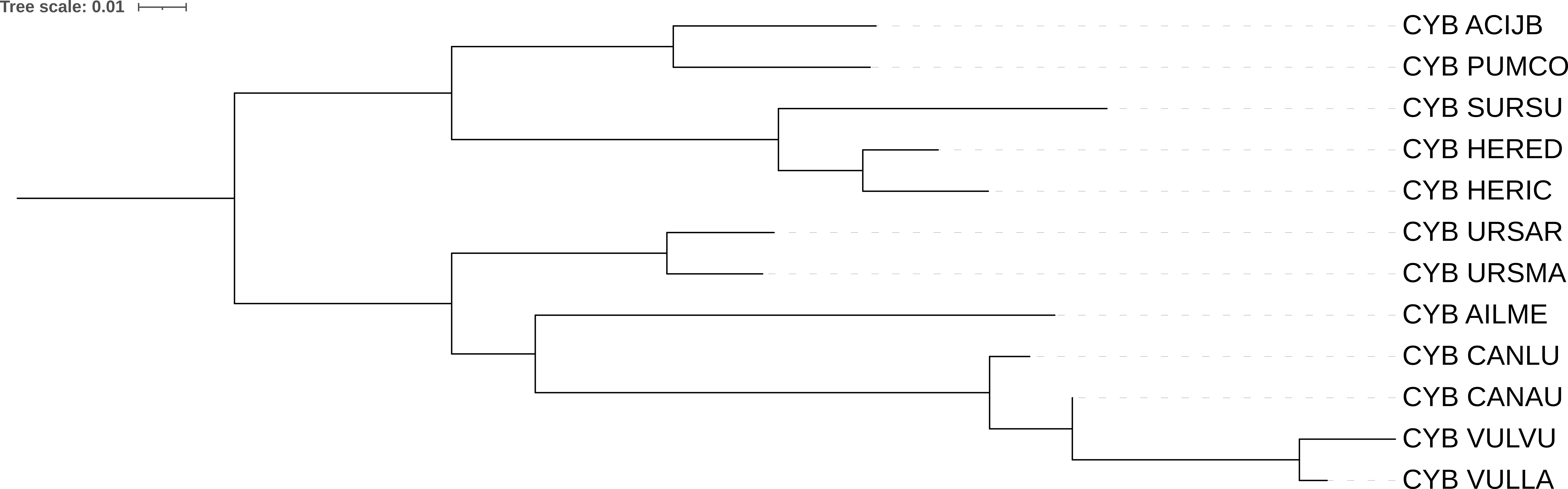
Сравнивать дерево, реконструированное по последовательностям цитохромов из прошлого практикума программой iqtree (рис 4) с полученным сейчас (рис 1), на мой взгляд достаточно странно. Там были свои отличия от таксономического (в кладе Caniformia (собакообразные), описанные в предыдущем практикуме), здесь в совсем другой кладе (Herpestidae - мангустовые).
В качестве внешней группы я выбрала Manis pentadactyla (Chinese pangolin), мнемоника: MANPE. Это наиболее близкий организм к таксону carnivora, но при этом из внешней группы.
Было построенно дерево по последовательностям 12S рРНК программой iqtree (рис 5).
Здесь снова произошла путаница в кладе мангустовых. На этот раз в одну кладу были объединены SURSU и HERIC, а 9CARN был выделен в сестринскую группу. Хотя таксономически в одной кладе должны быть HERIC и 9CARN.

Теперь, построим дерево программой FastME, использовав 100 реплик бутстрепа (рис 6).
Большинство ветвей имеют идеальную, 100% поддержку.
В кладе мангустовых снова перестановки. На этот наблюдается клада (SURSU, 9CARN). Поддержка этой клады гораздо меньше чем остальных ветвей (55, тогда как почти все остальные ветви имеют поддержку 99-100). Это закономерно, опираясь на предыдущие деревья, но непонятно.
Ветвь, ведущая к кладе кошкообразных (ACIJB, PUMCO, HERIC, SURSU, 9CARN) имеет самую маленькую поддержку - 49, что на мой взгляд достаточно странно.
