Паралоги, визуализация
В отчете содержатся скоращения из первого практикума, они продублированы в таблице 1.
| Видовое название | Мнемоническое название | ||
|---|---|---|---|
| Yersinia pestis | YERPE | ||
| Escherichia coli | ECOLI | ||
| Haemophilus influenzae | HAEIN | ||
| Pasteurella multocida | PASMU | ||
| Pseudomonas mendocina | PSEMY | ||
| Neisseria meningitidis | NEIMA | ||
| Polynucleobacter asymbioticus | POLAQ | ||
Для поиска гомологов были использованы протеомы бактерий из первых трех заданий, файл был получен командой:
cat ECOLI.fasta YERPE.fasta HAEIN.fasta PASMU.fasta PSEMY.fasta NEIMA.fasta POLAQ.fasta > ~/proteom.fasta
Он был перемещен в директорию блока, проиндексирован для blastp и использован в качестве базы данныз для выравнивания:
makeblastdb -dbtype prot -in proteom.fasta
blastp -query CLPX_ECOLI.fasta -db proteom.fasta -evalue 0.001 -out al2
В итоге найденные выравнивания содержатся в файле.
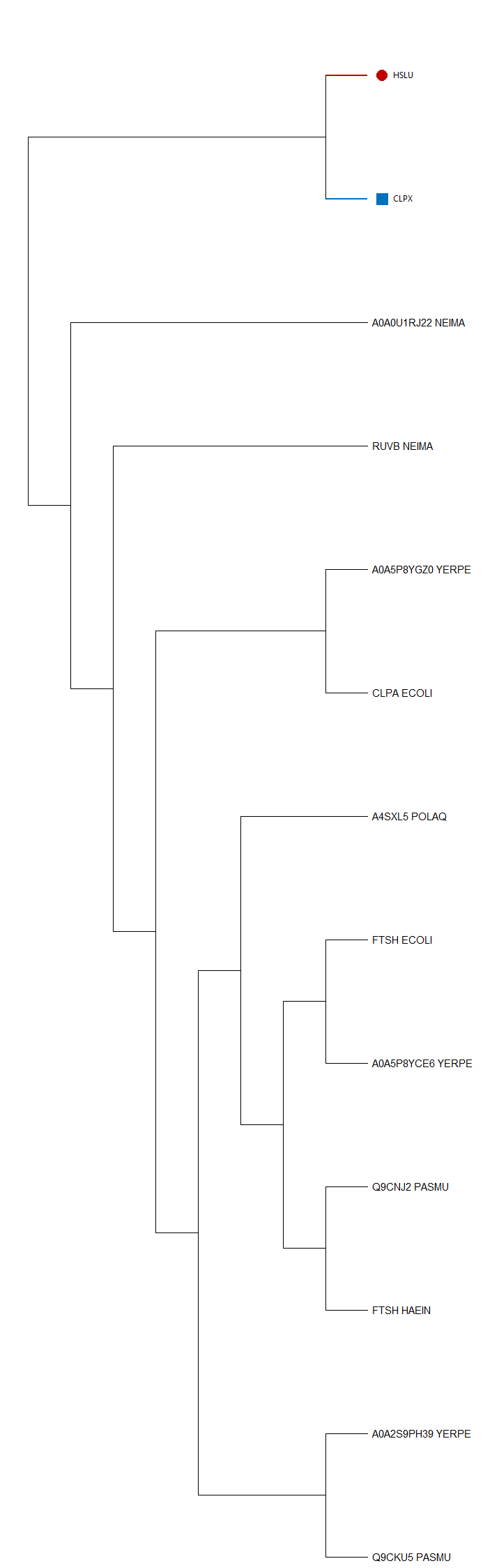
Для постройки дерева AC найденных белков были скопированы в форму поиска Uniprot, отображены на странице и скачены в файл. Далее было построено выравнивание и дерево (выравнивание с помощью muscle, дерево с помощью метода наибольшего правдоподобия из MEGA). В дереве были выделены семейства CLPX и HSLU (изображены на рисунке 1), на примере которых найдены паралоги и ортологи. Например, CLPX_HAEIN и HSLU_HAEIN, CLPX_PASMU и HSLU_PASUMU, CLPX_PSEMY и HSLU_PSEMY - три пары паралогов, а CLPX_PASMU и CLPX_HAEIN, HSLU_HAEIN и HSLU_PASMU, CLPX_PSEMY и CLPX_PASMU - три пары ортологов.
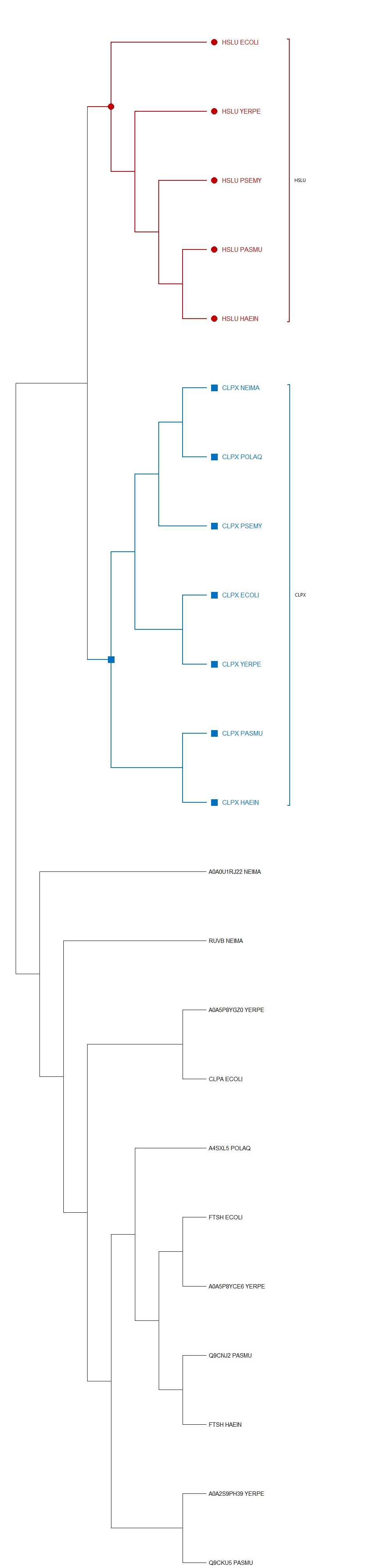
Далее ортологичные группы с более чем тремя последовательностями были "схлопнуты". Такими оказались группа CLPX (синяя) - АТФ-зависимые CLP протеазы из всех бактерий первого практикума и группа HSLU (красная) - субъединцы АТФ-зависимых протеаз из ECOLI, YERPE, PSEMY, PASMU и HAEIN. Филогения CLPX полностью повторяет филогению первого практикума, а филогения HSLU отливается тем, что кишечная и чумная палочки не объеденины рисунок 1. Компактизированное изображение представлено на рисунке 2.