Домены. Pfam. HMM профиль
Задание 1: выбор объектов и получение выравнивания
Для выполнения заданий Практикума я выбрала домен zf-MIZ, который в БД Pfam имеет
AC PF02891.
Имя MIZ является производным от
Msx-
interacting-
zinc finger. В молекулярной биологии MIZ-type zinc finger domain
является цинковым палецем, одним из ДНК-связывающих доменов.
Этот домен имеет SUMO (маленький убиквитино-подобный модификатор) лигазную активность и участвует в связывании ДНК и организации хромосомы.
Что известно для днного домена:
- 36 архитектур
- 2295 последовательностей
- 1 взаимодействие
- 765 видов
- 8 структур
|
Рис.1 Cтруктура MIZ1 zinc finger protein
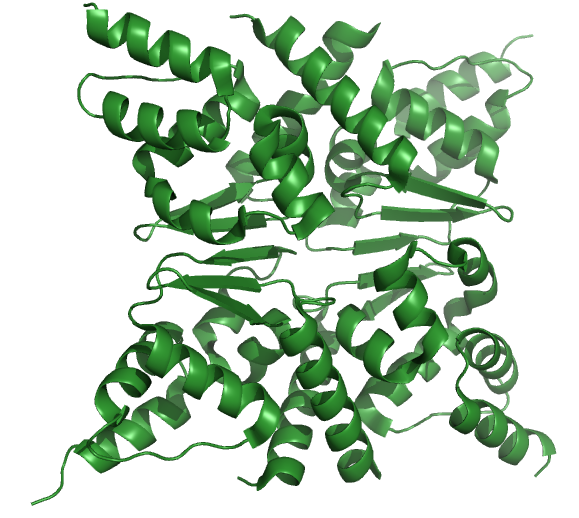
|
JalView-выравнивание этого домена доступно для просмотра по
ссылке
Были выбраны две доенные архитектуры(Рис.2). Помимо домена zf-MIZ в них присутствуют также домены
PRINIT(Домен PINIT - это домен белка, который содержится в белках PIAS) и в одной из них -
домен SAP(SAP (после SAF-A / B, Acinus и PIAS) мотив является предполагаемой ДНК/РНК-связывающей областью,
обнаруженной в различных ядерных и цитоплазматических белках).
Рис.2 Доменные архитектуры
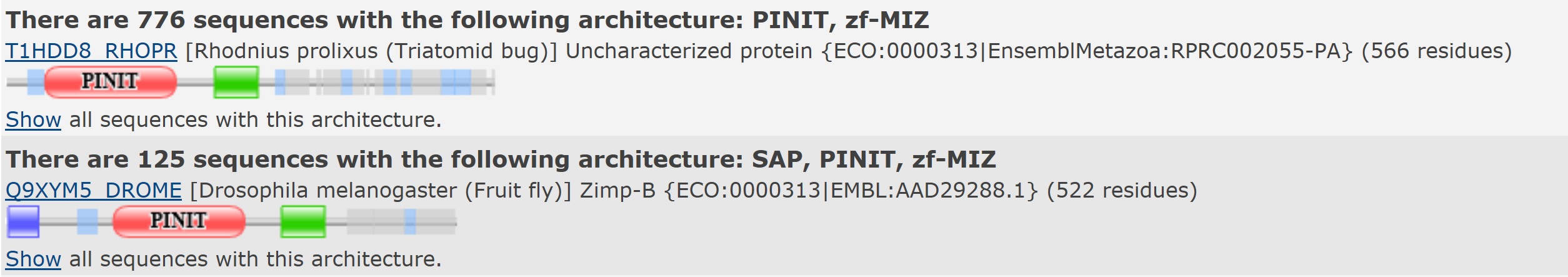
С помощью команды, запускающей скрипт swisspfam_to_xls.py
python swisspfam_to_xls.py -p PF02891 -i /srv/databases/pfam/swisspfam.gz -z -o architect.txt
я отобрала последовательности с указанным доменом и составила таблицу для Excel.
В список последовательностей были добавлкны колонки с информацией о таксономической принадлежности с помощью
команды, запускающей скрипт uniprot_to_taxonomy.py:
python uniprot-to-taxonomy.py -i tax.txt -o taxon.txt
В качестве подтаксонов я выбрала Царство Грибов( Fungi ), далее обозначим как F, и Подцарство Многоклеточные( Metazoa ),
далее обозначим как M.
Сводная Exel-таблица, содержащая также AC выбранных последовательностей доступна по
ссылке.
Далее с помощью Uniprot Retrieve получили fasta-последовательности для выравнивания в
JalView.
Всего было загружено 48 последовательностей, но я удалила 7 самых длинных. В выравниваниях выделяются заметные консервативные блоки,
которые примерно соответствуют расположению доменов.
Задание 2: построение филогенетического дерева домена
Дерево было построено алгоритмом Neighbour Joining cо 100 бутстреп-репликами. 1 и 2 - доменные архитектуры с Рис.1 соответственно;
F - Fungi и M - Metazoa. Цвета: 1 M - желтый, 2 M - красный, 1 F - голубой, 2 F - синий.
Рис.2 Филогенетическое древо
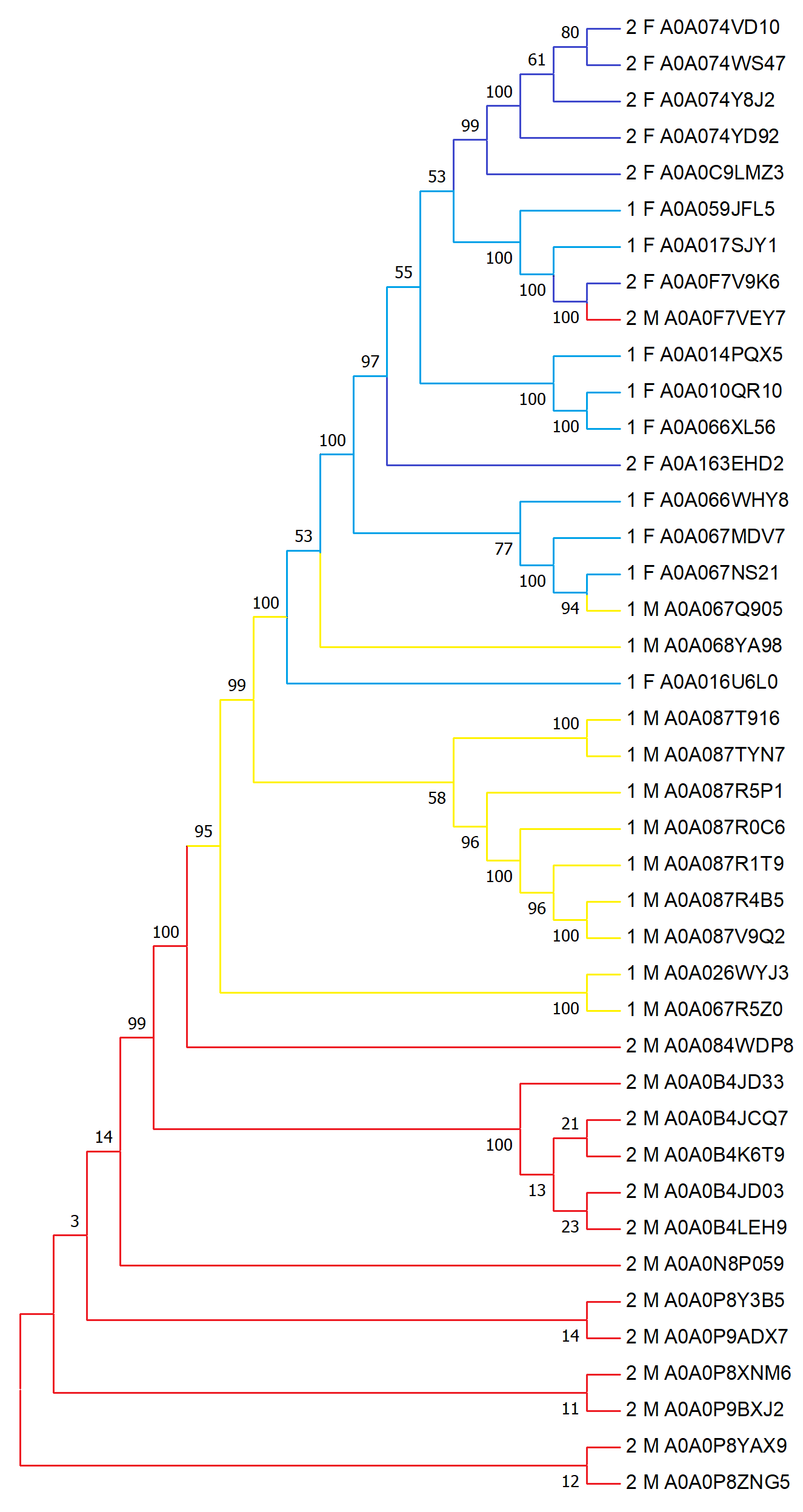
Скобочная формула древа:
((((((((((((2_M_A0A0P9ADX7,2_M_A0A0P9BXJ2),2_M_A0A0P8ZNG5),2_M_A0A0P8YAX9),2_M_A0A0P8Y3B5),2_M_A0A0P8XNM6),2_M_A0A0N8P059),(2_M_A0A0B4JCQ7,(2_M_A0A0B4JD03,(2_M_A0A0B4JD33,(2_M_A0A0B4K6T9,2_M_A0A0B4LEH9))))),2_M_A0A084WDP8),(1_M_A0A026WYJ3,1_M_A0A067R5Z0)),((1_M_A0A087T916,1_M_A0A087TYN7),(1_M_A0A087R5P1,(1_M_A0A087R0C6,(1_M_A0A087R1T9,(1_M_A0A087R4B5,1_M_A0A087V9Q2)))))),1_F_A0A016U6L0),1_M_A0A068YA98,((((1_F_A0A067NS21,1_M_A0A067Q905),1_F_A0A067MDV7),1_F_A0A066WHY8),(2_F_A0A163EHD2,(((1_F_A0A010QR10,1_F_A0A066XL56),1_F_A0A014PQX5),((((2_F_A0A0F7V9K6,2_M_A0A0F7VEY7),1_F_A0A017SJY1),1_F_A0A059JFL5),(2_F_A0A0C9LMZ3,(2_F_A0A074YD92,(2_F_A0A074Y8J2,(2_F_A0A074VD10,2_F_A0A074WS47)))))))));
Видно, что разделение грибов и животных прошло достаточно хорошо. А вот разные архитектуры заметно разделились только для животных, грибы
имеют несколько перемешанный вид, но все-таки обособлены малыми группами.
Из-за подобного разделения можно предположить, что сначала имело место разделение на таксоны, а уже после на доменные архитектуры.
Кроме того, стоит помнить о том, что малая часть последовательностей, выходящая за рамки нормы, отсеялась на стадии Bootstrap-анализа.
На Главную страницу
На страницу Семестра

