Практикум 4. Паралоги, визуализация.
В задании реконструируется филогения гомологов ClpX-субъединицы Clp протеазы E.coli.
Подготовка выравнивания.
Из базы данных о протеомах бактерий были отобраны протеомы 7 бактерий практикума 1. Эти протеомы были объединены в единый файл.
Далее был осуществлён поиск гомологов при помощи blastp:
makeblastdb -in proteomes.fasta -dbtype prot -out proteomes_db
blastp -query CLPX_ECOLI.fasta -db proteomes_db -evalue 0.001 -out clpx_ecoli_blastp.out
Выдача blasp:
sp|P0A6H1|CLPX_ECOLI ATP-dependent Clp protease ATP-binding sub... 860 0.0 sp|Q8ZC66|CLPX_YERPE ATP-dependent Clp protease ATP-binding sub... 805 0.0 sp|B4EU54|CLPX_PROMH ATP-dependent Clp protease ATP-binding sub... 769 0.0 sp|Q92QQ2|CLPX_RHIME ATP-dependent Clp protease ATP-binding sub... 596 0.0 sp|Q8UFY5|CLPX_AGRFC ATP-dependent Clp protease ATP-binding sub... 596 0.0 sp|Q8G0I5|CLPX_BRUSU ATP-dependent Clp protease ATP-binding sub... 586 0.0 sp|Q9JTX8|CLPX_NEIMA ATP-dependent Clp protease ATP-binding sub... 557 0.0 sp|B4F171|HSLU_PROMH ATP-dependent protease ATPase subunit HslU... 96.7 8e-22 sp|Q8ZJJ5|HSLU_YERPE ATP-dependent protease ATPase subunit HslU... 95.1 2e-21 sp|P0A6H5|HSLU_ECOLI ATP-dependent protease ATPase subunit HslU... 93.6 7e-21 sp|Q92TA7|HSLU_RHIME ATP-dependent protease ATPase subunit HslU... 92.8 1e-20 sp|Q8UJ87|HSLU_AGRFC ATP-dependent protease ATPase subunit HslU... 92.0 2e-20 sp|Q8FY12|HSLU_BRUSU ATP-dependent protease ATPase subunit HslU... 90.9 5e-20 tr|B4F2B3|B4F2B3_PROMH ATP-dependent zinc metalloprotease FtsH ... 46.6 2e-05 sp|P0AAI3|FTSH_ECOLI ATP-dependent zinc metalloprotease FtsH OS... 46.2 2e-05 tr|A0A2S9PH39|A0A2S9PH39_YERPE Putative magnesium chelatase fam... 46.2 2e-05 tr|A0A5P8YCE6|A0A5P8YCE6_YERPE Cell division protein OS=Yersini... 45.8 2e-05 tr|A0A0H3GCZ6|A0A0H3GCZ6_BRUSU ATP-dependent zinc metalloprotea... 45.4 3e-05 tr|Q92M98|Q92M98_RHIME ATP-dependent zinc metalloprotease FtsH ... 45.4 3e-05 tr|Q7CT50|Q7CT50_AGRFC ATP-dependent zinc metalloprotease FtsH ... 45.4 4e-05 sp|Q9JUB0|RUVB_NEIMA Holliday junction ATP-dependent DNA helica... 42.7 2e-04 tr|A0A0U1RJ22|A0A0U1RJ22_NEIMA Replication-associated recombina... 40.8 9e-04
Создан файл с перечислением ID находок blastp в USA формате.
Fasta-последовательности белков были выровнены muscle:
seqret @prot.list stdout | cut -d ' ' -f 1 | muscle > homolog_alignment.fasta
Реконструкция филогении.
По выравниванию в MEGA7 было построено ML-дерево.
Дерево в newick-формате было визуализировано в FigTree и укоренено в среднюю точку. На рисунках 1 и 2 приведены изображения этого дерева.
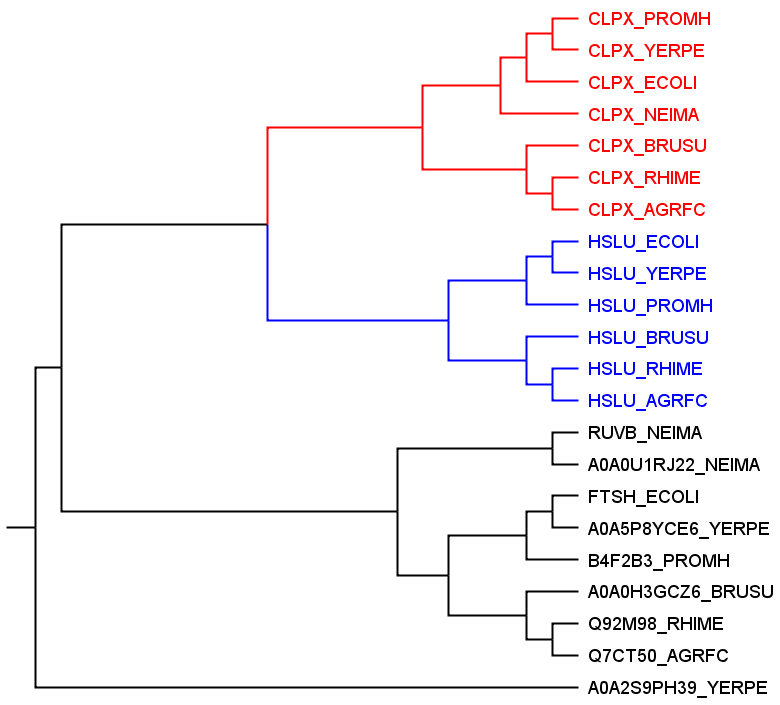
Рис.1
Цветом покрашены группы попарно ортологичных белков.
4 белка металлопротеаз не выделились в единую кладу с тремя и более последовательностями, поэтому не были отмечены цветом на рисунках.
Пары паралогов:
1) HSLU_PROMH - CLPX_PROMH
2) CLPX_BRUSU - HSLU_BRUSU
3) CLPX_AGRFC - HSLU_AGRFC
Пары ортологов:
1) CLPX_PROMH - CLPX_YERPE
2) CLPX_BRUSU - CLPX_RHIME
3) HSLU_AGRFC - HSLU_BRUSU
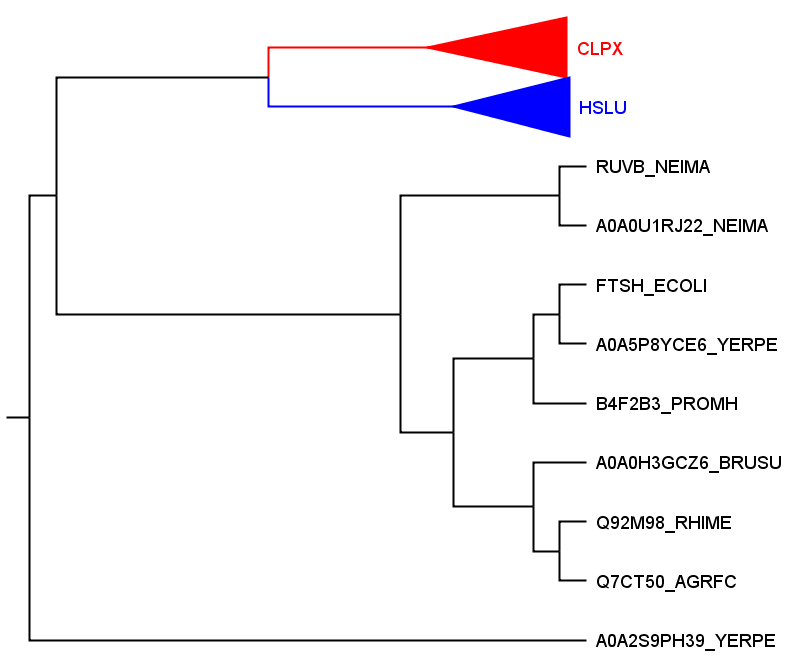
Рис.2
Клады с ортологичными белками схлопнуты.
1) CLPX:
ClpX субъединица Clp протеазы. Присутствует у всех бактерий в выборке. Филогения белков немного отличается от филогении бактерий: PROMH и YERPE формируют отдельную кладу.
2) HSLU:
HslU субъединица протеазы с шаперонной активностью. Присутствует у 6 из 7 бактерий, отсутствует у NEIMA. Филогения белков полностью соответствует филогении бактерий.