Алгоритмы (окончание). Укоренение. Сравнение деревьев. Бутстрэп
Петренко Павел
Факультет биоинженерии и биоинформатики, Московский Государственный Университет имени М.В.Ломоносова
Реконструкция дерева по нуклеотидным последовательностям
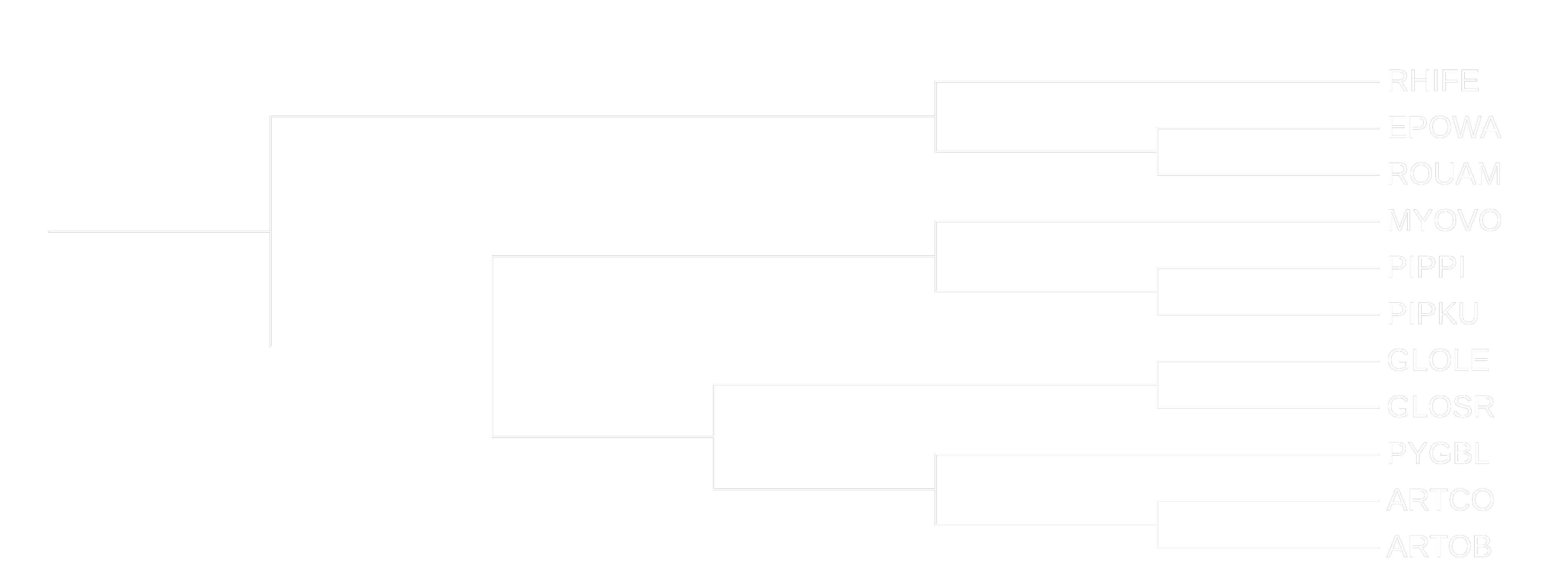
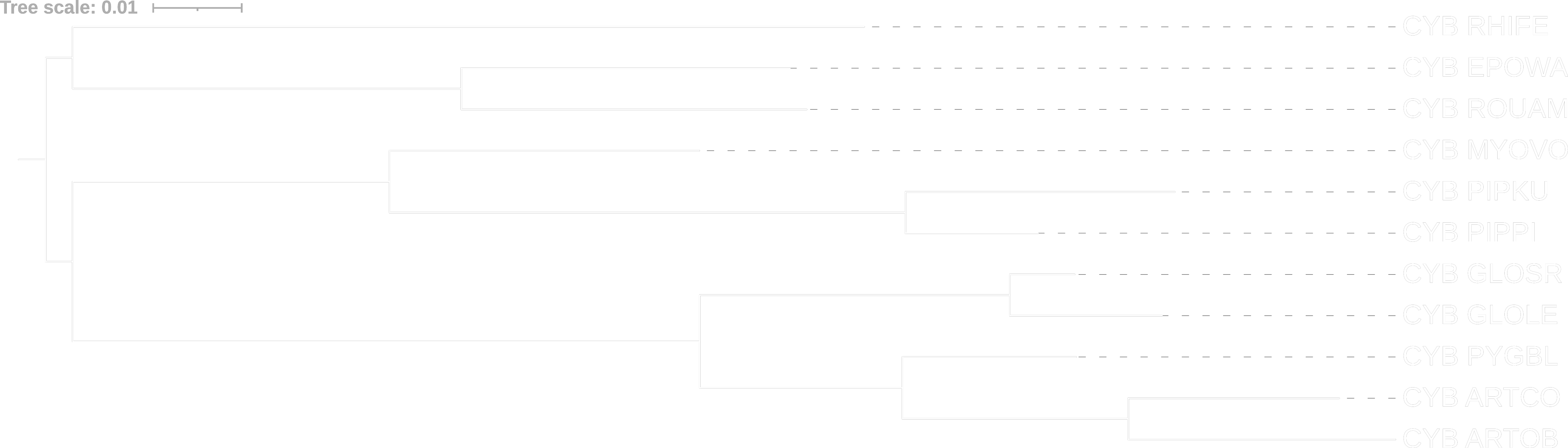
Сразу покажем деревья из предыдущих практикумов, чтобы нам было легче их сравнивать с новым, построенным по нуклеотидным последовательностям:
Подготовка:
Сначала достанем записи, описывающие митохондриальный геном наших зверюшек:
Теперь запишем все последовательности в один файл:
Теперь подготовим файл (как в предыдущем отчёте) для запуска программы fastme и реконструируем дерево (c опцией -d для нуклеотидного выравнивания):
Видим, что полученное дерево (построенное по нуклеотидному выравниванию последовательностей 12S rRNA) совпадает с деревом из предыдущего практикума (которое мы строили по белковому выравниванию цитохрома B), за исключением некоторых эволюционных расстояний.
Укоренение во внешнюю группу
Нижним таксоном, к которому принадлежат все мои зверюшки оказался отряд, поэтому для внешней группы я решил взять кого-то из отряда Грызунов. Мой выбор пал на Желтогорлую мышь (APOFL) (тоже мышь, но нелетучая). Построим по цитохромам B новое дерево с укоренением во внешнюю группу. Сначала в рабочую директорию скопировали текстовый файл cyb.list с предыдущего практикума и добавили строку:
Далее по полному подобию командами из предыдущего отчёта построили дерево:
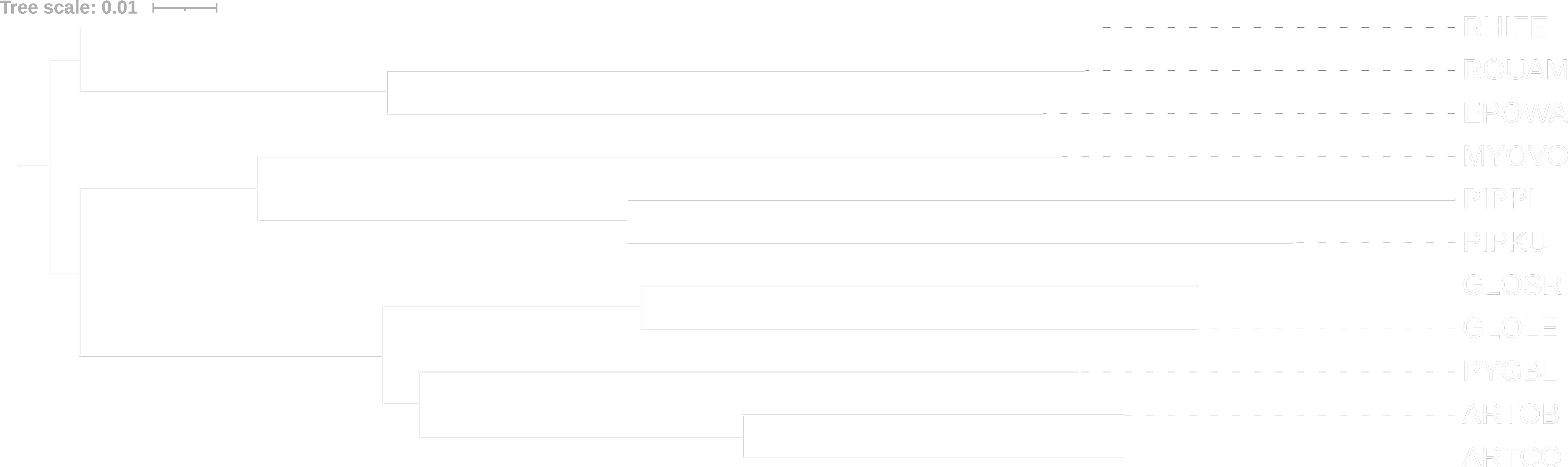
В данном случае видим, что большой подковонос (RHIFE) является сестринским ко всем остальным зверушкам из подотряда Yangochiroptera (GLOLE, GLOSR, PYGBL, ARTCO, ARTOB, PIPKU, PIPPI, MYOVO), что является в корне неправильно, так как мы знаем, что большой подковонос (RHIFE) относится к подотряду Yinpterochiroptera и является сестринской для летучей собаки (ROUAM) и фруктовой летучей мыши Уолберга с эполетом (EPOWA). Если же мы углубимся в деление на подотряды, то поймём, что оно основано на анатомических, физиологических и поведенческих особенностях, в то время как некоторые современные учёные считают, что данное деление устарело и оно должно быть изменено в соответствии с молекулярными и генетическими особенностями организмов (что возможно и наблюдается в наших результатах).
Бутстреп
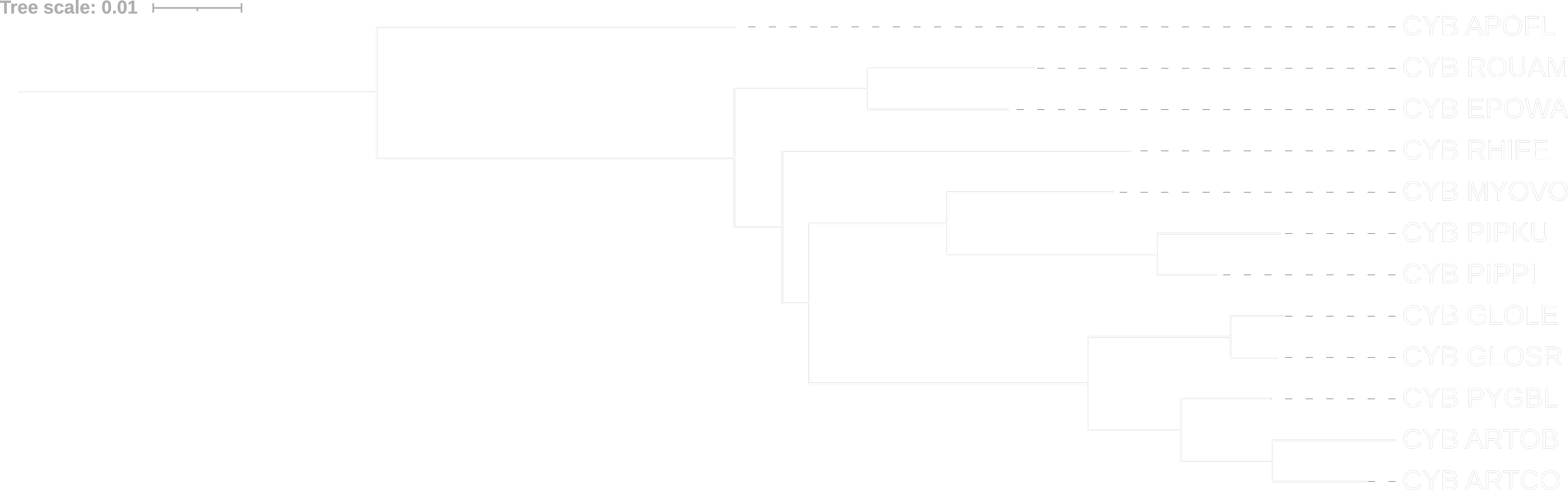
Теперь посмотрим на то же самое дерево, только зададим 100 реплик бутстрепа.
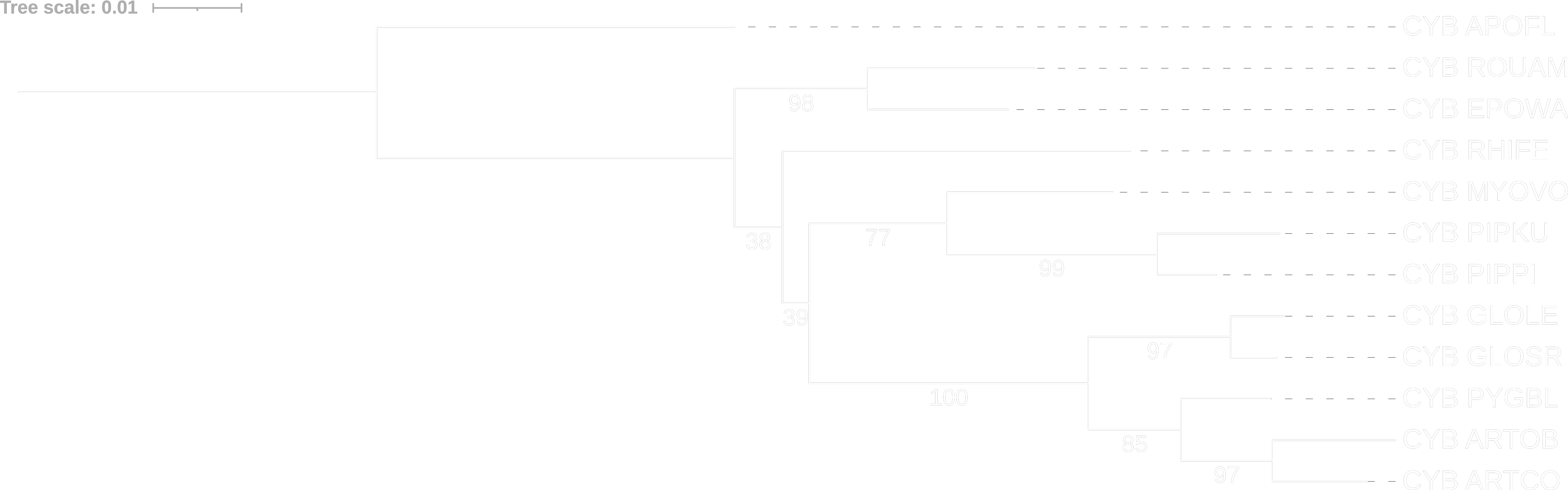
Видим, что неправильно реконструированные ветви (относящие большого подковоноса (RHIFE) к подотряду Yangochiroptera и отделяющие от подотряда Yinpterochiroptera) имеют малую бутстреп поддержку (всего 38% и 39%). Очевидно, данное дерево неверно. Возможно такое дерево получилось в результате того, что семейство летучих мышей (Rhinolophoidea), к которому относится большой подковонос (RHIFE) отделилось очень рано в подотряде Yinpterochiroptera, что со временем привело к накоплению мутаций и сближению его с семействами в подотряде Yangochiroptera.