Алгоритмы филогенетической реконструкции
Петренко Павел
Факультет биоинженерии и биоинформатики, Московский Государственный Университет имени М.В.Ломоносова
Выбранные животные
Напомню, что я в текущем блоке биоинформатики выбрал для работы рукокрылых. Конкретные зверюшки, их таксономия и мнемоника представлены в первом отчёте.
Построение выравнивания цитохромов B из выбранных животных
Сначала в рабочей директории создали текстовый файл cyb.list со следующими строками:
sw:cyb_GLOSR
sw:cyb_PYGBL
sw:cyb_RHIFE
sw:cyb_ARTCO
sw:cyb_ARTOB
sw:cyb_ROUAM
sw:cyb_EPOWA
sw:cyb_PIPKU
sw:cyb_PIPPI
sw:cyb_MYOVO
Затем вытащили необходимые нам последовательности цитохромов B:
И выровняли:
Реконструирование дерева
Так как программа FastME принимает только выравнивания в формате "phylip-relaxed", то сначала переведём наше выравнивание в него с помощью небольшого питоновского скрипта:
from sys import argv
inh = open("cyb-alignment.fasta", "r")
outh = open("cyb.phy", "w")
alignment = AlignIO.parse(inh, "fasta")
AlignIO.write(alignment, outh, "phylip-relaxed")
inh.close()
outh.close()
Теперь у нас всё готово, чтобы реконструировать деревья:
Сравнение полученных деревьев
Для наглядности и удобства сначала покажем филогенетическое дерево из предыдущего прака:
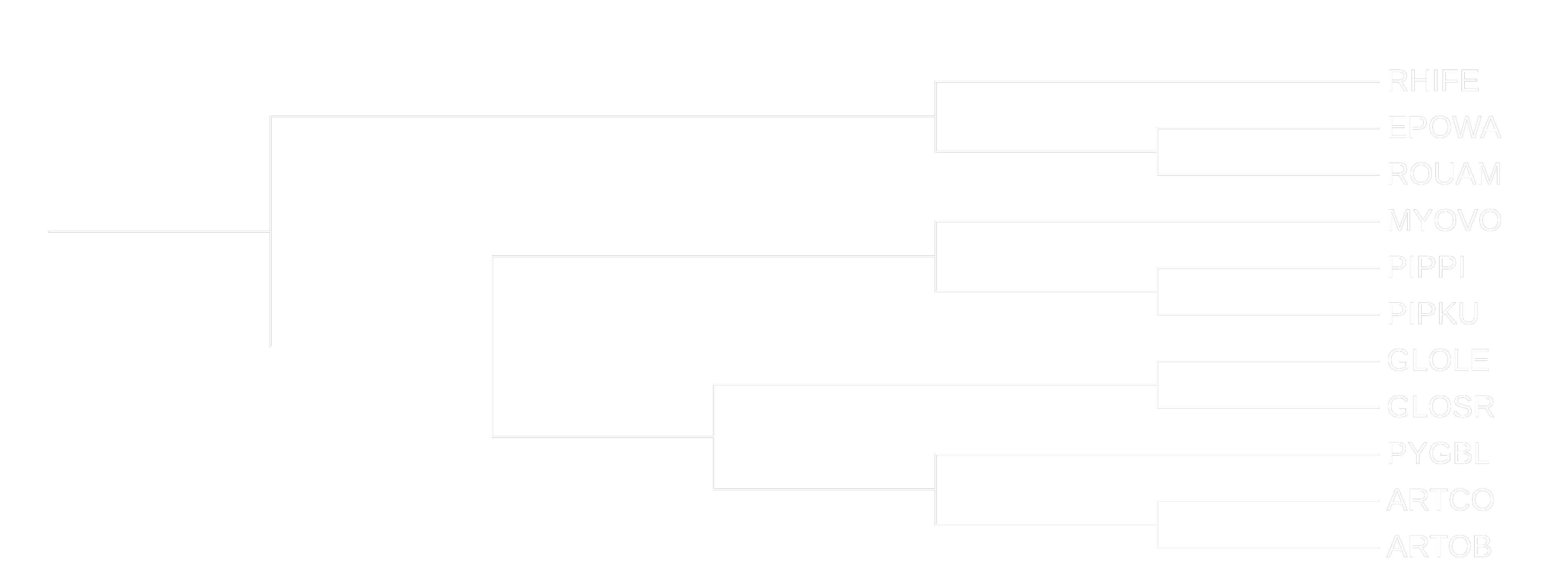
Ниже представлены визуализации деревьев, построенных с помощью выше упомянутых программ по выравниваниям аминокислотных последовательностей цитохромов B. Все деревья были укоренены так, чтобы разделить их на подотряды Yinpterochiroptera и Yangochiroptera.
fastme
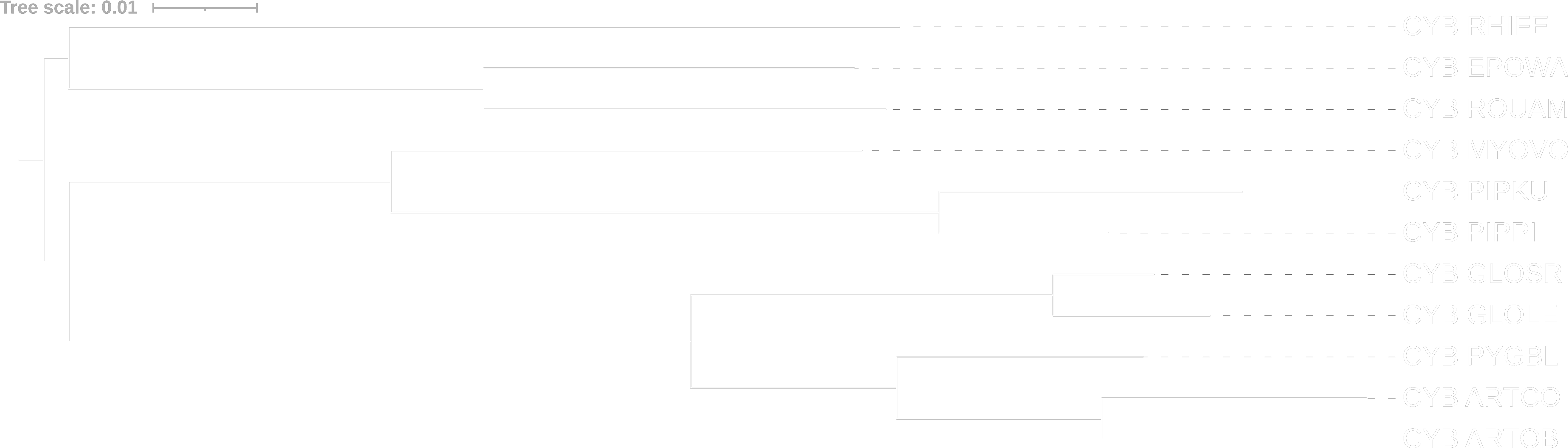
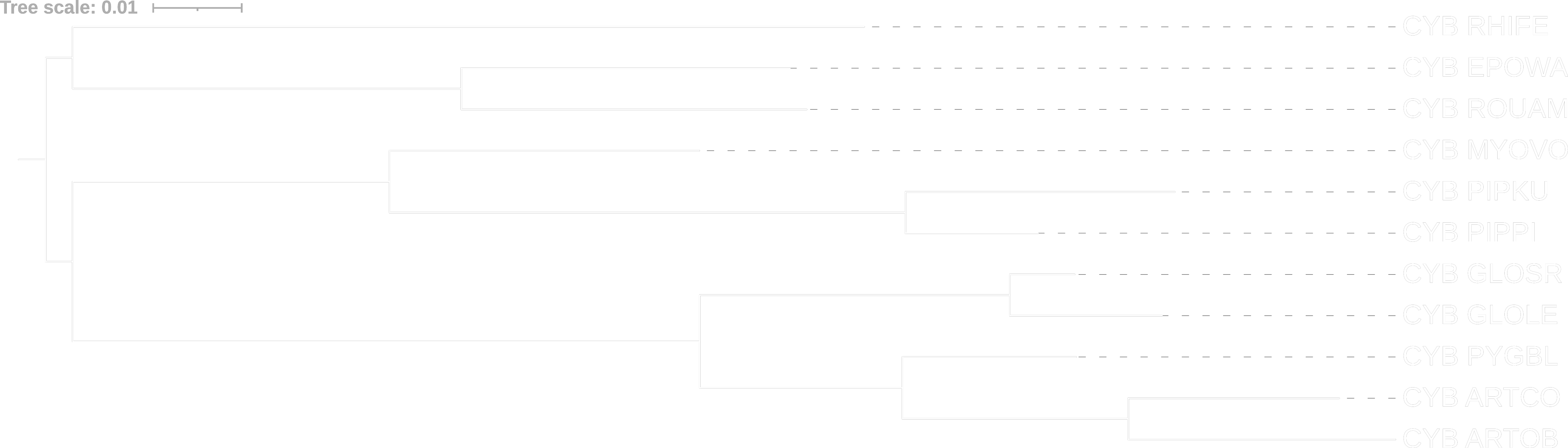
Видим, что между собой деревья отличаются лишь длиной ветвей из-за использования разных моделей оценки эволюционных расстояний. Из интересного можем заметить, что оценка p-distance считает цитохром B длинноногого миотиса (MYOVO) более "прогрессивным", чем цитохром B фруктовой летучей мыши Уолберга с эполетом (EPOWA) в сравнении с оценкой MtREV. Если сравнивать деревья с полученным из предыдущего прака, то отличий нет.
iqtree
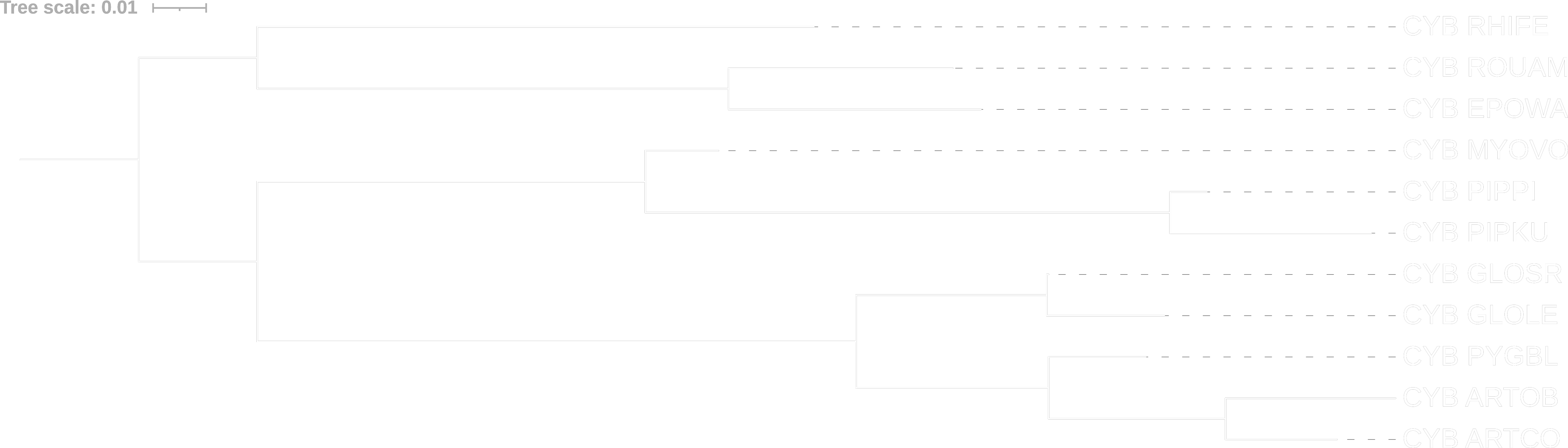
Полученное дерево совпадает с предыдущими и отличается опять лишь эволюционными расстояниями. Так, на дереве, полученном с помощью программы iqtree видно, что цитохромы B большого подковоноса (RHIFE), длинноногого миотиса (MYOVO) и землеройковидного листоноса (GLOSR) менее "прогрессивны", чем показали деревья, полученные с помощью программы fastme. Также программа iqtree показала, что цитохромы B нетопырей (PIPKU и PIPPI) изменились сильнее, а цитохромы B длинноязыких листоносов (GLOLE и GLOSR) слабее, в сравнении с программой fastme.