Моделирование эволюции гена
(А:110,((В:65,(С:40,D:40):25):35,(Е:45,F:45):50):10);
под веткой a имеется ввиду ветка между A и кластером BCDEF, а не расстояние между A и корнем |
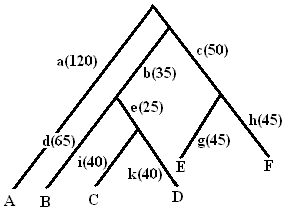 |
A B C D E F b . * * * . . c . . . . * * e . . * * . . |
Nx = nx * 8,19, где nx – длина ветви x.
Получим последовательности всех листьев и промежуточных узлов (программа msbar, скрипт):
msbar aroE_Ecoli.fasta A.fasta -point 4 -count 901 -auto msbar aroE_Ecoli.fasta BCDEF.fasta -point 4 -count 82 -auto msbar BCDEF.fasta BCD.fasta -point 4 -count 287 -auto msbar BCD.fasta B.fasta -point 4 -count 532 -auto msbar BCD.fasta CD.fasta -point 4 -count 205 -auto msbar CD.fasta C.fasta -point 4 -count 328 -auto msbar CD.fasta D.fasta -point 4 -count 328 -auto msbar BCDEF.fasta EF.fasta -point 4 -count 410 -auto msbar EF.fasta E.fasta -point 4 -count 369 -auto msbar EF.fasta F.fasta -point 4 -count 369 -auto |
- алгоритм максимального правдоподобия (программа fdnaml)
Получено деревоfdnaml list.fasta -ttratio 1 -auto
+--------------------------F +---------------------------4 | +-----------------E | | +------------------------------B 3--------------1 | | +--------------------D | +----------2 | +-----------------C | +---------------------------A - алгоритм Neighbor-joining (программа fneighbor с параметром -treetype n по умолчанию)
(программа fdnadist определяет попарные расстояния между последовательностями, выходной файл *.fdnadist)fdnadist list.fasta -ttratio 1 -auto fneighbor list.fdnadist -outfile NJ.fneighbor -auto
+------------------E +----------------------------1 ! +------------------------F ! ! +---------------------------------B 2---------------3 ! ! +-----------------C ! +---------4 ! +---------------------D ! +----------------------------A - UPGMA (программа fneighbor с параметром -treetype u)
fdnadist list.fasta -ttratio 1 -auto fneighbor list.fdnadist -outfile UPGMA.fneighbor -treetype u -auto
+-------------------------------------A +--------4 ! ! +-------------------------------B ! +-----3 ! ! +-------------------C --5 +-----------1 ! +-------------------D ! ! +---------------------E +------------------------2 +---------------------F
| ветка | максимального правдоподобия | Neighbor-joining | UPGMA | Реальное дерево |
| b .***.. | + | + | + | + |
| c ....** | + | + | + | + |
| e ..**.. | + | + | + | + |
Топология всех трех деревьев совпадают с истинным. Деревья, построенные алгоритмами максимального правдоподобия
и Neighbor-joining идентичны, незначительно отличаются только длины некоторых ветвей.
UPGMA-дерево, в отличие от двух предыдущих, укорененное. Оно также ультраметрично, то есть
длины всех "полных" ветвей равны (расстояния от корня до листьев одинаковы). Однако это
неверно – исходное дерево не является ультраметричным.
Итак, все использованные алгоритмы правильно восстановили ход эволюции (топологию, но не корень).
Bootstrap и drawtree
Для этого используем программы fseqboot (построение 100 "бутстреп-реплик" дерева, при значении параметра -test b по умолчанию), fdnaml (получение скобочных структур для каждого дерева) и fconsense (вычисление "консенсусного" дерева).
fseqboot list.fasta -auto fdnaml list.fseqboot -ttratio 1 -auto fconsense list.treefile |
Получено неукорененное дерево:
+--------------------B
+100.0-|
| | +-------------A
| +100.0-|
+------| | +------E
| | +100.0-|
| | +------F
| |
| +---------------------------D
|
+----------------------------------C
Полученное дерево совпадает с реальным. Бутстреп-значения всех внутренних ветвей равны 100, то есть эти ветви вошли во все бутстреп-реплики дерева. Таким образлм, не вошедших в конечное дерево ветвей (с малыми бутстреп-значениями) нет:
Sets included in the consensus tree Set (species in order) How many times out of 100.00 ..**** 100.00 ...*** 100.00 ...**. 100.00 Sets NOT included in consensus tree: NONE |
fdrawtree str.txt drawtree.ps (иллюстрация исходного дерева) |