Семестры
Сайт ФББ МГУ
Kodomo Wiki
NCBI
RanHummer personal web-site
Сравнение геномов
1. Построить карту сходства хромосом двух родственных бактерий
Были выбраны бактерии рода Mesorhizobium: Mesorhizobium opportunistum WSM2075 и Mesorhizobium loti MAFF303099.
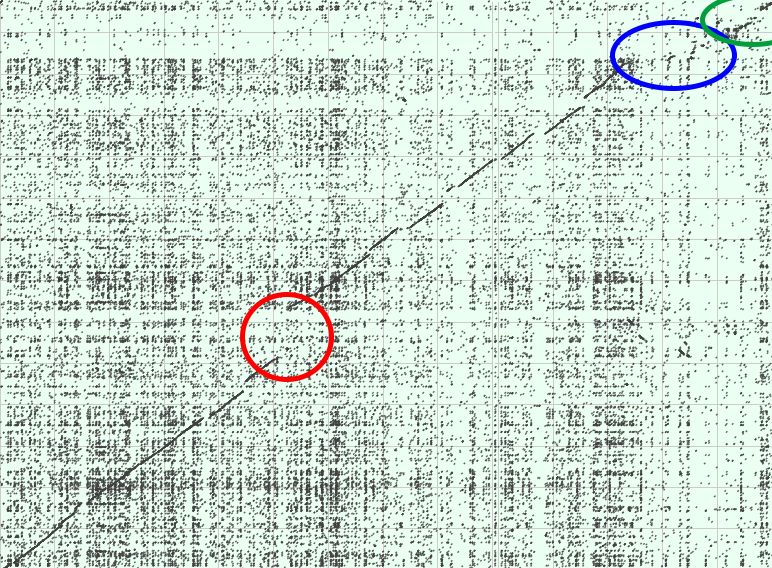
Их карта локального сходства:

В таком виде смотреть не очень удобно, поэтому я развернул одну кольцевую хромосому и сдвинул начало отсчета. Результат гораздо более привычен. Если не обращать внимания на шум, можно выделить полтора десятка хороших гомологичных участков, область сильной делеции (вставки) в первой трети (красная), почти не гомологичная область под конец отсчета (синяя) и область некольких маленьких (относительно) участков гомологий в самом конце (зеленая). Что интересно, транслокаций совершенно не видно, почти все различия заключаются во вставках (делециях).
2. Описать сходство и различие геномов близкородственных бактерий
Я взял 1-е хромосомы Brucella canis, Brucella ovis и Brucella pinnipedialis.
Ссылка на genomes.tsv
Ссылка на папку с результатами работы NPGE
Синтеничные участки - g-блоки.
Число g-блоков: 4
Выравнивание:
|
Brucella canis |
- |
g3x858113 |
g3x123 |
i1x5 |
g3x514767 |
g3x766025 |
i1x2 |
|
Brucella pinnipedialis |
g3x766025 |
g3x858113 |
g3x123 |
i2x5 |
g3x514767 |
- |
- |
|
Brucella ovis |
- |
g3x858113 |
g3x123 |
i2x5 |
g3x514767 |
g3x766025 |
- |
|
Консервативность |
- |
g3x858113 |
- |
- |
g3x514767 |
- |
- |
Ядро пангенома - s-блоки.
Число s-блоков: 148
Суммарная длина: 2034679
Процент от длины генома в среднем: 96.44%
Процент консервативных позиций, если объединить s-блоки: 99.6019%
Повторы - r-блоки
|
Блок |
Число фрагментов |
Длина |
Процент консервативных колонок |
Число генов |
|
r50x849 |
50 |
849 |
95,58% |
112 |
|
r14x100 |
14 |
100 |
90,5% |
8 |
Делеции - h-блоки
|
Блок |
Число фрагментов |
Длина |
Процент консервативных колонок |
Число генов |
В ком нет |
|
h2x14776 |
2 |
14776 |
99,45% |
38 |
Brucella canis |
|
h2x7500 |
2 |
7500 |
99,81% |
17 |
Brucella ovis |
|
h2x6109 |
2 |
6109 |
99,91% |
17 |
Brucella canis |
Уникальные последовательности - u-блоки
|
Блок |
Число фрагментов |
Длина |
Число генов |
В ком есть |
Аннотация |
Горизонтальный перенос от другой бактерии |
|
1 |
148 |
1 |
Brucella pinnipedialis |
Ген не аннотирован |
Возможен. Последовательность блока выровнялась на геномы многих представителей рода Brucella. |
|
|
u1x118 |
1 |
118 |
1 |
Brucella ovis |
Ген не аннотирован |
Последовательность блока выровнялась на многих представителей рода Brucella и на представителей из рода Sphingobium, Sphingomonas и Sphingopixys (по одному представителю), поэтому он очень вероятен. |
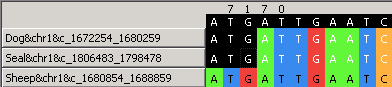
Несоответствия между аннотациями генов
Блок: s3x8006
Координаты блока: 1672254-1680259 B.canis, 1680854-1688859 B. ovis
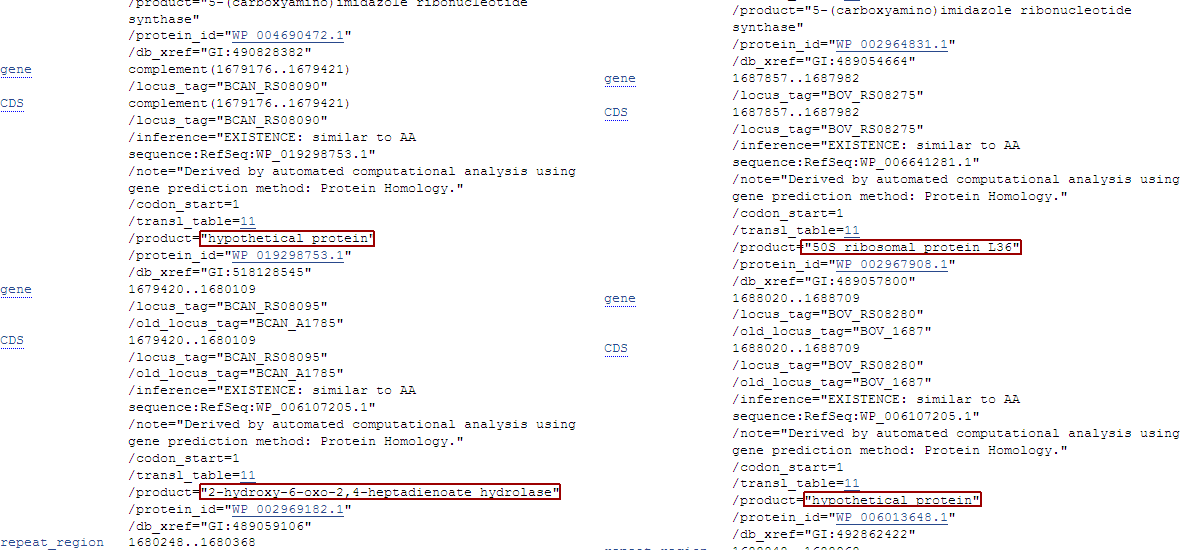
Сверху показано 2 несоответсвия в аннотациях генов в Brucella canis(слева) и Brucella ovis(справа) в предпоследнем и последнем генах блока. В первом случае, гены по-разному называются и совершенно разные белки (эти гены, очевидно, неортологичны), а во втором белки очень похожи, но у B. canis 2-hydroxy-6-oxo-2,4-heptadienoate hydrolase, а у B. ovis - hypotetical protein. Эти гены, очевидно, ортологичны, но в случае B. ovis ген хуже аннотирован. Координаты старт-кодонов одни и те же. Скриншот qnpge с координатами старт-кодонов вышеописанных ортологичных генов с разной аннотацией приведен ниже.