
Практикум 3
1. Укоренение с использованием внешней группы
Скобочная форма дерева
Деревья, построенные методом максимальной экономии ("Maximum parsimony") невозможно укоренить в среднюю точку, но можно укоренить с помощью внешней группы.
В качестве внешней группы белок того же семейства из сенной палочки (Bacillus subtilis, мнемоника BACSU в Uniprot).
После реконструкции дерева нужно в меню Subtree выбрать Root и указать в качестве корня ветвь, ведущую к BACSU. Наконец, чтобы получить изображение укоренённого дерева без BACSU, нужно воспользовавться кнопкой "Show Subtree Separately" (изображение голубой лупы на фоне дерева на левой панели окна MEGA),Открыл JalView командой jalview в терминале, в меню File выбрал Fetch sequences, в окне Select Database выбрал Uniprot. Убрал галочку у Autosearch, а то мешает тратой времени на загрузку после каждого редактирования запроса. Вбил запрос "EFTS_AGRFC; EFTS_BRUSU; EFTS_BURCA; EFTS_HAEIN; EFTS_RHIME; EFTS_ROSDO; EFTS_SACD2; EFTS_SHEDO; EFTS_BACSU", где на первом месте мнемоника белка, а на втором после _ идёт мнемоника организма из 1 практикума + мнемоника Bacillus subtilis. Выделил выдачу, нажал Ok внизу. Открылось окно с последовательностями. В меню выбрал Web Service → Alignment → Run Muscle With Defaults. Получилось выравнивание. Сохранил его в формате fasta, переписал в файле для удобства аннотации на мнемоники организмов.
Открыл MEGA. File → Open a File/Session. Появилось всплывающее окно "Analyze or align?". Выбрал Analize, в новом окне выбрал Protein sequences. Реконструировал дерево Maximum parsimony методом.
После реконструкции дерева в меню Subtree выбрал Root и указал в качестве корня ветвь, ведущую к BACSU, нажав на неё. Чтобы получить изображение укоренённого дерева без BACSU, в меню слева нажал кнопку "Show Subtree Separately" (у меня не синяя, а красная),2. Бутстрэп
При осуществлении Maximum parsimony метода в всплывающем окне с параметрами в графе Test of Phylogeny выбрал "Bootstrap method". Поставил число реплик, равное 100.
Деревья, названные "Original tree" и "Bootstrap consensus tree", не отличаются.
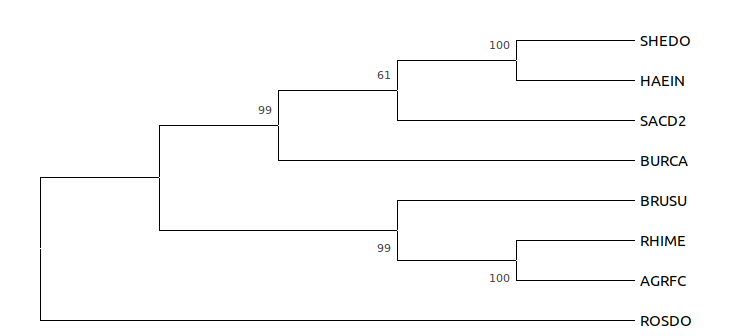
Что означают цифры
Процент деревьев, в которых встретилась данная ветвь.

3. Построение дерева по нуклеотидным последовательностям
Нашёл на сайте NCBI геномы бактерий, в геномах нашёл последовательности 16s РНК, поместил в 1 файл, выровнял, загрузил в MEGA описанным выше способом. Получил дерево, изображённое на Рис. 2.
