Пространственное строение белка дегидратазы (dehydratase) из генома бактерии Chloroflexus aurantiacus, штамм J-10-fl
Jmol — программа, дающая возможность просмотра структуры молекул в трёх измерениях. Она написана на языке Java и поддерживает многие форматы файлов: Protein Data Bank (pdb), MDL Molfile (mol), Crystalographic Informatic File (cif) и так далее.
Protein Data Bank — это банк данных 3-D структур нуклеиновых кислот и белков. Файлы в pdb-формате содержат в себе информацию о белке (состав молекулы, трёхмерная структура), полученную методами рентгеновской кристаллографии или ЯМР-спектроскопии.
Для каждого белка и нуклеиновой кислоты из PDB существует свой идентификатор. Для белка дегидратазы бактерии C. aurantiacus, штамм J-10-fl, ID — 4E3E.
Трёхмерная структура белка представлена на Рисунке 1. PDB-файл с информацией о белке можно скачать здесь.
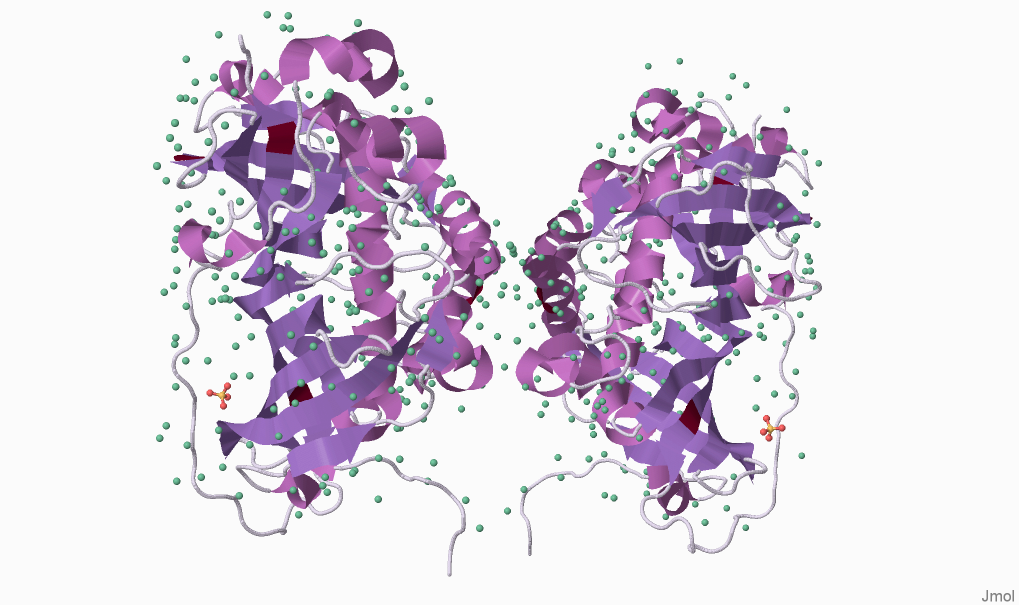
Рисунок 1. Пространственное строение дегидратазы C. aurantiacus, штамм J-10-fl (идентификатор записи PBD 4E3E).
Рисунок получен с помощью программы Jmol.
Зеленоватым цветом обозначены молекулы воды,
сиреневым — α-спирали, фиолетовым — β-листы; участки, не обладающие вторичной структурой — сероватым. Бордовые участки β-листов — селенметионин, жёлтый и красный — атомы серы и кислорода соответственно, входящие в состав сульфат-иона.
Для того, чтобы данный белок выглядел именно так, как на приведённом выше изображении, был написан Jmol скрипт. Скачать скрипт можно здесь. Его текст размещён ниже:
load 4E3E.pdb
backbone off
wireframe off
ribbons off
cpk off
# selects main chain
select *.CA
cartoons
#coloring
color [158,113,197]
select 118-122
color [230,220,240]
select 193-195
color [230,220,240]
select 351-353
color [230,220,240]
select 320-338
color [230,220,240]
select 280-288
color [230,220,240]
select 214
color [230,220,240]
select 208-211
color [230,220,240]
select 201-204
color [230,220,240]
select 241-249
color [230,220,240]
select 3-10
color [230,220,240]
select 151-170
color [230,220,240]
select 16-19
color [230,220,240]
select 268-270
color [230,220,240]
select 176-181
color [230,220,240]
select 302-307
color [230,220,240]
select 43-44
color [230,220,240]
select 134-138
color [230,220,240]
select 97-104
color [230,220,240]
select 58-64
color [230,220,240]
select 29
color [230,220,240]
select 23-26
color [230,220,240]
select 83-84
color [230,220,240]
select 227-229
color [230,220,240]
#HOH coloring
select hoh
cpk 110
color [113,196,157]
#SO4 coloring
select SO4
backbone 100
wireframe 50
cpk 110
select 500.s
color [255,201,102]
select 500.o4
color [255,102,102]
select 500.o1
color [255,102,102]
select 500.o2
color [255,102,102]
select 500.o3
color [255,102,102]
#two parts
select helix
color [196,113,194]
#mse
select mse
color [128,0,43]
#bgrnd
background [249,249,249]
center
rotate Z 26
Для того, чтобы посмотреть скрипт в действии, необходимо скачать сам скрипт и pdb-файл, а также иметь установленной программу Jmol.
Кроме координат молекул, как было написано ранее, в pdb-файле содержится информация об источнике белка, его структура и использованный метод анализа. Информация, выделенная из данного файла представлена ниже в Таблице 1 и 2.
| Графа | Значение |
| TITLE | crystal structure of putative maoc domain protein dehydratase from chloroflexus aurantiacus j-10-fl |
| COMPD | mol_id: 1
molecule: maoc domain protein dehydratase chain: a, b engineered: yes |
| SOURCE | mol_id: 1
organism_scientific: chloroflexus aurantiacus organism_taxid: 324602 strain: j-10-fl gene: caur_0173 expression_system: escherichia coli expression_system_taxid: 469008 expression_system_strain: bl21(de3)codon+ril expression_system_vector_type: plasmid expression_system_plasmid: bc-psgx3(bc) |
| EXPDTA | x-ray diffraction |
| HETNAM | mse selenomethionine
SO4 sulfate ion |
| FORMUL | mse 8(C5H11NO2Se)
SO4 2(O4 S2-) HOH *480(H2O) |
| Графа | Значение |
| Название | Кристаллическая структура предполагаемого MaoC домена белка дегидратазы |
| Состав |
Молекула: MaoC домен белка дегидратазы
Цепи: a, b |
| Источник | Chloroflexus aurantiacus |
| Метод расшифровки | рентгеноструктурный анализ |
| Малые молекулы и ионы | Mse селенометионин
SO4 сульфат-ион |
| Формулы малых молекул и ионов | Mse 8(C5H11NO2Se)
SO4 2(O4 S2-) HOH *480(H2O) |
Из Таблицы 2 очевидно, что данная пространственная структура белка, который состоит из двух цепей, была получена из бактерии C. aurantiacus методом рентгеноструктурного анализа.
Сравнение строения белка с его биологической единицей
Биологическая единица — это макромалекулярная структура, которая считается функциональной формой молекулы.
У данного белка две биологических единицы. я проанализировала каждый в программе Jmol, и оказалось, что каждый из них представляет собой одну из двух цепочек исходного белка. Строение абсолютно аналогичное.
Ниже на Рисунке 2 приведено изображение этих биологических единиц. Сравнив Рисунок 1 и 2, приходим к выводу об их сходстве.
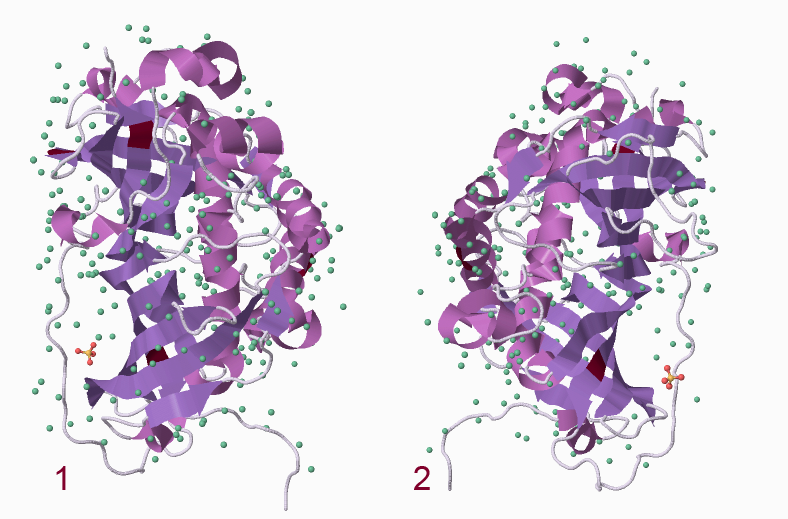
Рисунок 2. Биологические единицы белка дегидратазы.
Для того, чтобы полностью убедиться в абсолютном сходстве субъединиц и белка, было построено выравнивание их последовательностей из аминокислот. Из Рисунка 3 видно, что эти последовательности полностью идентичны.

Рисунок 3. Сравнение последовательностей белка дегидратазы и его биологических единиц.
Рисунок получен с помощью программы Jalview. Скачать файл с последовательностями можно здесь.
Также благодаря сайту PDB удалось выяснить, что биологическая единица данного белка является гомотримером. Это показано на Рисунке 4.
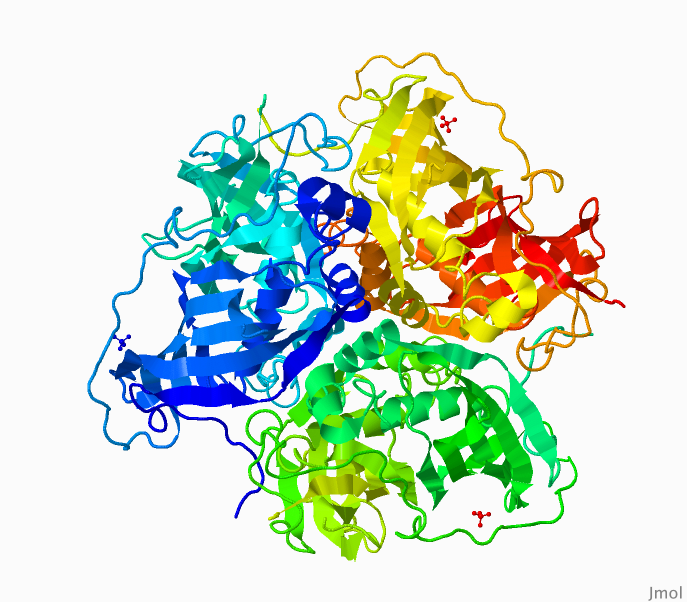
Рисунок 4. Пространственное строение биологической единицы дегидратазы как тримера.
Рисунок получен с помощью программы Jmol. Окрашивание при помощи команды color group. N-конец показан более холодным цветом, С-конец — тёплым (синий — сине-зелёный, сине-зелёный — жёлтый, жёлтый — красный). PDB-файл можно скачать отсюда.
При нажатие на изображение появляется анимированная структура для лучшего рассмотрения данной субъединицы.