Переводя нашу метаболическую карту в режим "Reference map (KO)", получаем карту, на которой фиолетовым цветом веделены те ферменты, на которые есть ссылки в БД KEGG Orthology (KO). KO - это БД устанавливающая связь между номером фермента, группой ортологичных генов и их продуктов. Разберемся на примере фермента 3.5.1.9, что содержит запись БД KEGG Orthology.
- Код записи KO: K01432
- Имя (EC код фермента): 3.5.1.9
- Определение (расшифровка кода): арилформамидаза
- Участие в метаболических путях (функциональная классификация): Метаболизм; Метаболизм углеводов; Метаболизм глиоксилата и декарбоксилата [PATH:ko00630].
Метаболизм; Метаболизм аминокислот; Метаболизм триптофана [PATH:ko00380]. - Ссылки на другие БД: RN: R00988 R01959 R04911
EC: 3.5.1.9
GO: 0004061 - Список ортологичных генов: HSA: 125061(AFMID)
MMU: 71562(Afmid)
REH: H16_A3005 H16_B1997
BMV: BMASAVP1_A0652(kynB)
BML: BMA10299_A2487(kynB)
BMN: BMA10247_0100(kynB)
BPL: BURPS1106A_0897(kynB)
BPD: BURPS668_0894(kynB)
GFO: orf69
Изучая запись БД KO можно понять в каких организмах такой фермент аннотирован по данным KEGG.
Как было показано в предыдущем упражнении для пути деградации триптофана до ацетилкофермента А по данным KEGG у E.coli существуют не все ферменты из 13 необходимых. (Зеленым выделены те ферменты, гены которых есть у E.coli)
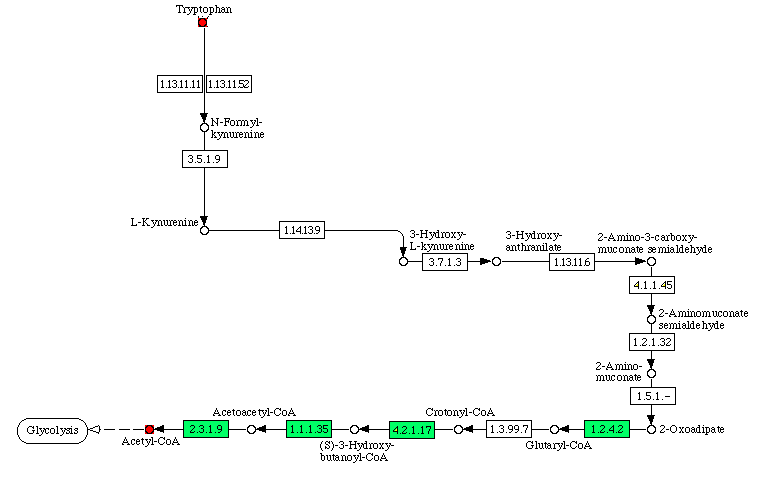
Ввиду того, что очень много необходимых ферментов отсутствует, скорее всего такой путь у E.coli не осуществляется. Тем не менее попробуем определить есть ли такие ферменты у кишечной палочки с помощью других БД. Поиск начнем с UniProt. Запрос SRS:
([uniprot-ID:*_ECOLI] & ((((((((([uniprot-ECNumber:1.13.11.11] | [uniprot-ECNumber:1.13.11.52]) | [uniprot-ECNumber:3.5.1.9]) | [uniprot-ECNumber:1.14.13.9]) | [uniprot-ECNumber:3.7.1.3]) | [uniprot-ECNumber:1.13.11.6]) | [uniprot-ECNumber:4.1.1.45]) | [uniprot-ECNumber:1.2.1.32]) | [uniprot-ECNumber:1.5.1.-]) | [uniprot-ECNumber:1.3.99.7]))
Из всех ферментов в UniProt присутствует только фермент EC 1.5.1.- (AC: P75893), добавленный в БД в 2002 году.
При поиске нуклеотидных последовательностей в NCBI по коду фермента вообще не удалось обнаружить у E.coli генов никаких ферментов кроме 1.5.1-.
В БД Brenda не было найдено таких ферментов. Таким образом, опираясь на современные данные (начало 2007 года) БД KEGG, Brenda, UniProt, NCBI можно говорить о том, что деградация триптофана до ацетилкофермента А вышеуказанным путем у кишечной палочки не осуществляется.