Входные данные: Ген AADAT.

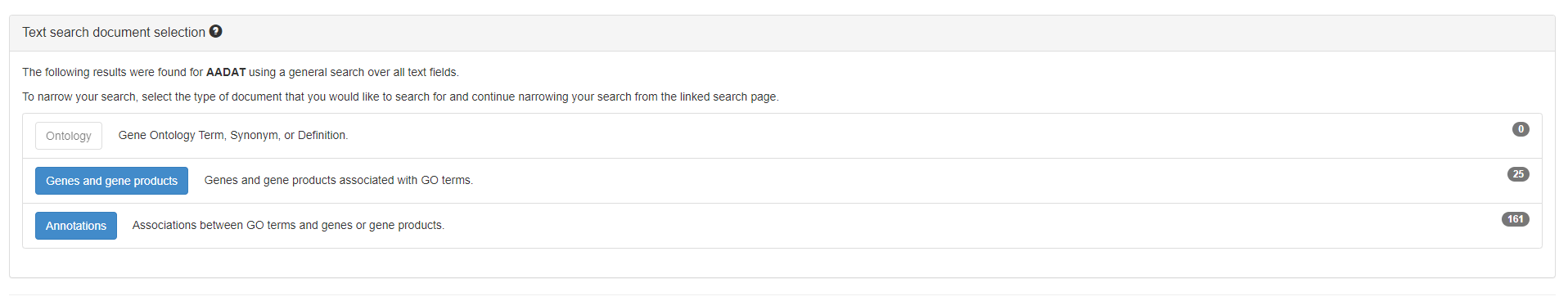
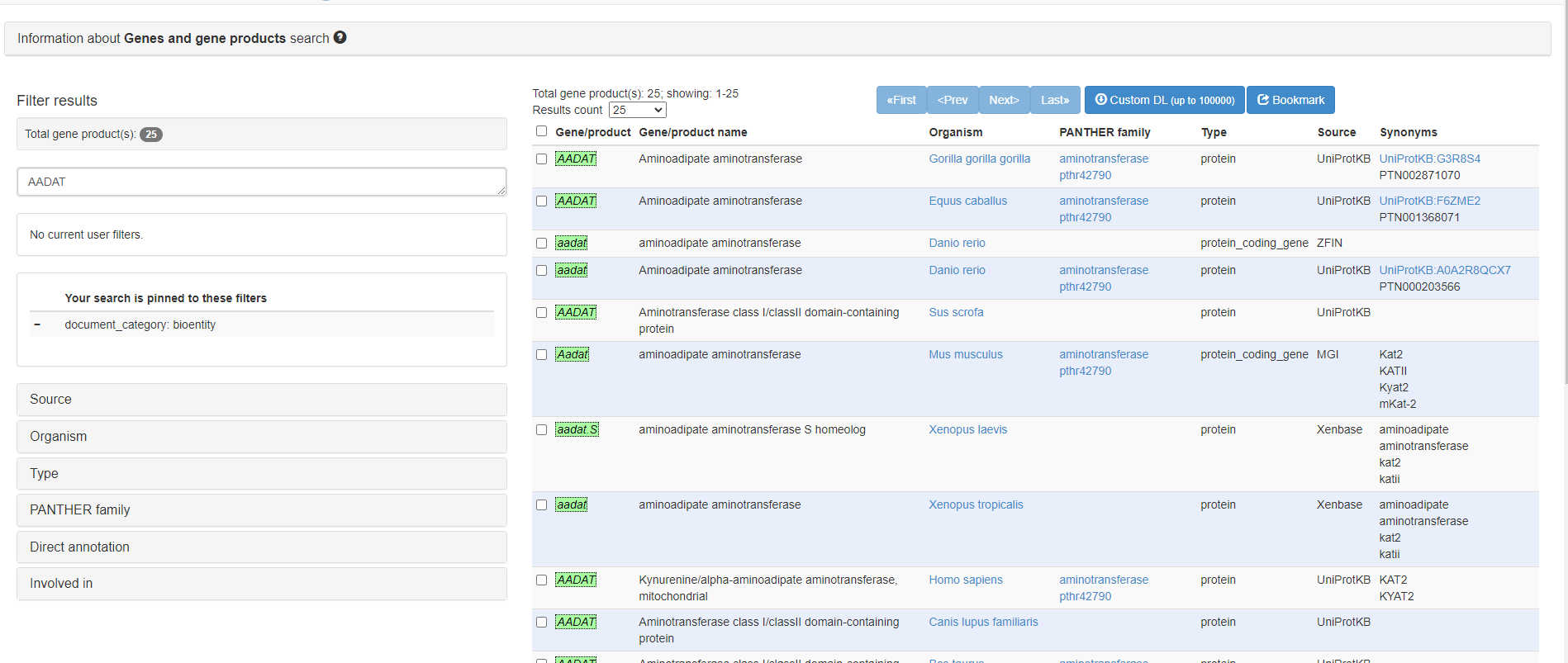
Попробуем воспользоваться GO(Gene Ontology) для первого анализа:
Входные данные: Ген AADAT.



Польза данного способа поиска информации по гену очевидна. Например, зная ID гена мыши мы можем найти что он синтезирует (ещё перед этим мы можем применить фильтр по организму, чтобы показало только мышь), узнать Uniprot ID или ID из другой базы данных и отправиться изучать данный ген более подробно.
Попробуем ознакомиться со STRING
Входные данные: белок с PDB ID 1Y2S (Простите за самодеятельность, но очень интересно посмотреть, что STRING даст по поводу прионного белка, который мы изучаем в лабе)
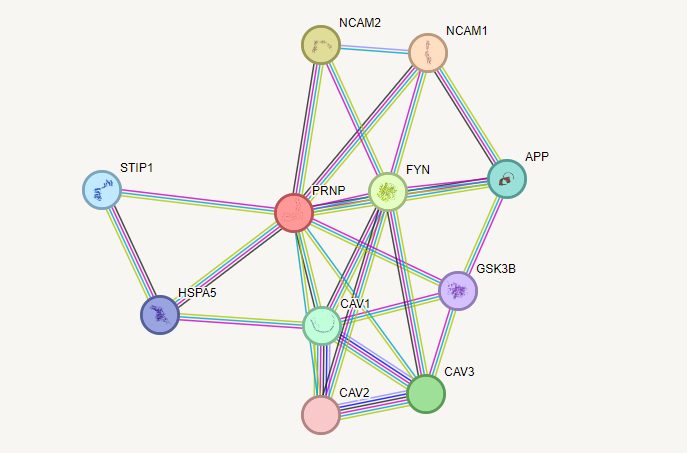

К сожалению STRING не показал, взаимодействует ли прион с интересующим меня белком, подтверждая то, что этим пока никто ещё не занимался
Вернёмся в систему GO и попробуем сделать для нашего списка ID анализ обогащения терминами по биологическим процессам:
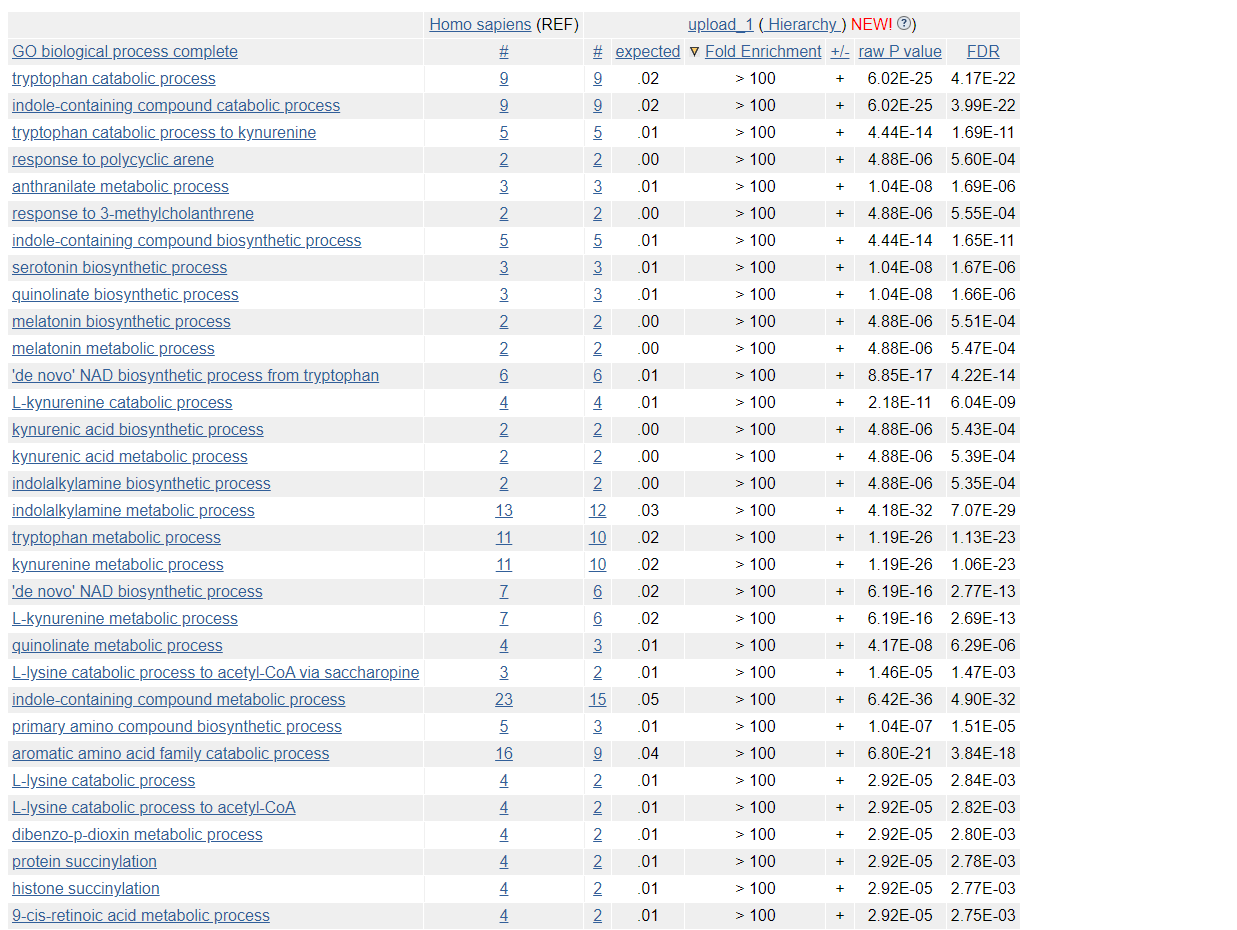
У нас есть довольно много строчек с обогащением >100. Можно даже прийти к выводу, что довольно крупная часть выборки представлена генами, занимающимися индол-содержащими метаболитными процессами (15 генов из выборки имеют данный термин из 23 возможных генов с таким термином из референсного генома). Всего в выборке у нас 42 ID
Назад