Структура аргининовой тРНК из Saccharomyces cerevisae
Введение
тРНК – самая маленькая нуклеиновая кислота, состоит обычно из 75-85 нуклеотидов. Функцией тРНК является перенос аминокислоты к месту трансляции и “включении” её в цепь собираемого белка. Практически все тРНК имеют сходную вторичную структуру, названную “клеверным листом”. В строении можно выделить несколько областей: акцепторный стебель, образованный 5’- и 3’-концами, TΨC-шпилька, содержащая риботимидин и псевдоуридин, DU-шпилька, содержащая дигидроурацил, и антикодоновая шпилька, несущая на себе уникальный триплет – антикодон.Цель данной работы – составить вторичную структуру тРНК со всеми взаимодействиями между нуклеотидами, определяющими её третичную структуру, при помощи PDB файла и вспомогательных программ.
Исследование
Для изучения был предложен файл 1f7v.pdb. Этот файл содержит молекулу аргининовой тРНК (идентификатор цепи — B) и аргинил-тРНК синтетазы (идентификатор цепи — A). Последовательность тРНК:| PSU | U | C | C | U | C | G | U | 1MG | 2MG | C | C | C | A | A | DHU | G | G | DHU | C | A | C | G | G | C | M2G | PSU | C | U | G | G | C | U | I | C | G | A | |||||||
| A | C | C | A | G | A | A | G | A | DHU | U | 5MC | C | A | G | G | 5MU | PSU | C | A | 1MA | G | U | C | C | U | G | G | C | G | G | G | G | A | A | G | C | C | A | |||||
В структуре тРНК присутствуют модифицированные основания:
Ψ(PSU) – Псевдоуридин
1mG – 1N-Метилгуанозин
2mG – 2N-Метилгуанозин
DHU – 5,6-Дигидроуридин
m2G – N2-Диметилгуанозин
5mC – 5-Метилцитидин
5mU – 5-Метилуридин
1mA – 6-Гидро-1-метиладенозин
I – Инозин
Первый нуклеотид тРНК имеет номер 901, последний — 973. А длина молекулы — 76 нуклеотидов! Отсутствует акцепторный конец ССА. Других пропусков или вставок нет.
Чтобы предсказать вторичную структуру, была использована программа find_pair. На вход был подан PDB-файл. В результате программа выдала таблицу, из которой можно почерпнуть информацию о спиралях в тРНК:
- Акцепторная (7 пар нуклеотидов): 901-907, 966-972. На схеме последовательности выделена бирюзовым.
- D-спираль (3 п.н.): 910-912, 923-925. Выделена ярко-зеленым.
- Антикодоновая (5 п.н.): 927-931, 939-943. Выделена темно-бордовым.
- Т-спираль (5 п.н.): 949-953, 961-965. Выделена темно-серым.
Визуализация расположения этих спиралей проводилась в Rasmol (рисунок слева) и вручную (схема справа):
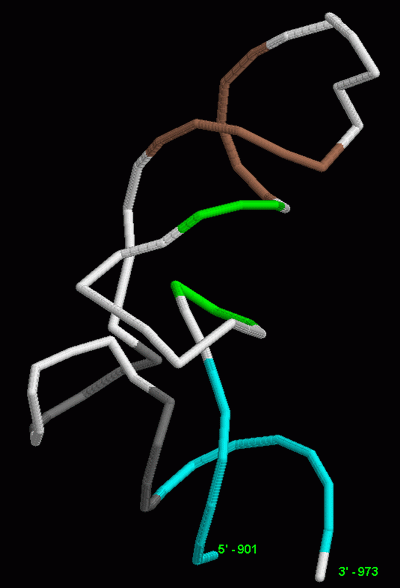
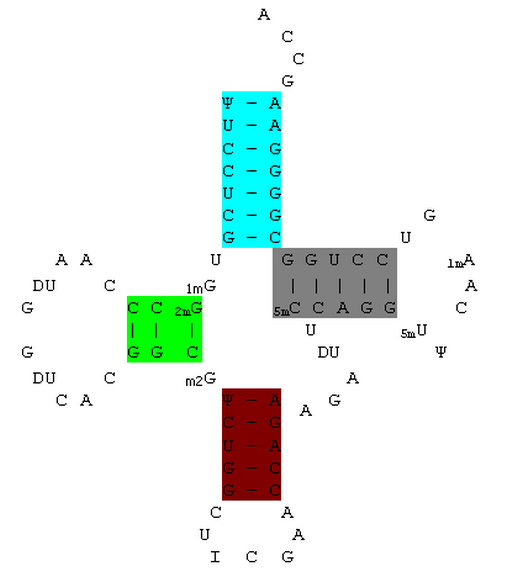
В схеме был добавлен акцепторный конец (ССА) для правдоподобности картины, а 5,6-дигидроуридин обозначен как DU, чтобы не загромождать схему.
Межмолекулярные взаимодействия
Нас интересуют два вида взаимодействия: внеспиральный стекинг и не Уотсон-Криковское спаривание. Именно эти два типа обеспечивают уникальную вторичную структуру: сворачивание "клеверного листа" в L-образную фигуру.
Поиск стекинг-взаимодействий проводился вручную. Структура РНК просматривалась нуклеотид за нуклеотидом. В итоге были найдены 6 случаев внеспирального стекинга:
В ДНК стекинг обеспечивает сохранение стройной структуры двойной спирали. Слабые Ван-дер-Ваальсовые связи, проходя сквозь всю спираль, образуют своего рода каркас. В РНК спирали — лишь один из элементов структуры, и основания, не входящие в них, могут образовывать стекинг-связи с отдаленными основаниями, таким образом сворачивая цепь.
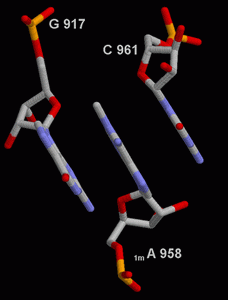
В нашем случае имеют место 4 пары и две тройки связанных оснований. Самым интересным я считаю последний случай, поскольку в этой связи участвуют основания из противоположных TΨC- и DU-шпилек, соединяя их (показан на рисунке справа).
Для определения не Уотсон-Криковских взаимодействий были использованы результаты программы find_pair и информация из PDB-файла. Помимо этого структура просматривалась вручную, на предмет потенциальных связей. В итоге осталось 8 пар оснований:
Проанализировав структуру тРНК программой analyze были получены данные о конформационно важных
торсионных углах. Из них ясно, что спирали тРНК похожи на А-форму ДНК.
Для быстрого поиска инвертированных последовательностей была использована программа einverted. Самое интересное, что лучший результат программа выдала при значении параметра Minimum score threshold равного 15. При меньшем значении программа находит только одну последовательность, при большем — ни одной:
Алгоритм Зукера
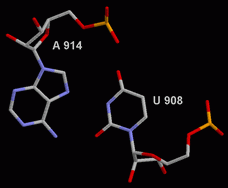
По сравнению со стекингом, водородные связи гораздо сильней. Самая очевидная их функция — соединение двух цепей в спиралях. В РНК связи могут образовывать не только противостоящие друг другу основания, но и находящиеся на противоположных концах молекулы, создавая необходимую конформацию. При этом в общем случае соблюдается принцип комплементарности, но бывают и исключения. Так в тРНК достаточно часто встречаются минорные основания, которые также способны образовывать водородные связи (5, 7, 8 пары). Кроме того основание может связываться с себе подобным (6 пара), а комплементарные могут образовывать неканонические варианты взаимодействия (U 908—A 914 на рисунке справа).
tRNA: Score 15: 5/5 (100%) matches, 0 gaps
27 tctgg 31
|||||
43 agacc 39
tRNA: Score 15: 5/5 (100%) matches, 0 gaps
49 ccagg 53
|||||
65 ggtcc 61
Эти стебли найдены точно. D-спираль состоит лишь из 3 пар нуклеотидов, поэтому неудивительно, что программа её не нашла. Самая большая акцепторная спираль не была найдена, видимо, потому что в ней имеется нестандартная пара U—G.
Данный алгоритм осуществляется программой mfold. При составлении файла с последовательностью нуклеотидов была произведена замена всех нестандартных оснований их стандартными “родственниками”, которые определялись из названия. Единственное основание неподдающееся подобной оценке – инозин. Но, сравнив его формулу с четырьмя классическими основаниями, было выявлено его сходство с гуанином. Эта замена и последовала. К сожалению, результат был неутешительным. Не было ни одного изображения правильной структуры. Тогда было принято решение вернуть инозин на место. После этого алгоритм Зукера сработал верно. Полученное изображение полностью соответствует построенной тРНК. Оно было реализовано при значении параметра P=10. Данное изображение оказалось шестым по счету.