Практикум 2: A- и В- формы ДНК. Структура РНК
Задание 1
С помощью программы fiber пакета 3DNA были построены A-, B- и Z-формы дуплекса ДНК, последовательность одной из нитей которого представляет собой 5 раз повторенную последовательность "gatc".
Использовались следующие команды:
fiber -a -seq=AGCT -rep=5 gatc-a.pdbfiber -b -seq=AGCT -rep=5 gatc-b.pdbfiber -z -seq=AGCT -rep=5 gatc-z.pdb
Были получены следующие структуры: A-форма, B-форма, Z-форма.
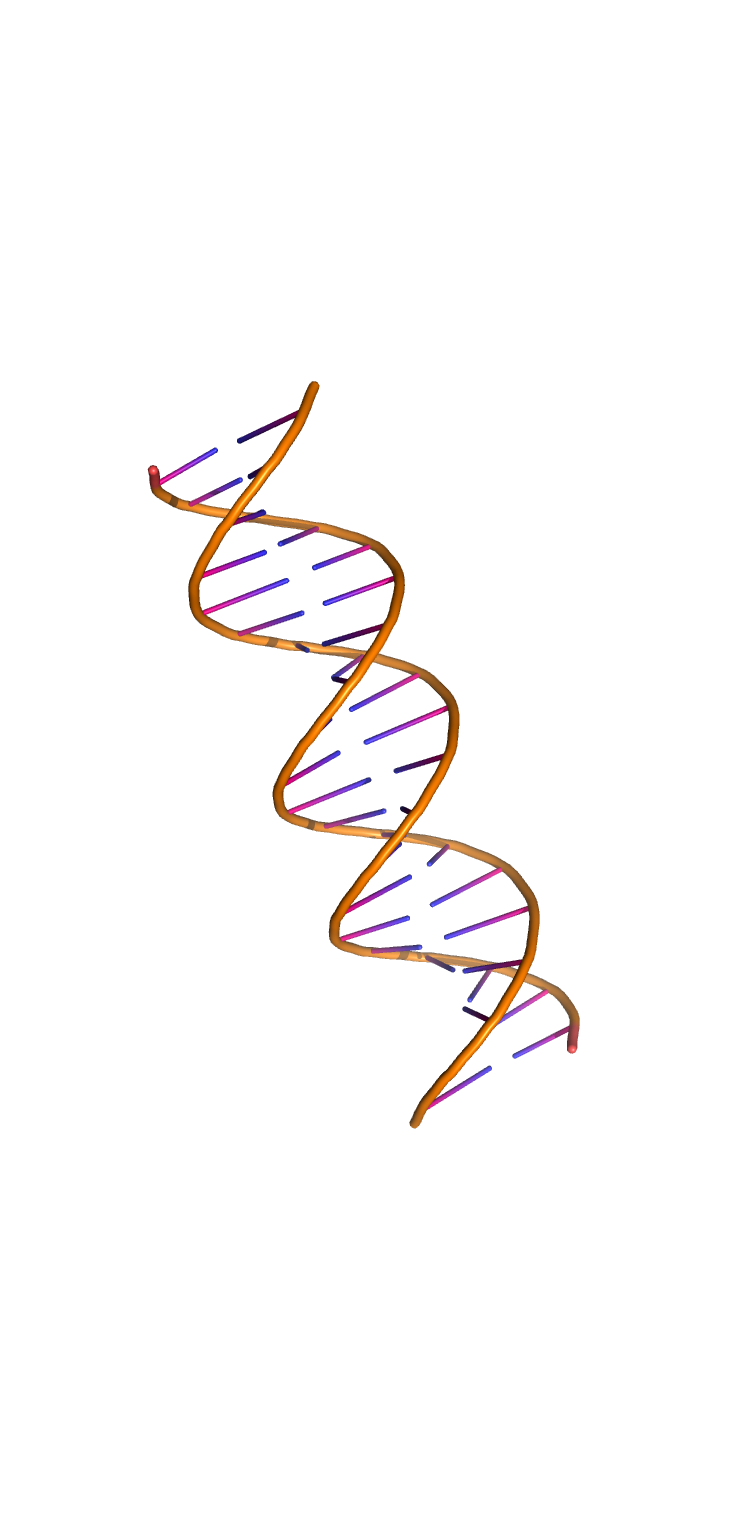
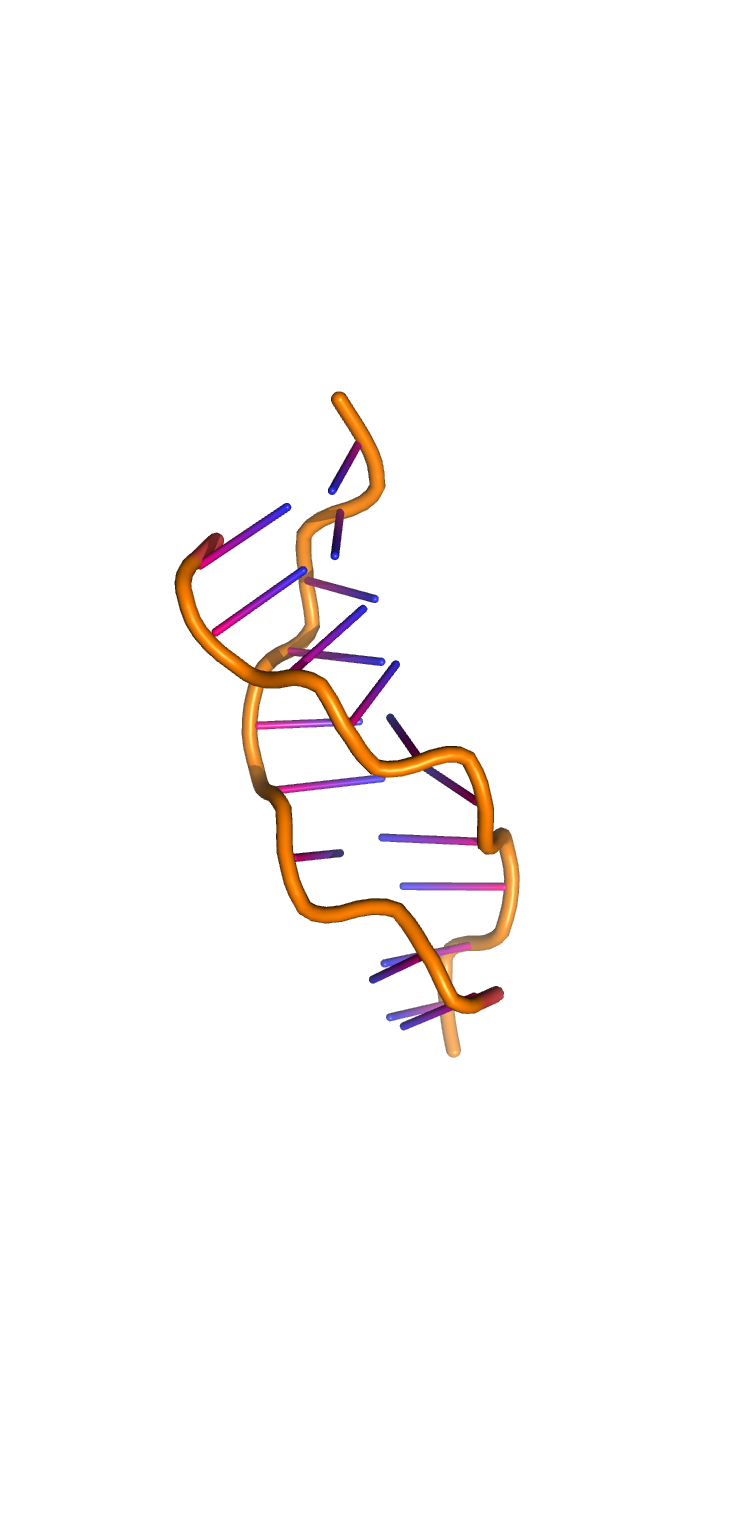
Задание 2
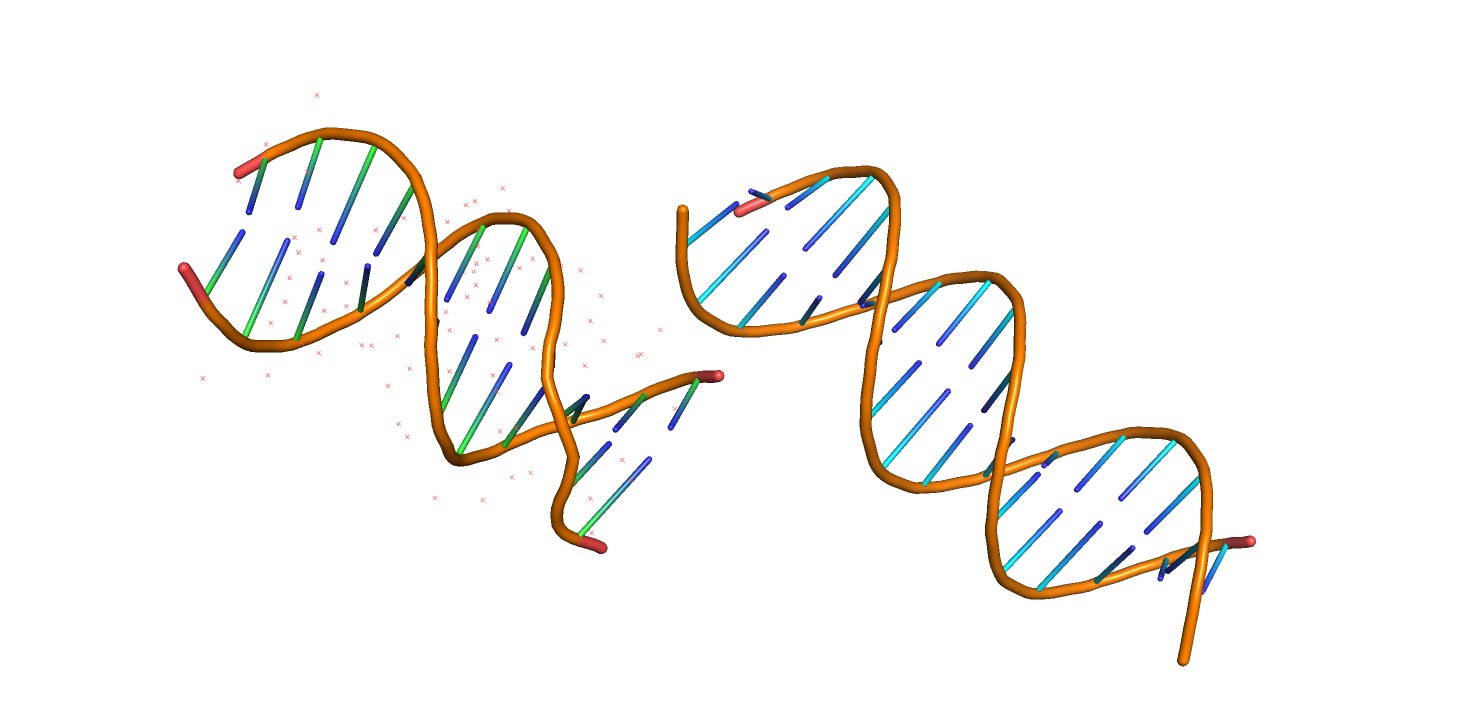
Для сравнения сгенерированной и экспериментальной структур была выбрана B-форма ДНК. В качестве экспериментальной структуры использован файл 1bna.pdb (B-ДНК додекамер). Сравнение сгенерированной структуры (gatc-b.pdb) и экспериментальной представлено на рис. 2.
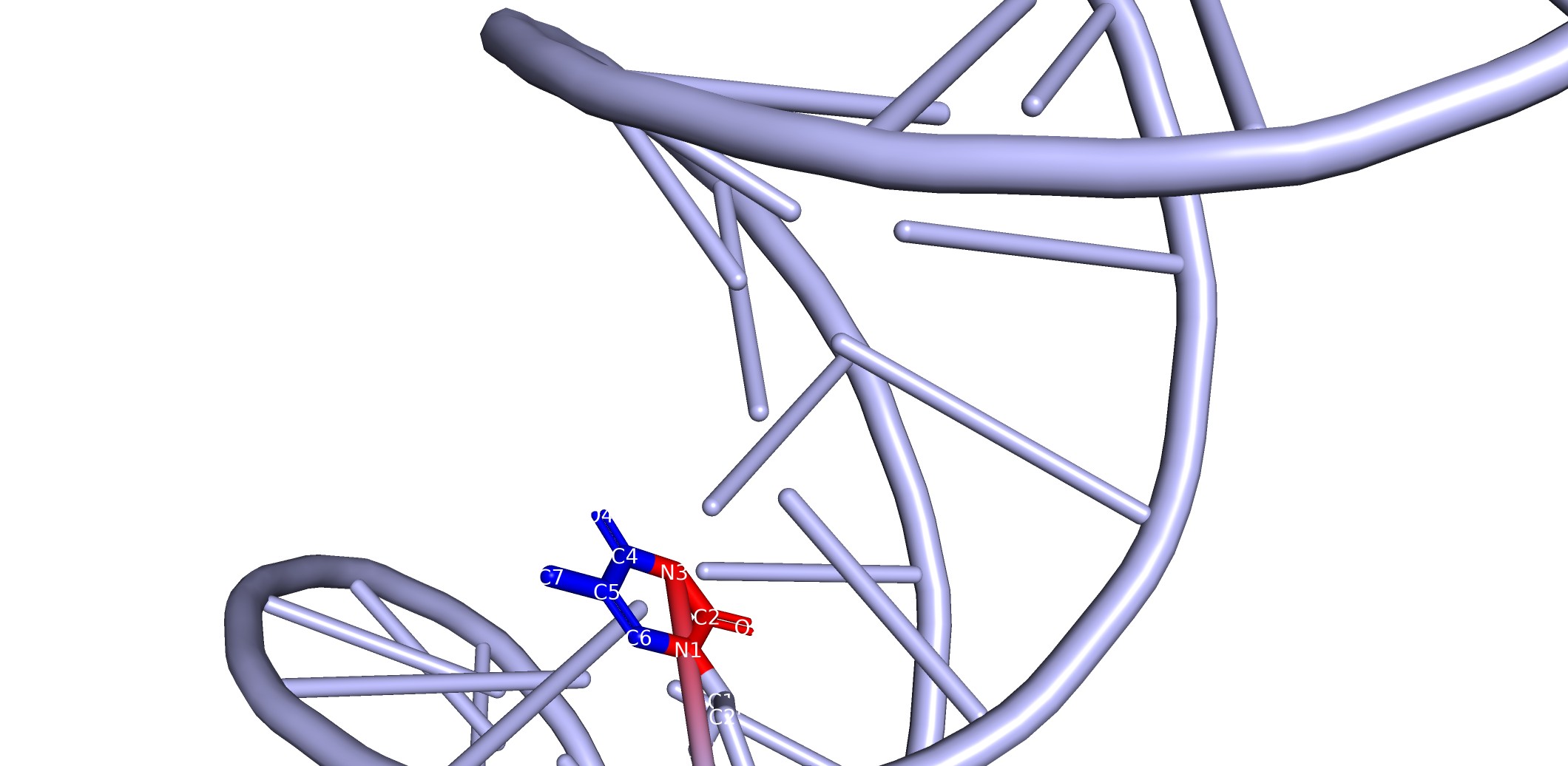
Для определения ориентации атомов азотистого основания относительно бороздок был выбран тимин с номером 7 (DT7) в экспериментальной структуре. С помощью визуализации в PyMol установлено, какие атомы этого основания обращены в сторону большой и малой бороздок. На рис.3 красным цветом выделены атомы, направленные в большую бороздку, синим – в малую.
- В сторону большой бороздки обращены атомы: 7.N3, 7.C2, 7.O2, 7.N1.
- В сторону малой бороздки обращены атомы: 7.O4, 7.C4, 7.C5, 7.C6, 7.C7.

| Параметр | A-форма | B-форма | Z-форма |
|---|---|---|---|
| Тип спирали | Правая | Правая | Левая |
| Шаг спирали (Å) | 28,0 | 33,8 | 42,3 |
| Число оснований на виток | 11 | 10 | 12 |
| Ширина большой бороздки (Å) | 18,1 (/A/DA2/P – /B/DT31/P) | 18,8 (/A/DA10/P – /B/DT23/P) | 15,2 (/A/DG9/P – /B/DC32/P) |
| Ширина малой бороздки (Å) | 8,0 (/A/DT7/P – /B/DC20/P) | 11,7 (/A/DT7/P – /B/DA30/P) | 9,9 (/A/DG15/P – /B/DC30/P) |
Примечание: В таблице указаны фосфаты, использованные для измерения ширины бороздок (например, /A/DA2/P` означает фосфат второго нуклеотида цепи A).
Задание 3
Для выполнения задания была проанализирована структура тРНК с идентификатором PDB 1i9v (тРНК Phe). Все расчёты проводились с помощью пакета 3DNA: предварительная конвертация файла в старый формат PDB (remediator), построение списка пар оснований (find_pair) и анализ геометрических параметров (analyze).
Выполненные команды:
wget https://files.rcsb.org/download/1i9v.pdbremediator --old 1i9v.pdb > 1i9v_old.pdbfind_pair 1i9v_old.pdb stdout | analyze
В результате работы были созданы файлы 1i9v_old.out и 1i9v_old.inp, содержащие всю необходимую информацию для дальнейшего анализа.
Упражнение 1: Торсионные углы нуклеотидов
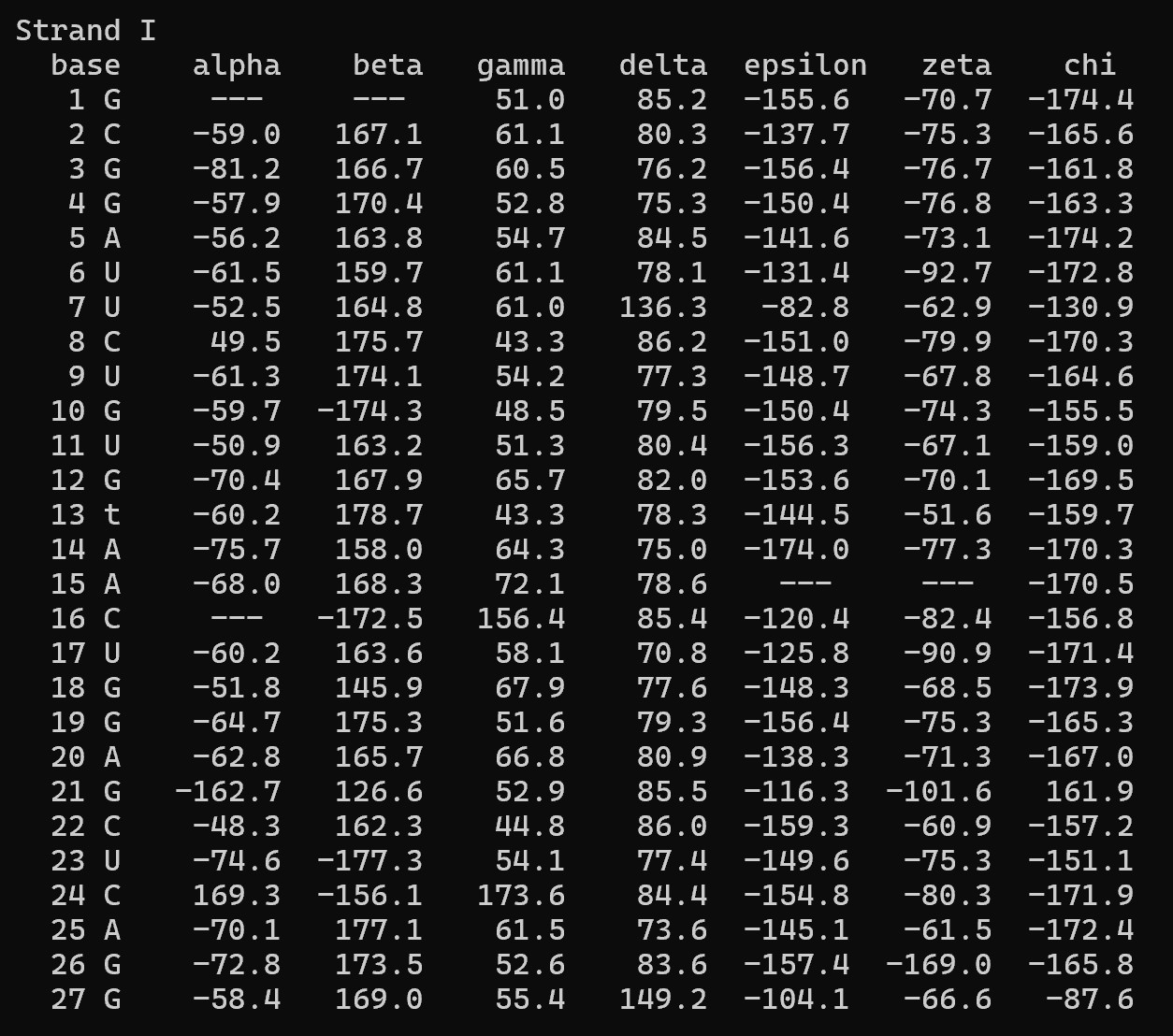
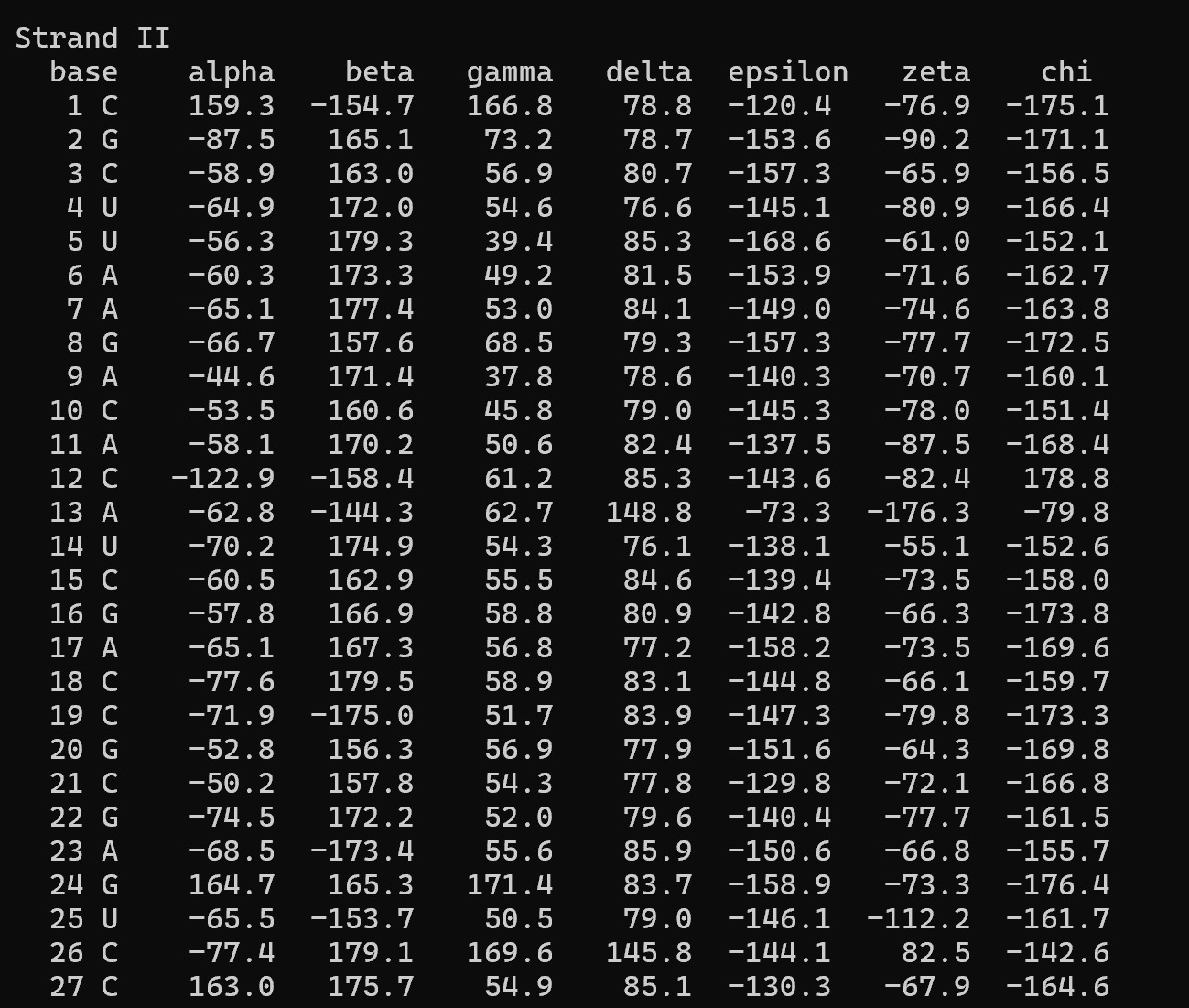
В выходном файле 1i9v_old.out были определены значения торсионных углов для всех нуклеотидов структуры. На рис. 5 и 6 представлены торсионные углы для нуклеотидов, входящих в состав стеблей (акцепторного и Т-стебля). Значения угла δ (определяющего конформацию сахара) для большинства нуклеотидов стеблей находятся в диапазоне 80–95°, что соответствует C3′-эндо конформации. Такая конформация характерна для А-формы нуклеиновых кислот.
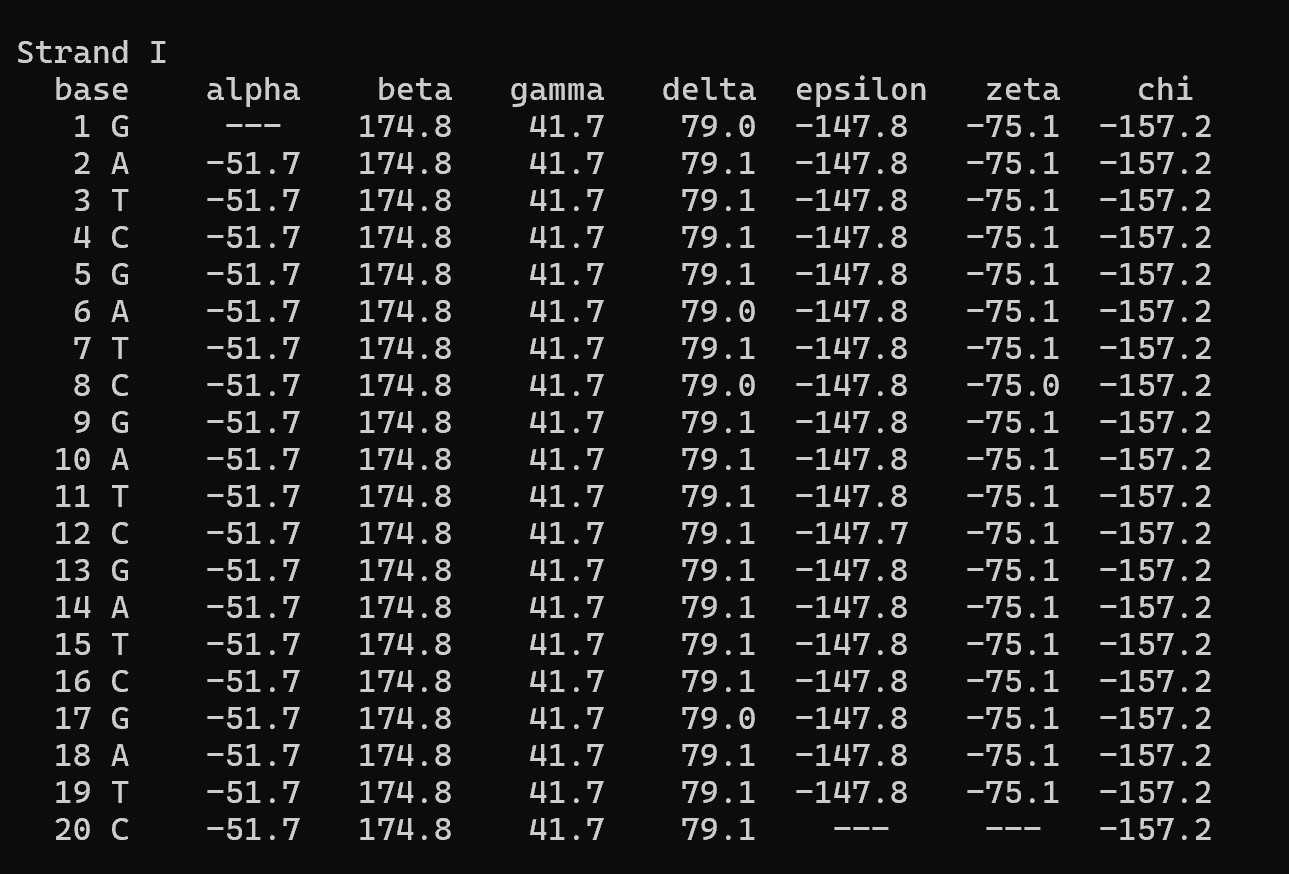
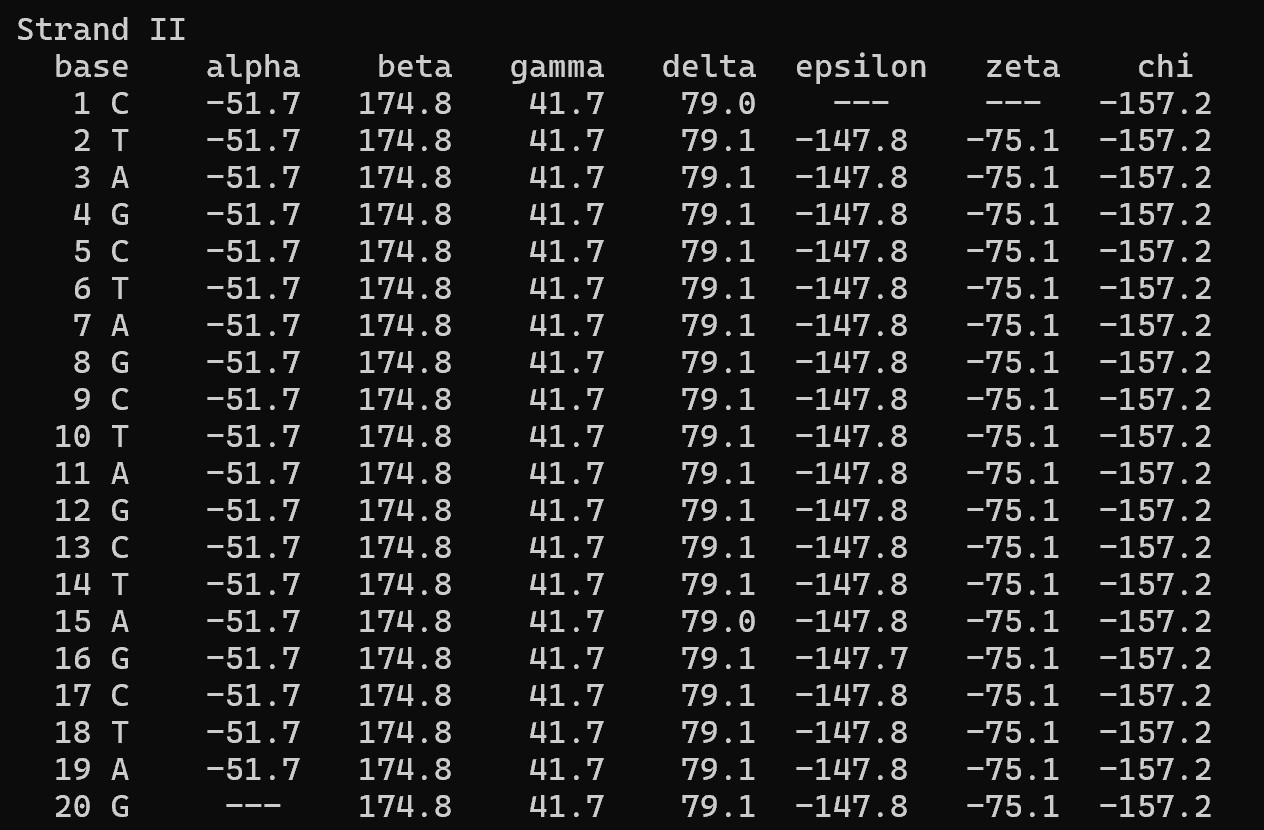
Для сравнения на рис. 7 и 8 приведены торсионные углы для модельной А-формы ДНК, полученной в задании 1. Видно, что распределение углов (особенно δ) в стеблях тРНК близко к А-форме. Таким образом, тяжи тРНК 1i9v по конформационным параметрам больше всего похожи на А-форму ДНК.
Упражнение 2: Водородные связи, стебли и неканонические пары
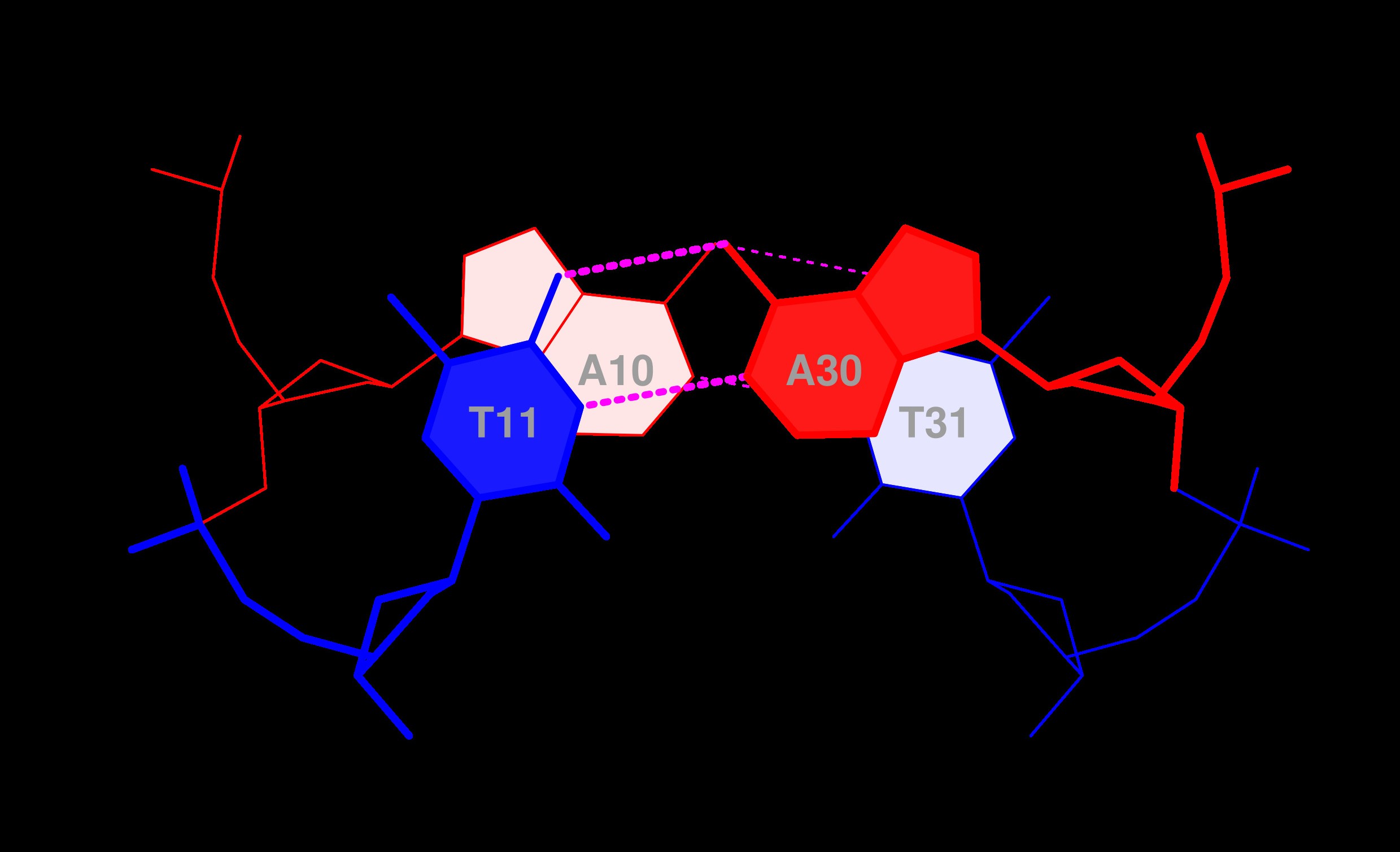
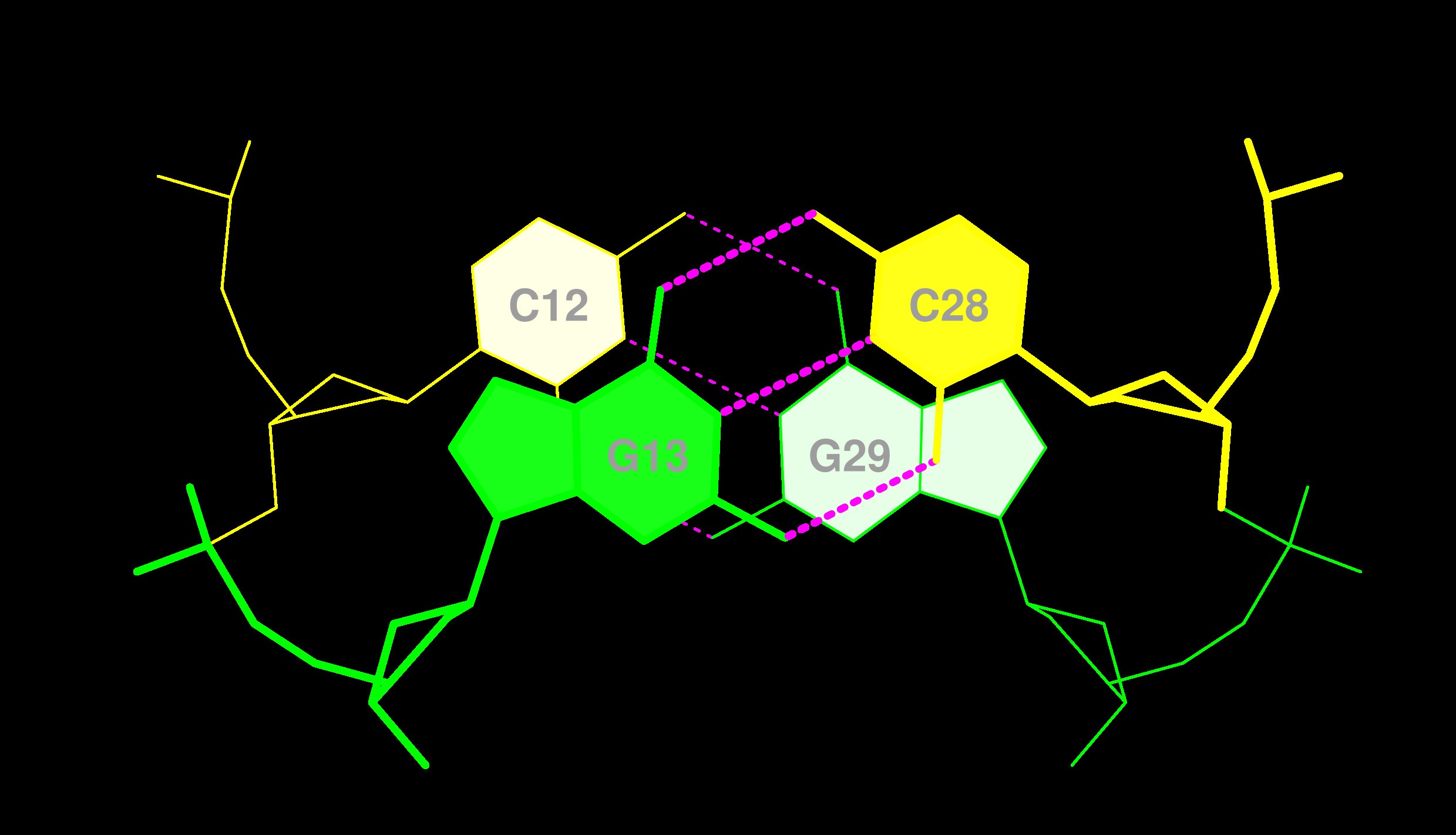
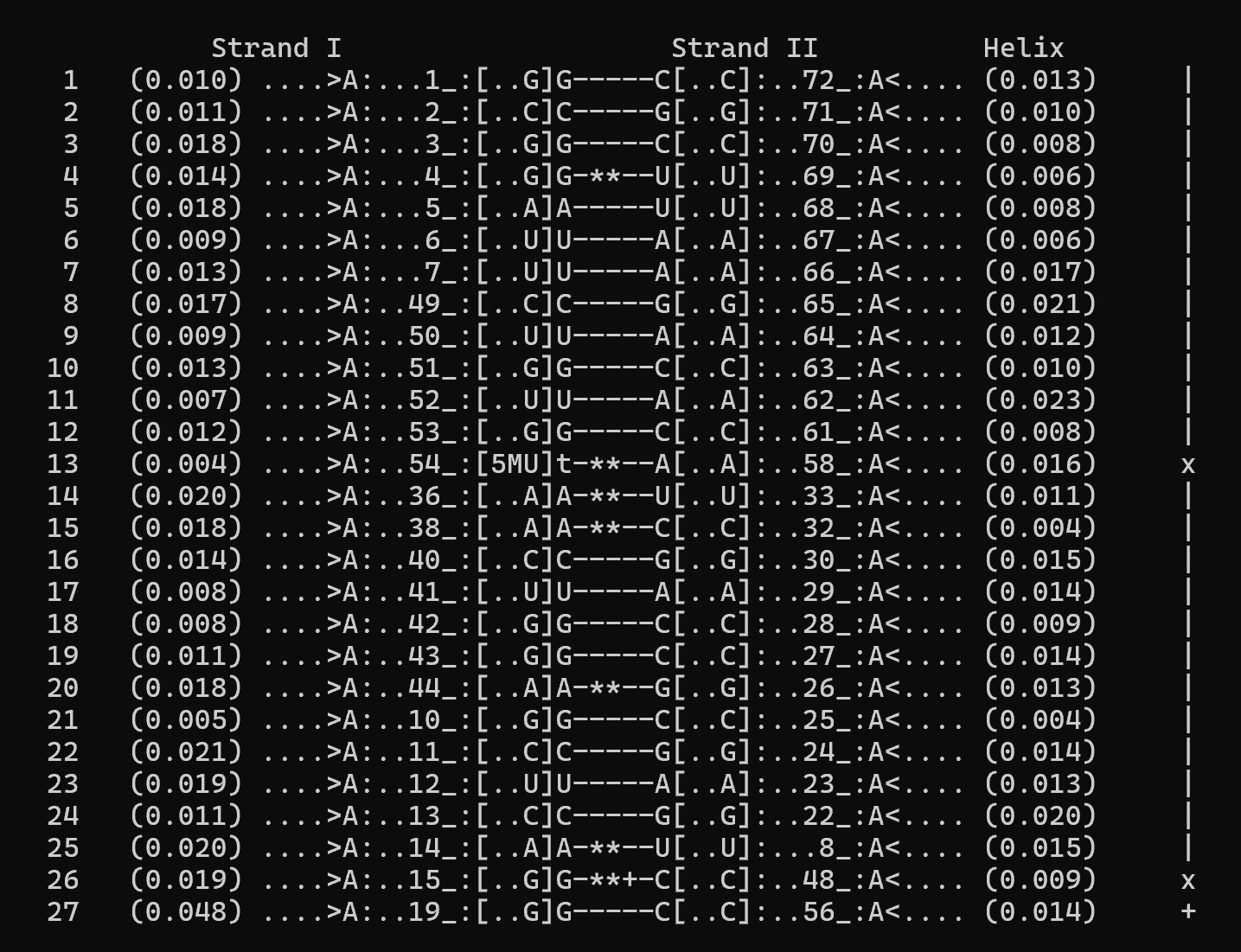
На основе анализа файла 1i9v_old.out были определены все пары оснований, стабилизированные водородными связями. На рис. 9 показаны нуклеотиды, образующие стебли (регулярные двойные спирали) во вторичной структуре тРНК.
Стебли тРНК 1i9v (номера нуклеотидов соответствуют PDB-нумерации):
- Акцепторный стебель: 1–7 и комплементарные им 66–72.
- Т-стебель: 49–52 и комплементарные 62–65.
- D-стебель: 10–13 и комплементарные 22–25.
- Антикодоновый стебель: 40–43 и комплементарные 27–30.
Неканонические пары оснований
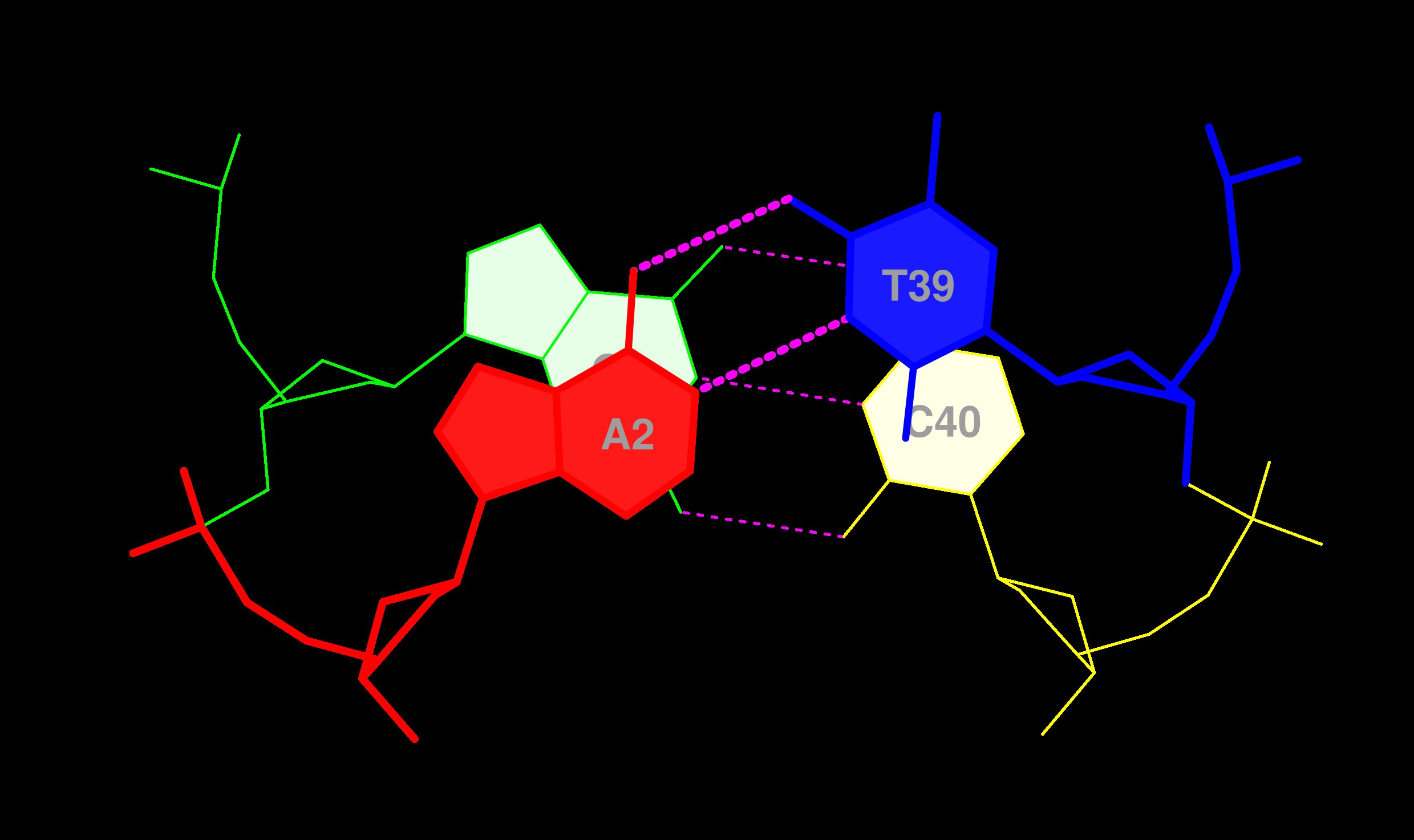
В структуре обнаружено 7 неканонических пар (не принадлежащих к стандартным парам Уотсона–Крика). Их перечень, согласно данным 3DNA, приведён ниже. Некоторые из этих пар участвуют в формировании третичной структуры.
- G4 – U69
- T – A58 (модифицированный тидин)
- A38 – C32
- A44 – G26
- A14 – U8
- G15 – C48
Дополнительные водородные связи, стабилизирующие третичную структуру
Пара G15–C48 не входит ни в один из стеблей и представляет собой типичное третичное взаимодействие (tertiary interaction), соединяющее D-петлю и вариабельную петлю. Её наличие подтверждено в списке пар оснований с указанием длин водородных связей.
| step | последовательность | площадь перекрывания (Ų) |
|---|---|---|
| 1 | GC/GC | 10.02 |
| 10 | GU/AC | 10.13 |
| 12 | Gt/AC | 11.85 |
Наибольшая площадь перекрывания наблюдается для шага 12 (Gt/AC), где плоскости оснований расположены практически параллельно и имеют минимальный сдвиг друг относительно друга, что обеспечивает оптимальный стекинг.