Практикум 3: Предсказание вторичной структуры тРНК и анализ НК-белкового комплекса
Задание 1. Предсказание вторичной структуры заданной тРНК (1i9v)
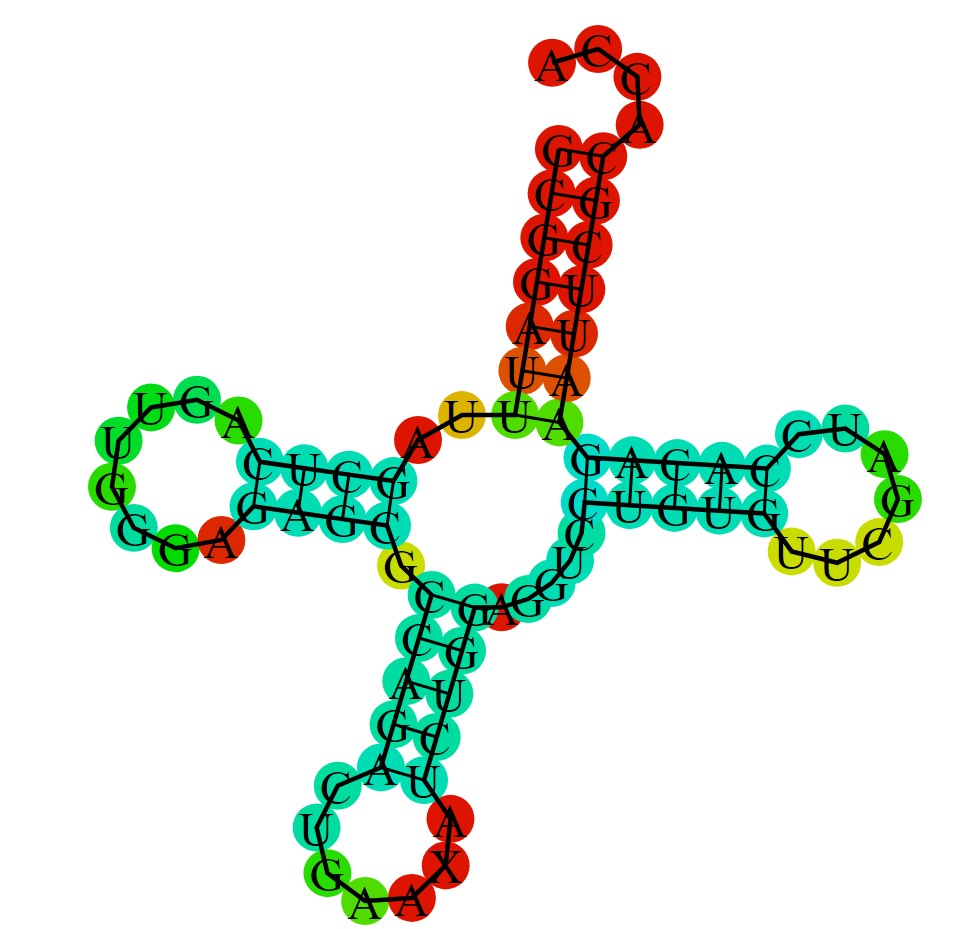
С помощью einverted из пакета EMBOSS были найдены инвертированные участки нуклеотидных последовательностей. Далее с помощью алгоритма Зукера и программы RNAfold была предсказана вторичная структура тРНК(1i9v) и получено ее изображение.
Параметры einverted: запуск проводился со значениями -gap 12 -threshold 10 -match 3 -mismatch -3. Программа нашла участки, соответствующие T-стеблю (5 из 5 пар) и антикодоновому стеблю (4 из 4 пар, однако предсказала 4 лишних пары, вероятно, из-за внутристеблевых повторов). Акцепторный и D-стебель не обнаружены из-за малой длины или наличия неканонических пар.
| Участок структуры | Позиции в структуре по find_pair | Результаты с помощью einverted | Результаты предсказания по алгоритму Зукера |
|---|---|---|---|
| Акцепторный стебель | 1-7:66-72 (6 пар + 1 неканоническая) | нет | 7 из 7 пар |
| D-стебель | 10-13:22-25 (4 пары) | нет | 4 из 4 пар |
| T-стебель | 49-52:62-65 (5 пар) | 5 из 5 пар | 5 из 5 пар |
| Антикодоновый стебель | 40-43:27-30 (4 пары) | 4 из 4 пар, 4 лишних | 4 из 4 пар, 1 лишняя |
| Общее число канонических пар нуклеотидов | 19 | 9 | 19 |
Примечание: Для акцепторного и D-стебля einverted не дал результата, вероятно, из-за малой длины шпилек. Антикодоновый стебель программа нашла, но с четырьмя лишними парами (ошибочное спаривание внутри петли). Алгоритм Зукера (RNAfold) предсказал все канонические пары правильно, но добавил одну лишнюю пару в антикодоновом стебле.
Задание 2. Поиск ДНК-белковых контактов в структуре 1mdm
Файл скрипта, определяющего множество атомов (JMol)
Файл скрипта, выдающего последовательное изображение структуры (JMol)
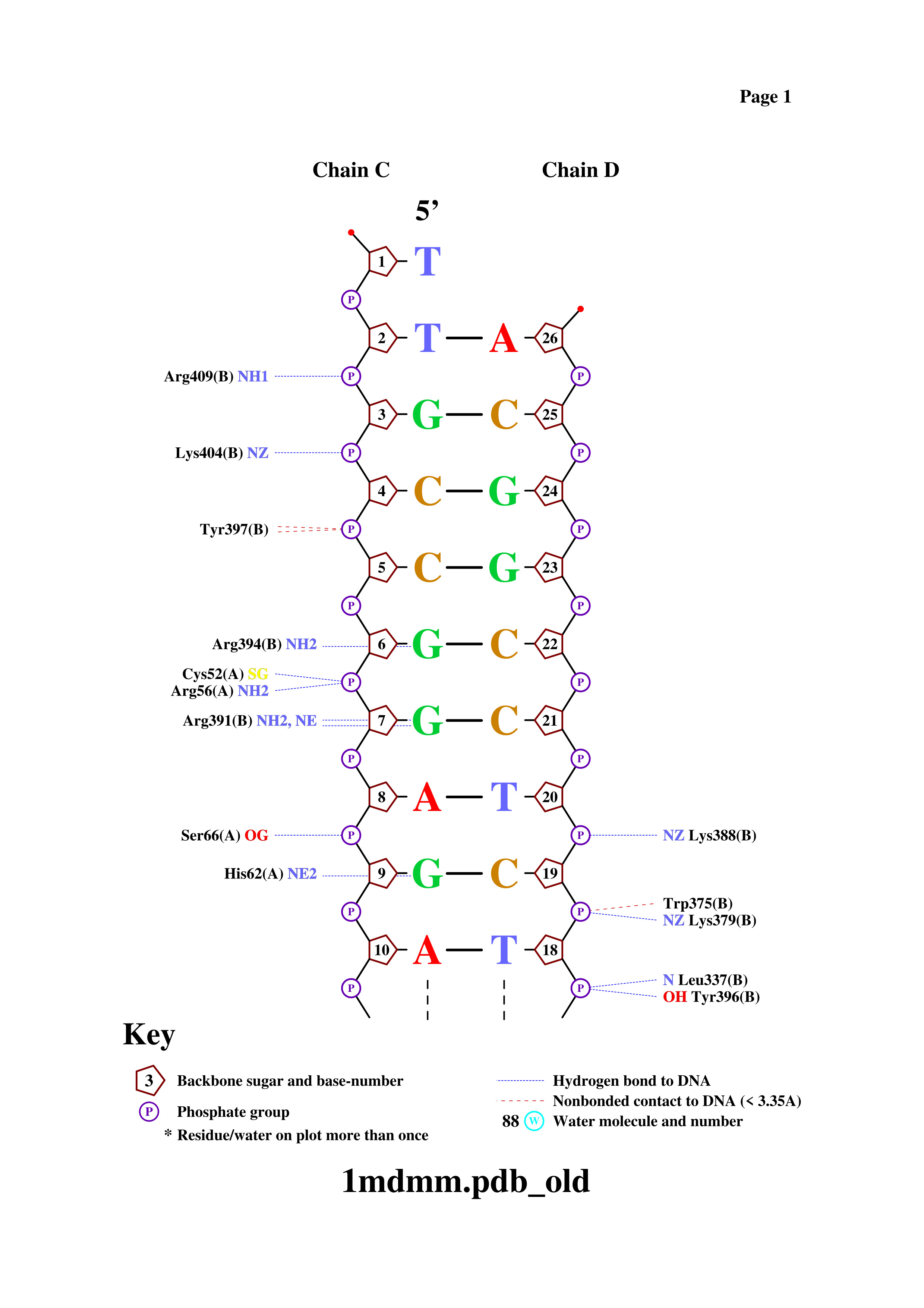
Подсчёт контактов проводился по следующим критериям: полярные атомы (O, N) на расстоянии < 3.5 Å, неполярные (C, P, S) на расстоянии < 4.5 Å.
| Контакты атомов белка с | Полярные | Неполярные | Всего |
|---|---|---|---|
| остатками 2'-дезоксирибозы | 3 | 13 | 16 |
| остатками фосфорной кислоты | 9 | 6 | 15 |
| остатками азотистых оснований со стороны большой бороздки | 4 | 11 | 15 |
| остатками азотистых оснований со стороны малой бороздки | 0 | 1 | 1 |
Резюме: Наибольшее число контактов приходится на сахарофосфатный остов (рибоза + фосфат — 31 контакт), что характерно для неспецифического связывания. Контакты с азотистыми основаниями сосредоточены в большой бороздке (15 против 1 в малой), что указывает на специфическое распознавание последовательности ДНК преимущественно через большую бороздку.
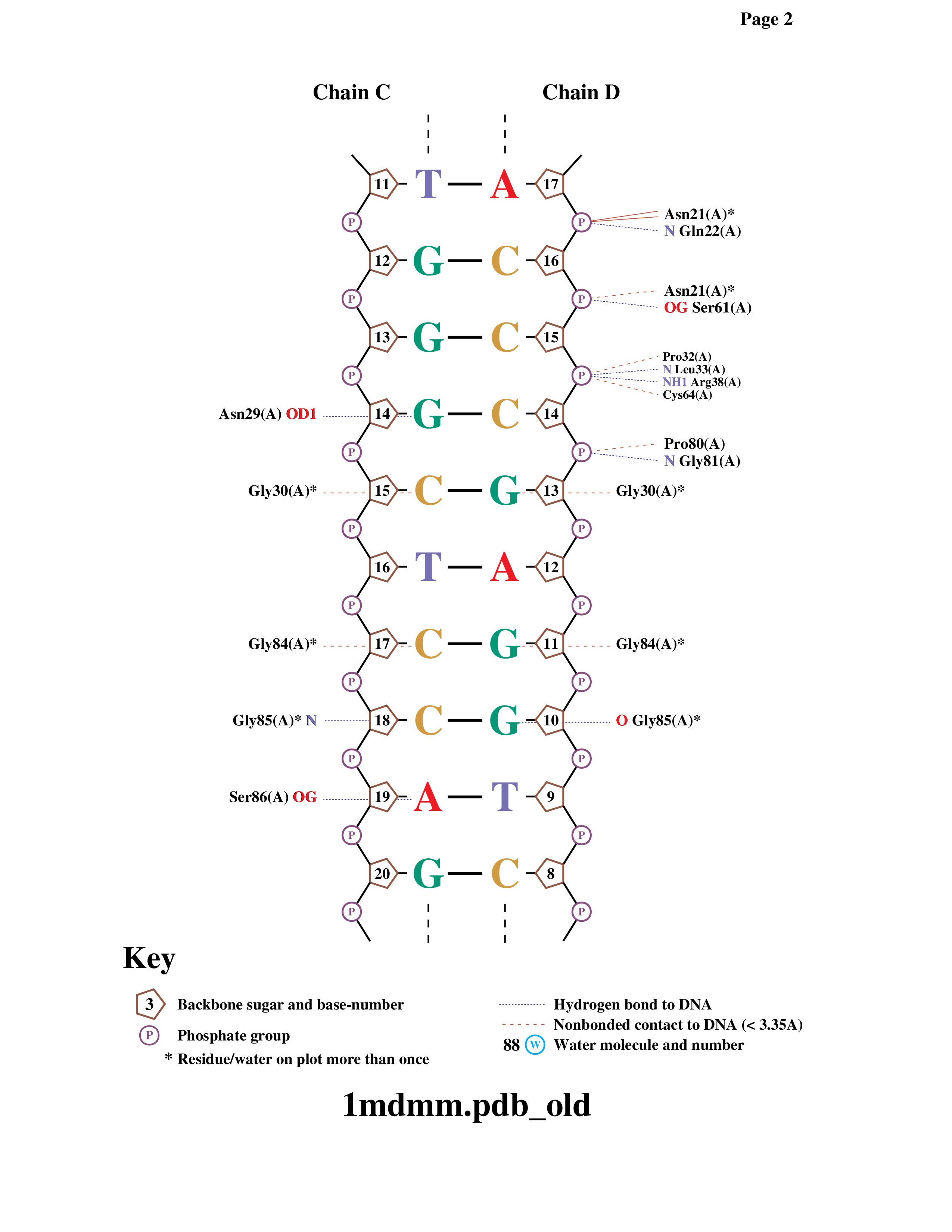
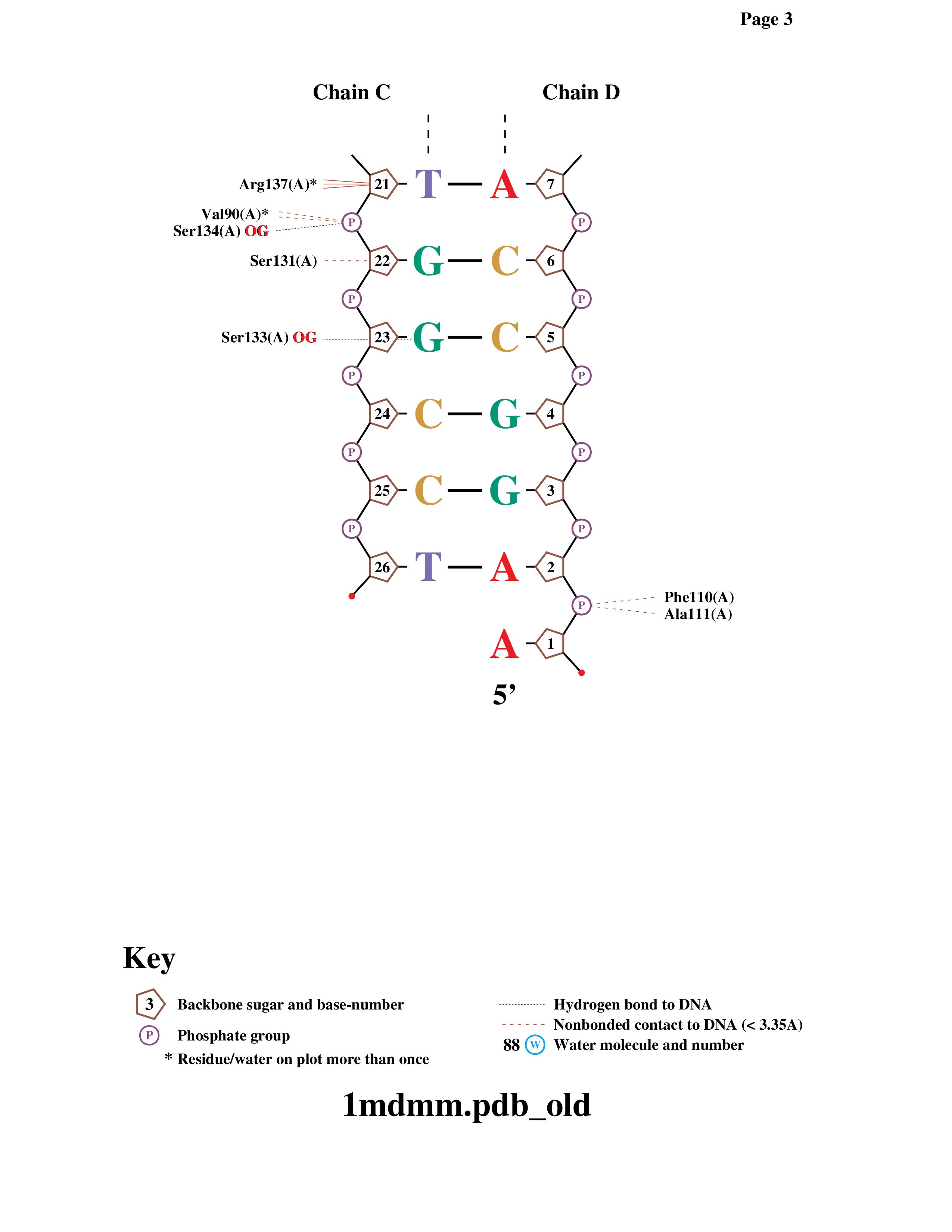
Задание 3. Схема ДНК-белковых контактов (nucplot)
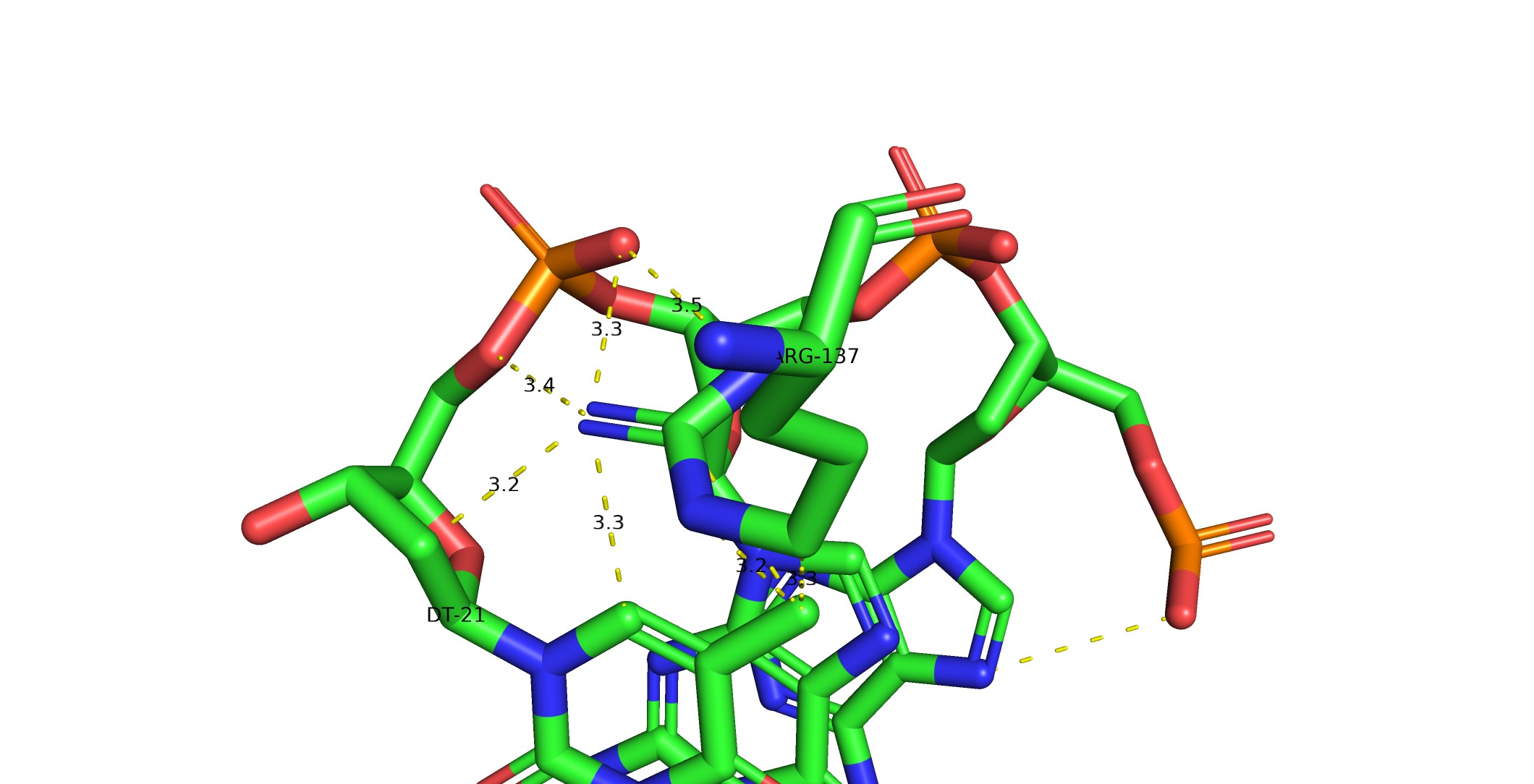
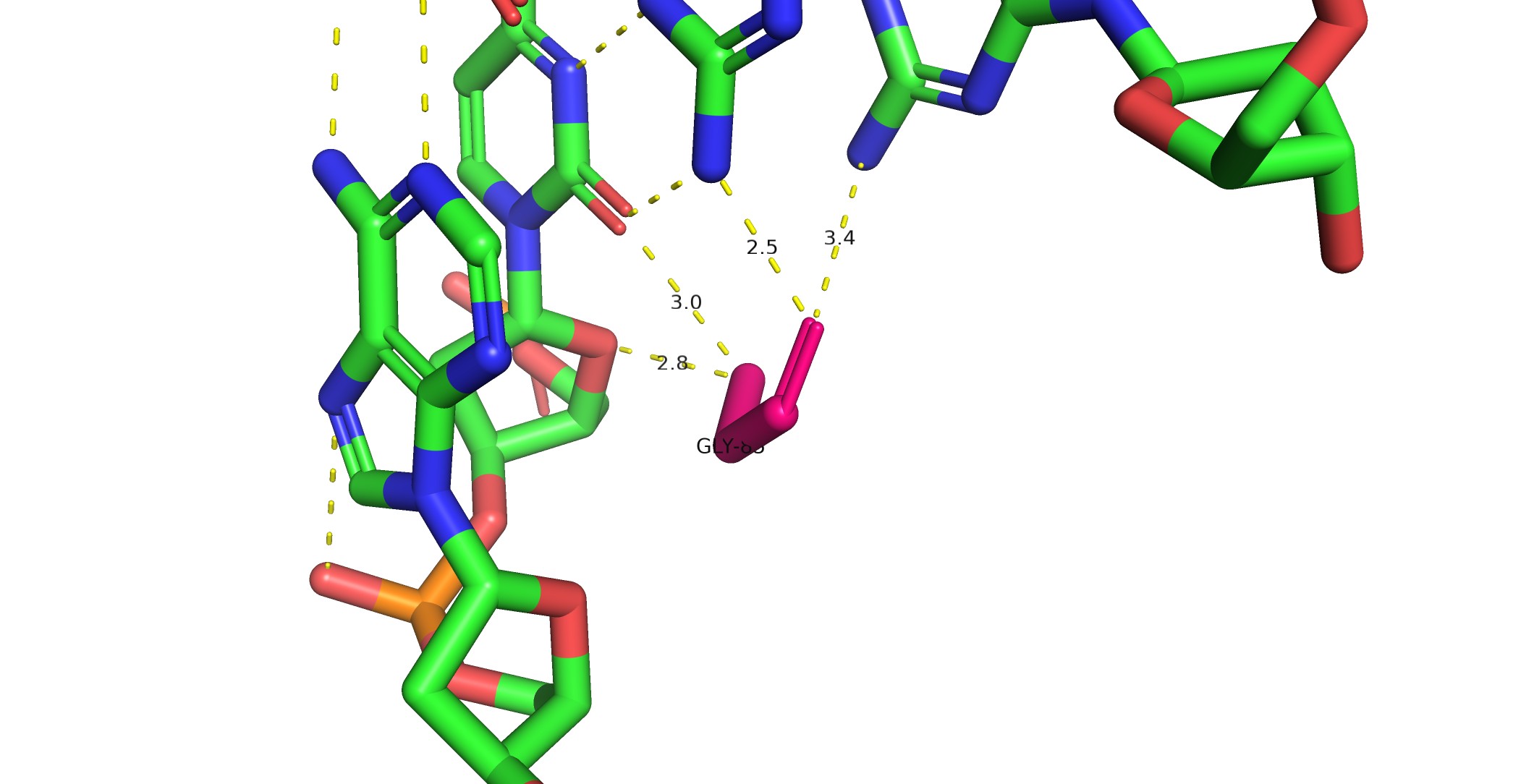
С помощью программы nucplot получены схемы контактов между ДНК и белком в структуре 1mdm. На рисунках 2–4 представлены все межмолекулярные взаимодействия.
Задание 4. Анализ ключевых аминокислотных остатков
ARG 137 — аминокислотный остаток с наибольшим числом указанных на схеме контактов с ДНК (5 связей). Он образует множественные водородные связи с фосфатными группами и основаниями, играя ключевую роль в удержании ДНК.
GLY 85 — остаток, наиболее важный для распознавания последовательности ДНК, так как он контактирует непосредственно с двумя азотистыми основаниями (а не с остовом), обеспечивая специфичность связывания.