Реконструкция по нуклеотидным последовательностям
Поиск митохондриальных последовательностей наших видов
Мы искали митохондриальные последовательности видов, для которых мы выравнивали цитохромы B в прошлом практикуме.
К сожалению, полные митохондриальные последовательности нашлись не для всех видов.
Для дятла Sphyrapicus varius ближайший родственник с митохондриальной ДНК в базе это Dendrocopos leucotos, тоже дятел. SPHVA -> DENLC Американскую ворону Corvus brachyrhynchos заменили - на Ворону обыкновенную Corvus corax CORBR -> CORCX Nothoprocta perdicaria на Nothoprocta pentlandii NOTPE -> 9AVES Kуропатку Callipepla gambelii - на Callipepla squamata CALGU -> CALSU Paradisaea minor - на Paradisaea raggiana PARMI -> 9CORV Для Paradisaea rudolphi в том же роде и отряде не нашлось замены, пришлось исключить. PARRU -> _ Catharus guttatus на Catharus fuscescens 9TURD - это два дрозда CATGU -> 9TURD Южномексиканского сокола (Falco femoralis) заменили на Сапана - Falco peregrinus FALFE -> FALPE CHICK, CORCD без изменений
Извлекали командами типа:
seqret embl:AF090339[1230:2192] RHEAM_12S_rRNA.fasta
Получилось 10 последовательностей. Записали это всё в файл cat *12S_rRNA.fasta > combined_12S.fasta и выровняли в MSAProbs в Jalview. Дерево построили с помощью iqtree, визуализировано в iTOL.
В местах с двойными названиями показаны замены видов.
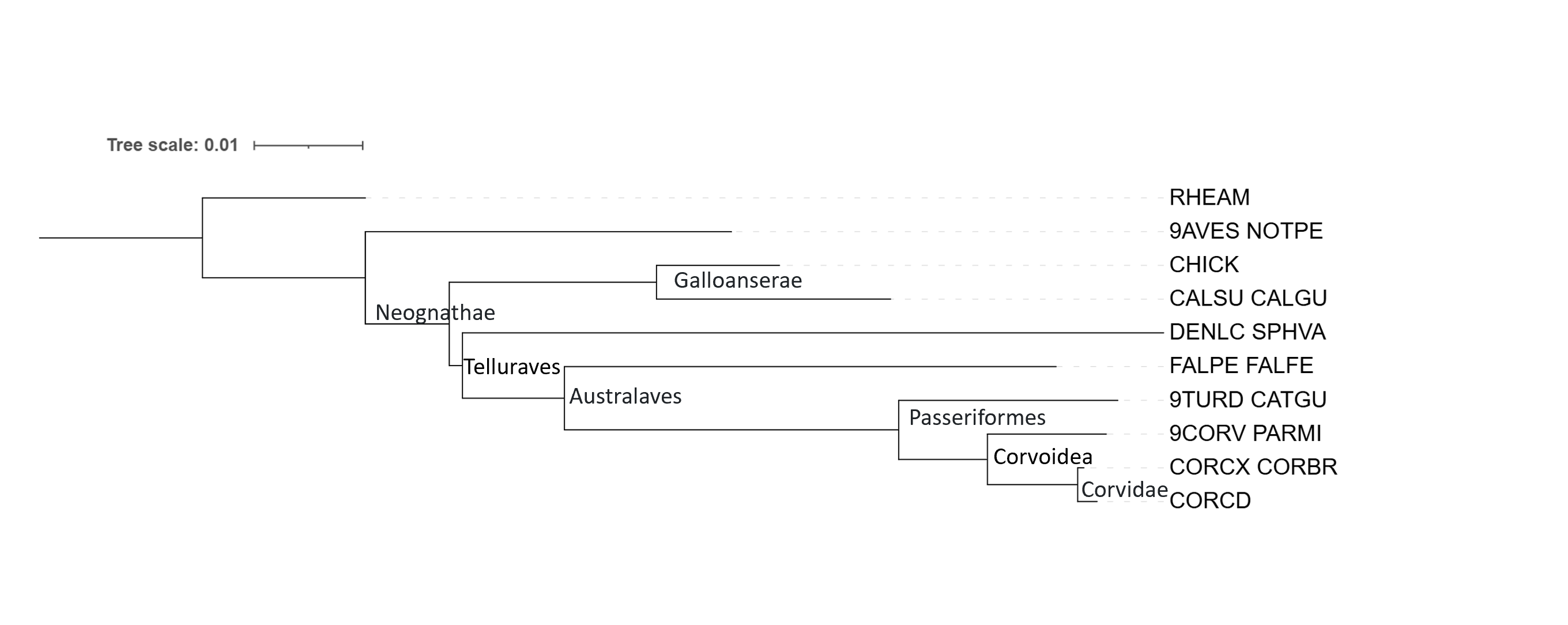
Дерево сделано гораздо лучше, чем те что мы строили ранее. Оно полностью соответствует таксономическому дереву.
Сначала отделяются курица (CHICK) и куропатка (CALSU), а уже потом идут хищные - FALPE и дятлы - DENLC. Курицы, куропатки это Galloanseres, а не Neoaves.
Дятел DENLC отделяется раньше, чем FALPE. DENLC в кладе Afroaves, а FALPE и тд это Australaves
Тут сначала отделяется дрозд 9TURD, а потом Райская птица 9CORV, в дереве по цитохрому B было наоборот. Верным является эта вариация. Райские птицы (Paradisaeidae) находятся в надсемействе Виреоновые (Corvoidea), вместе с врановыми (Corvidae).
Вороны в одной кладе, но с отличающимися от прошлого дерева эволюционными расстояниями.
Переукоренение относительно внешней группы
Мы взяли другого родственника динозавров — варана Varanus salvator komaini (VARSL). Хотели взять крокодила, но их митохондриальные геномы не отсеквенировали((

RHEMA и NOTPE поменялись местами, но не в одной кладе, как должны быть. И дятла DENLC отнесло от клады, где он должен быть к Galloanseres (CHICK и CALSU). Это неправильно. Правильно в предыдущем дереве, где DENLC в одной кладе с FALPE и воробьинообразными.
Bootstrap
fastme -i task3_ali.phy -pM -o task3.fastme -b 100
Маленькая достоверность у ветви с DENLC, это уже обсуждалось много раз, что этот дятел должен быть в одной кладе с FALPE и Passeriformes, внутри Telluraves