Практикум №2
Визуализация реконструированных деревьев
С помощью программы Fastme, используя две разные модели для оценки эволюционных расстояний: p-distance; MtREV, а также с помощью программы iqtree, были реконструированны филогенетические деревья на основе организмов, по которыми было построено дерево в практикуме №1.
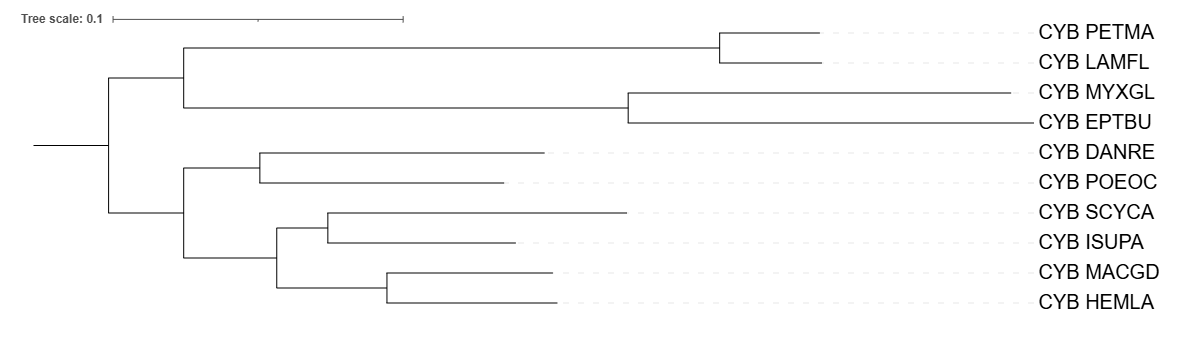
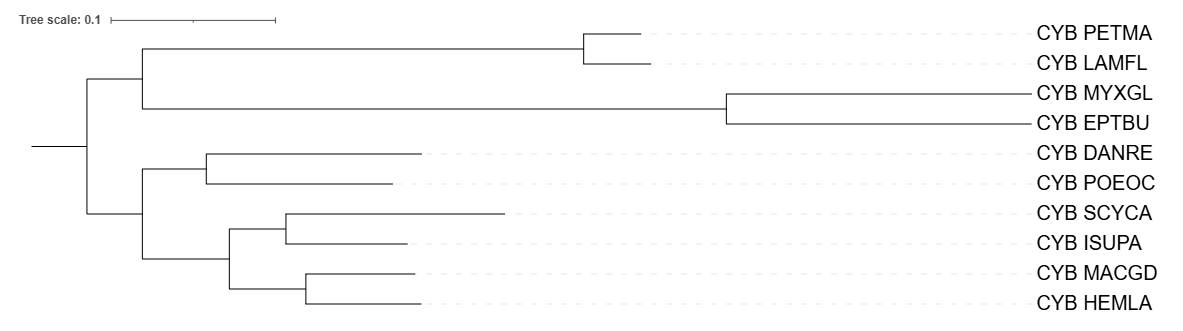
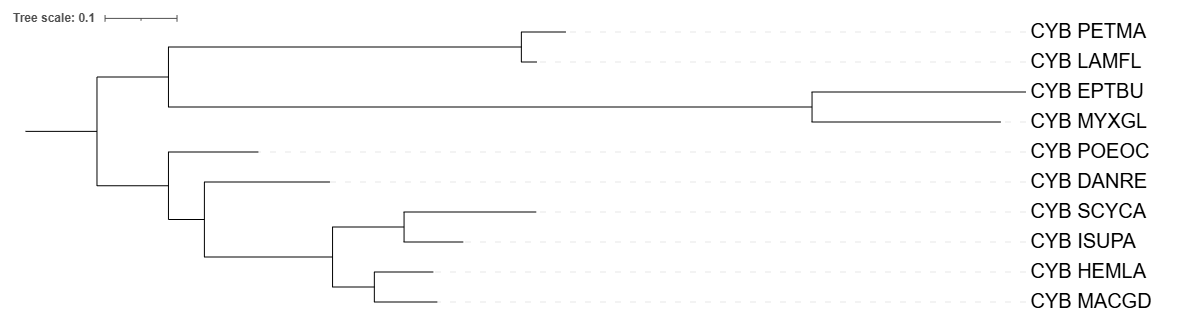
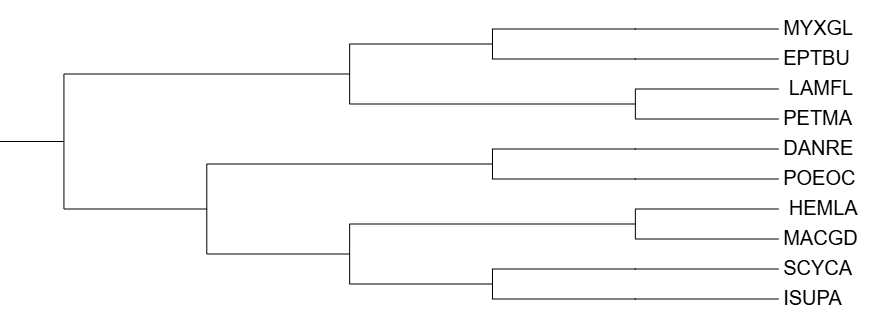
Все деревья удалось укоренить в соответсвии с таксономией, по сравнению с исходным деревом, построенным по таксономии NCBI Taxonomy, после работы программы Fastme никаких изменений не наблюдалось, клады остались прежними. Но при построении дерева программой iqtree клада (POEOC; DANRE) разделилась на две отдельные ветви. В целом реконструированные деревья не сильно отличаются от исходного, построенного вручную, я считаю, что это связано с тем, что были подобраны довольно близкородственные организмы.