Практикум №3
1. Реконструкция дерева по нуклеотидным последовательностям
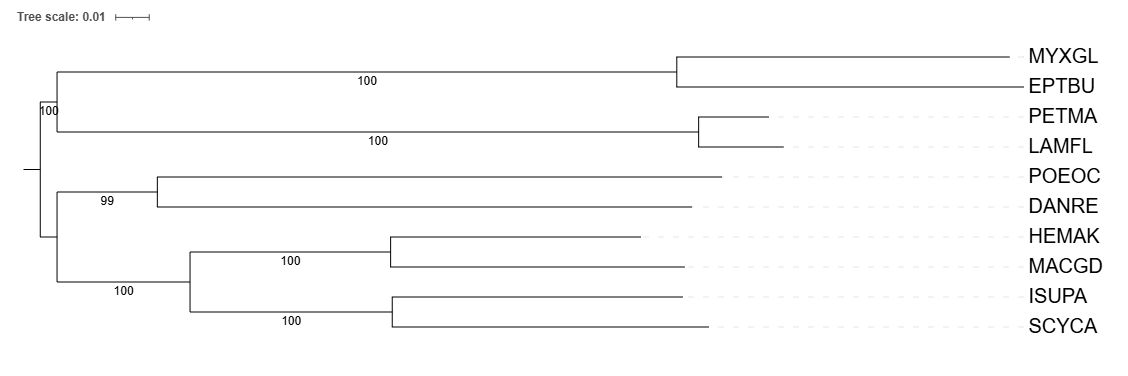
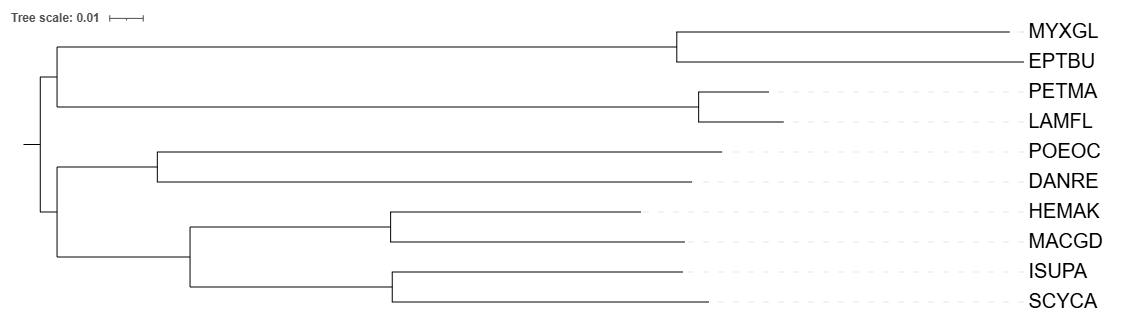
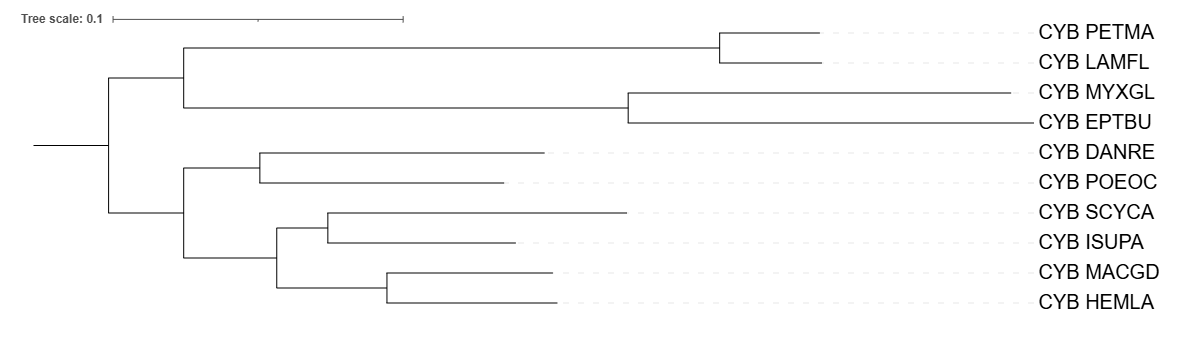
Никаких значительных изменений не обнаружено, за исключением замены вида Hemitrygon laosensis (HEMLA) на вид Hemitrygon akajei (HEMAK) при реконструировании дерева по 12s субъединице рРНК. При этом у HEMAK последовательности Цитохрома Б я не нашел.
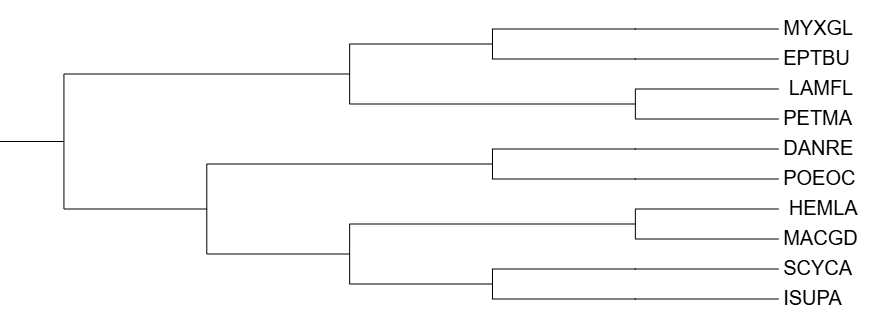
2. Укоренение во внешнюю группу
Посколько все мои организмы относились к подтипу Craniata, я выбрал организм, относящийся к подтипу Cephalochordata - Branchiostoma lanceolatum, я подобрал его так, что у него есть белок Cytochrome b, но реконструировал дерево с участием данного организма по нуклеотидной последовательности 12s субъединицы рРНК.
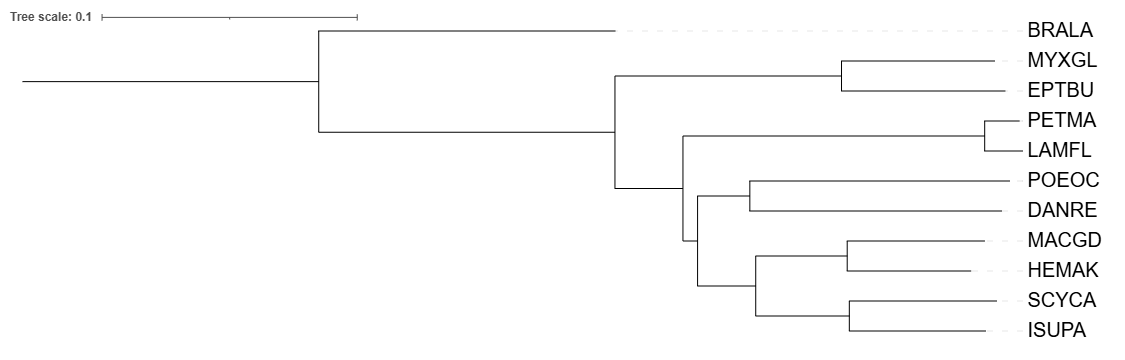
3. Бутстреп
На реконструированном дереве можно увидеть, что ветви имеют высокие числа поддержки - 100, а одно 99, но это все равно говорит о том, что реконструкция была проведена корректно.