Практикум №4
1. Составление списка гомологичных белков, включающих паралоги
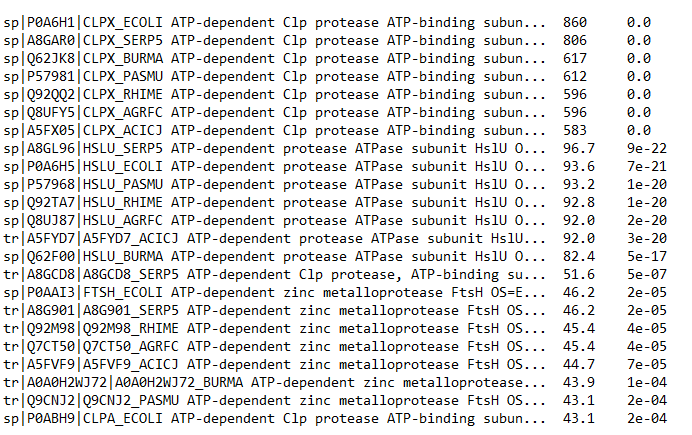
Я выбрал следующие бактерии: ACICJ; AGRFC; BURMA; ECOLI; RHIME; PASMU; SERP5 с помощью blastp с e-value 0.0001 я нашел гомологичные белки и составил их список с последовательностями.
2. Реконструкция и визуализация
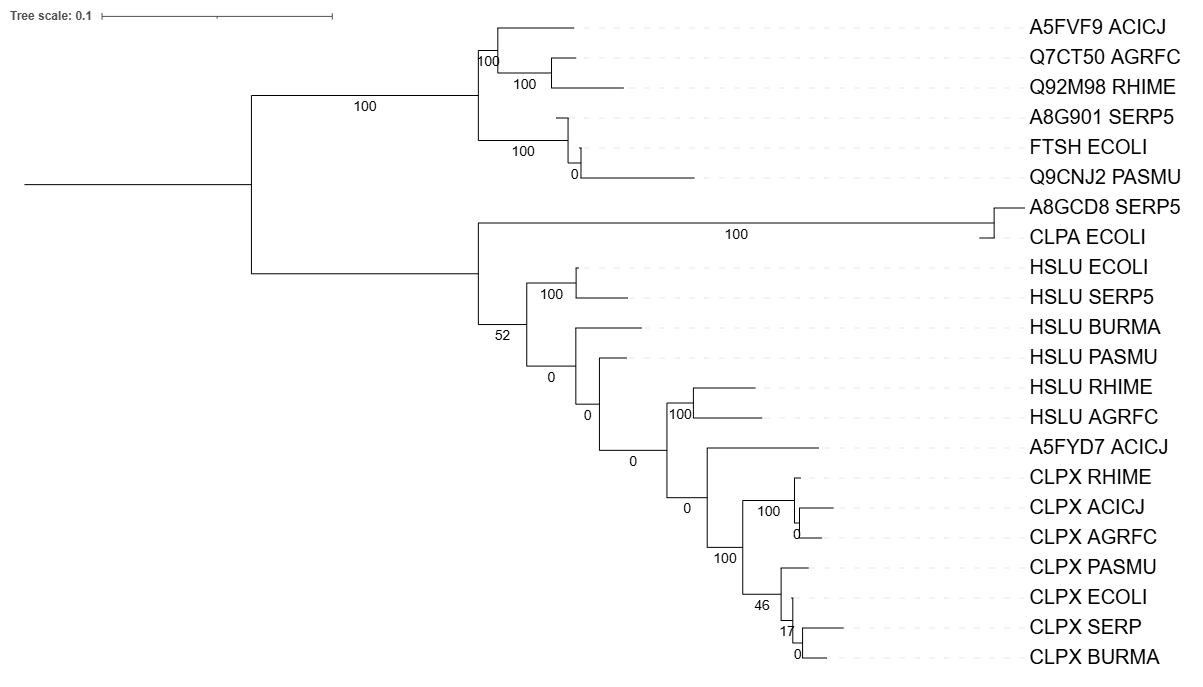
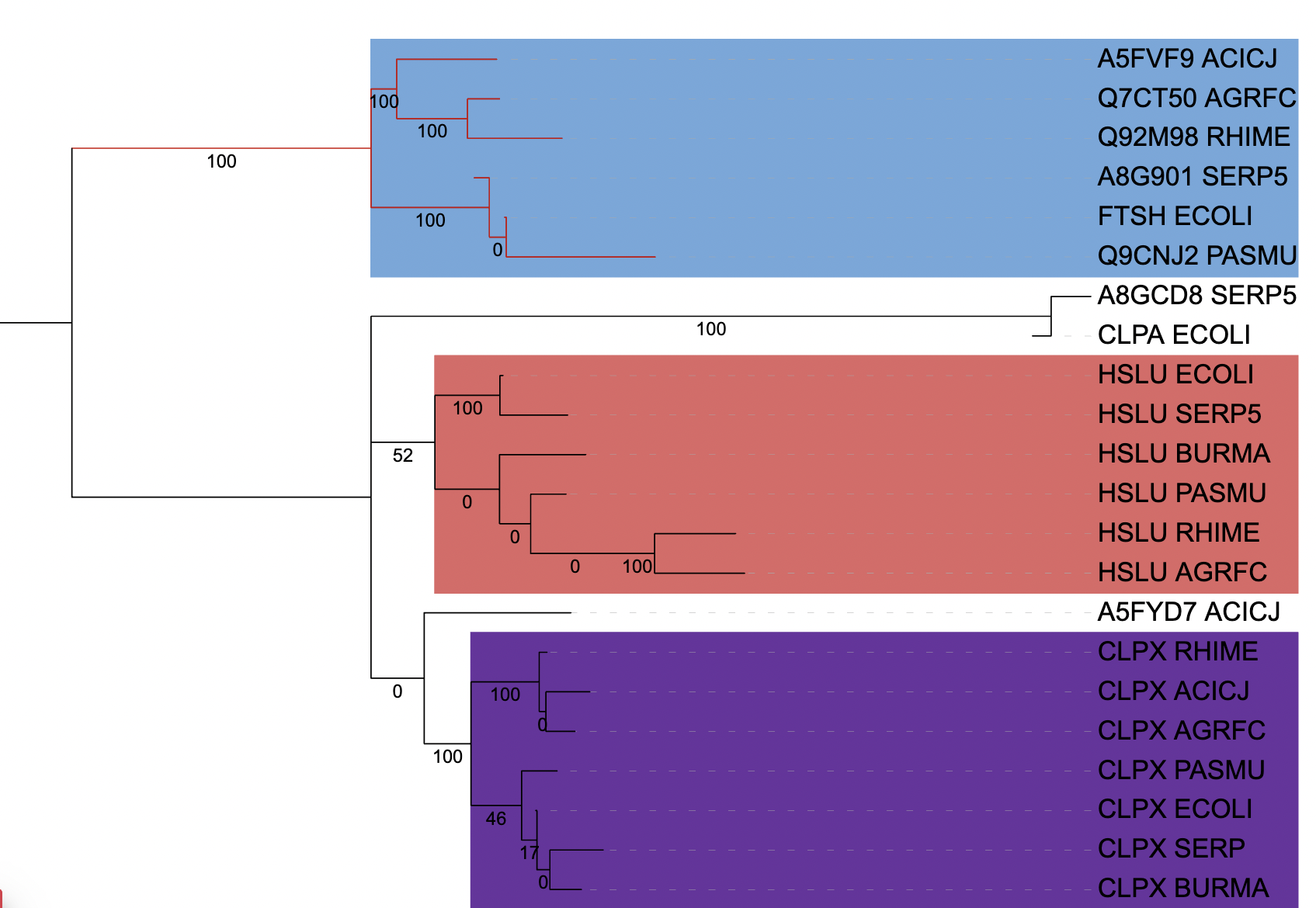
Паралоги: HSLU_ECOLI - CLPX_ECOLI; HSLU_SERP5 - CLPX_SERP5; HSLU_RHIME - CLPX_RHIME
Ортологи: CLPX_SERP5; CLPX_BURMA; CLPX_ACICJ
Тоже ортологи: Q9CNJ2_PASMU; FTSH_ECOLI; A8G901_SERP5; A5FVF9_ACICJ; Q92M98_RHIME; Q7CT50_AGRFC
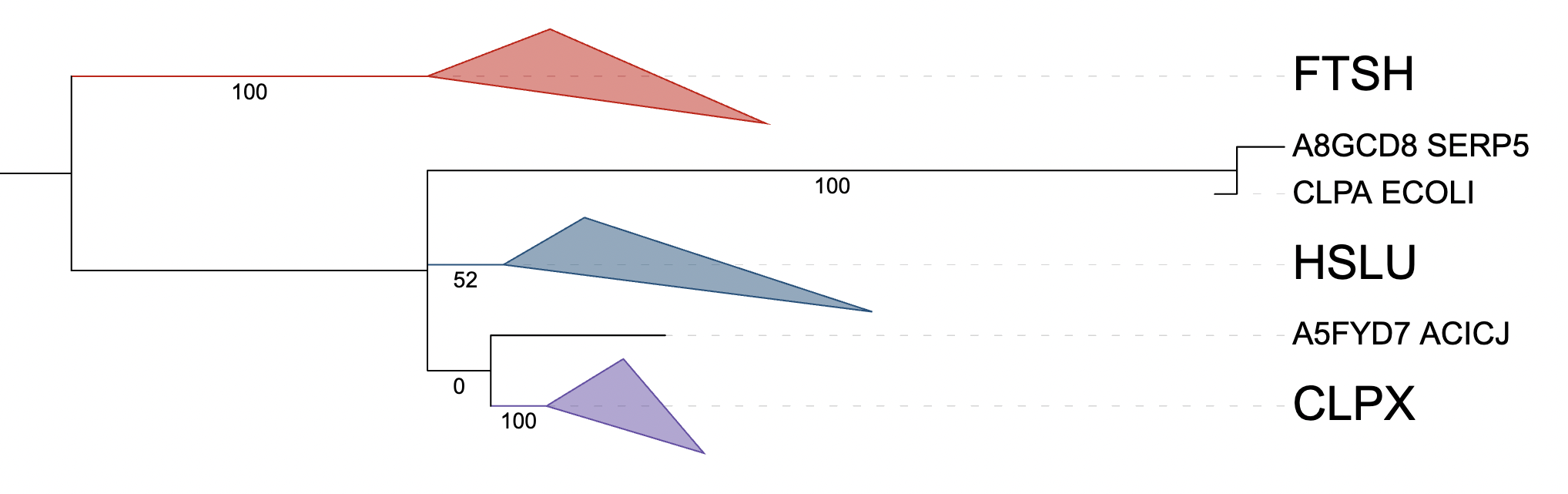
Были схлопнуты в группу CLPX (ATP-dependent Clp protease ATP-binding subunit ClpX) CLPX_RHIME; CLPX_ACICJ; CLPX_AGRFC; CLPX_PASMU; CLPX_ECOLI; CLPX_SERP5; CLPX_BURMA, а также в группу HSLU (ATP-dependent protease ATPase subunit HslU) HSLU_ECOLI; HSLU_SERP5; HSLU_BURMA; HSLU_PASMU; HSLU_RHIME; HSLU_AGRFC и в группу FTSH (если я правильно выявил мнемонику, в названии белка везде есть ftsh, хотя сами мнемоники отдедьно у всех белков этой группы разные, полное название у них одинаковое) : ATP-dependent zinc metalloprotease FtsH Q9CNJ2_PASMU ; FTSH_ECOLI ; A8G901_SERP5; A5FVF9_ACICJ; Q92M98_RHIME; Q7CT50_AGRFC
Я считаю, что филогения белков реконструированного дерева много где соответсвует филогении бактерий, но есть и некоторые расхождения. Один из примеров: в филогении бактерий SERP5; ECOLI находятся близко друг к другу, как и белки HSLU_ECOLI; HSLU_SERP5, в то же время PASMU; BURMA находятся дальше на дереве бактерий, чем HSLU_BURMA; HSLU_PASMU на дереве белков. Все белки ортологи FTSH остались в том же виде, что и на исходном дереве.