
|
|
|
||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|
Задание 1. Модели структур A-, B- и Z-формы ДНК, построенные с помощью программы fiber из пакета 3DNA: gatc-a gatc-b gatc-z Задание 2 Упражнение 1. С помощью программы Jmol я выделила различные множества атомов: 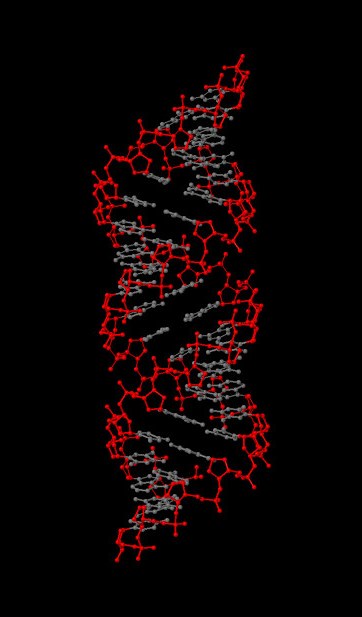 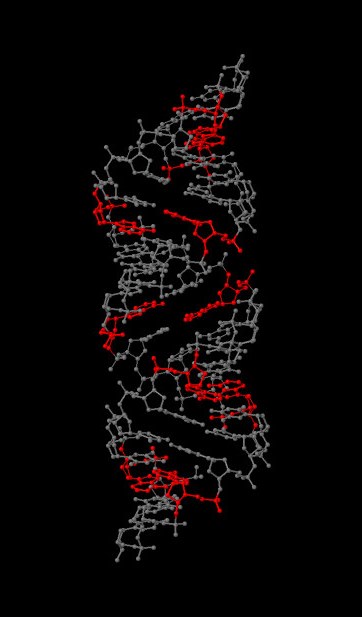 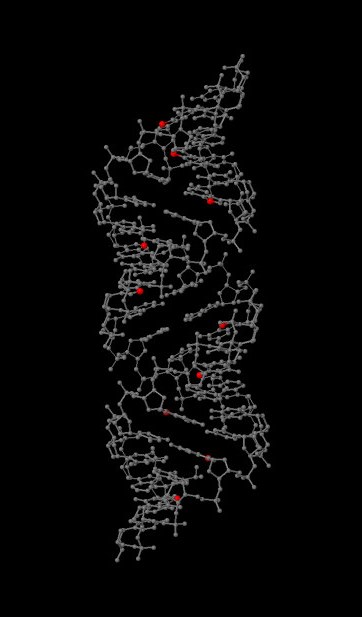 На самом левом изображении красным цветом выделен сахарофосфатный остов ДНК, на центральном все нулеотиды, содержащие основание аденин, на правом атом N7 во всех гуанинах. Упражнение 3. С сайта pdb я получила файлы структуры тРНК с ID 1n78 и ДНК-белкового комплекса с ID 1irj. Чтобы проверить их на разрывы, я выделила в программе Jmol только атомы, относящиеся к нуклеиновым кислотам, и представила в удобном виде(слева - wireframe, справа - backbone). ДНК: 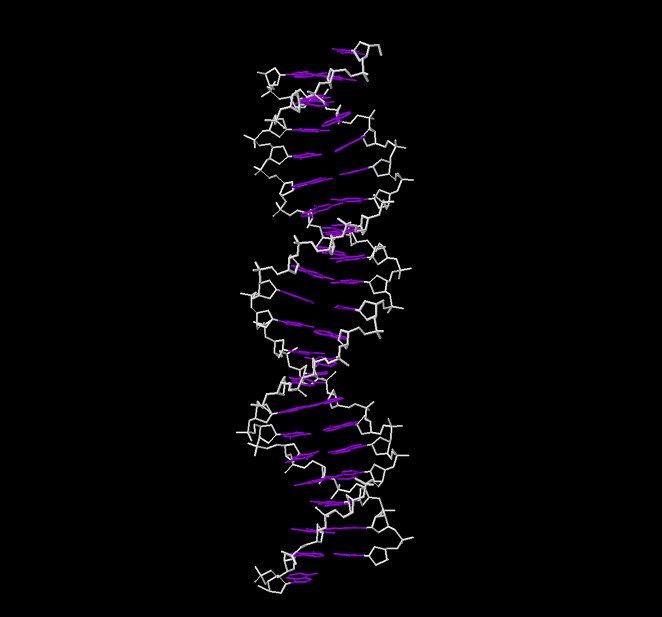  РНК:   На рисунках видно, что разрывов ни в ДНК, ни в РНК нет. Задание 3. Упражнение 1. С помощью Jmol я рассмотрела различные формы ДНК и определила для гуанина, в сторону каких бороздок направлены различные, составляющие его атомы. На изображениях ниже красным цветом обозначены атомы, смотрящие в сторону большой бороздки, синим в сторону малой. Изображения получены в программе ChemSketch. Упражнение 2. Ниже приведена таблица с основными спиральными параметрами различных форм ДНК.
Далее привожу иллюстрации к измерениям. Измерение Длины витка и количества остатков на виток. Белым цветом выделены атомы C1. А-форма: 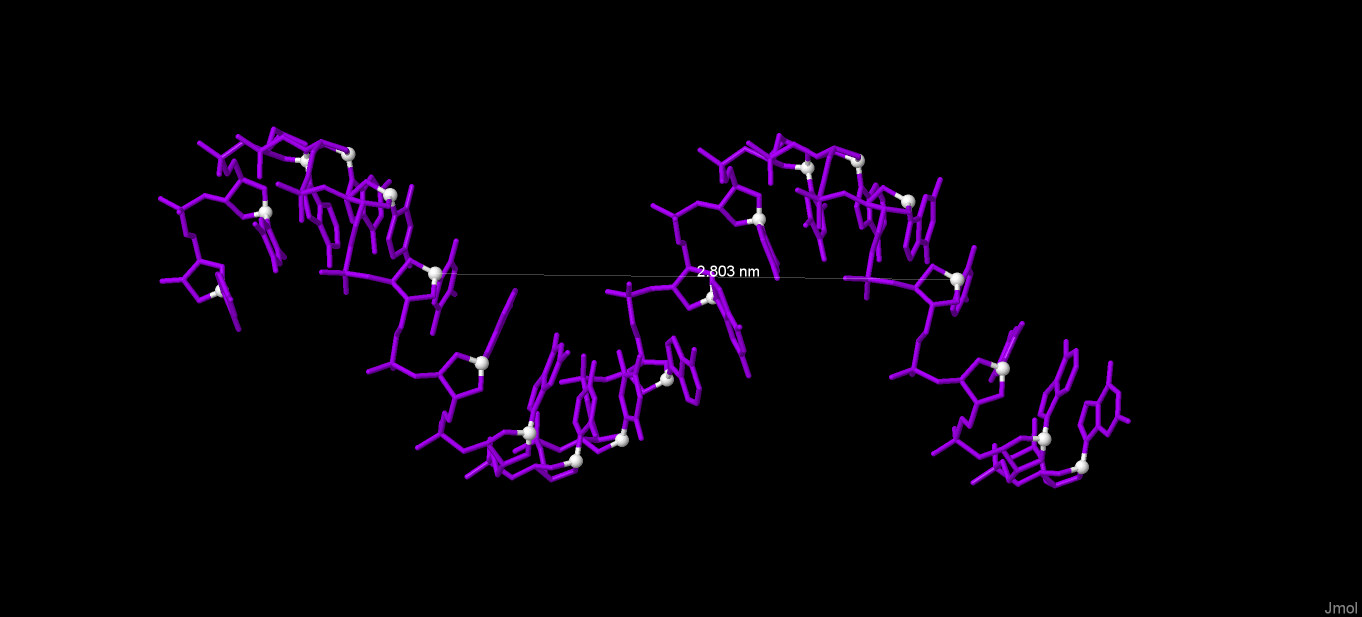 B-форма: 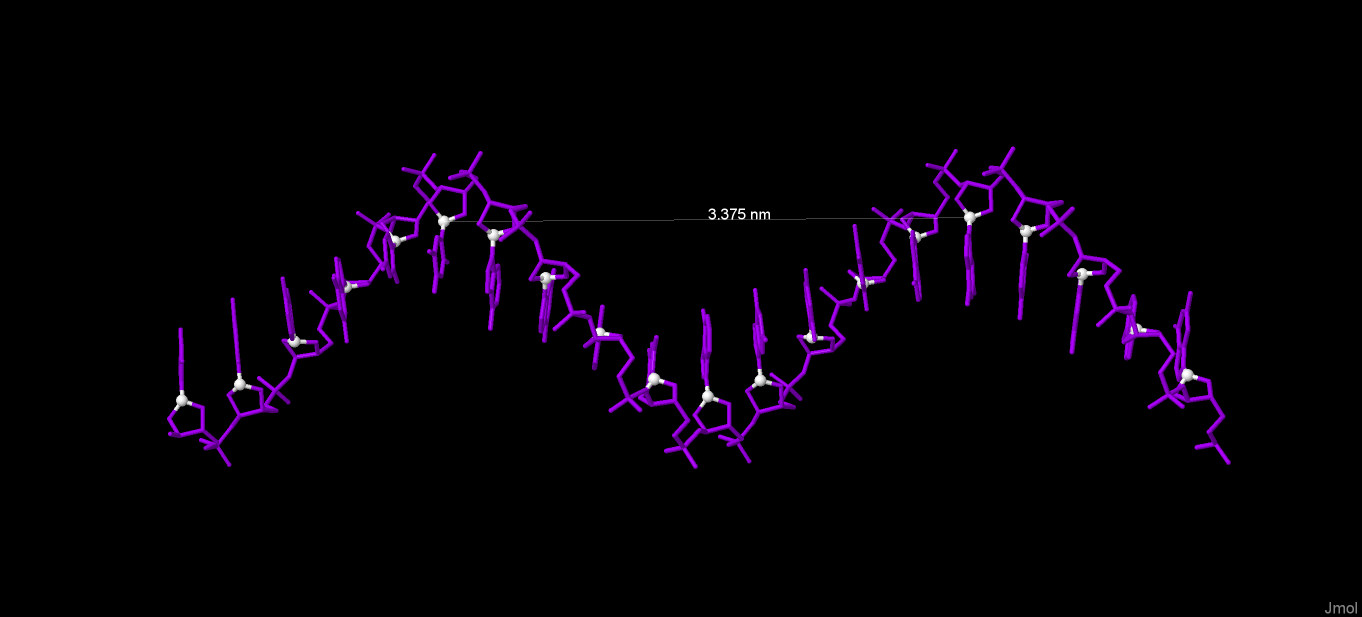 Z-форма: 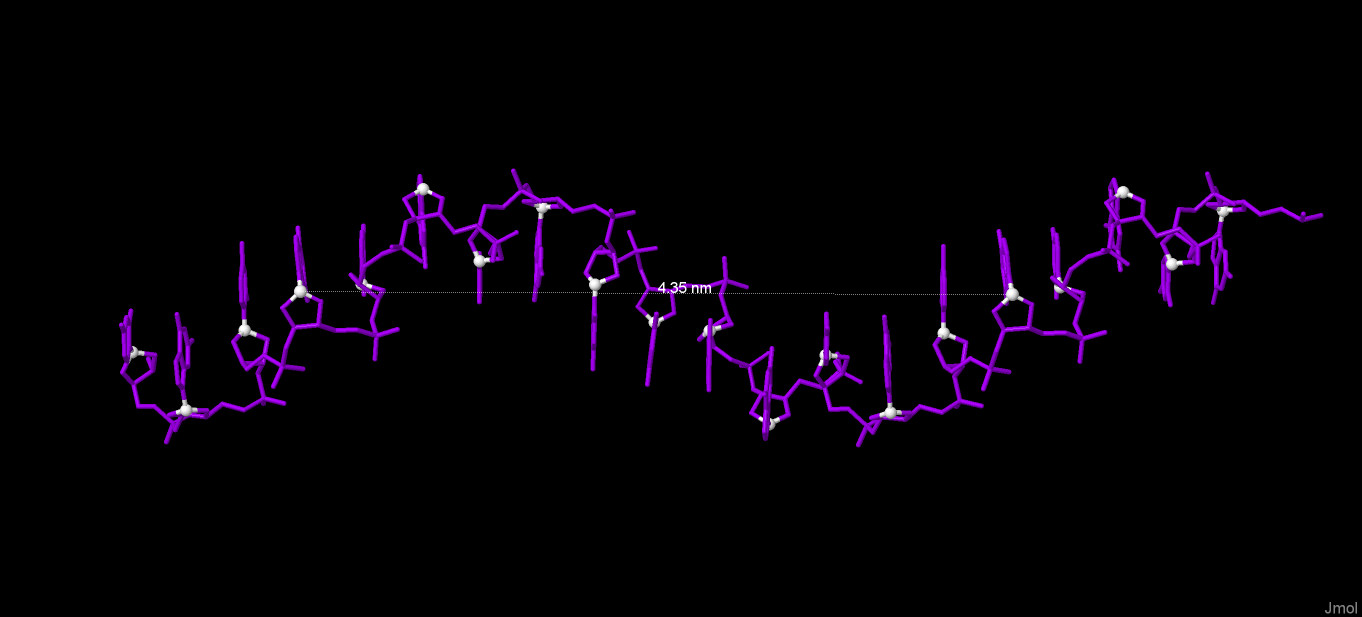 Измерение ширины большой и малой бороздок. Красным и зеленым цветами выделены атомы фосфора разных цепей. А-форма: 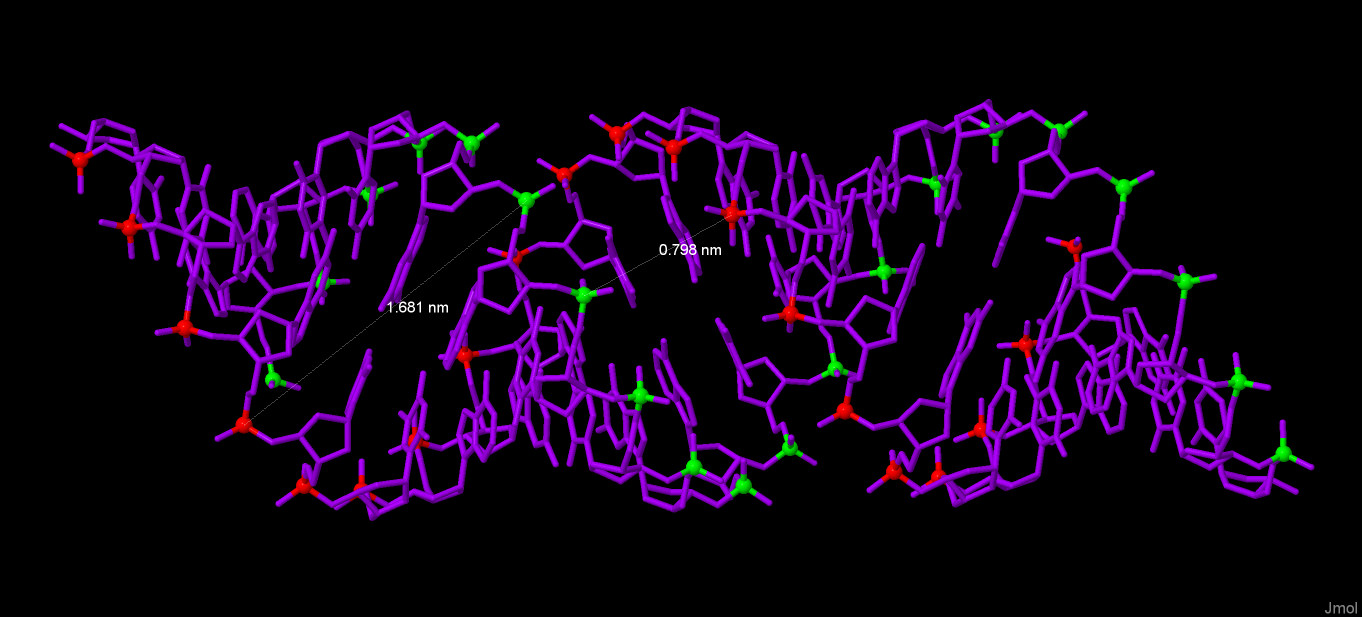 B-форма: 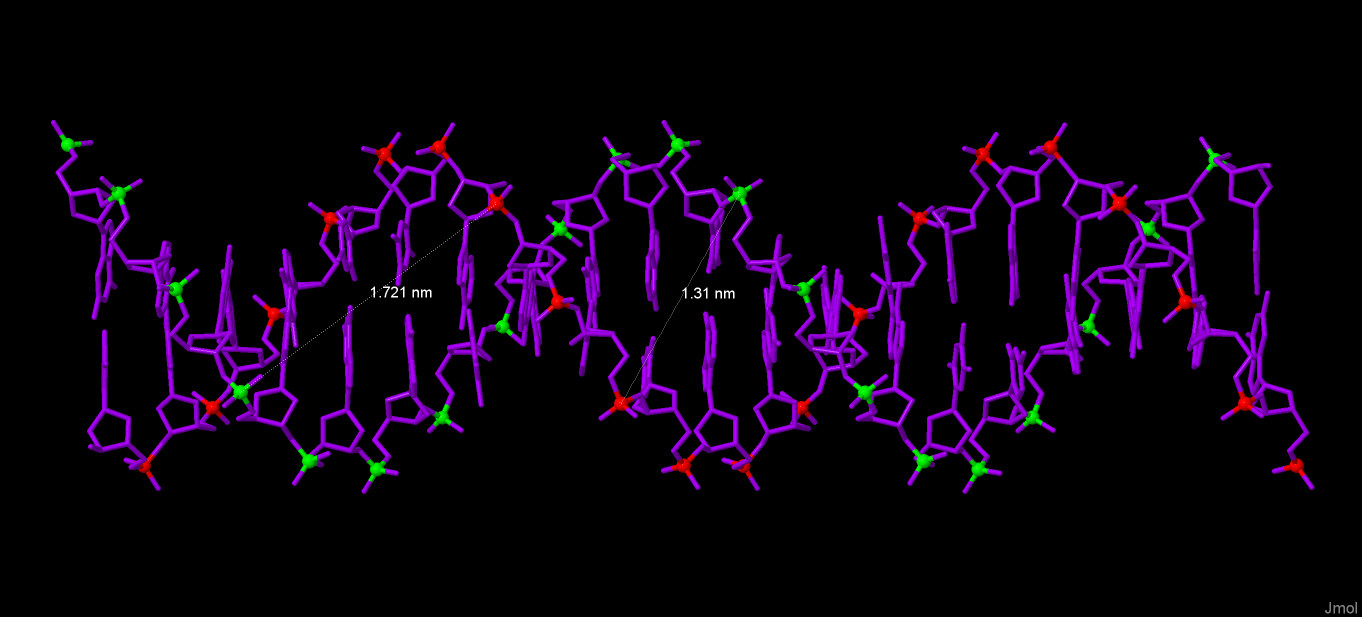 Z-форма: 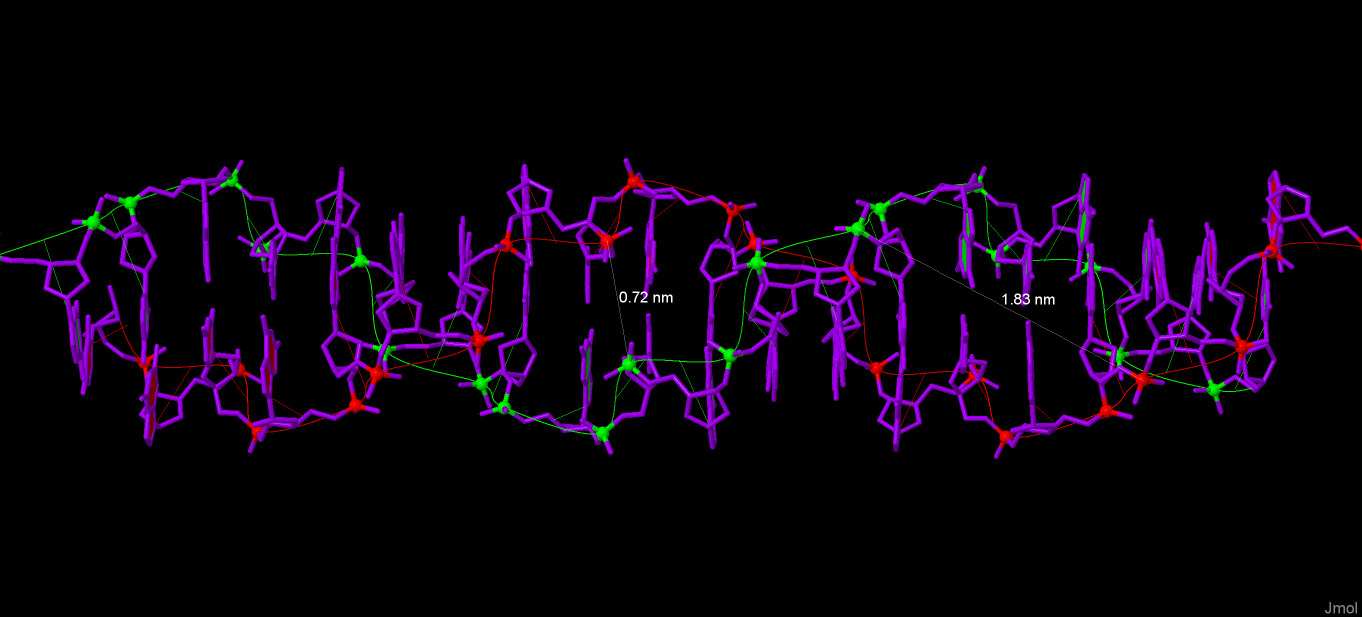 Упражнение 3.
Задание 4. Упражнение 1. С помощью программы remediator я перевела свои pdb-структуры в старый формат - тРНК_old и ДНК_old. Далее я получила набор параметров структур из данных файлов с помощью последовательного применения программ find_pair и analyse. Из файла 1I3J_old.out я получила значения торисонных углов в заданной структуре ДНК. Результат представлен в таблице Excel. Приведенные под таблицами по двум цепям средние значения торсионных углов не всегда хорошо отражают данные, так как среди них есть большие положительные и отрицательные значения, из-за чего средний угол получается маленьким. Самым отклоняющимся нуклеотидом я бы назвала С9 первой цепи. Углы альфа и гамма у него наибольшие среди других нуклеотидов, дельта и хи наименьшие. Аналогичную работу я проделала для тРНК(выдача analyse, таблица по торсионным углам РНК). Для данной структуры наиболее выделяющимся оказался G11 первой цепи.
Ссылки на таблицы в html-виде: тРНК и ДНК Упражнение 2. На изображении ниже в рамку обведены пары нуклеотидов, образующие петли в данной мне структуре тРНК:[501-507] - [566-572];[549-553] - [561-565];[538-544] - [526-532];[510-513] - [522-525]. Далее красной рамкой выделены неканонические пары оснований: G[502]-U[571], U[555]-G[518], A[538]-C[532], A[544]-G[526], U[513]-G[522].  В структуре также присутствует одна водородная связь, обеспечивающая дополнительную стабильность структуры. 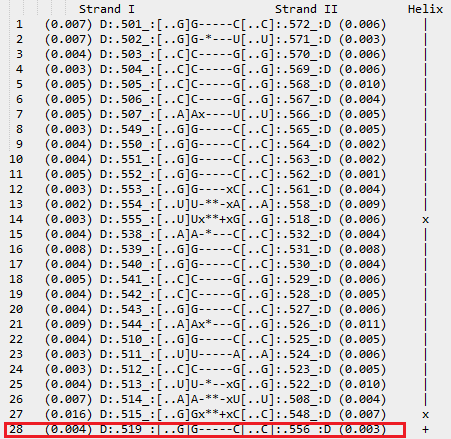 Упражнение 3. Рассмотрим стекинг взаимодействия между разными парами оснований в тРНК. 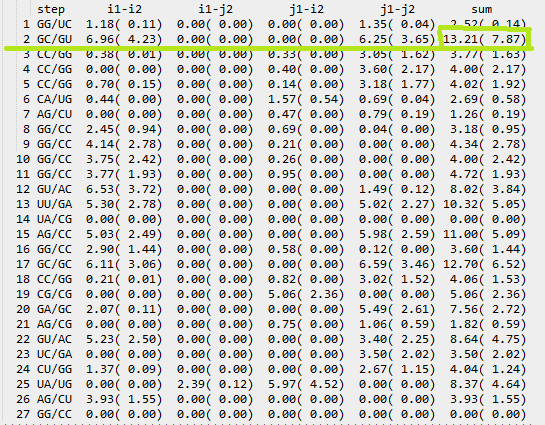 Зеленой рамочкой выделена наибольшая площадь перекрывания двух последовательных пар азотистых оснований. Я получила стандартное изображение стекинг-взаимодействия. 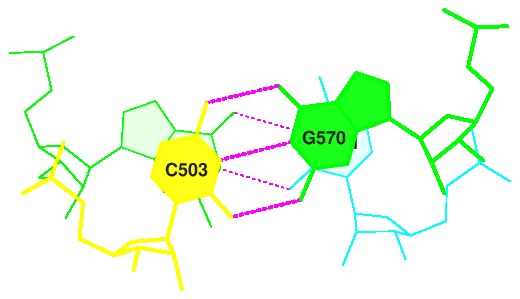 ПРИМЕЧАНИЕ: где-то в середине семестра я случайно удалила файл с этим практикумом, заметила это совсем недавно, и мне пришлось делать его заново. Изначально он был сделан вовремя, это должны подтверждать даты создания файлов от программы analyse, например. |
|||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
© Шугаева Т.Е. 2015