
|
|
|
||||||||||||||||
|
Занятие 12, блок 4. Эволюционные домены. Задание 1. Построение выравнивание представителей домена Pfam белков с разной доменной архитектурой Выбран домен, гомологичный меприновым и TRAF-белкам(ссылка на страницу в Pfam). Меприновые белки расщепляют белковые субстраты по гидрофобным остаткам. АС: PF00917 ID: MATH Доменные архитектуры, содержащие MATH перечислены на соответствущей странице Pfam. Я выбрала 2 доменные архитектуры: одна содержит домены MATH(946 последовательностей), вторая MATH и BTB(814 последовательности). BTB - относительно распространенный домен, который регулирует гомомерную, а в некоторых случаях и гетеромерную димеризацию. В качестве таксона я выбрала царство Eukaryota, подтаксоны - Metazoa(настоящие животные), Viridiplantae(зеленые растения) и Amoebozoa. Таблица - таблица, содержащая информацию о всех (имевшихся в swisspfam.gz) белках, включающих выбранный мною домен. На вкладке "Отобранные" приведен краткие данные о выбранных последовательностях. Проект jalview с выравниванием отобранных последовательностей. Выравнивание разделено на две группы в соответствии с архитектурой. Раскраска ClustalX с порогом консервативности 5% в обеих группах (при повторном открытии проекта порог консервативности может выставиться по умолчанию - 30%, ничего не могу с этим сделать). Я удалила из выравнивания несколько коротких и плохо выровненных последовательностей, в остальном оно выглядит правильно. Задание 2. Построение филогенетического дерева последовательностей домена 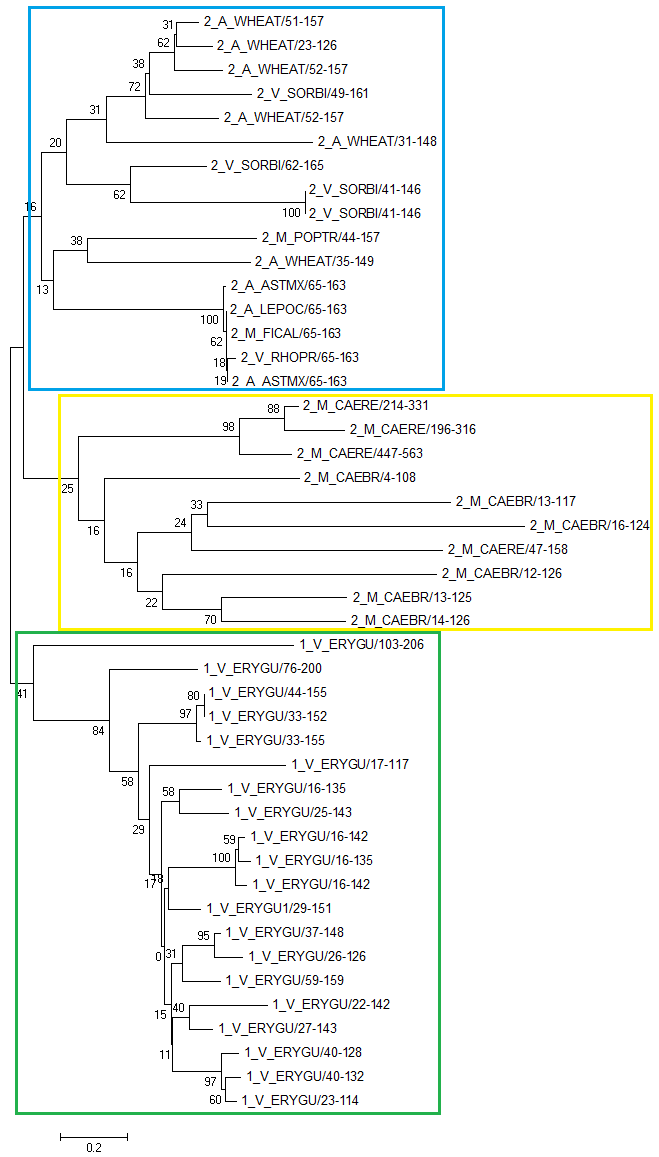
Дерево, построенное по последовательностям домена MATH. 1 - доменная архитектура "MATH", 2 - доменная архитектура "MATH, BTB", M - metazoa, A - amoebozoa, V - viridiplantae. Дерево построено методом NJ с 100 бутстрэп репликами. Скобочная формула дерева - файл. Видно, что дерево точно разбтлось на клады по доменным архитектурам, а также что в одтельную большую кладу выделились последовательности представителей Metazoa вида Caenorhabditis remanei(нематода). Задание 3. Построить профиль подсемейства и охарактеризовать качество его работы. Выбранное мною подсемейство выделено на рисунке фиолетовой рамочкой. 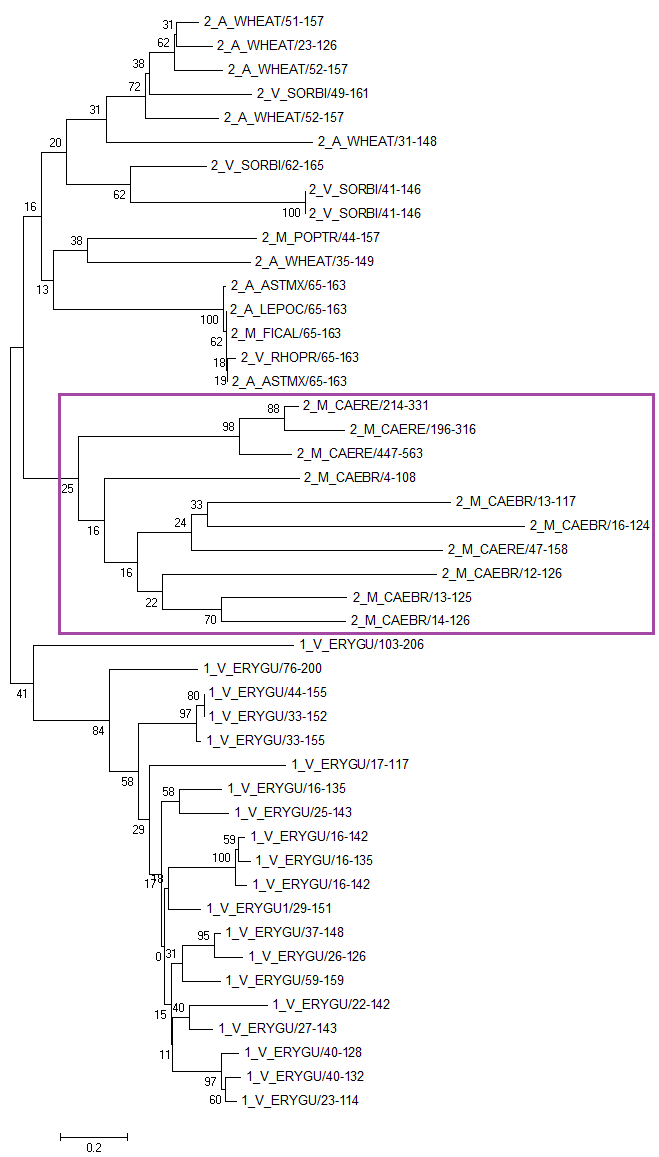 Файл с выбранным подсемейством - ссылка. Далее с помощью команды hmm2build hmm_built special_fam.fasta я построила профиль, командой hmm2calibrate --histfile hmm_histo hmm_built откалибровала его. После этого я провела поиск по всем белкам, включающим мой домен, с использованием профиля (команда hmm2search hmm_built PF00917_full.fasta > hmm_search). Полученные данные привожу в таблице Excel(. Находкам, принадлежащим моему подсемейству, соответствуют "1" в колонке "Мое подсемейство". На другом листе приведена рассчитанная ROC-кривая. Порог E-value - 7,10E-29 Таблица 1.Результаты при данном пороге.
|
|||||||||||||||||
© Шугаева Т.Е. 2016