A- и В- формы ДНК. Структура РНК
Задания 1,2
Сравнение структур 3-х форм ДНК с помощью средств JMol
Требовалось построить модели структур A-, B- и Z-формы ДНК с помощью инструментов пакета 3DNA.Пакет 3DNA - один из
популярных пакетов программ для анализа и простейшего моделирования структур нуклеиновых кислот. С помощью программы
fiber пакета 3DNA были построены A-, B- и Z-формы дуплекса ДНК, последовательность одной из нитей которого представляет
собой 5 раз повтореную последовательность "gatc".
На рис.1 представлены изображения разных форм ДНК, полученные в JMol.
 Рис. 1.A, B, Z формы ДНК (JMol)
Рис. 1.A, B, Z формы ДНК (JMol)
В структуре двойной спирали ДНК можно визуально различить малую и большую бороздки. Для определенного азотистого основания
можно определить, в сторону какой бороздки обращены его атомы. Я выбрала 28-й остаток цитозина цепи B. На рис.2 представлена
структура цитозина. Графическое представление структуры тимина. Атомы, обозначенные красным цветом, направлены в сторону большой
бороздки в стуктуре дуплекса ДНК, атомы синего цвета направлены в сторону малой бороздки.
Рисунок получен с помощью программы MarvinSketch.
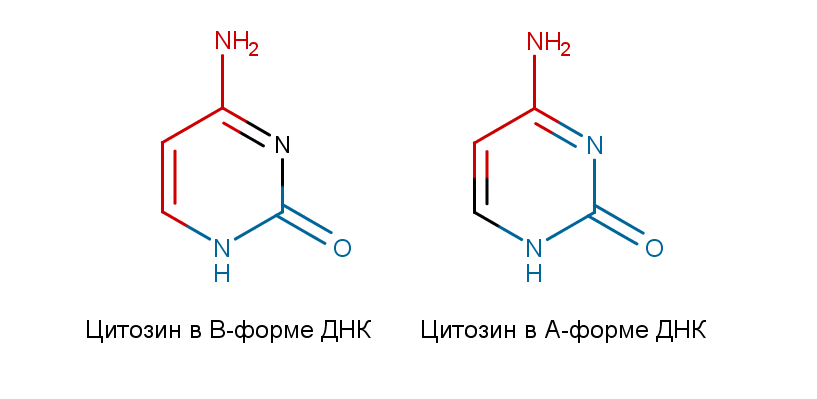 Рис. 2.Структура цитозина в B- и A-формах ДНК. Красным выделены атомы, смотрящие в
сторону большой бороздки, синим - в сторону малой.
Рис. 2.Структура цитозина в B- и A-формах ДНК. Красным выделены атомы, смотрящие в
сторону большой бороздки, синим - в сторону малой.
Для B-формы ДНК:
В сторону большой бороздки обращены атомы C:28:B.N4, C:28:B.C4, C:28:B.C5, C:28:B.C6
В сторону малой бороздки обращены атомы C:28:B.N1, C:28:B.C2, C:28:B.O2
Остальные атомы основания: C:28:B.N3
Для A-формы ДНК:
В сторону большой бороздки обращены атомы C:28:B.C4, C:28:B.N4, C:28:B.C5
В сторону малой бороздки обращены атомы C:28:B.N1, C:28:B.C2, C:28:B.O2, C:28:B.N3
Остальные атомы основания: C:28:B.C6
Для Z-формы ДНК:
В сторону большой бороздки обращены атомы C:28:B.N1, C:28:B.C6, C:28:B.C5, C:28:B.N4, C:28:B.C4
В сторону малой бороздки обращены атомы C:28:B.C2, C:28:B.O2
Остальные атомы основания: C:28:B.N3
Сравнение основных спиральных параметров разных форм ДНК.
| Основные спиральные характеристики форм ДНК |
A-форма |
B-форма |
Z-форма |
| Тип спирали (правая или левая) |
Правая |
Правая |
Левая |
| Шаг спирали, Å |
28,03 |
33,8 |
43,5 |
| Число оснований на виток |
11 |
10 |
12 |
| Ширина большой бороздки, Å |
16,97 ([G]33:B.P) - ([T]11:A.P) |
17,21 ([G]25:B.P) - ([G]13:A.P) |
7,2 ([G]31:B.P) - ([G]13:A.P) |
| Ширина малой бороздки, Å |
7,98 ([C]24:B.P) - ([T]11:A.P) |
11,69 ([G]33:B.P) - ([C]12:A.P) |
15,17 ([C]24:B.P) - ([G]17:A.P) |
Таблица 1. Результаты измерения и сравнения основных спиральных параметров A-,B- и Z- форм ДНК.
Сравнение торсионных углов в А- и В-формах ДНК.
Конформация полинуклеотидной цепи определяется набором торсионных углов
(или углов вращения группы атомов относительно связи) сахарофосфатного остова.Конформационные изменения в
спиральных полинуклеотидах сопряжены с согласованными изменениями всех торсионных углов.
С помощью программы JMol были измерены торсионные углы в цитидиловом нуклеотиде. Результаты представлены в табл.2
и на рис.3.
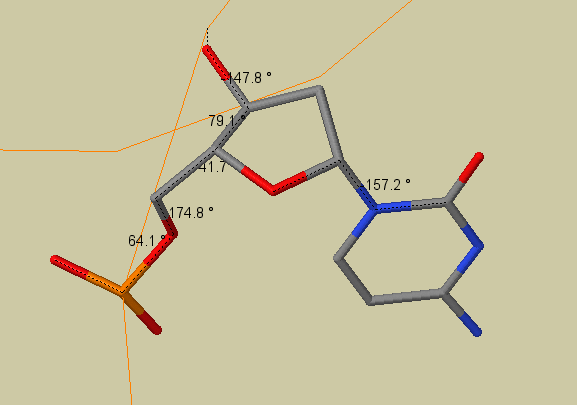 Рис. 3.Торсионные углы в цитидиловом нуклеотиде в A-форме ДНК (JMol)
Рис. 3.Торсионные углы в цитидиловом нуклеотиде в A-форме ДНК (JMol)
| угол |
α |
β |
γ |
δ |
ε |
ξ |
χ |
| A-форма |
64.1 |
174.8 |
41.7 |
79.1 |
-147.8 |
-75.1 |
-157,2 |
| B-форма |
85.9 |
136.3 |
31.2 |
143.3 |
-140.8 |
-160.5 |
-98.0 |
Таблица 2. Значения торсионных углов в цитидиловом нуклеотиде
Задание 3
Упражнение 1. Определение торсионных углов нуклеотидов
С помощью программ пакета 3DNA были определены торсионные углы нуклеотидов в разных формах ДНК. Результаты преддставлены в табл.3.\
Анализируя эту таблицу, можно заметить, что в пределах одной формы торсионные углы нуклеотидов отличаются незначительно, за исключением Z-формы.
Формы A- и B- отличаются друг от друга в основном по углам δ, ξ и χ. Z-форма ДНК наиболее сильно отличается от форм A- и B-.
| Форма ДНК | Нуклеотид | α | β | γ | δ | ε | ξ | χ |
| A | G | -51.70 | 174.80 | 41.70 | 79.09 | -147.79 | -75.10 | -157.20 |
| B | G | -29.90 | 136.34 | 31.14 | 143.34 | -140.80 | -160.50 | -98.00 |
| Z | G | 51.93 | 179.00 | -173.80 | 94.90 | -103.60 | -64.80 | 58.70 |
| A | A | -51.70 | 174.80 | 41.70 | 79.08 | -147.80 | -75.10 | -157.20 |
| B | A | -29.90 | 136.34 | 31.14 | 143.34 | -140.80 | -160.50 | -98.00 |
| Z | A | - | - | - | - | - | - | - |
| A | T | -51.70 | 174.80 | 41.70 | 79.10 | -147.80 | -75.10 | -157.20 |
| B | T | -29.90 | 136.34 | 31.14 | 143.34 | -140.80 | -160.50 | -97.98 |
| Z | T | - | - | - | - | - | - | - |
| A | C | -51.70 | 174.80 | 41.70 | 79.09 | -147.79 | -75.09 | -157.20 |
| B | C | -29.90 | 136.34 | 31.14 | 143.34 | -140.80 | -160.50 | -97.98 |
| Z | C | -139.50 | -136.77 | 50.87 | 137.60 | -96.50 | 81.97 | -154.30 |
Таблица 3. Сравнение торсионных углов в различных нуклеотидах в A-,B- и Z-формах.
Кроме того, торсионные углы были определены в тРНК с PDB ID: 1C0A. В табл.4 представлены средние арифметические
значения по 4 нуклеотидам тРНК.
| Нуклеотид |
α |
β |
γ |
δ |
ε |
ξ |
χ |
| A |
-63,6 |
75,7 |
55,5 |
92,6 |
91,2 |
-36,4 |
-150,9 |
| C |
-49,8 |
66,6 |
34,6 |
85,3 |
-149,2 |
-66,5 |
-158,8 |
| G |
-43,8 |
102,8 |
40,0 |
90,0 |
-139,1 |
-64,6 |
-158,2 |
| U |
-64,5 |
125,1 |
52,1 |
83,3 |
-146,6 |
-81,9 |
-160,0 |
Таблица 4. Торсионные углы тРНК(PDB ID: 1C0A)
Анализируя табл. 3 и 4 можно сказать что данная тРНК (PDB ID:1C0A) по торсионным углам больше похожа на A-форму ДНК.
Для заданного фрагмента ДНК (PDB ID:1LQ1) также были определены торсионные углы и посчитаны средние арифметические значения.
Результаты представлены в табл.5. Следует отметить, что не все исходные значения были одинакового знака, некоторые посчитанные
средниезначения не имеют смысла. Однако можно выделить некоторые "деформированные" (наиболеее отклоняющиеся ао одному из углов)
нуклеотиды. В частности, по углу α таким нуклеотидом является цитозин, а по углу ε - аденин.
| Нуклеотид |
α |
β |
γ |
δ |
ε |
ξ |
χ |
| A |
-49,3 |
-72,0 |
39,2 |
148,7 |
1,1 |
-104,8 |
-97,8 |
| C |
29,5 |
12,6 |
1,9 |
152,9 |
-94,7 |
-107,4 |
-91,2 |
| G |
-30,1 |
89,7 |
21,6 |
151,9 |
-54,1 |
-95,2 |
-96,9 |
| T |
-4,6 |
-128,3 |
-4,5 |
150,9 |
-35,4 |
-106,0 |
-102,0 |
Таблица 5. Торсионные углы фрагмента ДНК (PDB ID:1LQ1)
Упражнение 2. Определение структуры водородных связей
Отдельные участки молекулы РНК могут соединяться и образовывать двойные спирали. Таким образом формируется вторичная структура
РНК, состоящая из стеблей, выпетливаний, петель, мультипетель, псевдоузлов. Пакет программ 3DNA позволяет получить
информацию о всех водородных связях в заданной структуре. Соответственно, можно определить номера нуклеотидов,
образующих стебли(stems) во вторичной структуре заданной тРНК. На рис. 4 разным цветом обозначены участки, образующие стебли.
Те пары нуклеотидов, которые не выделены цветом, являются изолированными. Они принимают участие в образовании третичной структуры тРНК.
 Рис. 4. Cтебли тРНК(PDB ID: 1C0A)
Рис. 4. Cтебли тРНК(PDB ID: 1C0A)
В данной структуре тРНК встречаются неканонические взаимодействия. Они помечены * и происходят между парами
нуклеотидов, изображенных на рис.5.
 Рис. 5. Неканонические взаимодействия тРНК(PDB ID: 1C0A)
Рис. 5. Неканонические взаимодействия тРНК(PDB ID: 1C0A)
Упражнение 3. Поиск стэкинг-взаимодействий
Дополнительным видом взаимодействи, придающим структуре РНК устройчивость, являются стэкинг-взаимодействия. Это
взаимодействия перекрывающихся пи-облаков азотистых оснований, расположенных в параллельных плоскостях. В исходном файле PDB
находится информация о перекрывании пар нуклеотидов. На рис. 6 голубым и оранжевым цветами отмечены пары с наибольшей и наименьшей
площадью перекрывания соответственно.
 Рис. 6. Пары нуклеотидов с наибольшим и наименьшим перекрыванием в тРНК(PDB ID: 1C0A)
Рис. 6. Пары нуклеотидов с наибольшим и наименьшим перекрыванием в тРНК(PDB ID: 1C0A)
С помощью программ convert ex_str и stack2img были получены изображения с максимальной и минимальной площадью перекрыванием(рис.7).
пар нуклеотидов.
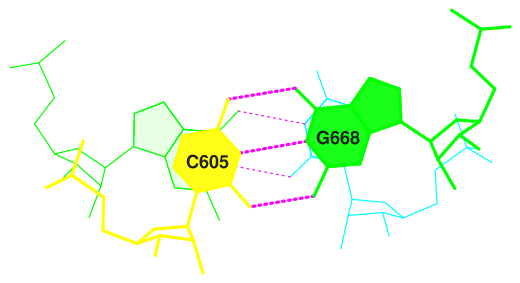
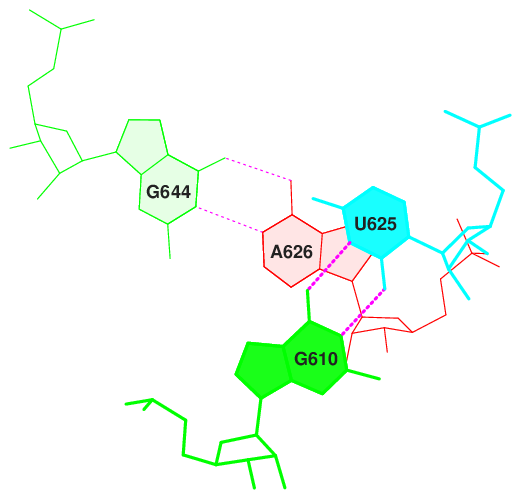 Рис. 7. Изображение пар нуклеотидов с наибольшим(слева) и наименьшим(справа) перекрыванием
Рис. 7. Изображение пар нуклеотидов с наибольшим(слева) и наименьшим(справа) перекрыванием
Аналогичные изображения, полученные в JMol, представлены на рис.8.
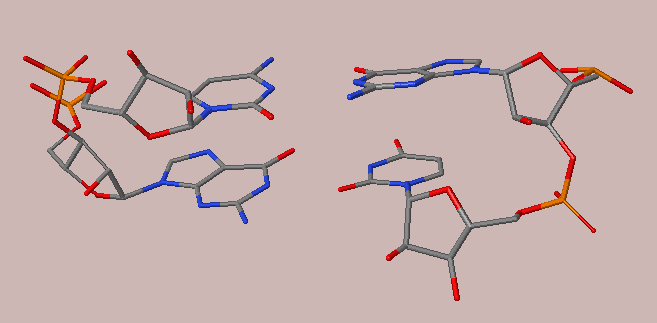
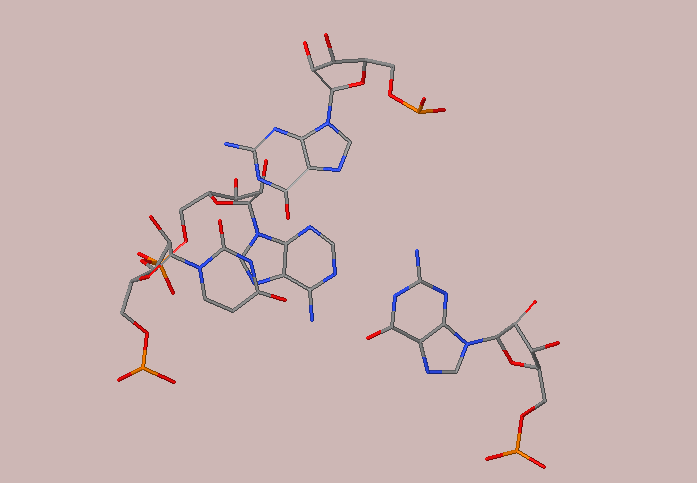 Рис. 8. Изображение пар нуклеотидов с наибольшим(слева) и наименьшим(справа) перекрыванием (JMol)
Рис. 8. Изображение пар нуклеотидов с наибольшим(слева) и наименьшим(справа) перекрыванием (JMol)









