|
|||||||||||||||||||||||||
|
|
Для построения множественного выравнивания я использовала последовательности девяти белков, которые представлены в данном
fasta-файле. Проект в формате .jvp можно скачать по
ссылке.
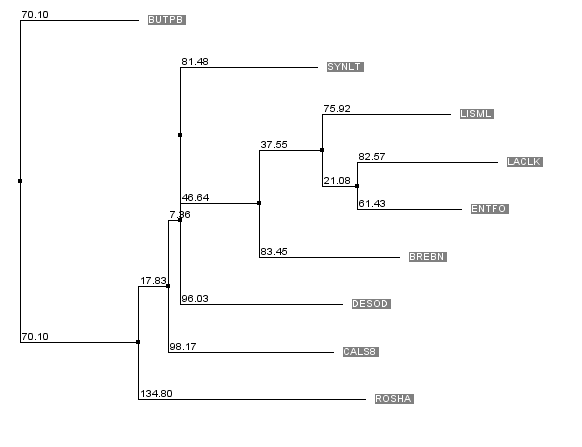
Рисунок 1. Дерево для последовательностей из файла align_06.fasta, получено методом Neighbour Joining Using PAM 250 Для начала я сделала изображения выравнивания с раскраской BLOSUM62 с порогом консервативности 30 и ClustalX. Они представлены на рисунках 2а и 2b соответственно. 
Рисунок 2a. Выравнивание последовательностей с раскраской BLOSUM62, порог консервативности 30% 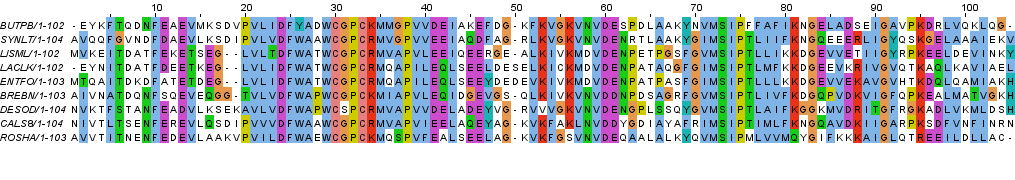
Рисунок 2b. Выравнивание последовательностей с раскраской ClustalX Затем я добавила строку разметки BLOCKS, в которой отмечены участки, где можно ожидать гомологию между всеми аминокислотными остатками из разных последовательностей. Всего я нашла 3 блока (позиции 21-46, 52-61 и 69-83), из них 2 последних можно объединить в кластер, потому что между ними нет гэпов. Самые длинные участки, не входящие в состав блоков и кластеров, расположены в начале и в конце последовательностей и имеют длину 20 и 21 аминокислотных остатков соответственно (позиции 1-20 и 84-105). Выравнивание с разметкой приведено на рисунках 3a и 3b. 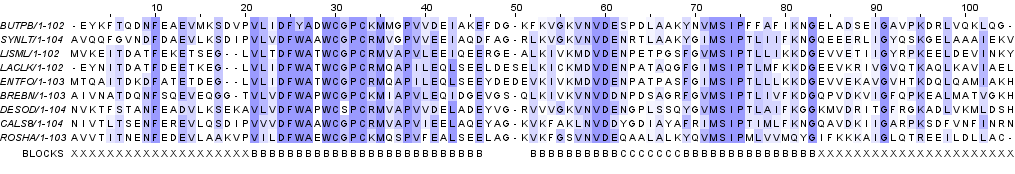
Рисунок 3a. Выравнивание последовательностей с раскраской BLOSUM62, порог консервативности 30%. Символами B обозначены блоки, символом С - участок между блоками, объединенными в кластер, символами X - участки, не входящие в состав блоков и кластеров. 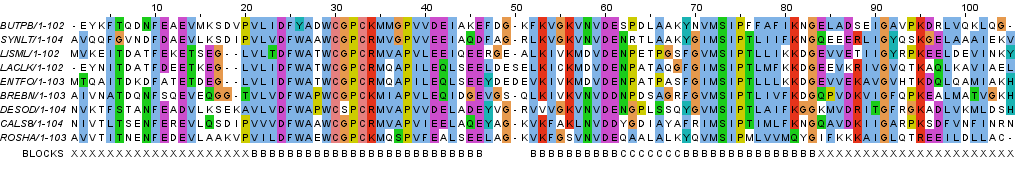
Рисунок 3b. Выравнивание последовательностей с раскраской ClustalX. Символами B обозначены блоки, символом С - участок между блоками, объединенными в кластер, символами X - участки, не входящие в состав блоков и кластеров. Можно выделить несколько последовательностей, которые скорее всего составляют отдельную группу, потому что они более близки друг к другу, чем все остальные последовательности. Я выделила 3 таких посдедовательности: LISML, LACLK и ENTFO. На рисунке 4 эти последовательности обведены черной рамкой, а также отмечены некоторые участки, на которых видны отличия этих последовательностей от всех остальных (символами H и черной рамкой). Можно заметить, что на выделенном участке (позиции 14-16 и 18-20) нельзя говорить о гомологии всех последовательностей выранивания, однако выбранные последовательности имеют высокое сходство, и можно считать, что аминокислотные остатки в соответствующих позициях для данных последовательностей гомологичны. На дереве, построенном для этого выравнивания (представленно на рисунке 1), также видно, что отмеченные последовательности составляют отдельную эволюционную группу. 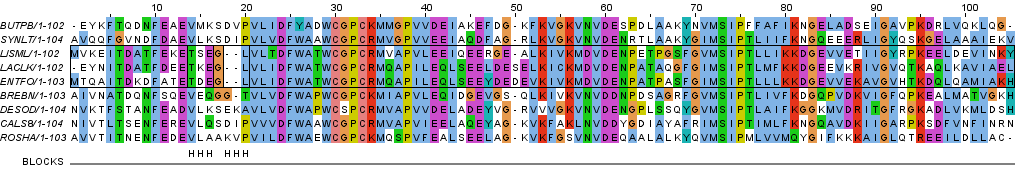
Рисунок 4. Группа гомологичных последовательностей (обведена черной рамкой), раскраска ClustalX. Символом H отмечены участки, на которых можно увидеть отличия этих последовательностей от остальных. Отличающиеся аминокислотные остатки обведены черной рамкой. Для первого блока (отдельно представлен на рисунках 5a и 5b) я посчитала число и процент абсолютно консервативных позиций, абсолютно функционально консервативных, консервативных и функционально консервативных на 70%. Полученные данные записаны в таблице 1. 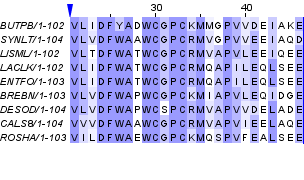
Рисунок 5a. Первый блок, раскраска BLOSUM62, порог консервативности 30% 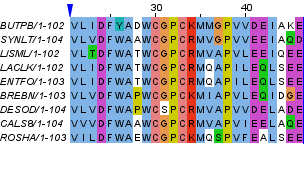
Рисунок 5b. Первый блок, раскраска ClustalX
Для самых длинных участков, не входящих в состав блоков и кластеров, были посчитаны число и процент позиций с гэпами. В первом таком участке гэпов 3, во втором 1. Это составляет 15% и 4,76% соответственно от общей длины участка. Далее к уже имеющемуся выравниванию я добавила еще одну последовательность, которую можно скачать по ссылке. Я добавила несколько гэпов в участок между блоками, где уже был гэп. Получившееся выравнивание можно посмотреть на рисунках 6a и 6b, новая последовательность расположена снизу, ее название EUBR3. 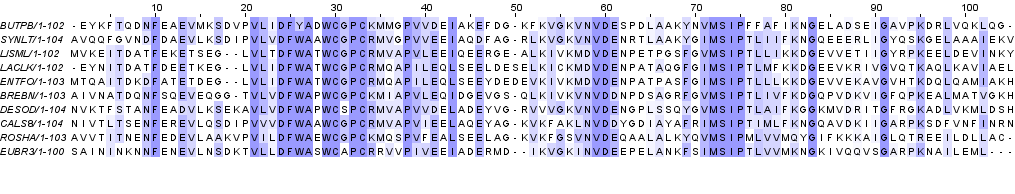
Рисунок 6a. Выравнивание с добавленной последовательностью EUBR3, раскраска BLOSUM62, порог консервативности 30% 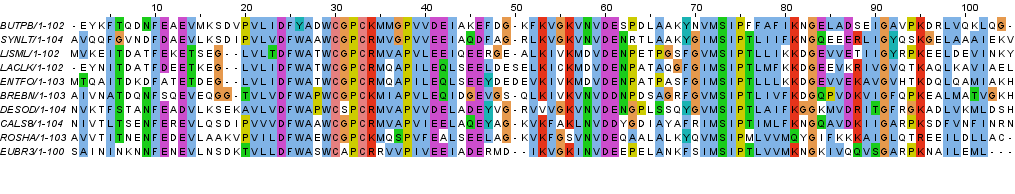
Рисунок 6b. Выравнивание с добавленной последовательностью EUBR3, раскраска ClustalX К исходному выравниванию я также попыталась добавить негомологичную последовательность. Для этого я использовала последовательность своего белка D-аланил-D-аланин карбоксипептидазы (ссылка на fasta-файл). Так как этот белок гораздо длиннее белков в выравнивании, я взяла фрагмент длиной 105 а.о. из середины его последовательности. Результаты выравнивания показаны на рисунках 7a и 7b, добавленная последовательность обозначена как YP. 
Рисунок 7a. Выравнивание с добавленной последовательностью белка YP_007078865.1 (обозначение YP, последняя строчка), раскраска BLOSUM62, порог консервативности 30% 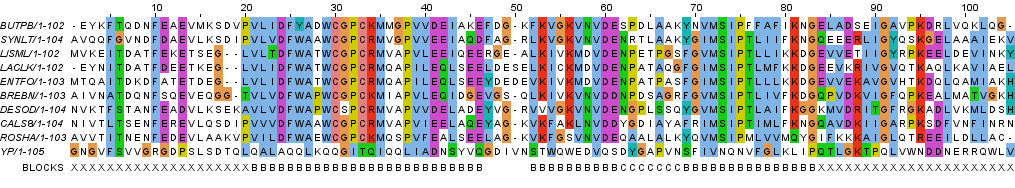
Рисунок 7b. Выравнивание с добавленной последовательностью белка YP_007078865.1 (обозначение YP, последняя строчка), раскраска ClustalX Как видно на рисунке 7b, некоторые позиции новой негомологичной последовательности совпадают с консервативными позициями в блоках исходного выравнивания (они раскрашены одним цветом). Таких позиций 12, то есть всего совпадений с негомологичным белком 11,43%. Совпадающие позиции 22, 27, 35, 39, 40, 41, 54, 59, 71, 72, 77, 79. Если учитывать такие функциональные группы аминокислот, как все гидрофильные и все гидрофобные аминокислоты и сходные по структуре доноры или акцепторы водородных связей, то число совпадений увеличивается до 20, что составляет 19,05%. Такие функционально консервативные позиции - это 32, 34, 38, 46, 58, 60, 61, 73. Однако эти совпадения можно считать случайными, потому что консервативные позиции нельзя объединить в блоки, поэтому участки последовательностей друг другу не гомологичны.
Также я построила выравнивание заведомо негомологичных последовательностей. Для этого я использовала 6 белков из
списка белков, с которыми работают мои
однокурсники. AC выбранных белков в базе данных UniProt: B8D2N2, F4BY60, I0I273, B2KEJ9, D1C2A4, F0QTE2.
Выравнивание было построено с помощью команды "Muscle with Default". Результат представлен на рисунке 8.
Совпадающих позиций очень мало, так как последовательности негомологичны друг другу. Самые лучшие блоки (те,
в которых аминокислотные остатки гомологичны в половине или более последовательностей) представлены отдельно
на рисунках 9a, 9b и 9c (позиции 68-71, 106-113, 157-162 соответственно). Однако эти блоки слишком короткие,
и совпадения можно считать случайными.

Рисунок 8. Выравнивание негомологичных последовательностей белков, раскраска ClustalX. Черной рамкой обведены участки более-менее хорошего выравнивания 
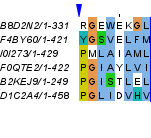

Рисунок 9a (слева). Первый блок выравнивания негомологичных последовательностей, позиции 68-71,
раскраска ClustalX
|
||||||||||||||||||||||||
|
© Наталия Кашко, 2015 |
|||||||||||||||||||||||||