|
||||||||||||||||||||||||||||||||||||||||||||||
|
|
Из множественного выравнивания последовательностей белков, с которым я работала в предыдущем практикуме,
я выбрала две наименее схожие последовательности с помощью метода главных компонент (Principal component analysis). Эти последовательности -
DESOD и ROSHA (при нажатии на ссылку показывается fasta-файл).
Парное выравнивание этих последовательностей, полученное из множественного вырвавнивания align_06.fasta,
представлено на рисунке 1.

Рисунок 1. Парное выравнивание последовательностей DESOD и ROSHA, полученное из множественного выравнивания align_06.fasta. Раскраска ClustalX.
Далее с помощью программ needle и water, которые используют алгоритм Нидлмана - Вунша и алгоритм Смита - Ватермана соответственно, были
построены парные выравнивания этих последовательностей. Needle строит глобальное парное выравнивание, water - локальное. На рисунках 2 и 3
представлены парные выравнивания, построенные со стандартнымы параметрами (матрица BLOSUM62, gap open = 10.0, gap extension = 0.5). Gap open
задает штраф за первый гэп, то есть за открытие, а gap extension - штраф за каждый последующий гэп, то есть за продолжение.

Рисунок 2. Парное глобальное выравнивание последовательностей DESOD и ROSHA, полученное с помощью программы needle с параметрами gap open = 10.0, gap extension = 0.5, раскраска ClustalX. 
Рисунок 3. Парное локальное выравнивание последовательностей DESOD и ROSHA, полученное с помощью программы water с параметрами gap open = 10.0, gap extension = 0.5, раскраска ClustalX. Затем я изменила параметры gap open и gap extension. Для глобального выравнивания (needle) я уменьшила штраф за открытие гэпа (gap open = 1.0). Полученное выравнивание можно увидеть на рисунке 4, а также скачать fasta-файл. 
Рисунок 4. Парное глобальное выравнивание последовательностей DESOD и ROSHA, полученное с помощью программы needle с параметрами gap open = 1.0, gap extension = 0.5, раскраска ClustalX. Для локального выравнивания (water) я изменила параметр gap extension, однако получившееся выравнивание ничем не отличалось от представленного на рисунке 3. Поэтому я также уменьшила и штраф за открытие гэпа. Полученное выравнивание, построеное с помощью программы water с параметрами gap open = 5.0, gap extension = 0.1, представлено на рисунке 5, fasta-файл можно скачать по ссылке. 
Рисунок 5. Парное локальное выравнивание последовательностей DESOD и ROSHA, полученное с помощью программы water с параметрами gap open = 5.0, gap extension = 0.1, раскраска ClustalX. Далее я построила парные выравнивания последовательностей двух заведомо негомологичных белков (рисунки 6 и 7). Идентификаторы выбранных белков в базе данных UniProt: K9R0L9 и I0I273 (при нажатии на ссылку показывается fasta-файл). Выравнивания построены с помощью программ needle и water со стандартными параметрами, fasta-файлы можно скачать по ссылкам: needle и water. 
Рисунок 6. Парное глобальное выравнивание последовательностей K9R0L9 и I0I273, полученное с помощью программы needle с параметрами gap open = 10.0, gap extension = 0.5, раскраска ClustalX. 
Рисунок 7. Парное локальное выравнивание последовательностей K9R0L9 и I0I273, полученное с помощью программы water с параметрами gap open = 10.0, gap extension = 0.5, раскраска ClustalX.
Для сравнения построенных выравниваний последовательностей DESOD и ROSHA с исходным, полученным из множественного выравнивания (рисунок 1),
я объединяла сравниваемые выравнивания в одно окно Jalview и выравнивала их друг относительно друга. Колонки, которые присутствуют одновременно
в обоих выравниваниях, считаются совпадающими, а те, которые присутствуют только в одном из выравниваний, - различными. Так как выравнивания,
полученные с помощью программ needle и water со стандартными параметрами (рисунки 2 и 3), ничем не отличаются от исходного (в локальном выравнивании
просто не учитываются первая и три последних позиции), я сравнивала выравнивания с измененными параметрами.

Рисунок 8. Сравнение парных выравнивание последовательностей DESOD и ROSHA: сверху полученное из множественного выравнивания, снизу - с помощью программы needle с параметрами gap open = 1.0, gap extension = 0.5, раскраска ClustalX. 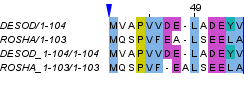
Рисунок 9. Участок с различиями сравниваемых выравниваний с 40 по 54 позиции. Раскраска ClustalX. На рисунке 10 представлено сравнение исходного выравнивания с выравниванием, построенным программой water с параметрами gap open = 5.0 и gap extension = 0.1 (рисунок 5). Колонки в позициях со 2 по 82 полностью совпадают, далее в отдельных последовательностях были добавлены участки с гэпами, поэтому выровнять их друг относительно друга сложно, а совпадающих колонок нет. Всего различающихся колонок 27. 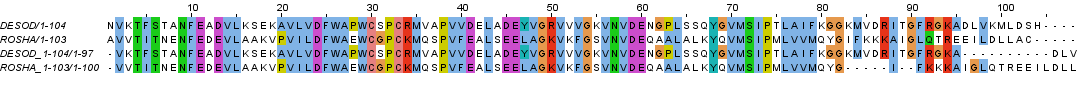
Рисунок 10. Сравнение парных выравнивание последовательностей DESOD и ROSHA: сверху полученное из множественного выравнивания, снизу - с помощью программы water с параметрами gap open = 5.0, gap extension = 0.1, раскраска ClustalX. В таблице 1 представлены данные о числе и проценте консервативных колонок, колонок со сходными аминокислотными остатками, о количестве гэпов в построенных глобальных и локальных выравниваниях гомологичных и немогологичных последовательностей, а также в выравнивании, полученном из множественного.
* - в скобках представлено количество гэпов в том случае, если гэпом считается каждый отдельный символ черточки ("-")
По данным таблицы и по выравниваниям, представленным на рисунках, можно сравнить способы построения парных выравниваний.
Во-первых, можно считать, что локальное выравнивание в целом лучше, чем глобальное. Наиболее значительные отличия возникают
при выравнивании негомологичных последовательностей. Это вызвано тем, что при построении локального выравнивания те участки,
которые плохо выравниваются, вообще не учитываются, гомологичные участки ищутся не во всей последовательности, а только в ее
части. Однако локальное выравнивание может подходить не для всех задач.
|
|||||||||||||||||||||||||||||||||||||||||||||
|
© Наталия Кашко, 2015 |
||||||||||||||||||||||||||||||||||||||||||||||