|
|||||||||||||||||||||
|
|
При выполнении заданий данного блока было сделано следующее:
Восстановление предкового состояния доменной архитектуры
Для работы был выбран домен B_lectin, способный специфически связывать D-маннозу, находящуюся на поверхности клеток.

Рисунок 1. Одна из доменных архитектур белков, содержащих домен B_lectin. Изображение получено из базы данных Pfam. 
Рисунок 2. Одна из доменных архитектур белков, содержащих домен B_lectin.
Первая архитектура (рисунок 1) встречается в 232 последовательностях. В ее состав входят 3 домена: B_lectin,
S_locus_glycop и Pkinase.
Построение выравнивания представителей домена Pfam белков с разной доменной архитектурой
Для построения выравнивания было получено выравнивание всех белков, содержащих этот домен (их доменных участков). Это выравнивание доступно
в формате fasta и в проекте JalView.
Построение филогенетического дерева последовательностей доменаНа основании полученного выравнивания было построено филогенетическое дерево последовательностей домена. Для построения использовался метод Maximum Likelihood в программе MEGA. Изображение дерева представлено на рисунке 3. На рисунке 4 представлено неукорененное круговое дерево. Также эти деревья доступны в более крупном формате по ссылкам: круговое и укорененное. Дерево в Newick-формате (скобочная формула): tree.nwk. 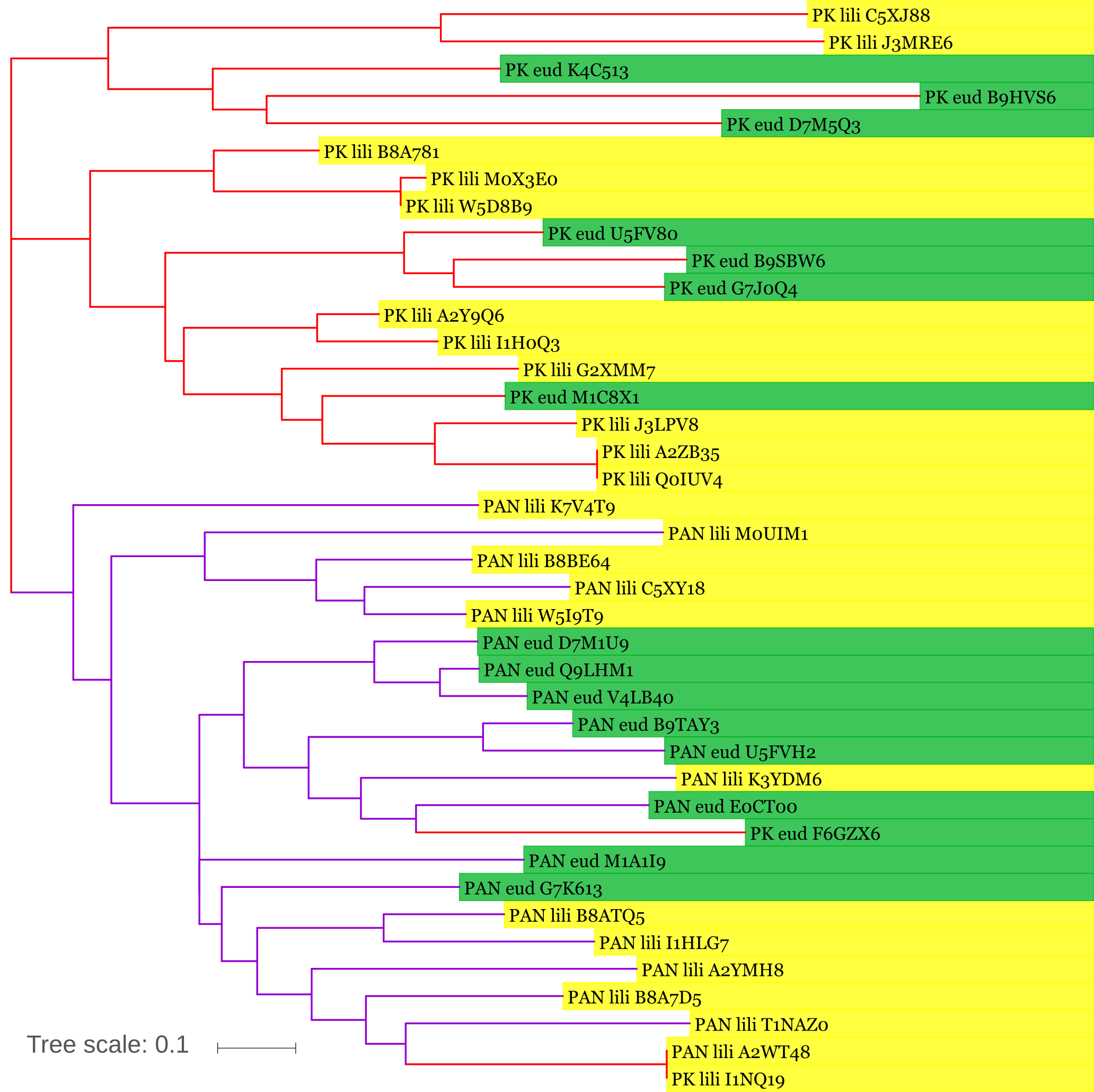
Рисунок 3. Изображение укорененного дерева, полученное из выравнивания доменов B_lectin из белков с разной доменной архитектурой: PAN (фиолетовые ветви на дереве) - архитектура из рисунка 2, PK (красные ветви) - архитектура из рисунка 1. Желтым отмечены последовательности из таксона Liliopsida, зеленым - из таксона Eudicotyledons. Изображение получено с помощью Itol. Более крупное изображение: ссылка 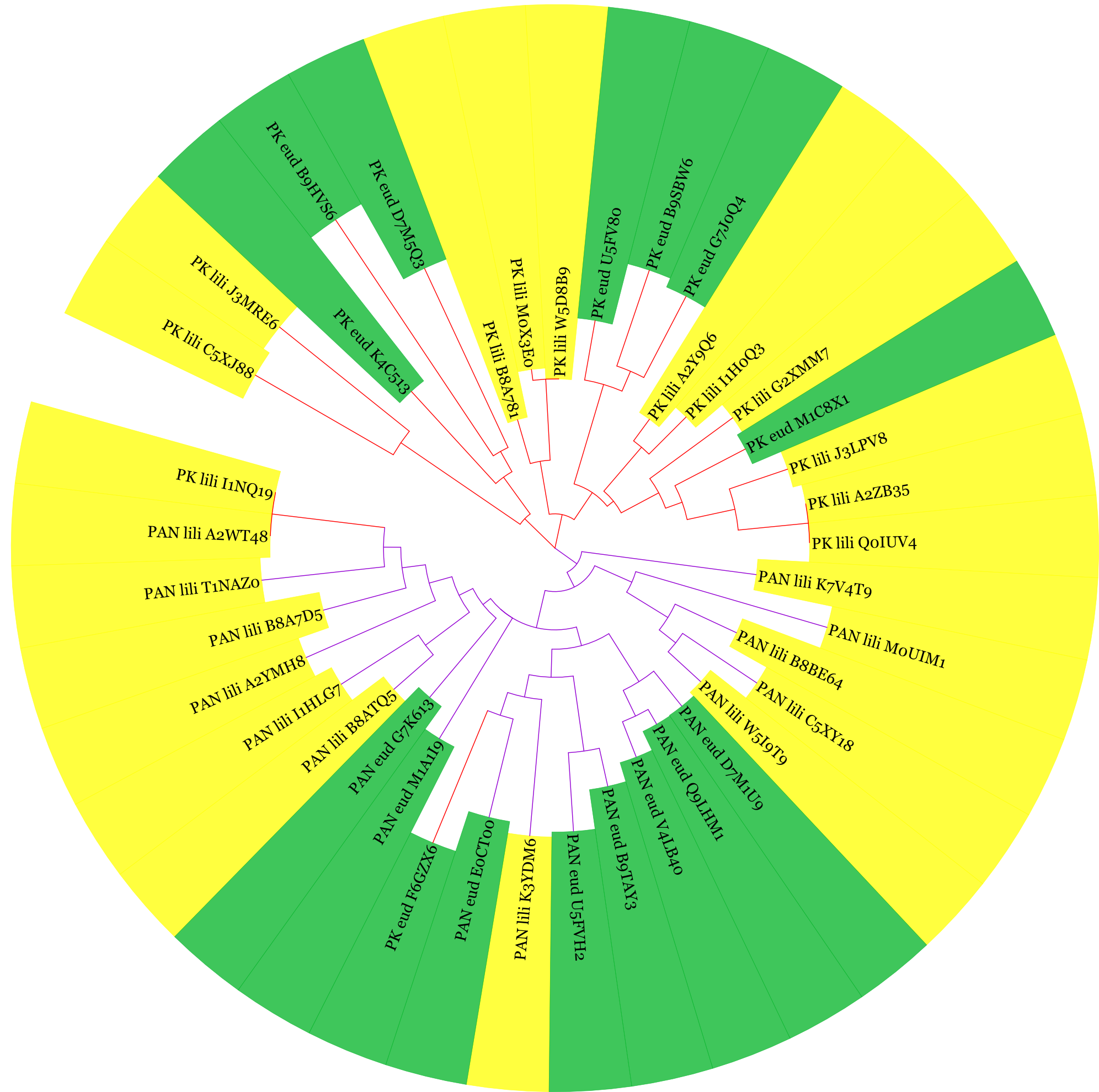
Рисунок 4. Изображение укорененного дерева, полученное из выравнивания доменов B_lectin из белков с разной доменной архитектурой: PAN (фиолетовые ветви на дереве) - архитектура из рисунка 2, PK (красные ветви) - архитектура из рисунка 1. Желтым отмечены последовательности из таксона Liliopsida, зеленым - из таксона Eudicotyledons. Изображение получено с помощью Itol. Более крупное изображение: ссылка
По рисункам 3 и 4 видно, что большинство белков, имеющих разную доменную архитектуру, принадлежат к разным кладам на дереве. Скорее всего, это связано
не с ошибкой при построении выравнивания, так как вырванивание и внутри архитектур, и всех последовательностей в целом достаточно хорошее,
последовательности гомологичны, а плохо выровненные последовательности были удалены. Возможно, был общий предок для этих двух доменных архитектур
(например, с двумя доменами, которые для них являются общими), а затем некоторые белки приобрели домен с протеинкиназной активностью, а другие
- домен из семейства PAN. Таким образом, белки функционально разошлись. При этом с точки зрения таксономии распределение архитектур в таксонах
Liliopsida и Eudicotyledons примерно одинаковое и слабо выражено на дереве. Вероятно, эти белки являются консервативными для всех групп
покрытосеменных растений.
Профиль семейства последовательностей белковДля построения профиля было выбрано подсемейство, отмеченное на рисунке 5. Затем с помощью программы HMMER был построен и откалиброван профиль по выравниванию отобранных последовательностей. Для этого использовались программы hmm2build и hmm2calibrate. 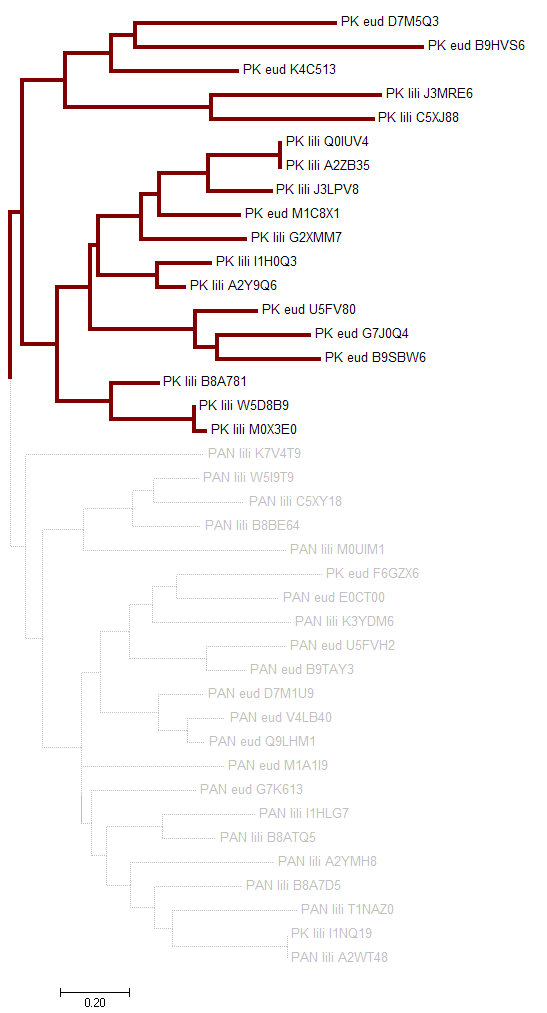
Рисунок 5. Филогенетическое дерево доменных архитектур из предыдущего задания. Бордовым отмечено подсемейство, выбранное для построения профиля.
С помощью программы hmm2search с использованием полученного профиля был проведен
поиск по всем белкам UniProt, содержащим домен B_lectin. В результате был получен следующий файл.
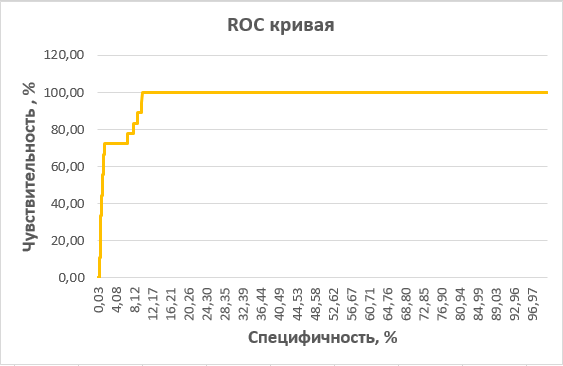
Рисунок 6. ROC-кривая, построенная по результатам поиска по профилю. По оси X - специфичность, по оси Y - чувствительность профиля (в %). С помощью ROC-кривой я выбрала порог E-value, по которому можно судить о принадлежности последовательности подсемейству. Пороговое значение E-value оказалось равным 7,6e-43. Значения при выбранном пороге представлены в таблице 1.
|
||||||||||||||||||||
|
© Наталия Кашко, 2016 |
|||||||||||||||||||||